Clear Sky Science · de
Fäkale Besiedlung und molekulare Charakterisierung von ESBL-produzierenden Enterobacteriaceae bei Landwirtinnen und Landwirten in West-Zentral-Uganda
Warum Keime im Darm von Landwirtinnen und Landwirten uns alle betreffen
Antibiotikaresistente Bakterien werden oft als ein auf Krankenhäuser beschränktes Problem betrachtet, doch diese Studie zeigt, dass sie stillschweigend im Alltag verbreitet sind — auch auf Kleinbetrieben im ländlichen Uganda. Die Forschenden untersuchten Bakterien, die im Darm von Landwirtinnen und Landwirten leben, und fragten: Wie häufig sind hochresistente Stämme, wodurch werden sie resistent, und welche Alltagsbedingungen begünstigen ihre Ausbreitung? Ihre Ergebnisse beleuchten, wie Resistenzen zwischen Menschen, Tieren und Umwelt zirkulieren können — und warum das für jeden wichtig ist, der einmal auf funktionierende Antibiotika angewiesen sein könnte.
Untersuchung der Darmflora auf Kleinbetrieben
Das Team arbeitete in der Kibimba Parish, einem überwiegend landwirtschaftlich geprägten Gebiet in West-Zentral-Uganda, in dem viele Familien Vieh und Geflügel halten. Sie rekrutierten 250 erwachsene Landwirtinnen und Landwirte, die eine kleine Stuhlprobe abgaben. Im Labor züchteten die Wissenschaftler Bakterien aus diesen Proben und konzentrierten sich auf eine Mikrobenfamilie namens Enterobacteriaceae, zu der bekannte Arten wie Escherichia coli gehören. Mit standardisierten Kulturmethoden und biochemischen Tests identifizierten sie die vorhandenen Spezies. Anschließend prüften sie, wie diese Bakterien auf eine Auswahl gebräuchlicher Antibiotika reagierten, und setzten eine spezielle Methode ein, um solche Stämme zu erkennen, die in der Lage sind, potente Wirkstoffe der dritten Cephalosporin-Generation zu zerstören.
Suche nach Resistenzgenen in den Mikroben
Um zu verstehen, wodurch manche Bakterien so schwer zu behandeln sind, suchten die Forschenden nach drei bekannten Resistenzgenen: blaCTX-M, blaTEM und blaSHV. Diese Gene codieren für Enzyme, sogenannte erweitertes Spektrum Beta-Laktamasen (ESBLs), die Bakterien befähigen, viele wichtige Antibiotika inaktiv zu machen. Mit einer Methode namens PCR überprüften sie, ob diese Gene in den ESBL-positiven Stämmen vorhanden waren. Sie untersuchten auch, ob einzelne Bakterien mehr als ein Resistenzgen gleichzeitig trugen, was darauf hindeuten würde, dass Resistenzen über mobile genetische Elemente zwischen Mikroben geteilt und kumuliert werden können.
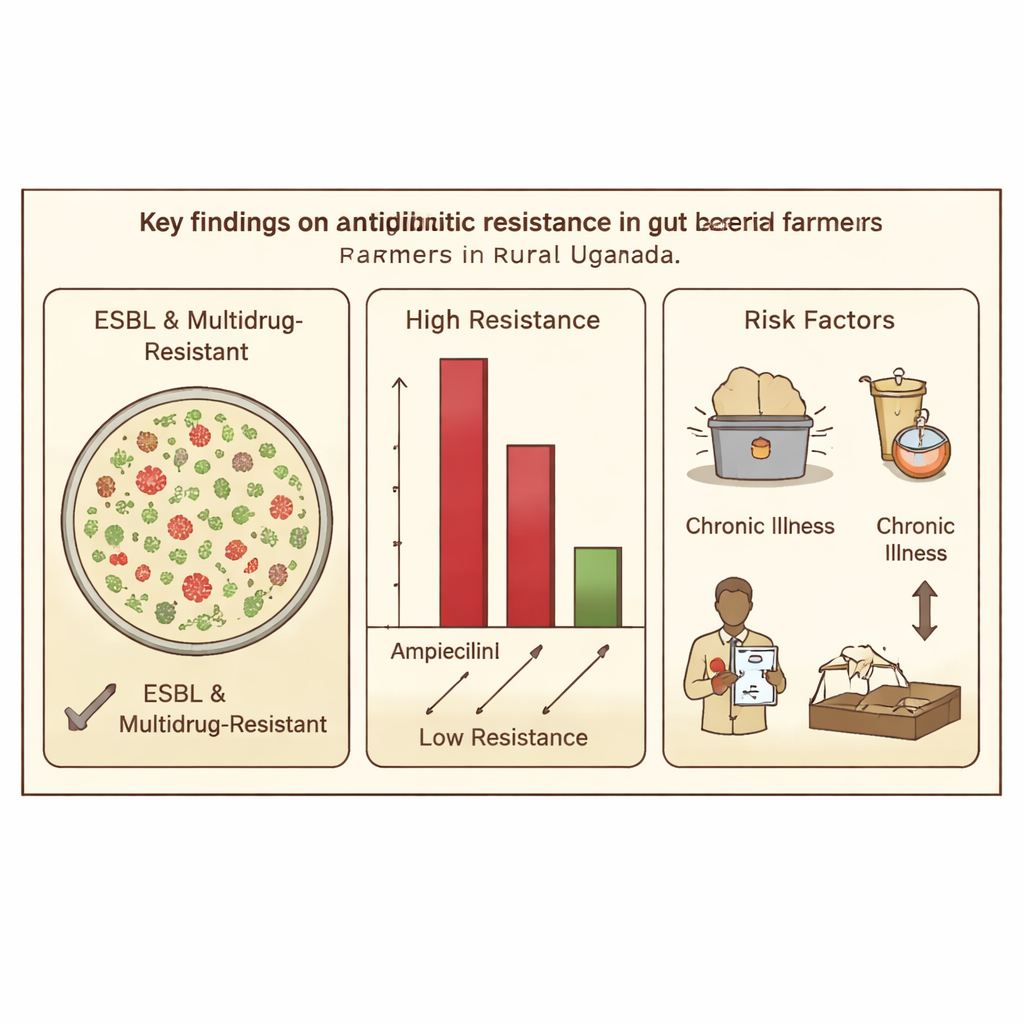
Was die Forschenden in den Stuhlproben der Landwirtinnen und Landwirte fanden
Von 250 Landwirtinnen und Landwirten trug mehr als jede dritte Person (36,4 %) ESBL-produzierende Bakterien im Darm — ein Hinweis darauf, dass diese schwer zu behandelnden Mikroben auch bei Nicht-Krankenhauspatienten verbreitet sind. Aus den Proben wurden 312 Bakterienisolate gezüchtet; Escherichia coli dominierte und machte rund 70 % aller Stämme und insbesondere der ESBL-Produzenten aus. Viele Isolate zeigten Resistenz gegen mehrere unterschiedliche Antibiotikaklassen gleichzeitig, ein Muster, das als Multiresistenz bekannt ist. Die Resistenz war besonders hoch gegenüber älteren, häufig verwendeten Antibiotika wie Ampicillin und Piperacillin, während ein Reservemittel, Imipenem, weitgehend wirksam blieb — vermutlich weil es teuer ist und im ländlichen Umfeld seltener eingesetzt wird.
Gene, die die Resistenz antreiben, und die Rolle des Alltags
Unter den bestätigten ESBL-produzierenden Bakterien trugen etwa vier von fünf mindestens eines der drei Schlüsselresistenzgene. Am häufigsten war blaCTX-M, gefolgt von blaTEM und blaSHV. Viele Bakterien trugen mehr als ein Gen gleichzeitig, und einige beherbergten alle drei, was darauf hinweist, dass diese Mikroben mehrere Mechanismen zur Überwindung von Antibiotika angehäuft haben. Die Forschenden verbanden die bakterielle Besiedlung außerdem mit Alltagsbedingungen. Landwirtinnen und Landwirte, die auf seichte Brunnen angewiesen waren, hatten häufiger ESBL-produzierende Bakterien, was darauf hindeutet, dass unbehandeltes Wasser als Reservoir dienen kann. Chronische Erkrankungen wie Bluthochdruck oder HIV/AIDS waren ebenfalls mit höheren Chancen für das Tragen resistenter Stämme verknüpft, möglicherweise wegen häufigerem Kontakt mit dem Gesundheitssystem und Antibiotika. Interessanterweise schien die Ziegenhaltung mit einem geringeren Risiko verbunden zu sein, was darauf hindeutet, dass verschiedene Tierarten und Haltungsformen den Kreis der Resistenz beeinflussen können.
Welche Bedeutung das für Landwirtinnen, Landwirte und die Allgemeinheit hat
In der Summe zeichnet die Studie ein klares Bild: In dieser ländlichen ugandischen Gemeinde tragen viele Landwirtinnen und Landwirte heimlich Darmbakterien, die mehreren Antibiotika standhalten und durch potente Resistenzgene befähigt sind. Für Laien bedeutet das, dass Infektionen, die früher leicht heilbar waren, deutlich schwerer zu behandeln sein könnten — selbst weit entfernt von Großstadtkrankenhäusern. Die Ergebnisse stützen eine „One Health“-Perspektive, nach der die menschliche Gesundheit mit Tieren und Umwelt verknüpft ist. Bessere Versorgung mit sauberem Wasser, Förderung von Hygiene, sorgfältigerer Antibiotikaeinsatz bei Menschen und Nutztieren sowie der Ausbau einfacher Labortests in ländlichen Kliniken könnten helfen, die Ausbreitung dieser gefährlichen Mikroben zu verlangsamen, bevor sie sich noch weiter festsetzen.
Zitation: Wilson, G., Micheal, K., Catherine, A. et al. Fecal carriage and molecular characterization of ESBL-producing Enterobacteriaceae among farmers in Mid-Western Uganda. Sci Rep 16, 6249 (2026). https://doi.org/10.1038/s41598-026-36817-3
Schlüsselwörter: Antibiotikaresistenz, ESBL-Bakterien, ländliche Landwirtschaft, One Health, Uganda