Clear Sky Science · de
Künstliche neuronale Netzwerkanalyse und Optimierung eines elektrochemischen Biosensors zur plasma-basierten miR-155-Erkennung bei Brustkrebs
Warum das für Früherkennungsuntersuchungen bei Krebs wichtig ist
Ärztinnen, Ärzte und Forschende suchen nach einfachen Bluttests, die Krebs lange vor dem Auftreten von Symptomen erkennen können. Ein vielversprechender Hinweis im Blut ist ein winziges genetisches Fragment namens miR-155, das mit Brustkrebs sowie mit verschiedenen Immun- und Entzündungszuständen in Zusammenhang steht. Einen Sensor zu entwickeln, der ein so schwaches Signal zuverlässig misst, ist anspruchsvoll und erfordert üblicherweise monatelanges Ausprobieren im Labor. Diese Studie zeigt, wie die Kombination intelligenter Computermodelle mit einem elektrochemischen Biosensor diesen Prozess schneller, kostengünstiger und wirkungsvoller machen kann und damit praxisnähere Tests zur Früherkennung näherbringt.
Aus einem Tropfen Blut ein Warnsignal machen
Die Arbeit konzentriert sich auf einen elektrochemischen Biosensor, der die Konzentration von miR-155 im Plasma, dem flüssigen Anteil des Blutes, erfasst. Das Herzstück des Geräts ist eine winzige Goldelektrode, deren Oberfläche in mehreren Schritten sorgfältig vorbereitet wird. Zunächst werden kurze DNA-Stränge, die miR-155 erkennen sollen, an das Metall gebunden. Danach füllt ein kleines Molekül die Lücken, damit Fremdstoffe nicht anhaften. Wird eine Patientenprobe aufgebracht, heftet sich vorhandenes miR-155 an die DNA-Stränge, und ein farbstoffähnliches Molekül namens Oracet Blue schiebt sich in diese Doppelstrukturen. Schließlich misst ein elektrischer Scan, wie viel Ladung übertragen wird, und erzeugt einen Strom, dessen Größe widerspiegelt, wie viel miR-155 in der Probe vorhanden ist. 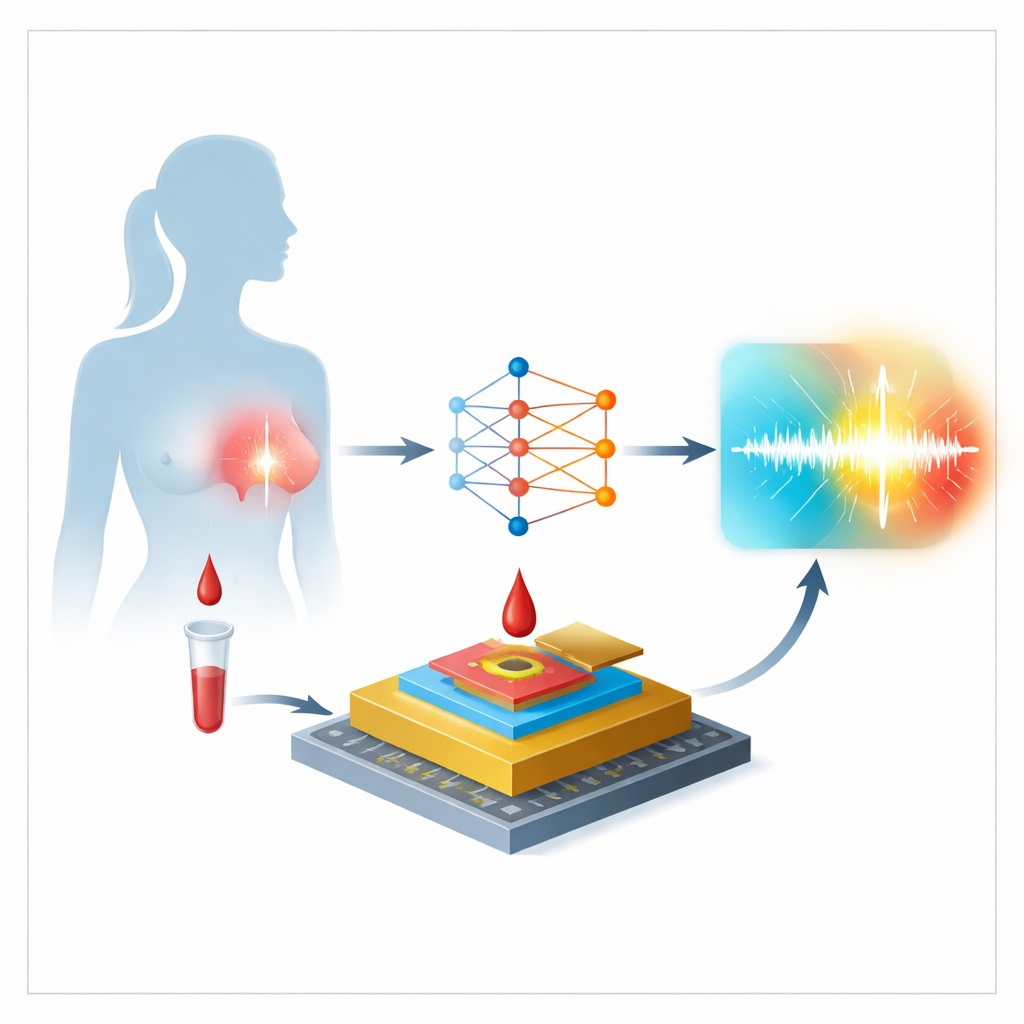
Warum traditionelle Optimierung langsam und verschwenderisch ist
Obwohl die grundlegende Messidee einfach ist, hängt die Leistung des Biosensors stark davon ab, wie er aufgebaut wird. Sechs Schlüsselparameter sind entscheidend: die Konzentration der DNA-Probe, die Dauer ihrer Anlagerung, die Einwirkzeit des Blockiermoleküls, die Bindungszeit des Ziel-miRNA sowie sowohl die Menge als auch die Inkubationszeit für Oracet Blue. In früheren Arbeiten veränderten Forschende meist ein oder zwei dieser Parameter gleichzeitig, führten neue Experimente durch und näherten sich so langsam einem besseren Design. Dieses Vorgehen verbraucht teure Materialien, bindet viel Arbeitszeit und kann die besten Kombinationen übersehen — insbesondere wenn das Verhalten stark nichtlinear ist: Kleine Änderungen bei Zeit oder Konzentration können das Signal plötzlich verdoppeln oder halbieren.
Computern erlauben, das beste Herstellrezept zu lernen
Um diesen Engpass zu überwinden, griffen die Autorinnen und Autoren auf maschinelles Lernen zurück und verwendeten zwei Modellierungsansätze: künstliche neuronale Netze (ANN) und ein adaptives neuro-fuzzy-System (ANFIS). Sie fassten Daten zu 51 verschiedenen Herstellungsvarianten desselben miR-155-Sensors zusammen, jede definiert durch eine einzigartige Kombination der sechs Schlüsselparameter, und protokollierten den resultierenden elektrischen Strom. Das ANN lernte, Herstellungsentscheidungen direkt auf das Sensorsignal abzubilden, mithilfe eines kompakten Netzwerks mit einer verdeckten Schicht und 13 internen Einheiten. Der ANFIS-Ansatz kombinierte fuzzy Regeln (wie „niedrig“ oder „hoch“) mit neuraler Lernphase und nutzte zusätzlich einen statistischen Trick, um Überschneidungen zwischen Eingaben zu reduzieren. Nach sorgfältigem Training und Testen erwies sich das ANN als genauer und leichter handhabbar und erfasste die komplexen Wechselwirkungen zwischen den Schritten besser als das regelbasiertere Fuzzy-Modell.
Den Entwurfsraum mit digitaler Evolution durchsuchen
Sobald das ANN den Biosensor zuverlässig nachbilden konnte, koppelte das Team es an einen genetischen Algorithmus, eine Suchmethode, die von der Evolution inspiriert ist. Dieser digitale Optimierer startete mit vielen zufälligen Rezepten zur Sensorherstellung und „kreuzte“ und mutierte sie wiederholt, wobei er jene behielt, von denen das ANN vorhersagte, dass sie stärkere Signale liefern würden. In dieser virtuellen Umgebung war keine neue Laborarbeit erforderlich: Der Computer konnte zahllose Möglichkeiten in silico erkunden. Das Gewinnerrezept war bemerkenswert. Im Vergleich zu den besten Bedingungen, die die Forschenden tatsächlich am Laborbank getestet hatten, verwendete die optimierte Kombination insgesamt weniger DNA-Probe und weniger Oracet Blue, verkürzte mehrere Inkubationsschritte und wurde dennoch vorhergesagt, den Ausgangsstrom des Sensors mehr als zu verdoppeln — von 98 auf 223 Nanoampere — wodurch das Signal stärker und leichter vom Hintergrundrauschen zu unterscheiden wäre. 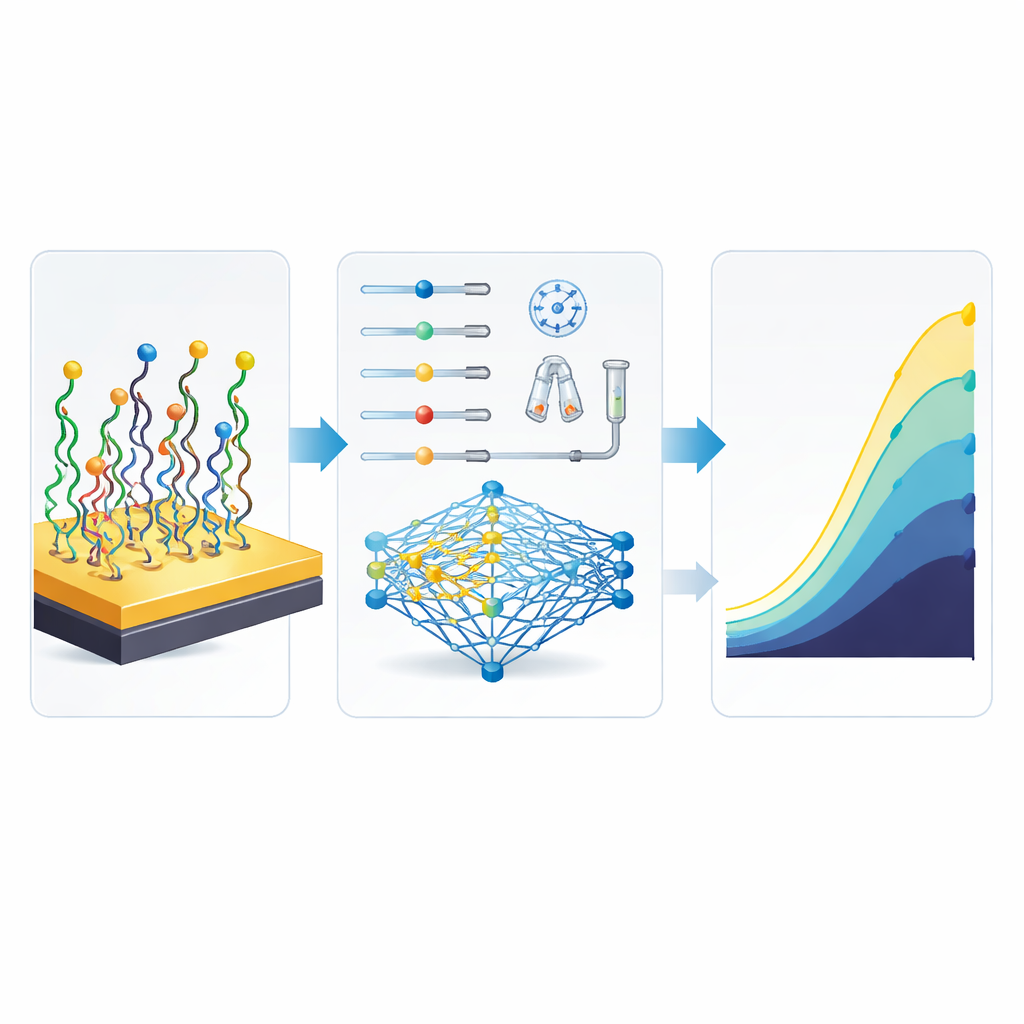
Was das für zukünftige Bluttests bedeutet
Für Nicht-Spezialisten ist die Kernbotschaft: Die Autorinnen und Autoren haben die Optimierung von Biosensoren von Ratespiel und Versuch-und-Irrtum in einen datengetriebenen, geführten Prozess überführt. Indem ein neuronales Netzwerk lernte, wie Herstellungsvarianten das finale elektrische Signal beeinflussen, und ein evolutionärer Algorithmus anschließend das beste Rezept suchte, fanden sie Bedingungen, die eine hellere, verlässlichere Ablesung von miR-155 liefern sollten und dabei weniger Zeit und Material verschwenden. Obwohl die optimierten Einstellungen noch vollständig experimentell bestätigt werden müssen und die Studie sich auf einen einzelnen Typen von Brustkrebsmarker konzentriert, lässt sich dieselbe Strategie auf viele andere Biosensoren anwenden. Langfristig könnte diese Art von intelligenter Entwicklung dazu beitragen, schnelle, kostengünstige Bluttests zur Früherkennung von Krebs und anderen Krankheiten in die routinemäßige klinische Anwendung zu bringen.
Zitation: Imani, A., Hosseinpour, S., Azimzadeh, M. et al. Artificial neural network modeling and optimization of an electrochemical biosensor for plasma miR-155-based breast cancer detection. Sci Rep 16, 7893 (2026). https://doi.org/10.1038/s41598-026-36466-6
Schlüsselwörter: Biosensor für Brustkrebs, Nachweis von microRNA-155, elektrochemischer Sensor, künstliche neuronale Netze, Optimierung durch genetischen Algorithmus