Clear Sky Science · de
Identifikation von Hub-Genen und Aufbau eines Überlebensvorhersagemodells für Patienten mit Nasopharynxkarzinom
Warum diese Krebsforschung wichtig ist
Das Nasopharynxkarzinom ist ein Krebs, der hinter der Nase und oberhalb des Rachens entsteht. Weltweit ist er relativ selten, in Teilen Südchinas und Südostasiens jedoch häufig und bedroht dort viele Familien trotz Fortschritten in der Strahlentherapie. Ärztinnen und Ärzte können die meisten Patienten behandeln, haben aber weiterhin Schwierigkeiten vorherzusagen, wer viele Jahre leben wird und wer ein höheres Sterberisiko durch die Erkrankung hat. Diese Studie untersucht Tumorzellen auf molekulare Warnzeichen — und übersetzt diese Hinweise in ein praktisches Werkzeug, um die Überlebenschancen eines Patienten nach der Therapie abzuschätzen.
Verborgene Signale innerhalb der Tumorzellen
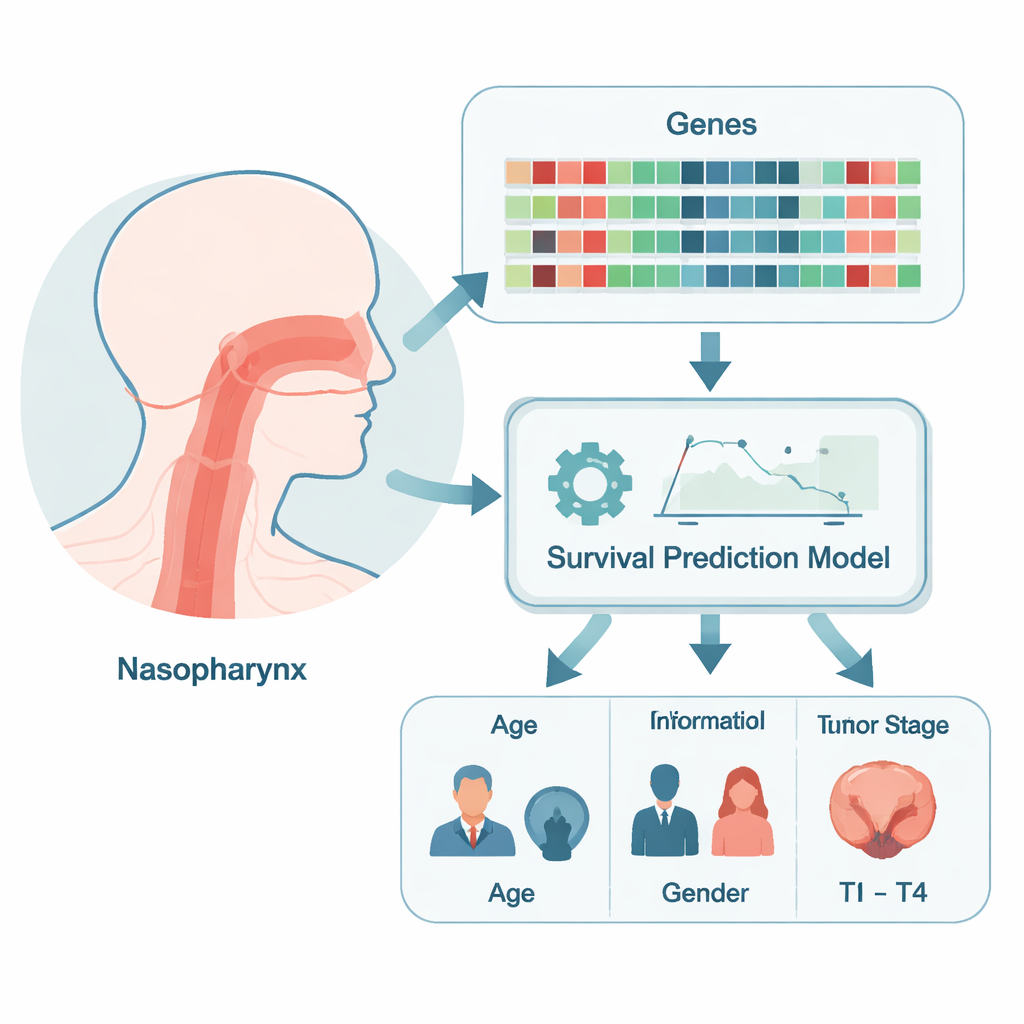
Krebszellen unterscheiden sich von gesunden Zellen nicht nur im Aussehen, sondern auch darin, welche Gene ein- oder ausgeschaltet sind. Die Forschenden durchsuchten zunächst öffentliche Datenbanken nach Genaktivitätsmustern in nasopharyngealen Tumoren und in normalem Gewebe aus derselben Rachenregion. Sie kombinierten zwei Datensätze und korrigierten technische Unterschiede, um faire Vergleiche zu ermöglichen. Diese Analyse deckte mehr als zweitausend Gene auf, deren Aktivität sich in Krebs deutlich veränderte; viele davon sind an der DNA-Replikation und an der Steuerung der Zellteilung beteiligt — der grundlegenden Maschinerie, die Tumorzellen das unkontrollierte Vermehren ermöglicht. Aus dieser dichten Landschaft fokussierte das Team eine kleine Gruppe von „Hub“-Genen, die scheinbar im Zentrum vieler wichtiger zellulärer Netzwerke stehen.
Sieben zentrale Akteure, drei herausragende
Mithilfe computergestützter Werkzeuge zur Kartierung von Protein‑Interaktionen identifizierten die Wissenschaftler sieben Hub‑Gene: AURKA, AURKB, BUB1, BUB1B, CCNA2, CCNB2 und CDK1. Alle waren in Tumorproben deutlich stärker aktiv als im Normalgewebe, und jedes ist dafür bekannt, die Steuerung von Zellteilungszeitpunkt und -ablauf zu unterstützen. Um zu prüfen, welche dieser Gene tatsächlich für Patienten relevant sind, sammelte das Team Tumorbiopsien von 120 Menschen mit Nasopharynxkarzinom, die an einem einzigen Krankenhaus behandelt wurden, und verfolgte sie über mehr als sieben Jahre. Bei Färbungen dieser Tumoren unter dem Mikroskop stachen drei Gene hervor — AURKA, BUB1 und CDK1: In Proben von Patienten, die später verstarben, leuchteten sie deutlich stärker als in denen von Überlebenden.
Verknüpfung von Genaktivität mit dem Patientenüberleben
Der nächste Schritt war zu testen, ob diese starken Signale sich in Unterschieden im Ergebnis widerspiegeln. Die Forschenden teilten Patienten in Gruppen mit hoher oder niedriger Expression jedes Gens und erstellten Überlebenskurven, die zeigen, wie viele Personen jeweils über die Zeit noch leben. Patienten, deren Tumoren hohe Werte von AURKA, BUB1 oder CDK1 aufwiesen, starben früher und häufiger als diejenigen mit niedrigen Werten derselben Gene. Im Gegensatz dazu trennten die anderen Hub-Gene nicht klar zwischen guten und schlechten Verläufen. Dieses Muster legt nahe, dass AURKA, BUB1 und CDK1 etwas Grundlegendes über die Aggressivität eines Tumors erfassen — wie schnell er wächst und wie widerstandsfähig er möglicherweise gegenüber Behandlungen ist.

Aufbau eines praktikablen Risiko-Rechners
Ärztinnen und Ärzte nutzen bereits klinische Merkmale wie Tumorgröße, Befall von Lymphknoten und Vorhandensein von Metastasen, um das Nasopharynxkarzinom zu stadieneinteilen und die Therapie zu steuern. Das Team fragte, ob das Hinzufügen von Geninformationen diese Vorhersagen verbessern könnte. Sie erstellten ein Überlebensvorhersagemodell, das Standardfaktoren — Alter, Geschlecht und die Tumorstadien T, N und M — mit den Messwerten von AURKA und BUB1 in den Tumoren kombinierte. Statistische Prüfungen zeigten, dass dieses kombinierte Modell sehr genau darin war, Patienten mit längerem Überleben von solchen mit höherem Risiko zu unterscheiden, und bessere Ergebnisse lieferte als ein Modell, das nur auf den üblichen klinischen Daten beruhte. Es trennte nicht nur zuverlässig Niedrig‑ und Hochrisikogruppen, sondern war auch gut kalibriert, das heißt: Die vorhergesagten Überlebenschancen stimmten mit den tatsächlich im Follow‑up beobachteten Ergebnissen überein.
Was das für Patientinnen und Patienten bedeutet
Diese Arbeit deutet darauf hin, dass drei an der Zellteilung beteiligte Gene, insbesondere AURKA und BUB1, als molekulare Warnlampen beim Nasopharynxkarzinom dienen könnten. Ihre Aktivität in Tumorbiopsien zusammen mit routinemäßigen klinischen Informationen zu messen, könnte Ärzten helfen, das Überleben eines Patienten präziser abzuschätzen und diejenigen zu identifizieren, die von engerer Überwachung oder intensiverer Behandlung profitieren könnten. Die Studie ist noch früh — sie basiert auf Daten aus einem einzigen Zentrum mit einer überschaubaren Patientenzahl — und verändert die tägliche Versorgung noch nicht. Sie weist jedoch auf eine Zukunft hin, in der ein einfacher Labortest an Tumorgewebe komplexe Genaktivitätsmuster in eine klare, personalisierte Überlebensprognose für Menschen mit dieser schweren Krebserkrankung übersetzen kann.
Zitation: Zhu, J., Feng, Y., Zhu, Z. et al. Identification of hub genes and construction of a survival prediction model for patients with nasopharyngeal carcinoma. Sci Rep 16, 5299 (2026). https://doi.org/10.1038/s41598-026-36395-4
Schlüsselwörter: Nasopharynxkarzinom, Krebs-Biomarker, Gengenexpression, Überlebensprognose, AURKA BUB1 CDK1