Clear Sky Science · de
Hinweise auf eine genomische Grundlage für Wachstumsratenunterschiede in einer natürlichen Tangpopulation
Warum das Wachstum von Seetang für uns wichtig ist
Seetangwälder sind das Unterwasser-Pendant zu Regenwäldern: Sie bieten Fischen Schutz, dämpfen Küsten gegen Stürme und stützen Fischereien sowie Aquakultur. Doch wachsen nicht alle Tangpflanzen im gleichen Tempo, und Wissenschaftler fragen sich lange, wie viel dieser Unterschiede durch die Umwelt — etwa Temperatur und Licht — bedingt ist und wie viel in der DNA des Tang verankert ist. Diese Studie untersucht, ob die Gene einer häufigen Tangart, Ecklonia radiata, mitbestimmen, wie schnell einzelne Pflanzen in der Natur wachsen, mit Folgen für den Schutz von Tangwäldern und die Steigerung von Erträgen auf Tangfarmen.

Einzelne Tangpflanzen in der Natur verfolgen
Die Forschenden arbeiteten an subtidalen Riffen bei Perth, Westaustralien, wo goldener Tang dichte Unterwasserwälder bildet. Taucher markierten 52 ausgewachsene Tangpflanzen an drei nahe beieinander liegenden Riffen und verfolgten ihr Wachstum über fast drei Monate im Frühling, der Saison, in der diese Art am schnellsten wächst. Das Wachstum wurde mit einer einfachen „Lochstanzen“-Methode gemessen: In jedes Blatt wurde ein winziges Loch in einem festen Abstand zur Wachstumszone gestochen, und die Verschiebung dieses Lochs entlang des Blatts diente dazu, die tägliche Verlängerung in Zentimetern zu berechnen. Gleichzeitig entnahmen sie von jeder markierten Pflanze kleine Gewebeproben, um Abschnitte ihrer DNA zu analysieren.
Die Tang-DNA lesen, um Hinweise auf Wachstum zu finden
Um die genetische Ausstattung des Tang zu untersuchen, nutzte das Team eine Methode, die Tausende von Positionen im Genom abtastet und sich auf einzel-Buchstaben-Unterschiede in der DNA, sogenannte SNPs, konzentriert. Dadurch entstanden Daten für 5.121 genetische Marker pro Individuum. Die Wissenschaftler verwendeten dann ein Set statistischer Werkzeuge — entliehen aus der Human- und Pflanzenforschung — um zu testen, ob bestimmte DNA-Varianten wiederholt mit schnellem oder langsamerem Wachstum assoziiert sind. Wichtig war, dass sie Ergebnisse mit drei verschiedenen Analyseansätzen prüften und nur jene Marker betonten, die in mehreren Methoden auftauchten, um die Wahrscheinlichkeit zu verringern, dass Muster in der relativ kleinen Stichprobe nur Zufall sind.
Starke Verknüpfungen zwischen Genen und Wachstum
Obwohl das Gesamtwachstum zwischen den Riffen nicht unterschiedlich war, zeigten einzelne Tangpflanzen sehr verschiedene Wachstumsraten, mit fast einer vierfachen Spannweite der täglichen Verlängerung. Auffällig war, dass ein winziger Bruchteil der genetischen Marker — nur 18 von mehr als 5.000 — zusammen etwa die Hälfte der beobachteten Variabilität der Wachstumsrate erklären konnten. Fünf dieser Marker wurden von allen drei statistischen Methoden hervorgehoben, und jeder von ihnen allein erklärte ungefähr ein Viertel der Wachstumsunterschiede zwischen Individuen. In einem „polygenen“ Modell ermöglichten die 18 Marker zusammen den Forschenden, die Feldwachstumsrate einer Pflanze mit überraschend hoher Genauigkeit vorherzusagen, obwohl die Pflanzen der vollen Komplexität realer Bedingungen wie Wellen, Konkurrenz und feinen Mikrohabitatunterschieden ausgesetzt waren.
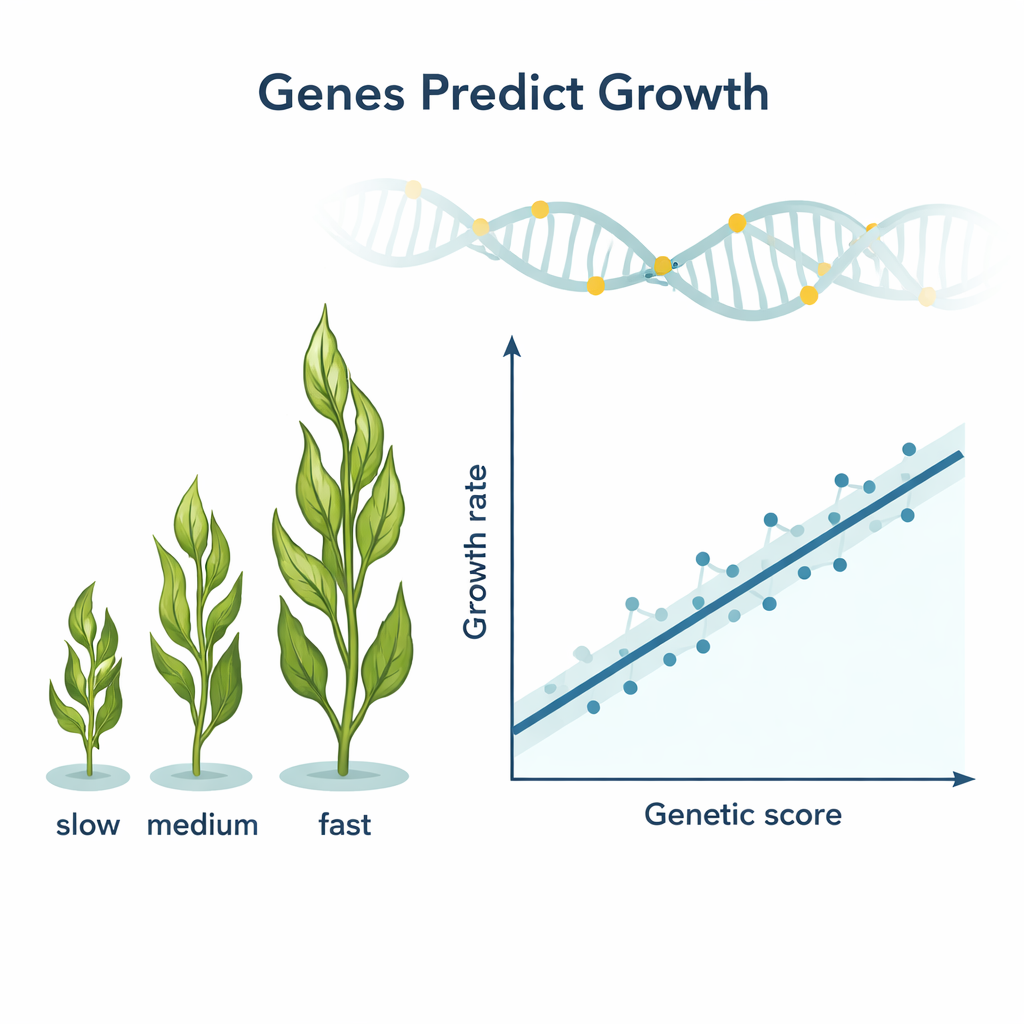
Was die Kandidatengene tun könnten
Um über einfache Korrelationen hinauszukommen, prüfte das Team, ob diese Schlüssel-DNA-Marker in der Nähe aktiver Gene liegen und ob diese Gene in anderen Organismen bekannte Funktionen haben. Viele der assoziierten Regionen stimmten mit Teilen des Transkriptoms von Ecklonia überein, was bedeutet, dass sie im Tang aktiv sind und RNA produzieren, doch die meisten ähnelten keiner gut bekannten Genfamilie und wurden als „Funktion unbekannt“ bezeichnet. Zwei Ausnahmen stachen heraus. Einige wachstumsverbundene Marker lagen in der Nähe von Genen, die Proteinen der ROCO-Familie ähneln, welche in Braunalgen ungewöhnlich häufig vorkommen und in anderen Arten an der Zellsignalübertragung beteiligt sind. Andere befanden sich neben Genen, die Caffeoyl-CoA O-Methyltransferase-ähnlich sind — Enzyme, die beim Aufbau struktureller Bestandteile von Pflanzenzellwänden helfen. Zusammengenommen deuten diese Hinweise darauf hin, dass sowohl Zellwandaufbau als auch interne Signalkaskaden eine Rolle dabei spielen könnten, wie schnell Tangindividuen wachsen können.
Warum das für Tangwälder und Zucht wichtig ist
Der Nachweis eines starken genetischen Signals hinter der Wachstumsrate in wildem Tang hat praktische und ökologische Implikationen. Für Wiederherstellungsprojekte und „unterstützte Anpassungs“-Maßnahmen, die Tang helfen sollen, mit wärmeren Meeren zurechtzukommen, eröffnet die teils vererbbare Natur des Wachstums die Möglichkeit, Spendepflanzen mit vorteilhaften genetischen Profilen auszuwählen. In der Aquakultur, wo die Nachfrage nach Tang als Nahrungsmittel, Futtermittel und Kohlenstoffsenke steigt, könnten diese Marker die gezielte Zucht schneller wachsender Linien lenken, ähnlich wie bei Nutzpflanzen und Bäumen. Gleichzeitig macht die Studie deutlich, dass ein großer Teil des Tanggenoms noch wenig verstanden ist und dass Umweltbedingungen sowie Zielkonflikte mit anderen Merkmalen — etwa Hitzetoleranz oder Widerstand gegen Sturmschäden — ebenfalls bestimmen werden, welche genetischen Varianten in der Natur bevorzugt werden.
Eine einfache Erkenntnis für Nicht-Spezialisten
Einfach gesagt zeigt diese Forschung, dass einige Tangpflanzen von Natur aus „zum Schnellwachsen geboren“ sind und dass sich dieser Unterschied auf bestimmte Abschnitte ihrer DNA zurückverfolgen lässt. Indem sie eine kleine Anzahl genetischer Marker identifizieren, die vorhersagen, wie schnell einzelne Tangpflanzen im Ozean verlängern, liefert die Studie einen der ersten klaren Nachweise dafür, dass Wachstum in einer wilden Tangpopulation eine starke genomische Grundlage hat. Zwar sind weitere Arbeiten mit größeren Proben und kontrollierten Experimenten nötig, um festzustellen, welche Gene tatsächlich schnelleres Wachstum verursachen, doch die frühen Befunde legen nahe, dass Tangwälder — und Tangfarmen — nicht nur von der Umwelt, sondern auch durch gezielten Einsatz genetischer Informationen beeinflusst werden könnten.
Zitation: Starko, S., Burkholz, C., Edgeloe, J.M. et al. Evidence of a genomic basis for growth rate variation in a natural kelp population. Sci Rep 16, 6622 (2026). https://doi.org/10.1038/s41598-026-36286-8
Schlüsselwörter: Genetik von Seetang, Wachstumsrate, marine Wälder, Seetang-Aquakultur, genomische Selektion