Clear Sky Science · de
Bakterielle Genomrekonstruktion und Gemeinschaftsprofilierung bei neotropischen Drosophila
Warum winzige Fliegen und ihre Keime wichtig sind
Fruchtfliegen mögen wie Küchenplagen wirken, doch für Wissenschaftler sind sie mächtige Modelle, um zu verstehen, wie Mikroben die Gesundheit von Tieren – auch unserer eigenen – prägen. Diese Studie untersucht das mikroskopische Leben in und auf wilden Fruchtfliegen aus Ecuador und nutzt moderne DNA-Sequenzierung, um die Genome ihrer Bakterien zu rekonstruieren und zu kartieren, wer wo lebt und wie die Interaktionen aussehen. Indem sie Dutzende Fliegenarten aus den tropischen Anden näher betrachten, stellen die Forschenden eine einfache, aber weitreichende Frage: Sind die Mikroben einer Fliege hauptsächlich Ergebnis ihrer Verwandtschaftslinie oder von Nahrung und Umwelt, denen sie ausgesetzt ist?
Fliegen aus den Anden unter dem Mikroskop
Das Team sammelte 24 Arten neotropischer Drosophila aus neun Provinzen in Ecuador und hielt sie anschließend unter kontrollierten Laborbedingungen auf derselben bananenbasierten Nahrung. Statt nur einige wenige Gene ins Visier zu nehmen, verwendeten sie Shotgun-Metagenomik und lasen die gesamte DNA in jeder Probe. Dadurch konnten sie nicht nur die vorhandenen Mikroben aufzählen, sondern auch vollständige bakterielle Genome aus der gemischten genetischen Suppe zusammensetzen. Nach Entfernung der Fliegen-DNA und möglicher menschlicher Kontamination zeigten die restlichen Sequenzen eine reiche Gemeinschaft von Bakterien und Pilzen, die mit diesen tropischen Fliegen assoziiert sind.
Wer lebt im Fliegendarm?
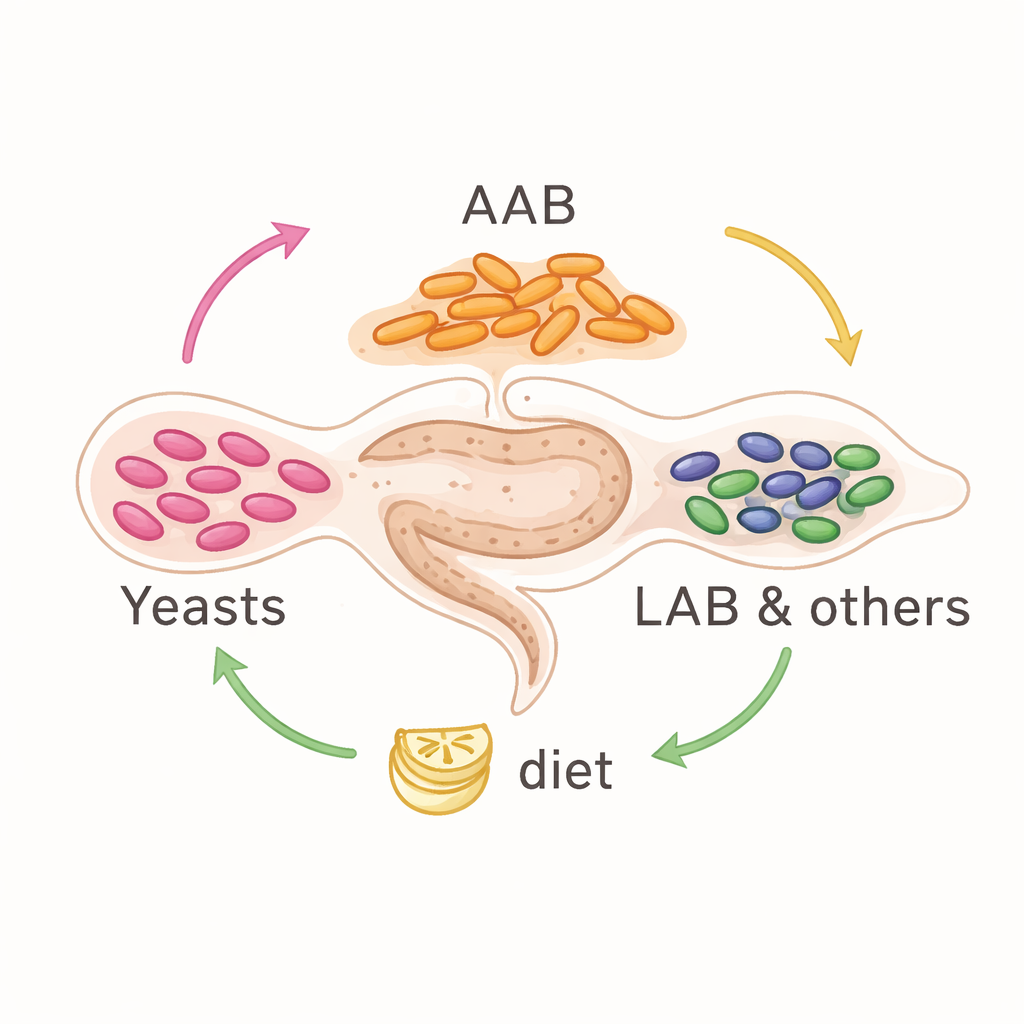
Über die Arten hinweg war die mikrobielle Besetzung überraschend konsistent. Hefen aus der Gruppe Saccharomycetales waren die häufigsten nicht-bakteriellen Bewohner, während die wichtigsten bakteriellen Akteure Essigsäurebakterien (wie Acetobacter und Gluconobacter), Milchsäurebakterien und Mitglieder der Enterobacterales waren; zudem trat bei einigen Fliegen der Fortpflanzungsparasit Wolbachia auf. Diese Gruppen erschienen jedoch nicht in festen Anteilen. Die Proben fielen tendenziell in zwei breite Muster: Einige wurden von Essigsäurebakterien und Hefen dominiert, andere wiesen stattdessen mehr Enterobacterales und Milchsäurebakterien auf. Das deutet darauf hin, dass sich die Gemeinschaft in verschiedene stabile Mischungen umorganisieren kann, statt auf eine einzelne Zusammensetzung festgelegt zu sein.
Rekonstruktion bakterieller „Baupläne“
Mithilfe der metagenomischen Daten rekonstruierten die Forschenden 64 hochqualitative bakterielle Genome, überwiegend aus den Linien der Essigsäurebakterien und Enterobacterales. Zu diesen Genomen gehörten wiederkehrende Vorkommen von Arten wie Acetobacter thailandicus und Gluconobacter kondonii, die auch in der gängigen Laborfliege Drosophila melanogaster gefunden wurden. Detaillierte Vergleiche zeigten, dass die rekonstruierten Genome bekannten Referenzstämmen stark ähneln und Gene tragen, die an ein Leben in zuckerreichen, fermentierenden Umgebungen angepasst sind. Viele waren ausgestattet, Zucker über spezialisierte Wege abzubauen, mit Fermentationsprodukten wie Lactat und Acetat umzugehen und Vitamine sowie Aminosäuren zu synthetisieren, die potenziell ihren Fliegenwirten zugutekommen könnten.
Umwelt vor Abstammung
Eine zentrale Frage war, ob nahe verwandte Fliegenarten ähnlicher Mikrobiota beherbergen – ein Konzept, das als Phylosymbiose bekannt ist. Um dies zu prüfen, verglich das Team Evolutionsbäume, die aus Fliegengenomen gebaut wurden, mit Diagrammen, die die Ähnlichkeiten und Unterschiede ihrer Mikrobiota zusammenfassen. Sie konzentrierten sich außerdem auf eine weit verbreitete Bakterienart, Acetobacter thailandicus, und verglichen deren Evolutionsbaum mit dem ihrer Fliegenwirte. In beiden Fällen war die Übereinstimmung zwischen Wirtsverwandtschaft und mikrobieller Ähnlichkeit schwach. Stattdessen erklärten Faktoren wie das Verhältnis von Essigsäurebakterien zu Enterobacterales und die Häufigkeit von Hefen einen Großteil der Variation, was auf Nahrung und mikroben–mikroben-Interaktionen als wichtige Treiber hindeutet.
Eine veränderliche Gemeinschaft, geformt von Nahrung und Kooperation
In der Zusammenführung der Befunde schlagen die Autorinnen und Autoren vor, dass die Mikroben dieser neotropischen Fruchtfliegen eine flexible Gemeinschaft bilden, die weniger von der Familiengeschichte der Fliegen als von gemeinsamen Nahrungsquellen und mikrobieller Kooperation geprägt ist. In einer bananenbasierten, fermentierenden Umgebung tauschen Hefen und Bakterien Nährstoffe und Stoffwechselprodukte aus, wobei einige Gruppen anderen den Weg ebnen in einer Art ökologischer Staffel. Die neu rekonstruierten bakteriellen Genome, viele von Arten, die wiederholt in verschiedenen Fliegen auftauchen, bieten eine wertvolle Ressource, um zu erforschen, wie diese winzigen Partner ihren Wirten beim Wachsen, Stressbewältigen und Anpassen an wechselnde Nahrungen helfen – Einsichten, die unser übergeordnetes Verständnis davon vertiefen, wie Umwelt und Ökologie, nicht nur Abstammung, die unsichtbaren Welten innerhalb von Tieren formen.
Zitation: Ulloa, M.A., Serrano, A.V., Camelo, L.C. et al. Bacterial genome reconstruction and community profiling in Neotropical Drosophila. Sci Rep 16, 6601 (2026). https://doi.org/10.1038/s41598-026-36282-y
Schlüsselwörter: Fruchtfliegen-Mikrobiom, neotropische Drosophila, Darmbakterien, Metagenomik, Wirt–Mikroben-Interaktionen