Clear Sky Science · de
Genomeweite Analyse der MYB-Genfamilie und ihre stressrespon-sive Expression unter Salz- und Dürrebedingungen bei Sesam
Warum robustere Sesampflanzen wichtig sind
Sesam ist mehr als ein Brötchenbelag. Diese alte „Königin der Ölfrüchte“ wird wegen ihres aromatischen, antioxidanzienreichen Öls geschätzt und wegen ihrer Fähigkeit, dort zu wachsen, wo viele andere Kulturpflanzen scheitern. Da der Klimawandel härtere Dürren und versalzene Böden mit sich bringt, könnte das Verständnis, warum Sesam besser als die meisten Pflanzen zurechtkommt, helfen, Nahrungs- und Ölvorräte in trockenen Regionen zu sichern. Diese Studie gräbt in der DNA von Sesam, um eine große Familie von Steuerungsgenen aufzudecken, die der Pflanze helfen, Stress zu erkennen und ihr Wachstum anzupassen, und liefert Hinweise für die Züchtung zukunftssicherer Kulturen.
Die genetischen Schaltstellen der Pflanze
In jeder Sesamzelle wirken Hunderte von Genen wie Schalter, die andere Gene ein- oder ausschalten. Zu den wichtigsten gehören MYB-Gene, eine große Familie von „Master-Schaltern“, die bereits in anderen Pflanzen bekannt dafür sind, Wachstum, Farbe und Reaktionen auf Hitze, Kälte und Wassermangel zu beeinflussen. Die Forschenden durchsuchten das Sesamgenom und katalogisierten 148 MYB-Gene, von denen jedes das charakteristische DNA-Bindungssegment trägt, das ihm erlaubt, an Zielgene zu binden. Diese MYB-Schalter unterscheiden sich stark in Größe, Ladung und der vorhergesagten Stabilität, was auf ein Baukastensystem hindeutet, dessen Teile für verschiedene Aufgaben in der Pflanze abgestimmt sind.
Wo die Schalter sitzen und was sie umgibt
Das Team stellte dann zwei einfache Fragen: Wo liegen diese Gene im Genom, und welche „Regler“ befinden sich direkt stromaufwärts von ihnen? Sie fanden MYB-Gene auf allen 16 Sesamchromosomen, jedoch dichter gehäuft auf einigen wenigen, was auf frühere Duplikationsereignisse und Evolutions-Hotspots hindeutet. Die meisten entsprechenden MYB-Proteine werden voraussichtlich im Zellkern wirken, wo Genregulation stattfindet, einige könnten aber auch in Chloroplasten, dem Zytoplasma oder sogar an der Zellmembran aktiv sein. In den DNA-Regionen, die steuern, wann MYB-Gene angeschaltet werden, entdeckten die Wissenschaftler zahlreiche kurze Sequenzmotive, die mit Licht, Pflanzenhormonen und — entscheidend — Stressantworten wie Dürre, Kälte, Wunden und Salz in Verbindung stehen. Dieses Muster legt nahe, dass die MYB-Schalter selbst so verschaltet sind, dass sie bei widrigen Bedingungen schnell reagieren.
Familienbande nachzeichnen und verborgene Muster finden
Um die Vielzahl verwandter Gene zu ordnen, gruppierten die Forschenden die Sesam-MYBs in 11 Hauptzweige basierend auf Sequenzähnlichkeit und wiederkehrenden Aminosäuremuster, sogenannten Motiven. Manche Motive sind weit verbreitet und deuten auf grundlegende, housekeeping-ähnliche Funktionen hin; andere treten nur in kleinen Untergruppen auf und deuten auf speziellere Aufgaben, etwa die Feinabstimmung der Reaktion auf einen bestimmten Stress. Durch den Vergleich der Sesam-MYBs mit denen der Modellpflanze Arabidopsis und durch die Untersuchung DNA-Abschnitte, die zwischen den Arten ähnlich geblieben sind, zeigten die Autoren, dass viele MYBs durch Kopieren und Umordnen von Chromosomensegmenten im Laufe der Evolution entstanden sind. Einige dieser duplizierten Gene wurden erhalten und funktional differenziert, andere verschwanden wahrscheinlich wieder, sodass die MYB-Sammlung die lange Anpassung Sesams an herausfordernde Umgebungen widerspiegelt.
Stressgene in Aktion beobachten
Kataloge und Stammbäume sind nützlich, doch die Kernfrage lautet: Welche MYB-Schalter werden tatsächlich aktiv, wenn die Pflanze Durst hat oder gesalzen wird? Um das zu testen, konzentrierten sich die Autoren auf fünf Gene — SiMYB3, SiMYB63, SiMYB114, SiMYB305 und SiMYB308 — und maßen deren Aktivität in drei Sesam-Sorten mit unterschiedlicher Dürre- und Salz‑Toleranz. Keimlinge wurden entweder simulierter Trockenheit oder salzhaltigem Wasser ausgesetzt, und Blattproben wurden über 48 Stunden entnommen. Alle fünf Gene zeigten unter Stress erhöhte Aktivität, jedoch mit unterschiedlichen Mustern je nach Sorte und Stressdauer. Einige, wie SiMYB114 und SiMYB305, reagierten besonders bei Salz mit einem starken Anstieg, vor allem in toleranteren Sorten, während SiMYB308 bei einer Genotyp‑Variante unter Trockenheit früh und dramatisch anstieg. Diese zeit- und genotypspezifischen Muster deuten darauf hin, dass jedes Gen eine eigene Rolle dabei spielt, wie Sesam Stress wahrnimmt und bewältigt.
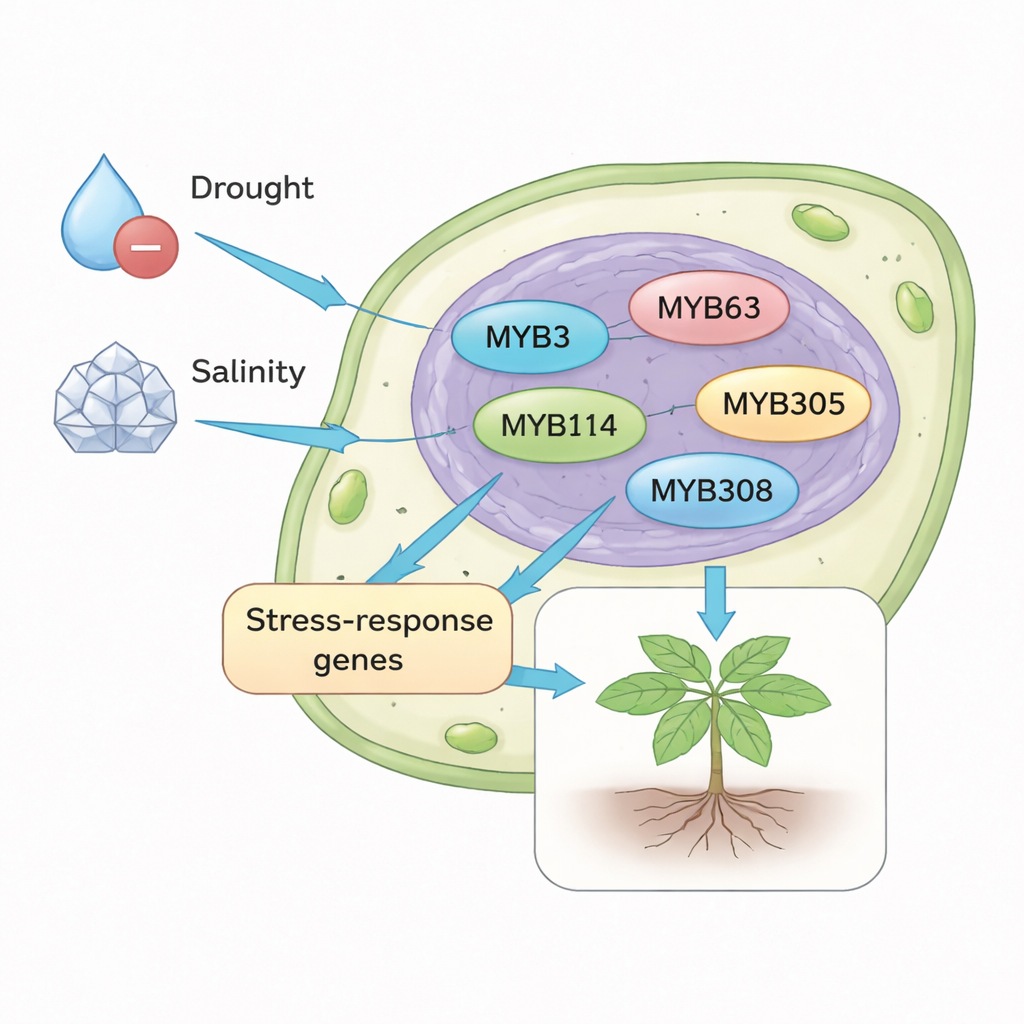
Was das für künftige Kulturen bedeutet
Für Nicht‑Fachleute ist die Kernbotschaft klar: Sesams Widerstandsfähigkeit ist kein Zufall, sondern das Ergebnis vieler fein abgestimmter genetischer Schalter. Durch die Kartierung der gesamten MYB-Genfamilie und den Nachweis, dass mehrere Mitglieder stark auf Dürre und Salz reagieren, liefert diese Studie konkrete Zielmoleküle für Züchter und Gentechniker. Die gezielte Modifikation der Aktivität zentraler MYB-Gene wie SiMYB114, SiMYB305 und SiMYB308 könnte eines Tages zu Sesam‑Sorten — und vielleicht auch zu anderen Kulturen — führen, die auf armen, trockenen oder salzhaltigen Böden produktiv bleiben und so der Landwirtschaft helfen, mit einer wärmeren und wasserärmeren Welt Schritt zu halten.
Zitation: Padyab, S., Asghari Zakaria, R., Zare, N. et al. Genome-wide analysis of the MYB gene family and its stress-responsive expression under salinity and drought in sesame. Sci Rep 16, 6203 (2026). https://doi.org/10.1038/s41598-026-36141-w
Schlüsselwörter: Sesam, Trockenheitstoleranz, Salzstress, MYB-Gene, Pflanzenresilienz