Clear Sky Science · de
Genetische Vielfalt und Übertragungsdynamik von SARS-CoV-2 in Ostafrika
Warum diese Geschichte der Virusreise wichtig ist
Als sich COVID-19 weltweit ausbreitete, tat es das nicht zufällig. Es folgte Menschen entlang von Straßen, Handelsrouten und Flugverbindungen. Diese Studie untersucht genau, wie sich das Coronavirus zwischen 2020 und 2022 in Ostafrika ausbreitete und entwickelte, anhand genetischer Hinweise aus dem Virus selbst. Indem die Forschenden die Reise des Virus durch Länder wie Kenia, Uganda, Ruanda, Burundi, Südsudan und die Demokratische Republik Kongo (DRK) zurückverfolgten, zeigen sie, wie die alltägliche Mobilität von Lkw-Fahrern, Händlern und Geflüchteten die Pandemie mitprägte – und was das für den Schutz der Region vor künftigen Ausbrüchen bedeutet.
Dem Virus anhand seiner genetischen Fingerabdrücke folgen
Jede Kopie des Coronavirus trägt einen genetischen Code, der sich bei der Übertragung von Person zu Person leicht verändert. Durch das Sammeln und Vergleichen von mehr als 11.000 hochwertigen Virengenomen aus Ostafrika konnte das Team erkennen, welche Virusversionen wo und wann auftauchten. Die meisten Sequenzen stammten aus Kenia und der DRK, mit einer guten Vertretung Ugandas; Ruanda, Burundi und der Südsudan lieferten deutlich weniger Proben, was eine schwächere Test- und Sequenzierungskapazität widerspiegelt. Dennoch ergaben die kombinierten Daten eine aussagekräftige Momentaufnahme davon, wie die Pandemie sich in der Region entwickelte und wie internationale Bewegungen lokale Ausbrüche befeuerten.
Wellen neuer Varianten in der Region
Mithilfe dieser Sequenzen kartierten die Forschenden, wie verschiedene COVID-19-Varianten im Zeitverlauf auf- und abnahmen. Frühe Formen des Virus wurden bald durch besser angepasste Varianten wie Beta, Delta und später Omikron ersetzt, was den globalen Trends entspricht. Kenia verzeichnete durchgängig die größte Anzahl und die größte Mischung an Varianten, mit deutlichen Spitzen während der Delta-Welle 2021 und dem Omikron-Anstieg 2022. Uganda und die DRK zeigten spürbare, aber kleinere Wellen, während Ruanda, Burundi und der Südsudan nur eine begrenzte Variantenvielfalt meldeten – wahrscheinlich eine Mischung aus weniger nachgewiesenen Infektionen und weniger sequenzierten Proben. Insgesamt erlebte die Region weitgehend synchronisierte Wellen, was darauf hindeutet, dass eine neue Variante, einmal in einem Land aufgetaucht, nicht lange dort blieb.
Ein verästelter Stammbaum, der Grenzen ignoriert
Um zu verstehen, wie diese Varianten miteinander verwandt waren, bauten die Forschenden einen großen „Stammbaum“ der Virengenome. Statt sauberer, auf ein Land beschränkter Cluster fanden sie Äste, in denen Sequenzen aus Kenia, Uganda, Ruanda, Burundi, Südsudan und der DRK durchmischt waren. Fünf große genetische Cluster enthielten Proben aus mehreren Ländern, was wiederholte Einschleppungen und grenzüberschreitende Ausbreitung statt isolierter nationaler Epidemien nahelegt. Kenia und Uganda, die die meisten Sequenzen beisteuerten, erschienen an vielen Stellen im Baum, während kleinere Staaten seltener vertreten waren, aber dennoch Linien mit ihren Nachbarn teilten. Das entstehende Bild ist das einer regionalen Epidemie, die durch Bewegung entlang von Straßen und durch Grenzstädte verflochten ist, nicht durch getrennte, abgeriegelte Ausbrüche.
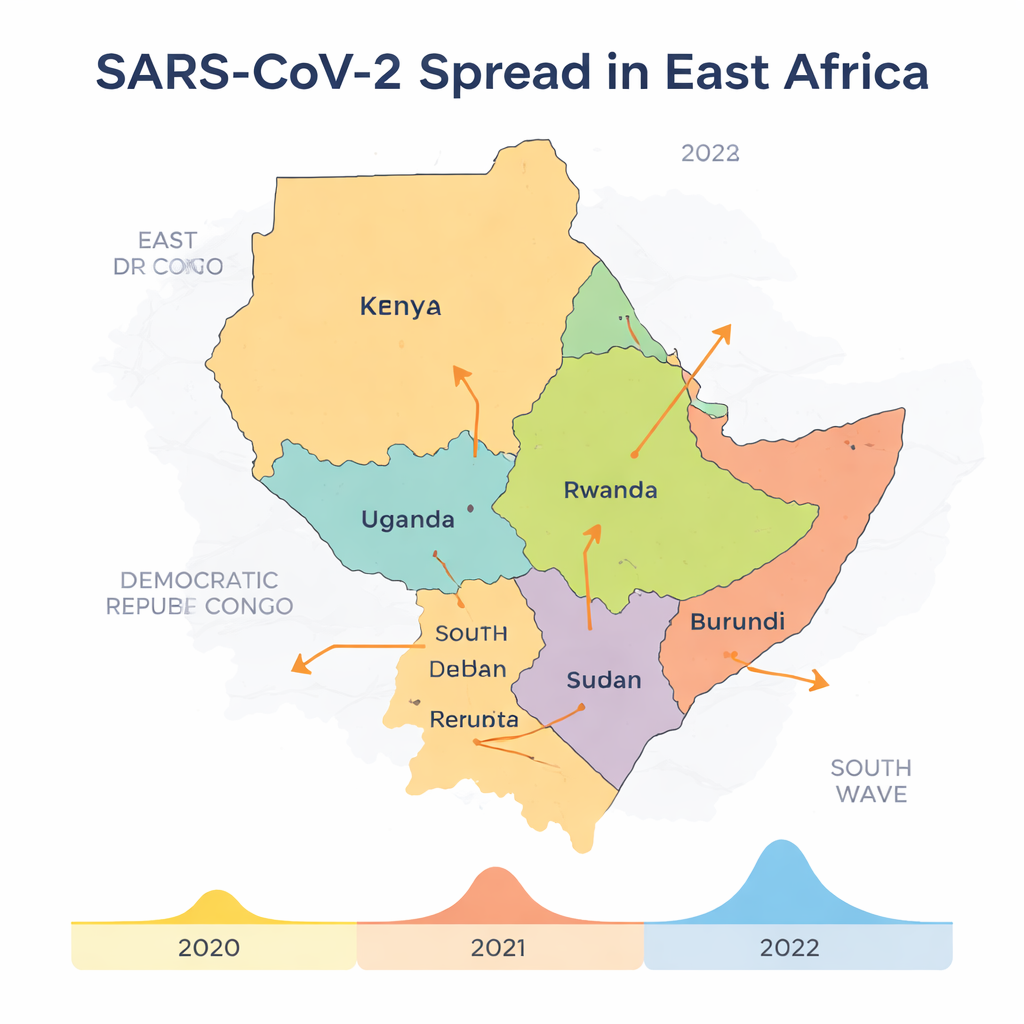
Straßen, Lkw und Geflüchtete als verborgene Autobahnen
Indem sie den genetischen Stammbaum mit Karten und Zeitachsen kombinierten, konnten die Forschenden wahrscheinliche Ausbreitungsrichtungen zurückverfolgen. Kenia tauchte als wichtiger Ursprung von Infektionen für die DRK, Uganda und den Südsudan auf, mit zusätzlichen Virusbewegungen zwischen DRK und Uganda sowie von Ruanda in den Südsudan. Dieses Muster passt zu Kenias Rolle als wichtigem Handels- und Verkehrsknotenpunkt Ostafrikas, mit stark frequentierten Autobahnen, Häfen und Flughäfen, die zumindest teilweise auch während Lockdowns in Betrieb blieben. Fernfahrer und Frachtpersonal, die häufig von strengen Reisebeschränkungen ausgenommen waren, wurden zu unbeabsichtigten Überträgern des Virus über Grenzen hinweg. Gleichzeitig schufen poröse Landgrenzen, informelle Übergänge und Flüchtlingsbewegungen – besonders zwischen DRK, Uganda, Ruanda und dem Südsudan – zahlreiche Gelegenheiten, dass das Virus offizielle Kontrollpunkte und Gesundheitschecks umging.
Lehren für die nächste Pandemie
Für Nichtfachleute ist die Kernbotschaft einfach, aber eindrücklich: Viren richten große Aufmerksamkeit auf unsere Bewegungsmuster. In Ostafrika hielt COVID-19 nicht an Grenzposten an; es floss entlang von Handelskorridoren und Migrationsrouten, wobei Kenia als großes Relais fungierte. Die Studie zeigt, dass das Verfolgen genetischer Veränderungen des Virus diese verborgenen Ausbreitungswege aufdecken und auf Bereiche hinweisen kann, in denen stärkere Kooperation nötig ist. Die Autorinnen und Autoren plädieren dafür, die Vorbereitung auf künftige Pandemien in der Region auf gemeinsame grenzüberschreitende Gesundheitssysteme, besseren Datenaustausch und breiteren Zugang zu genomischen Tests zu konzentrieren, damit Länder neue Bedrohungen rasch erkennen und gemeinsam handeln können. In einer Welt, in der sich eine Infektion innerhalb von Tagen über einen Kontinent bewegen kann, lässt sich die Gesundheitssicherheit eines Landes nicht von der seiner Nachbarn trennen.
Zitation: Nabisubi, P., Kanyerezi, S., Agasi, H. et al. Genetic diversity and transmission dynamics of SARS-CoV-2 in East Africa. Sci Rep 16, 5235 (2026). https://doi.org/10.1038/s41598-026-36094-0
Schlüsselwörter: COVID-19, SARS-CoV-2-Varianten, Ostafrika, genomische Überwachung, grenzüberschreitende Übertragung