Clear Sky Science · de
Haplotyp‑Ebene Analyse von Umwelt‑DNA‑Metabarcoding enthüllte Biogeographie und Phylogeographie von Süßwasserfischen in der Koreanischen Halbinsel
Flüsse lesen anhand unsichtbarer Spuren
Flüsse und Bäche mögen mit bloßem Auge klar erscheinen, doch sie sind voller mikroskopischer Lebensspuren. Diese Studie zeigt, wie Forschende diese unsichtbare genetische „Tinte“ im Wasser lesen können, um herauszufinden, welche Fische wo leben, wie ihre Populationen über die Koreanische Halbinsel zusammenhängen und ob einige Arten von Menschen von einer Region in eine andere verschleppt wurden. Die Arbeit gewährt einen Einblick, wie Naturschützer bald die Biodiversität überwachen und seltene Arten schützen können, ohne ein einziges Netz auszuwerfen.
Fischen mit DNA statt Netzen
Statt Fische zu fangen sammelten die Forschenden einfache Ein‑Liter‑Proben aus drei kleinen Bächen — Seom, Gilan und Oshipcheon — jeweils in unterschiedlichen biogeografischen Regionen Südkoreas. In diesen Proben suchten sie nach Umwelt‑DNA (eDNA): winzigen Fragmenten genetischen Materials, das Fische über Haut, Ausscheidungen und Schleim abgeben. Mit einer Methode namens Metabarcoding verstärkten und sequenzierten sie ein kurzes Stück Fisch‑DNA und verglichen dann Millionen von Reads mit Referenzdatenbanken, um zu identifizieren, welche Arten — und sogar welche genetischen Varianten oder Haplotypen — in jedem Bach vorkamen.
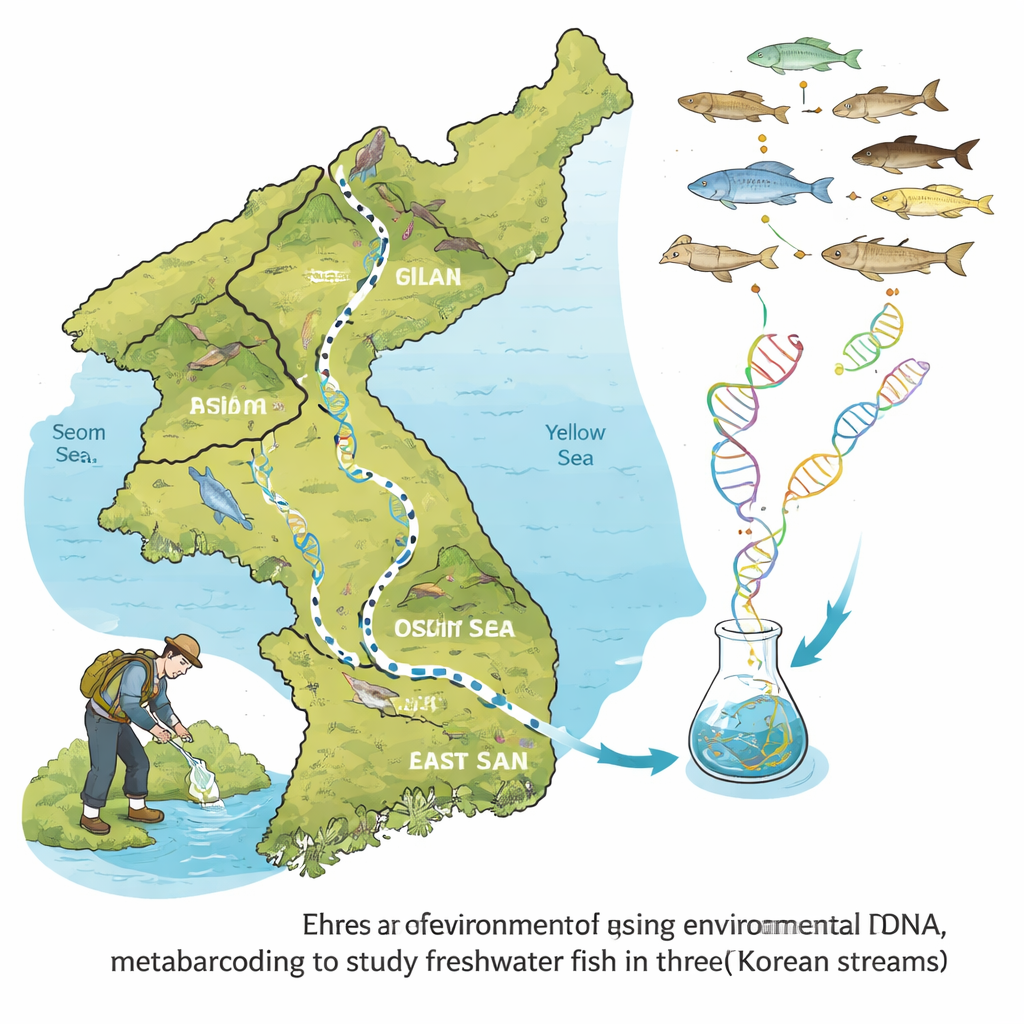
Wer lebt wo in Koreas Bächen?
Aus nur 54 Wasserproben, entnommen an neun Standorten, detektierte das Team 107 verschiedene DNA‑Varianten, die 76 Fischarten repräsentieren — etwa ein Drittel aller in Korea bekannten Süßwasserfische. Der Seom‑Bach, ein tiefer gelegenes Gewässer mit Verbindung zum Gelben Meer, beherbergte die artenreichste Fischgemeinschaft mit 49 Arten. Gilan und Oshipcheon, höhere und steilere Zuflüsse, die zu unterschiedlichen Küsten fließen, wiesen jeweils 28 Arten auf. Viele Arten teilten sich mehrere Bäche, doch fast 30 Arten erwiesen sich als endemisch für Koreas Süßwasserlebensräume, und jeder Bach hatte zudem eigene, einzigartige Artenzusammensetzungen. Insgesamt stimmten die Muster mit dem langjährigen Wissen überein, dass das Süßwasserleben Koreas durch Gebirgszüge und geologische Geschichte in drei Hauptregionen geteilt ist.
Genetische Fingerabdrücke und versteckte Verlagerungen
Weil die Forschenden auf Haplotyp‑Ebene arbeiteten — die feingliedrigen „Nuancen“ der DNA innerhalb einer Art — konnten sie mehr als Artenlisten erstellen; sie konnten Populationen vergleichen. Mehrere verbreitete einheimische Fischarten zeigten deutliche genetische Unterschiede zwischen den Regionen, was auf lang andauernde Trennung und begrenzten natürlichen Austausch über die Halbinsel hinweist. Gleichzeitig deckten die DNA‑Daten wahrscheinliche Fälle menschlich unterstützter Verbringung auf. Bei Arten wie Pungtungia herzi, Coreoleuciscus splendidus und Nipponocypris koreanus stimmten die Haplotyp‑Muster im östlichen Oshipcheon‑Bach eng mit denen aus westlichen oder südlichen Flüssen überein, was auf frühere Besatzmaßnahmen oder Translokationen hindeutet. Durch die virtuelle Rekonstruktion von „Stammbäumen“ dieser DNA‑Varianten konnte das Team wahrscheinliche Quellregionen für verschobene Fische ableiten — eine Art genetische Forensik für das Flussmanagement.
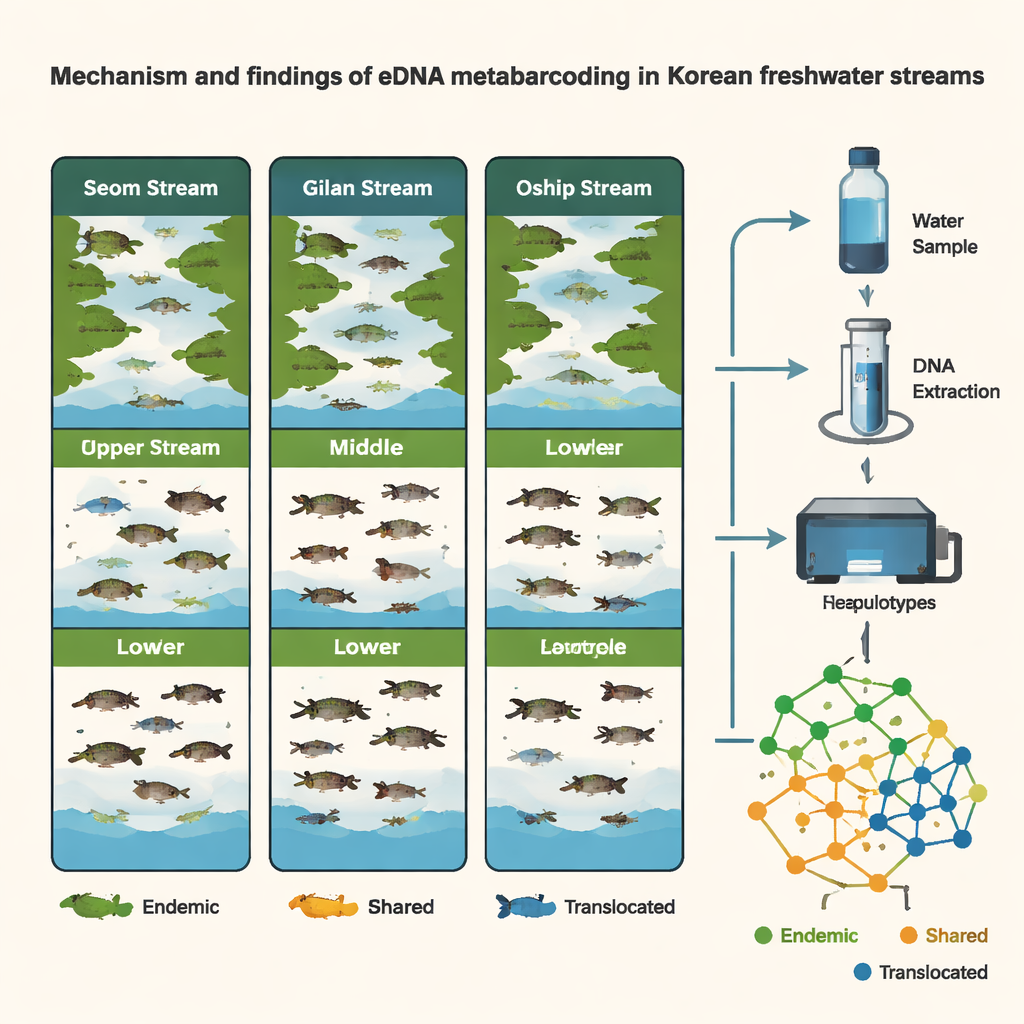
Jahreszeiten, Lebensräume und bewegliche Ziele
Die Studie verfolgte zudem, wie sich Fischgemeinschaften über Zeit und Raum veränderten. Beim Vergleich von Proben aus dem späten Winter (März) und dem Sommer (August) fanden die Forschenden eine höhere Artenvielfalt im Sommer und deutliche saisonale Verschiebungen, besonders im Seom‑Bach. Im Oshipcheon tauchte eDNA wandernder Arten — etwa von Lachsen und anderen Fischen, die zwischen Fluss und Meer pendeln — in Mustern auf und verschwand wieder, die mit ihren bekannten Lebenszyklen übereinstimmten. Überraschenderweise zeigten innerhalb eines Standorts Sohlen mit Stromschnellen, Fließstrecken und Tiefen keine starken Unterschiede in der Fisch‑DNA, wahrscheinlich weil der Wasserfluss eDNA lateral über diese kleinen Rinnsale vermischt. Stattdessen ergaben sich die wichtigsten Kontraste zwischen verschiedenen Bachabschnitten (oberer, mittlerer, unterer Lauf) und zwischen den drei Bächen selbst, was die Bedeutung des Probenahmeorts entlang eines Flusses unterstreicht.
Was das für den Schutz des Süßwasserlebens bedeutet
Kurz gesagt, diese Forschung demonstriert, dass eine Flasche Flusswasser ein detailliertes Abbild davon liefern kann, wer im Bach lebt, wie lokale Fischpopulationen über weite Regionen miteinander verwandt sind und ob Menschen diese Muster durch Verbringung von Fischen verändert haben. Für den Naturschutz bedeutet das, dass Verantwortliche seltene und endemische Arten schnell überwachen, invasive und translozierte Fische erkennen und saisonale Verschiebungen wandernder Populationen verfolgen können — ohne aufwändige Feldarbeit oder Schädigung der Tiere. Zwar kann eDNA traditionelle genetische Untersuchungen noch nicht vollständig ersetzen, doch bietet sie ein kraftvolles, wenig eingreifendes Werkzeug zur Beobachtung der Süßwasserbiodiversität in einer wärmer werdenden, stark bewirtschafteten Welt — und zur Sicherstellung, dass Koreas einzigartige Flussfische in ihren ursprünglichen Lebensräumen weiter gedeihen.
Zitation: Amin, M.H.F., Kim, A.R., Jang, J.E. et al. Haplotype-level analysis of environmental DNA metabarcoding revealed the biogeography and phylogeography of freshwater fishes in Korean Peninsula. Sci Rep 16, 6955 (2026). https://doi.org/10.1038/s41598-026-36043-x
Schlüsselwörter: Umwelt‑DNA, Süßwasserfische, Biodiversität, koreanische Flüsse, Erhaltungsgentik