Clear Sky Science · de
Direkte und pleiotrope SNP‑Effekte in Luzerne (Medicago sativa L.) durch kausales Graphenlernen entwirren
Warum das für Landwirtschaft und Ernährung wichtig ist
Luzerne ist ein Arbeitspferd der modernen Landwirtschaft: Sie ernährt Milchkühe und trägt zur Erhaltung gesunder Böden bei. Die Züchtung besserer Luzerne—Pflanzen, die den Winter besser überstehen, weniger Schäden erleiden und hochwertiges Futter liefern—wurde jedoch durch die enorme genetische Komplexität verlangsamt. Diese Studie stellt einen neuen Weg vor, von langen, verwirrenden Listen von DNA‑Markern zu klaren Ursache‑Wirkungs‑Karten zu gelangen, die zeigen, welche Genomabschnitte tatsächlich wichtige Stängelmerkmale antreiben und welche bloß mitlaufen.
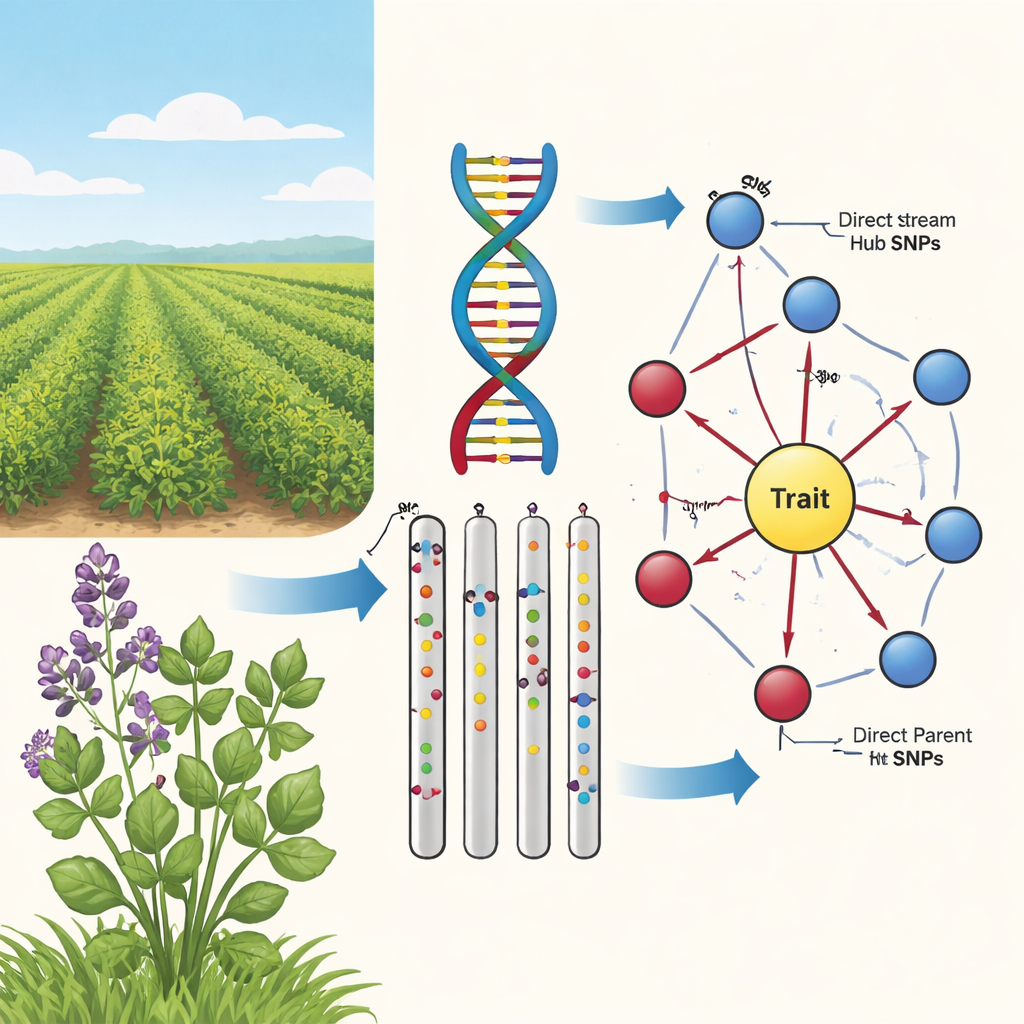
Von lockeren Assoziationen zu Ursache und Wirkung
Traditionelle genomweite Assoziationsstudien (GWAS) durchsuchen das Genom nach DNA‑Varianten, sogenannten SNPs, die vermehrt zusammen mit einem Merkmal auftreten, etwa Stängelfarbe oder Winterhärte. Bei Luzerne ist die Lage jedoch besonders verstrickt: Sie besitzt vier Kopien jedes Chromosoms, große DNA‑Abschnitte wandern gemeinsam und die Pflanzen sind genetisch stark vermischt. Das erzeugt einen "Nebel der Korrelation", in dem viele Marker wichtig erscheinen, aber nur wenige das Merkmal tatsächlich beeinflussen. Die Autoren argumentieren, dass Züchter mehr als einfache statistische Verknüpfungen brauchen; sie müssen wissen, welche Marker auf den tatsächlichen kausalen Pfaden vom Genotyp zu sichtbaren Pflanzenmerkmalen liegen.
Wie das neue Framework funktioniert
Die Forschenden entwickelten ein zweistufiges Framework, das moderne Machine‑Learning‑Methoden mit Konzepten aus der kausalen Graphentheorie kombiniert. Zuerst setzten sie eine Technik namens Double Machine Learning ein, um etwa 2.400 SNPs in 500 Luzerne‑Genotypen zu screenen. Dieser Schritt entfernt den Einfluss versteckter Faktoren wie familiärer Hintergrund und Geografie, indem Hauptkomponenten des Genoms als Stellvertreter genutzt werden. Das Ergebnis ist eine sauberere Sicht darauf, welche Marker nach Berücksichtigung dieser Störfaktoren weiterhin direkte Effekte auf Merkmale wie Stängelfarbe zeigen. In dieser gefilterten Ansicht traten starke, stabile Signale vor allem auf Chromosomen 2 und 4 hervor, und Schlüsselmarker zeigten Effektgrößen mit Konfidenzbereichen, die klar Null ausschlossen—ein Hinweis auf echte kausale Einflüsse.
Marker in genetische Straßenkarten verwandeln
In der zweiten Stufe verwendete das Team einen Algorithmus zum Erlernen kausaler Graphen, bekannt als PC‑Algorithmus, um die vielversprechendsten Marker zu einem gerichteten Netzwerk zu verbinden. In diesen Diagrammen repräsentieren Knoten SNPs und das Merkmal, Pfeile zeigen die wahrscheinlichste Richtung des Einflusses. Indem Kanten entfernt wurden, die der Biologie widersprechen (zum Beispiel können Merkmale die DNA nicht verändern) und nur SNPs beibehalten wurden, die in das Merkmal hineinwirken, erhielten die Autoren kompakte, biologisch sinnvolle Karten. Diese "Sonnenblumen"‑Netzwerke offenbaren eine geschichtete Struktur: ein innerer Ring von Direct‑Parent‑SNPs, die direkt mit dem Merkmal verbunden sind, und ein äußerer Ring von Upstream‑Hub‑SNPs, die mehrere Eltern beeinflussen, das Merkmal aber nicht direkt berühren.
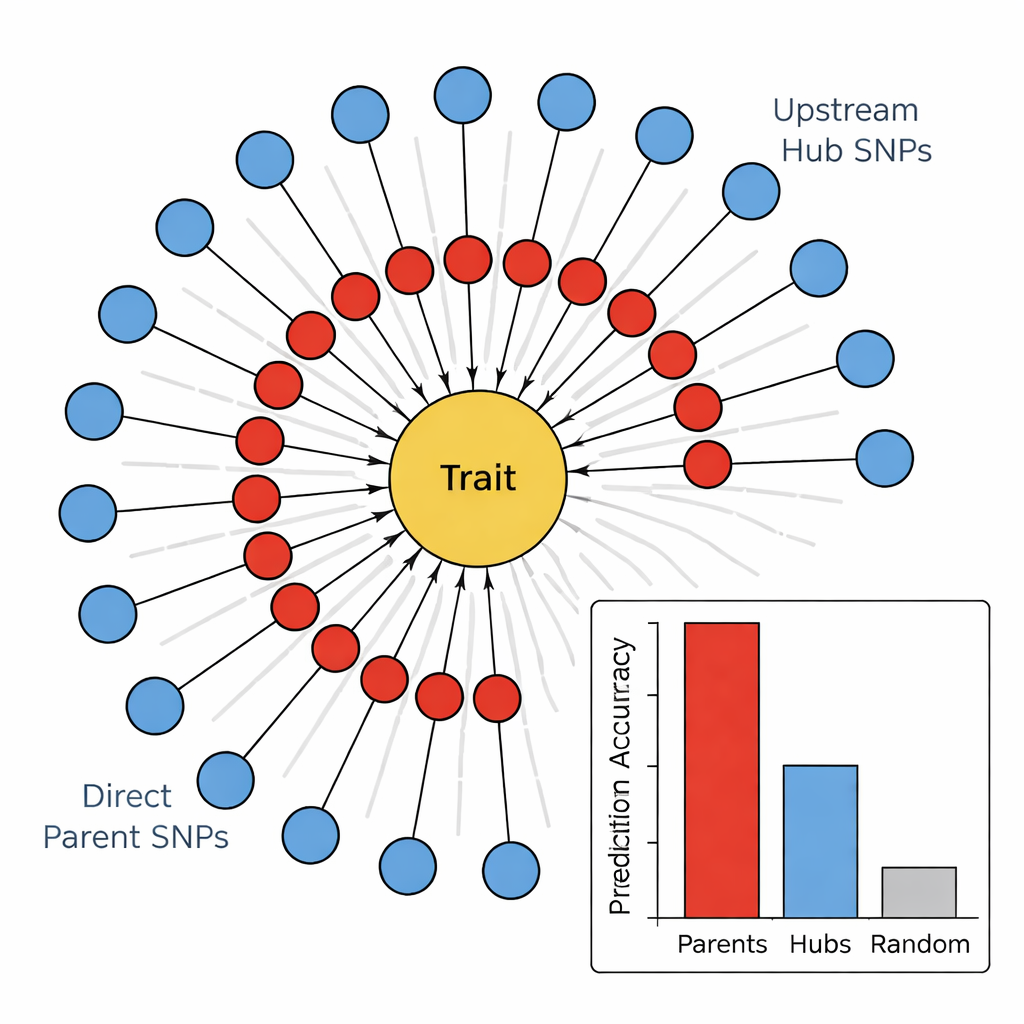
Ausführer versus Regisseure im Genom
Um zu prüfen, ob diese Hierarchie sinnvoll ist, verglichen die Autoren, wie gut verschiedene Markergruppen vier stängelbezogene Merkmale vorhersagen konnten: Stängelfarbe, Stängelfüllung, Stängelstärke und Winterverletzung. Über alle Merkmale hinweg waren die Direct‑Parent‑SNPs konsistent die besten Prädiktoren und erklärten oft um ein Vielfaches mehr Variation als zufällige Marker oder die Upstream‑Hubs. Im Gegensatz dazu zeigten die Hubs trotz ihrer hohen Vernetzung im Netzwerk schwache oder sogar negative Vorhersagekraft. Als das Team diese SNPs mit bekannten Genen verband, zeigte sich ein Muster: Direct Parents entsprachen häufig Enzymen oder Strukturproteinen, die direkt an Zellwänden, Pigmenten oder Stressschäden wirken, während Hubs tendenziell Transkriptionsfaktoren und regulatorische Proteine entsprachen, die viele Wege gleichzeitig modulieren.
Was das für die zukünftige Luzernezüchtung bedeutet
Für Züchter und Genetiker bietet die Studie einen Weg, lärmende Assoziationsergebnisse zu durchdringen und sich auf DNA‑Veränderungen zu konzentrieren, die konkret etwas an bestimmten Merkmalen bewegen. Die Autoren zeigen, dass die Kombination aus de‑konfundiertem Screening und kausalen Graphen als eingebauter Schutz gegen Overfitting dienen kann und lange Kandidatenlisten in kleine, interpretierbare Netzwerke verwandelt, die mit bekannter Biologie übereinstimmen. Praktisch werden Direct‑Parent‑SNPs zu hochpräzisen Markern für die Auswahl von Pflanzen mit besseren Stängeln oder verbesserter Winterhärte, während Upstream‑Hubs auf Hauptschalter hinweisen, die breitere Stressantworten umgestalten könnten—mit möglichen Zielkonflikten. Diese strukturelle Sicht des Genoms legt eine Grundlage für zuverlässigere genomische Selektion in komplexen Kulturpflanzen und für die Integration zukünftiger Datenschichten, wie Genexpression und Stoffwechsel, in kohärente Ursache‑Wirkungs‑Modelle zur Vorhersage von Pflanzenleistung.
Zitation: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
Schlüsselwörter: Luzerne‑Genetik, kausales Graphenlernen, genomische Selektion, Pflanzenzüchtung, polyploide Nutzpflanzen