Clear Sky Science · de
Strukturierte dissoziative PCA-Methoden zur Zerlegung hochdimensionaler neuroimaging Signale
Die verborgenen Signale des Gehirns entwirren
Moderne Hirnscans können die Aktivität von Hunderttausenden von Orten pro Sekunde aufzeichnen, doch aus diesem Zahlenstrom klare, aussagekräftige Netzwerke zu gewinnen, ist extrem schwierig. Verschiedene Hirnprozesse überlappen sich häufig in Raum und Zeit, ähnlich wie mehrere Radiosender auf benachbarten Frequenzen senden. Dieses Papier stellt neue mathematische Werkzeuge vor, die helfen, diese verflochtenen Signale sauberer zu trennen, und so schärfere Karten der Gehirnfunktion für Grundlagenforschung und klinische Studien versprechen.
Warum übliche Methoden an ihre Grenzen stoßen
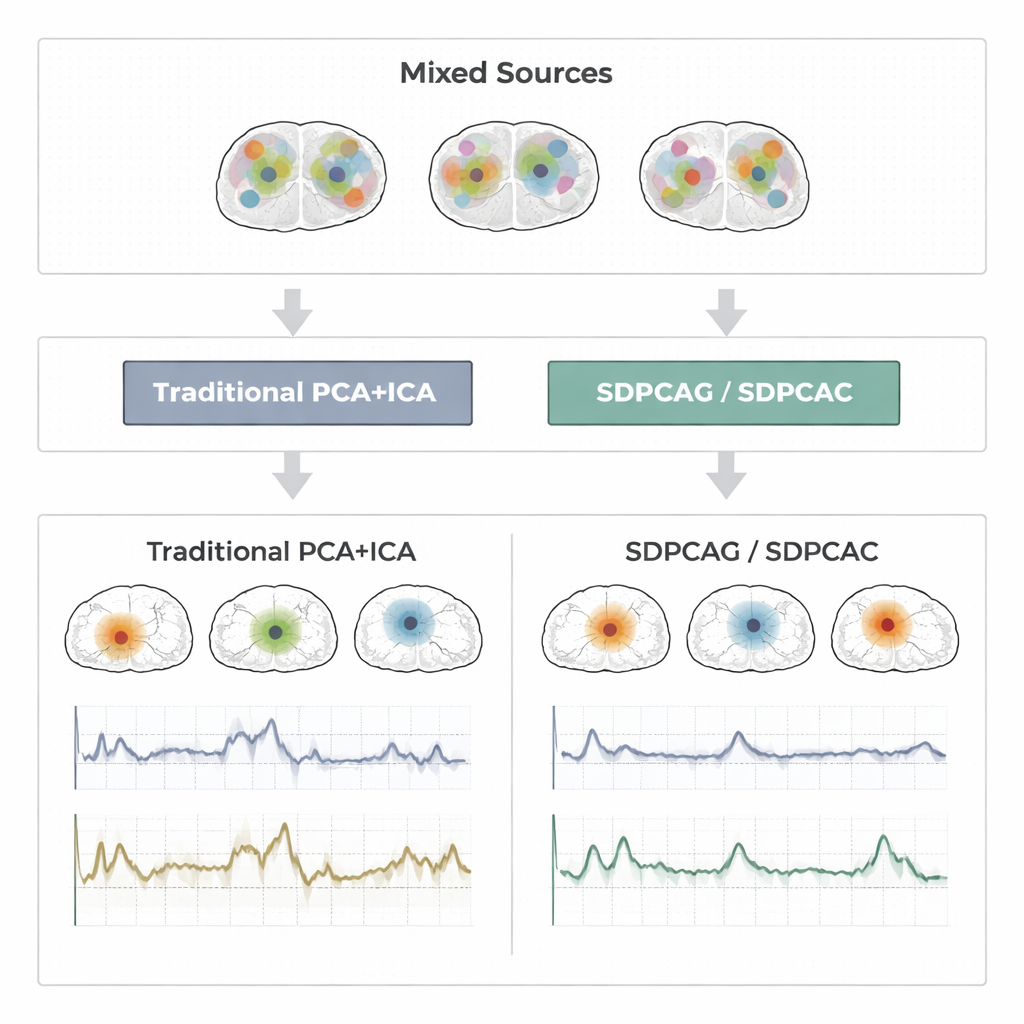
Jahrzehntelang haben Forschende Techniken wie Hauptkomponentenanalyse (PCA), sparse PCA und unabhängige Komponentenanalyse (ICA) verwendet, um funktionelle MRT-(fMRI-)Daten zu komprimieren und zu trennen. PCA findet Muster, die den größten Teil der Variation in den Daten erklären, aber jedes Muster mischt Informationen aus nahezu allen Hirnregionen, was die Interpretation erschwert. Sparse PCA versucht, dies zu beheben, indem sie jedes Muster auf eine Teilmenge von Orten beschränkt, und ICA geht weiter, indem sie annimmt, dass die zugrunde liegenden Hirnsignale statistisch unabhängig sind. In der Praxis jedoch überlappen sich reale Hirnnetzwerke und beeinflussen einander. Wenn das geschieht, versagen die Unabhängigkeits- und Sparsitätsannahmen. Das Ergebnis können fragmentierte Karten und verrauschte Zeitverläufe sein, die nicht mehr dem Verhalten echter Hirnnetzwerke entsprechen.
Eine neue Methode, Signale zu trennen
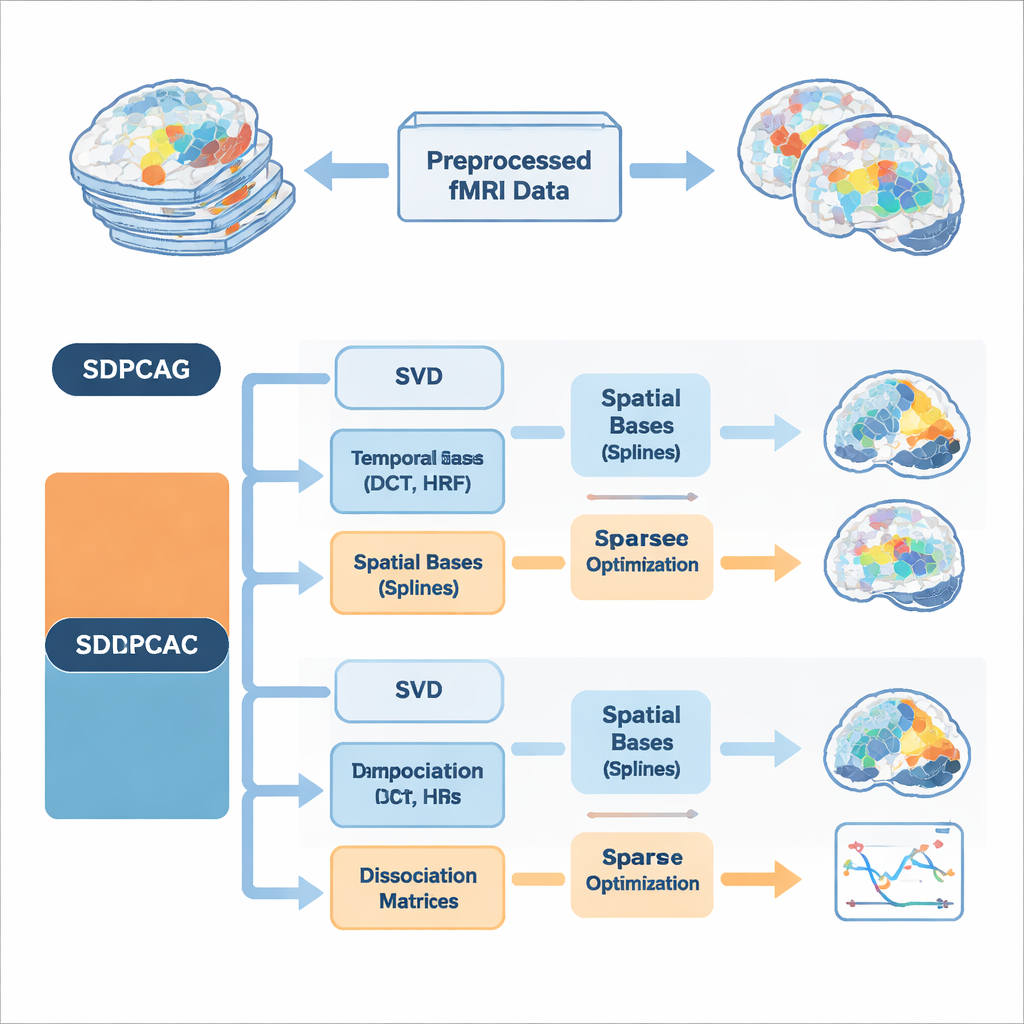
Die Autorinnen und Autoren schlagen einen einheitlichen Rahmen namens strukturierte dissoziative PCA vor, implementiert in zwei Algorithmen mit den Namen SDPCAG und SDPCAC. Anstatt Raum und Zeit getrennt zu behandeln, formt die Methode den gesamten fMRI-Datensatz durch eine einzige, sorgfältig gestaltete Zerlegung um. Sie startet mit einer standardmäßigen Niedrigrangzerlegung der Daten und führt dann spezielle „Dissoziations“-Matrizen ein, die räumliche Karten und Zeitverläufe gemeinsam umgewichten und drehen. Gleichzeitig stellt sie diese Komponenten mit Mengen glatter Bausteine dar: kosinusähnliche zeitliche Wellen, Modelle der hämodynamischen Antwort des Gehirns auf neuronale Aktivität und glatte räumliche Kurven, sogenannte Splines. Indem gelernt wird, wie diese Bausteine kombiniert werden, und dabei Sparsität erzwungen wird — es bleiben nur die wichtigsten Teile erhalten —, kann die Methode überlappende Netzwerke auseinanderziehen, ohne unrealistische Unabhängigkeitsannahmen aufzuerlegen.
Gehirnwissen von vornherein einbauen
Eine zentrale Innovation ist, dass die Algorithmen Vorwissen über Hirnsignale direkt in die Zerlegung einbetten, statt dies nachträglich zu bereinigen. Auf der zeitlichen Seite verwenden sie diskrete Kosinusfunktionen, um glatte Zeitverläufe zu begünstigen, und schließen Standardmodelle der hämodynamischen Antwort ein — das verzögerte Blut-Sauerstoff-Signal, das durch fMRI gemessen wird. Auf der räumlichen Seite helfen Spline-Basen, zusammenhängende, kohärente Aktivierungsmuster statt verstreuter Punkte zu bevorzugen. Zusätzliche Beschränkungen begrenzen, wie viele zeitliche und räumliche Basisfunktionen jede Komponente nutzen darf, was eine Überanpassung an Rauschen reduziert und die Idee widerspiegelt, dass reale Hirnnetzwerke in Raum und Zeit relativ kompakt sind. Es werden zwei komplementäre Optimierungsstrategien vorgestellt: SDPCAG aktualisiert ganze Matrizen in Blöcken, während SDPCAC eine Komponente nach der anderen anhand von Residualfehlern verfeinert und dafür einen etwas höheren Rechenaufwand gegen flexiblere Anpassungen eintauscht.
Methoden im Test
Um zu beurteilen, wie gut diese Ideen funktionieren, führen die Autorinnen und Autoren umfangreiche Tests an drei Datentypen durch: sorgfältig entworfene synthetische fMRI-Signale mit bekanntem Ground-Truth; ein Block-Design-Motor-Experiment aus dem Human Connectome Project; und eine ereignisbezogene Finger- Tapping-Studie aus einem unabhängigen Labor. In diesen Szenarien vergleichen sie SDPCAG und SDPCAC mit führenden Alternativen, die penalized matrix decomposition, sparse PCA, ICA und Dictionary Learning kombinieren. Gemessen wird, wie eng die wiedergewonnenen Zeitverläufe den bekannten Aufgabenmustern entsprechen, wie gut räumliche Karten mit etablierten Ruhezustandsnetzwerken übereinstimmen und wie genau Quellen bei unterschiedlichen Rauschpegeln rekonstruiert werden. Die neuen Methoden liefern durchweg sauberere, stärker lokalisierte Hirnkarten und weniger verrauschte Zeitserien und behalten starke Leistung, selbst wenn die Daten stark beeinträchtigt sind. Einer der Algorithmen, SDPCAG, verbessert die Quelle- Wiederherstellungsgenauigkeit um etwa 22 % gegenüber einer starken konkurrierenden Methode und ist dabei schneller als sein detaillierterer Verwandter SDPCAC.
Was das für die Hirnforschung bedeutet
Einfach gesagt bietet diese Arbeit eine bessere Möglichkeit, die Signale in fMRI-Daten zu „entmischen“. Durch die gemeinsame Modellierung von Raum und Zeit, die Verwendung realistischer Priors über das Verhalten von Hirnaktivität und Blutfluss sowie das Durchsetzen intelligenter Sparsität erzeugen SDPCAG und SDPCAC Hirnnetzwerke, die sowohl auf den Bildern schärfer als auch in ihren zugrunde liegenden Zeitverläufen treuer sind. Das kann zu zuverlässigerer Detektion aufgabenbezogener Aktivierungen und präziserer Kartierung von Ruhezustandsnetzwerken führen, was wiederum Studien zu Erkrankungen wie Alzheimer, psychiatrischen Störungen und anderen Hirnkrankheiten unterstützt. Zwar besteht weiterhin Raum, die Methode zu beschleunigen und zu erweitern — etwa für Multi-Subject-Studien oder multimodales Imaging —, doch stellt sie einen wichtigen Schritt dar, um hochdimensionale Scan-Daten in verlässliche, interpretierbare Abbildungen des arbeitenden menschlichen Gehirns zu verwandeln.
Zitation: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Schlüsselwörter: fMRI-Signalzerlegung, sparse PCA, Kartierung von Hirnnetzwerken, Blindquellentrennung, Ruhezustands-Konnektivität