Clear Sky Science · de
Eine Methode zur Segmentierung von Splenomegalie‑Bildern in der Magnetresonanz basierend auf einem Multi‑Skalen‑Aufmerksamkeitsmechanismus mit großem Kernel
Warum Ärztinnen und Ärzte sich für eine vergrößerte Milz interessieren
Die Milz ist ein faustgroßes Organ unter dem linken Rippenbogen, das stillschweigend Blut filtert, gegen Infektionen kämpft und bestimmte Blutzellen reguliert. Wenn sie vergrößert ist — ein Zustand, der als Splenomegalie bezeichnet wird — kann dies auf ernsthafte Erkrankungen hindeuten, von Leberleiden bis zu Blutkrebsen. Moderne Scanner liefern zwar detaillierte Bilder der Milz, doch diese Aufnahmen in zuverlässige Messwerte zu überführen, erfordert oft zeitaufwändige und fehleranfällige manuelle Arbeit durch Spezialisten. Diese Studie stellt eine neue Methode der künstlichen Intelligenz vor, die vergrößerte Milzen in MRT‑Aufnahmen automatisch mit sehr hoher Genauigkeit umreißt und damit Ärztinnen und Ärzten potenziell ein schnelleres und präziseres Werkzeug für Diagnose und Verlaufskontrolle bietet.
Die Herausforderung, die Milz klar zu erkennen
Auf MRT‑Bildern sticht die Milz nicht so deutlich hervor, wie viele erwarten würden: Ihr Grauton ähnelt häufig benachbarten Organen und Geweben. Erschwerend kommt hinzu, dass Milzen in Größe und Form stark zwischen Individuen variieren, besonders wenn sie durch Krankheit vergrößert sind. Bei manchen Patientinnen und Patienten ist das Volumen nur leicht erhöht, bei anderen ist das Organ vielfach größer als normal. Hochwertige Aufnahmen solcher Extremfälle zu sammeln ist in der Praxis ebenfalls schwierig, sodass Forschende oft mit relativ kleinen Datensätzen arbeiten müssen. All dies führt dazu, dass traditionelle Programme und selbst frühere Deep‑Learning‑Methoden Schwierigkeiten haben, saubere und präzise Grenzen der Milz in MRT‑Schnitten zu zeichnen.
Ein klügeres Netzwerk für anspruchsvolle medizinische Bilder
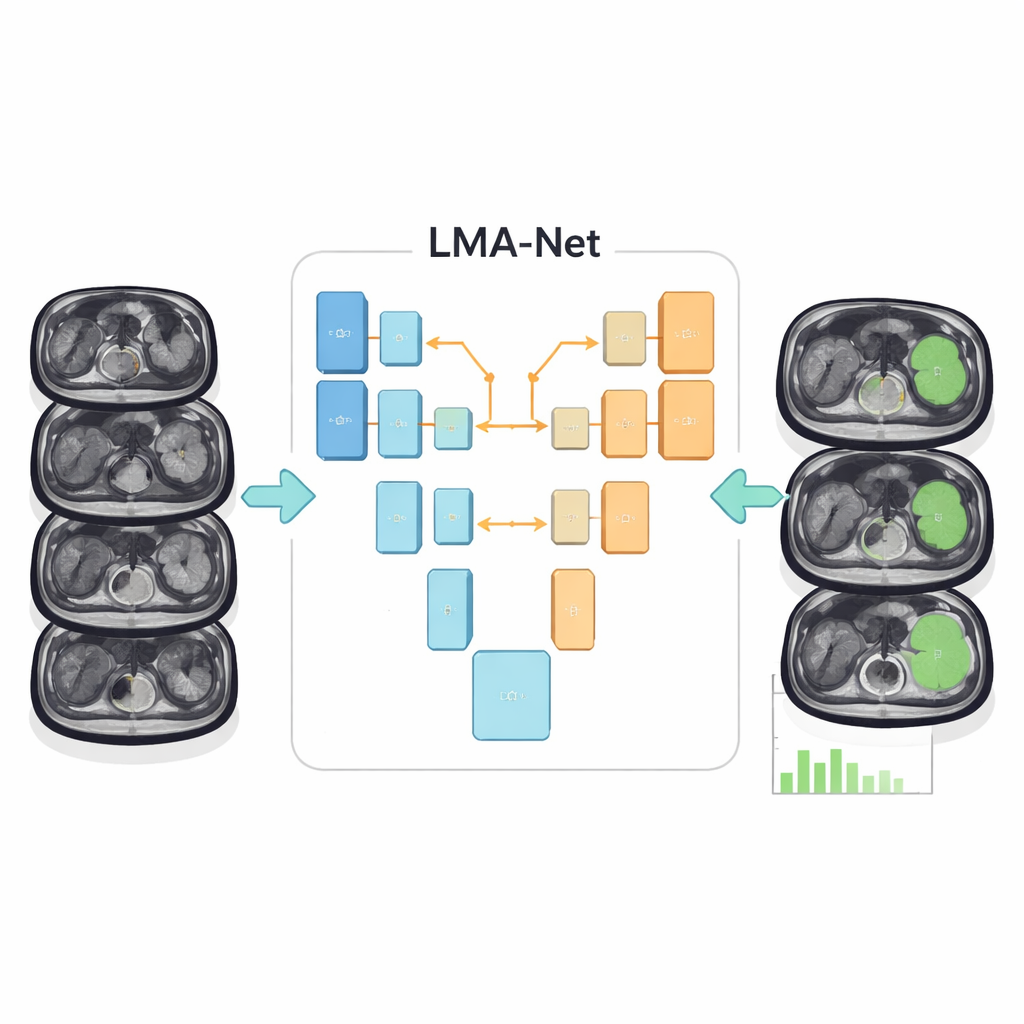
Die Autorinnen und Autoren stellen eine neue Deep‑Learning‑Architektur namens LMA‑Net (Large‑kernel Multi‑scale Attention Net) vor, die speziell für dieses Problem entwickelt wurde. Sie folgt einer U‑förmigen Struktur, die in der medizinischen Bildanalyse zum Standard geworden ist: Eine Seite des „U“ komprimiert das Bild schrittweise zu abstrakten Merkmalen (Encoder), während die andere Seite eine detaillierte Segmentierungsmap rekonstruiert (Decoder). LMA‑Net verwendet einen hybriden Encoder, der zwei leistungsfähige Ansätze kombiniert. Zuerst extrahiert ein konventionelles ResNet‑50‑Faltungsnetz feinkörnige lokale Details. Anschließend erfasst ein Transformer‑Modul, entlehnt aus modernen Sprach‑ und Visionsmodellen, weiterreichende Muster über das gesamte Bild, sodass der Algorithmus ein globales Verständnis dafür entwickelt, wo sich die Milz befindet und wie sie typischerweise aussieht.
Lernen, sich auf die richtigen Details zu konzentrieren
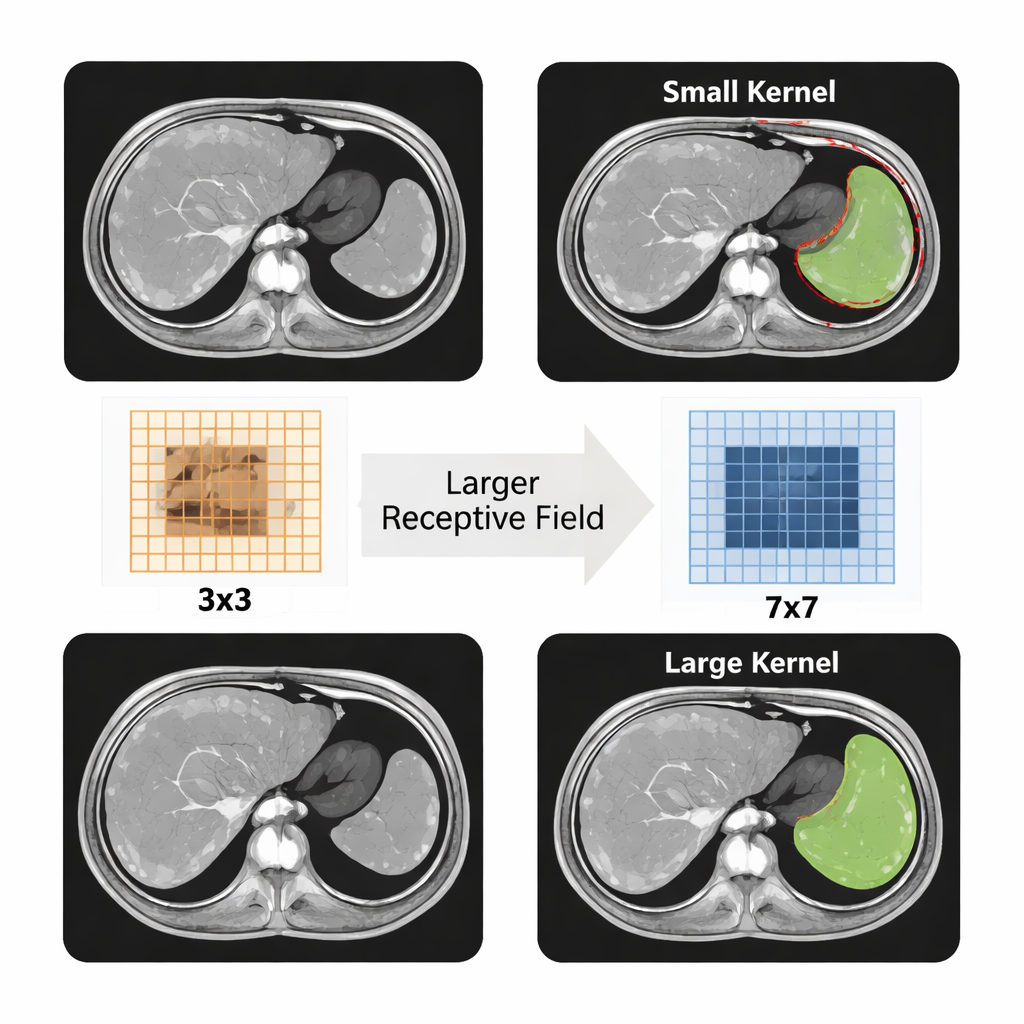
Zwischen Encoder und Decoder fügt LMA‑Net einen spezialisierten Aufmerksamkeitsblock ein, der das Bild gleichzeitig auf mehreren Skalen betrachtet. Er verwendet ungewöhnlich große Faltungsfilter zusammen mit einer effizienten Gruppierungsstrategie, um das Sichtfeld zu erweitern, ohne zu langsam oder ressourcenintensiv zu werden. Diese großen Filter helfen dem Netzwerk, die gesamte Kontur der Milz zu erfassen statt nur winziger Bildbereiche, was besonders wichtig ist, wenn die Grenzen unscharf sind. Das Modell lernt dann, höheren Gewichtungen die informativsten Kanäle und Bereiche zuzuweisen und „achtet“ so gezielt auf Regionen und Texturen, die wahrscheinlich zur Milz gehören. Im Decoder schärfen ein leichtgewichtiges Fusionsmodul und ein Rand‑Verfeinerungsblock die Organränder weiter, mit dem Ziel glatte, realistische Konturen zu erzeugen und gleichzeitig die Rechenkosten für die klinische Nutzung moderat zu halten.
Wie gut das System in der Praxis funktioniert
Um ihren Ansatz zu testen, trainierten und evaluierten die Forschenden LMA‑Net an zwei unterschiedlichen Bildsammlungen. Ein Datensatz enthielt MRT‑Aufnahmen von 51 Patientinnen und Patienten mit unterschiedlichen Graden der Splenomegalie, wobei präzise Umrisse von erfahrenen Radiologinnen und Radiologen gezeichnet worden waren. Der andere stammte aus dem öffentlichen Medical Segmentation Decathlon und bestand aus CT‑Scans mit Fokus auf die Milz. Mit weithin akzeptierten Genauigkeitsmaßen, die die Überlappung zwischen vorhergesagten und Experten‑Markierungen vergleichen, übertraf LMA‑Net mehrere gängige Segmentierungsnetzwerke, darunter U‑Net sowie neuere auf Aufmerksamkeit und Transformer basierende Modelle. Bei den MRT‑Daten zur Splenomegalie stimmte die Vorhersage im Schnitt zu über 96 % mit den Expertenmarkierungen überein — ein spürbarer Vorteil gegenüber konkurrierenden Methoden.
Was das für Patientinnen, Patienten und Kliniken bedeuten könnte
Für Nicht‑Spezialisten ist die wichtigste Erkenntnis, dass diese neue KI‑Methode vergrößerte Milzen in Routine‑MRTs automatisch und sehr präzise umreißen kann, selbst wenn die Organform ungewöhnlich ist oder die Ränder schwer zu erkennen sind. Das bedeutet, dass Ärztinnen und Ärzte schneller genaue Milzvolumina und ‑formen erhalten, Veränderungen über die Zeit verfolgen und die Reaktion von Patientinnen und Patienten auf Therapien bei Lebererkrankungen, Blutkrankheiten oder Milz‑betroffenen Krebserkrankungen besser beurteilen können. Zwar sind weitere Validierungen und die Integration in Krankenhaus‑Systeme noch nötig, doch LMA‑Net weist in Richtung einer Zukunft, in der detaillierte, quantitative Messungen aus medizinischen Bildern standardmäßig automatisiert zum Teil der Versorgung werden statt einer manuellen Aufgabe.
Zitation: Fu, Z., Zhao, C., Yan, H. et al. A method for magnetic resonance splenomegaly image segmentation based on large-kernel multi-scale attention mechanism. Sci Rep 16, 5227 (2026). https://doi.org/10.1038/s41598-026-35122-3
Schlüsselwörter: Splenomegalie, MRT‑Segmentierung, Tiefes Lernen, Medizinische Bildgebung, Aufmerksamkeitsnetzwerke