Clear Sky Science · de
Genetische Vielfalt von Pseudomonas aeruginosa, isoliert aus klinischen Proben mit ISSR‑Molekularmarker in einem tertiären Lehrkrankenhaus
Warum Krankenhauskeime uns alle betreffen
Wer Zeit in einem Krankenhaus verbracht hat – sei es als Patient oder beim Besuch eines Angehörigen – ist darauf angewiesen, dass Antibiotika dann wirken, wenn sie am dringendsten gebraucht werden. Manche Keime werden jedoch so widerstandsfähig, dass selbst unsere stärksten Medikamente kaum noch gegen sie ankommen. Dieser Beitrag beleuchtet einen solchen Störenfried, das Bakterium Pseudomonas aeruginosa, und zeigt, wie Wissenschaftler in einem indischen Krankenhaus seine verborgene genetische Vielfalt kartierten, um besser zu verstehen, warum es so schwer zu kontrollieren ist.
Ein hartnäckiger Erreger in modernen Krankenhäusern
Pseudomonas aeruginosa ist ein gerissener Gegner. Es gedeiht in feuchten Umgebungen, von Beatmungsschläuchen bis zu Wundverbänden, und befällt besonders Menschen, deren Abwehrkräfte durch Krankheit, Verbrennungen oder lange Krankenhausaufenthalte geschwächt sind. Es kann schwere Lungen‑, Blut‑, Harnwegs‑ und Wundinfektionen verursachen. Gefährlich macht es vor allem seine Fähigkeit, mehreren Antibiotikaklassen gleichzeitig zu widerstehen, wodurch alltägliche Infektionen zu lebensbedrohlichen Krisen werden und Behandlungsdauer sowie Kosten weltweit steigen.
Tiefer blicken in die Infektion
Um zu erkennen, wie vielfältig dieser Erreger innerhalb eines Krankenhauses wirklich ist, sammelten die Forschenden 100 bakterielle Proben aus Blut, Urin, Sputum und Wundabstrichen, die im Rahmen der routinemäßigen Versorgung in einem großen Lehrkrankenhaus im Osten Indiens entnommen wurden. Sie konzentrierten sich auf 18 Stämme, die gegen mehrere Wirkstoffe resistent waren, und testeten, wie jeder einzelne auf eine breite Palette von Antibiotika reagierte. Besorgniserregend war, dass mehr als vier von fünf Proben gegen wichtige Wirkstoffe wie Cefoperazon, Meropenem und Imipenem resistent waren – Arzneien, die oft als letzte Option dienen, wenn andere versagen. Einige Antibiotika, darunter weniger häufig eingesetzte, zeigten noch bessere Wirkung, was auf verbleibende, aber schrumpfende Behandlungsoptionen hindeutet. 
Die „Barcode“-Muster der Bakterien lesen
Zu zählen, welche Medikamente versagten, war nur die halbe Geschichte. Das Team wollte auch wissen, ob diese Infektionen von einem erfolgreichen „Superstamm“ stammten, der sich im Krankenhaus ausbreitet, oder von vielen nicht verwandten Linien, die unabhängig eintreffen und sich entwickeln. Dafür nutzten sie eine DNA‑Fingerprinting‑Methode namens ISSR, die die Sequenzen zwischen kurzen Wiederholungsabschnitten hervorhebt. Nach PCR‑Amplifikation und Gelelektrophorese bilden diese Abschnitte ein Bandenmuster, das wie ein Barcode für jeden Stamm wirkt. Mit 17 informativen Primern erzeugten die Forschenden 95 unterschiedliche DNA‑Banden und verglichen die Muster der 18 Stämme mithilfe von Computerwerkzeugen, die ähnliche Fingerprints gruppieren.
Viele entfernte Verwandte, kein einziger Supererreger
Die genetischen Vergleiche zeigten, dass das Krankenhaus es nicht mit einem einzigen außer Kontrolle geratenen Klon zu tun hatte. Stattdessen gliederten sich die Stämme in mehrere unterschiedliche Cluster mit Ähnlichkeitswerten von relativ nahen Verwandten bis hin zu weit entfernten Cousins. Einige Isolate, die sich in den Medikamententests ähnlich verhielten, waren genetisch unterschiedlich, während andere verwandte Isolate gemeinsame Resistenzmerkmale aufwiesen. Hauptkomponentenplots und baumartige Diagramme bestätigten das Bild mehrerer Koexistierender Linien in derselben Einrichtung anstatt eines dominanten Stamms, der sich ausbreitet. Diese Vielfalt entsteht wahrscheinlich dadurch, dass die Bakterien Gene austauschen, mutieren und sich unter dem dauernden Druck von Antibiotika und dem menschlichen Immunsystem anpassen. 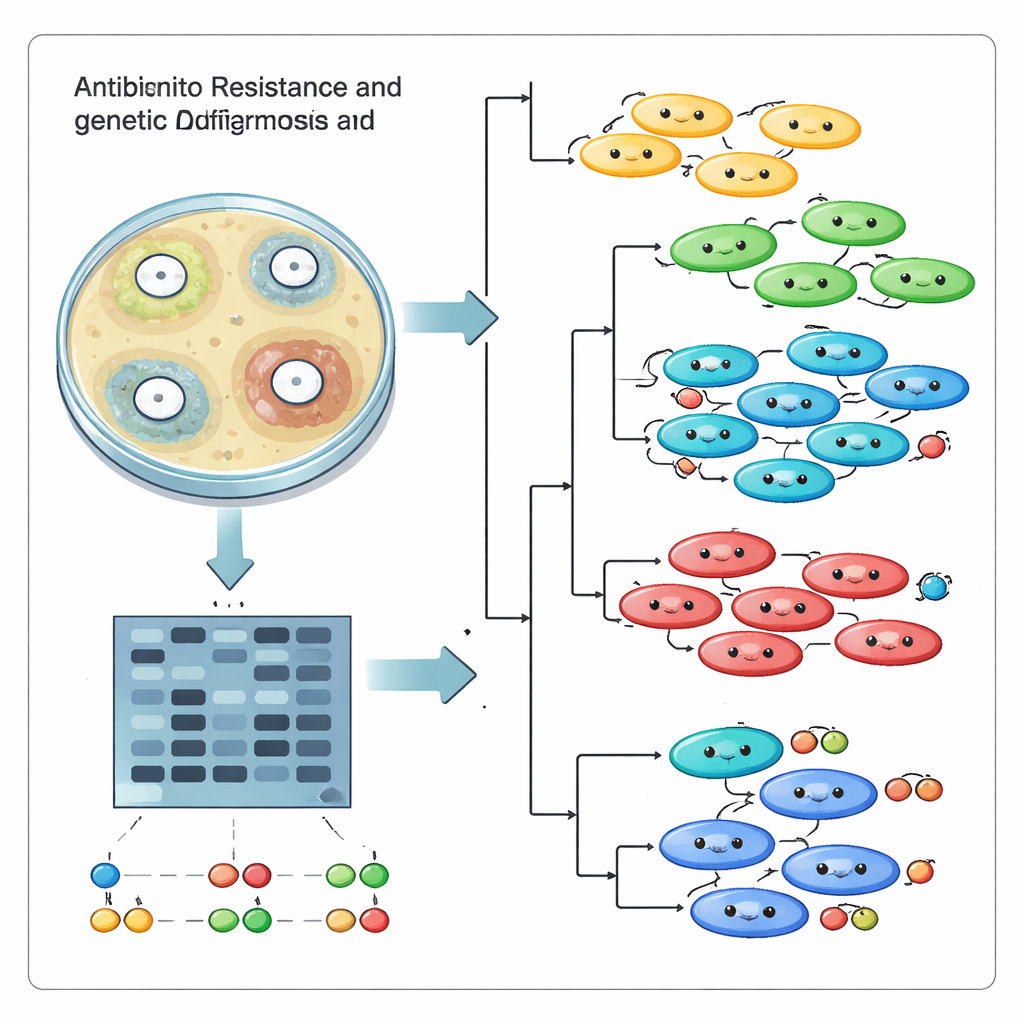
Was das für Patienten und Krankenhäuser bedeutet
Für Krankenhäuser haben diese Ergebnisse eine klare Botschaft: Es reicht nicht aus, nur zu verfolgen, welche Antibiotika versagen. Da genetisch unterschiedliche Stämme ähnliche Resistenzmuster teilen können – und eng verwandte Stämme sich unterschiedlich verhalten können – benötigen Behandlungsteams sowohl routinemäßige Empfindlichkeitsprüfungen gegenüber Antibiotika als auch regelmäßige genetische Überwachung, um zu erkennen, wie sich die bakterielle Population im Zeitverlauf verändert. Der hier verwendete ISSR‑Ansatz ist relativ einfach und kostengünstig, was ihn für ressourcenbegrenzte Einrichtungen attraktiv macht, wobei die Autoren betonen, dass eine Kombination mit umfassenderen Ganzgenomsequenzierungen in zukünftigen Studien ein vollständigeres Bild liefern würde.
Eine verborgene Landschaft, die Wachsamkeit verlangt
Einfach gesagt zeigt diese Studie, dass innerhalb eines einzelnen Krankenhauses Pseudomonas aeruginosa nicht ein einziger Feind ist, sondern eine Vielzahl verwandter, aber unterschiedlicher Störenfriede, von denen viele bereits gegen mehrere Antibiotika gewappnet sind. Indem die Forschenden diese verborgene Vielfalt kartieren, liefern sie Instrumente und Einsichten, die Ärzten helfen können, gezieltere Behandlungen zu wählen, und Infektionskontrollteams ermöglichen, klügere Eindämmungsstrategien zu entwerfen. Die kontinuierliche Überwachung dieser genetischen Muster wird entscheidend sein, um diesem anpassungsfähigen Keim einen Schritt voraus zu bleiben und die Krankenhausversorgung für Patienten sicher zu halten.
Zitation: Mishra, P., Sahoo, D. & Sahu, M.C. Genetic diversity of Pseudomonas aeruginosa isolated from clinical samples with ISSR molecular marker in a tertiary care teaching hospital. Sci Rep 16, 5315 (2026). https://doi.org/10.1038/s41598-026-35090-8
Schlüsselwörter: Pseudomonas aeruginosa, Antibiotikaresistenz, Krankenhausinfektionen, genetische Vielfalt, molekulare Typisierung