Clear Sky Science · de
Bewertung der Genmarker mdh, dld, tcfA und folE zum Nachweis von Enteric-Fieber mittels Echtzeit‑PCR
Warum schnellere Tests für Typhus wichtig sind
Enteric-Fieber – besser bekannt als Typhus und Paratyphus – erkranken nach wie vor Millionen von Menschen jedes Jahr, vor allem in Südasien und Afrika. Die Krankheit verbreitet sich über kontaminierte Nahrung und Wasser und kann wochenlang hohes Fieber, Bauchschmerzen und in manchen Fällen lebensbedrohliche Komplikationen verursachen. Dennoch ist die schnelle und zuverlässige Diagnose nach wie vor schwierig, besonders in überfüllten Krankenhäusern und Kliniken. Diese Studie untersucht einen DNA‑basierten Test, der typhuserzeugende Bakterien verlässlicher und deutlich schneller als traditionelle Methoden erkennen könnte, sodass Ärzte Patienten früher behandeln und Ausbrüche effektiver verfolgen können. 
Die Herausforderung, eine verborgene Infektion zu erkennen
Typhus und Paratyphus werden von eng verwandten Salmonella‑Bakterien verursacht, die im Blutkreislauf und im Darm leben. Ihre frühen Symptome – Fieber, Kopfschmerz, Müdigkeit und Magenbeschwerden – ähneln vielen anderen Infektionen wie Dengue, Malaria und Influenza. Standardlaborverfahren beruhen auf dem Anzüchten der Bakterien aus Blut oder Stuhl oder auf dem Nachweis der Immunantwort des Körpers. Diese Verfahren können mehrere Tage dauern, viele echte Fälle übersehen und Typhus gelegentlich mit anderen Erkrankungen verwechseln. In vielen Kliniken sind Ärzte gezwungen, aufgrund von Schätzungen zu behandeln, was die richtige Therapie verzögern und die Antibiotikaresistenz fördern kann.
Bakterielle Fingerabdrücke in der DNA lesen
Die Forscher wollten einen Schnelltest entwickeln, der die genetischen „Fingerabdrücke“ typhuserzeugender Bakterien direkt aus Patientenproben liest. Sie konzentrierten sich auf die Echtzeit‑PCR, eine Technik, die winzige DNA‑Mengen vervielfältigt und die Reaktion während des Ablaufs verfolgt. Mithilfe von Genomdatenbanken wählten sie vier Gene – mdh, dld, tcfA und folE – aus, die zusammen anzeigen sollten, ob Salmonella vorhanden ist und idealerweise, welche Art von typhuserzeugendem Bakterium vorliegt. Nachdem sie kurze DNA‑Primer entworfen hatten, die an jedes Gen binden, optimierten sie zunächst die Reaktionsbedingungen mittels konventioneller PCR und Gelelektrophorese und wechselten dann zu einem schnelleren SYBR‑Green‑basierten Echtzeit‑PCR‑Format.
Wie gut der neue Test funktionierte
Als das Team ihren Assay an klinischen Isolaten von Salmonella Typhi und Salmonella Paratyphi sowie an einer Reihe anderer Bakterien anwandte, stellte sich heraus, dass jedes Gen ein anderes Puzzlestück der Diagnose beisteuerte. Das mdh‑Gen, ein Kernstoffwechselgen, erwies sich als ausgezeichneter allgemeiner Marker für Salmonella und schlug in fast allen Typhusproben an, jedoch in keiner der Nicht‑Salmonella‑Stämme. Die Gene dld und tcfA wurden hauptsächlich in typhusassoziierten Stämmen nachgewiesen und lieferten zusätzliche Hinweise darauf, dass eine Probe die krankheitsverursachenden Formen des Bakteriums enthielt. Computerbasierte Vorhersagen legten zunächst nahe, dass folE für S. Typhi einzigartig sei, doch die Laborergebnisse zeigten ein nuancierteres Bild: folE trat auch in den meisten S. Paratyphi‑Isolaten auf und deutet darauf hin, dass dieses Gen bei typhuserzeugenden Stämmen geteilt wird und nicht nur auf eine Art beschränkt ist. 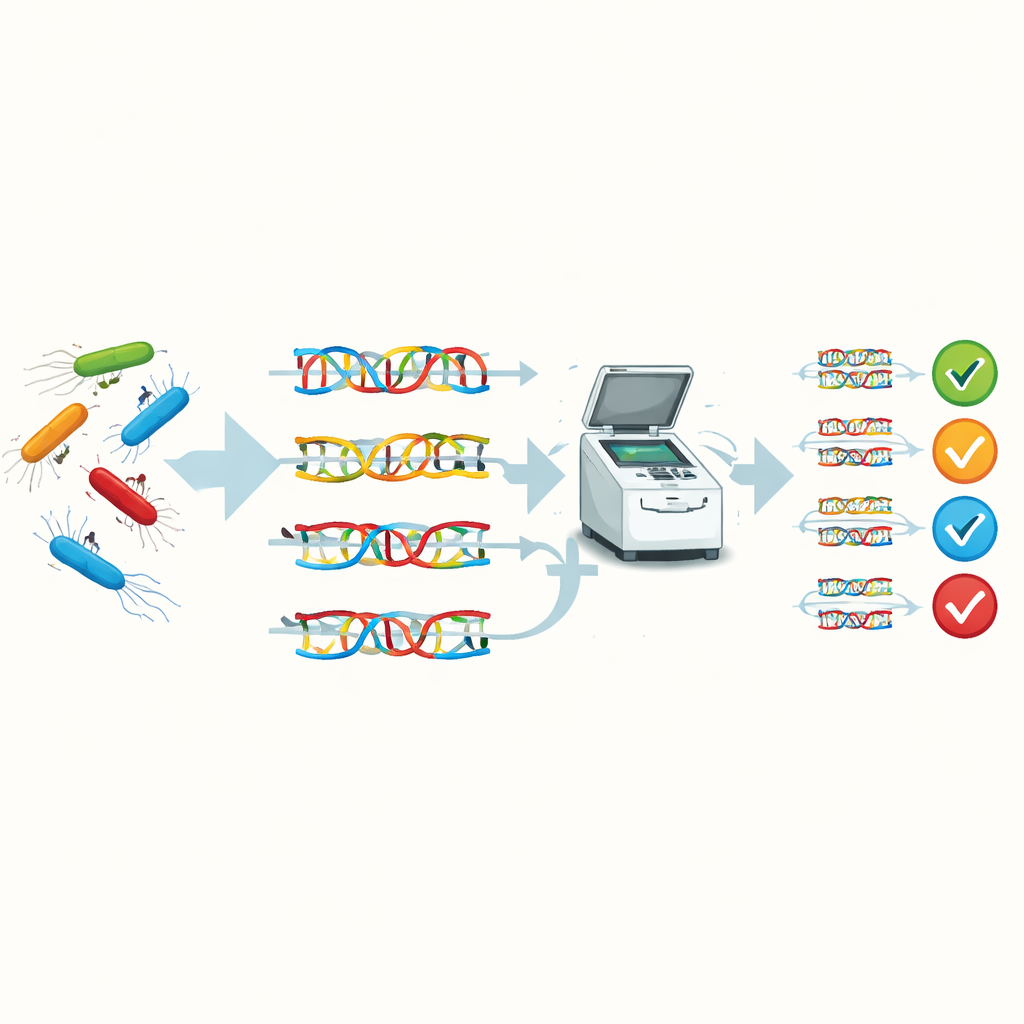
Genetische Hinweise und ihre Grenzen
Um diese Überraschung zu erklären, sequenzierten die Forscher folE aus je einer S. Typhi‑ und einer S. Paratyphi‑Probe. Die DNA‑ und Proteinsequenzen waren nahezu identisch und unterschieden sich nur an einer einzigen Stelle, ohne das resultierende Enzym zu verändern. Das bestätigte, dass folE in beiden Bakterien die gleiche Rolle spielt und ihnen hilft, Folat zu synthetisieren, ein lebenswichtiges Molekül für das Wachstum. Insgesamt zeigte das Vier‑Gen‑Panel eine gute Übereinstimmung mit der standardmäßigen biochemischen Identifikation: Es unterschied zuverlässig typhoidale Salmonella von nicht verwandten Bakterien und deckte gelegentliche Diskrepanzen auf, bei denen traditionelle Methoden einen Stamm möglicherweise falsch eingeordnet hatten. Da jedoch mehrere der Gene zwischen S. Typhi und S. Paratyphi geteilt werden, fällt es dem Assay weiterhin schwer, diese eng verwandten Erreger sauber voneinander zu trennen.
Was das für Patienten und die öffentliche Gesundheit bedeutet
Für Laien ist die Kernbotschaft, dass diese Arbeit uns einem schnellen, DNA‑basierten Test für Typhus näherbringt, der Antworten in Stunden statt Tagen liefern könnte. Durch die gleichzeitige Abfrage mehrerer genetischer Hinweise kann der Assay empfindlich das Vorhandensein typhuserzeugender Bakterien nachweisen und bestätigen, dass eine Infektion vorliegt – selbst wenn herkömmliche Kulturmethoden versagen. Gleichzeitig zeigt die Studie, dass verfeinerte genetische Marker nötig sind, um verschiedene Typhus‑Stämme auseinanderzuhalten – eine Information, die für die Überwachung von Ausbrüchen und die Anpassung von Impfstrategien wichtig ist. Kurz gesagt demonstriert diese Forschung, dass moderne molekulare Werkzeuge die Typhusdiagnostik deutlich beschleunigen und verbessern können und zugleich die nächsten Schritte auf dem Weg zu noch präziseren Tests aufzeigen.
Zitation: Arshad, S., Younas, S., Qadir, M.L. et al. Evaluation of mdh, dld, tcfA, and folE gene markers for detection of enteric fever using real-time PCR. Sci Rep 16, 8912 (2026). https://doi.org/10.1038/s41598-026-35011-9
Schlüsselwörter: Enteric-Fieber, Typhus-Diagnostik, Salmonella-Nachweis, Echtzeit‑PCR, molekulare Marker