Clear Sky Science · de
Eine hochwertige Chromosomen-auf-Ebene-Genomassemblierung der gering-chillbedürftigen Maulbeere Morus macroura
Warum ein besondere Maulbeerbaum wichtig ist
Stellen Sie sich eine Frucht vor, die früh reift, süß schmeckt, reich an Nährstoffen ist und fast ganzjährig angebaut werden kann – auch dort, wo die Winter mild sind. Das ist das Potenzial einer langfruchtigen Maulbeere namens Morus macroura, die in Teilen Chinas und Südasien bereits wegen ihres Frischverzehrs, ihrer Verarbeitung und ihrer Verwendung in der traditionellen Medizin geschätzt wird. Bislang mussten Züchter und Landwirte diese Kultur weitgehend per Versuch und Irrtum verbessern, weil ihr genetischer Bauplan unbekannt war. Diese Studie ändert das: Sie liefert eine detaillierte, auf Chromosomenebene erstellte Karte der Maulbeer-DNA und ebnet den Weg für gezieltere Züchtung mit Blick auf Ertrag, Geschmack und Klimaresilienz.
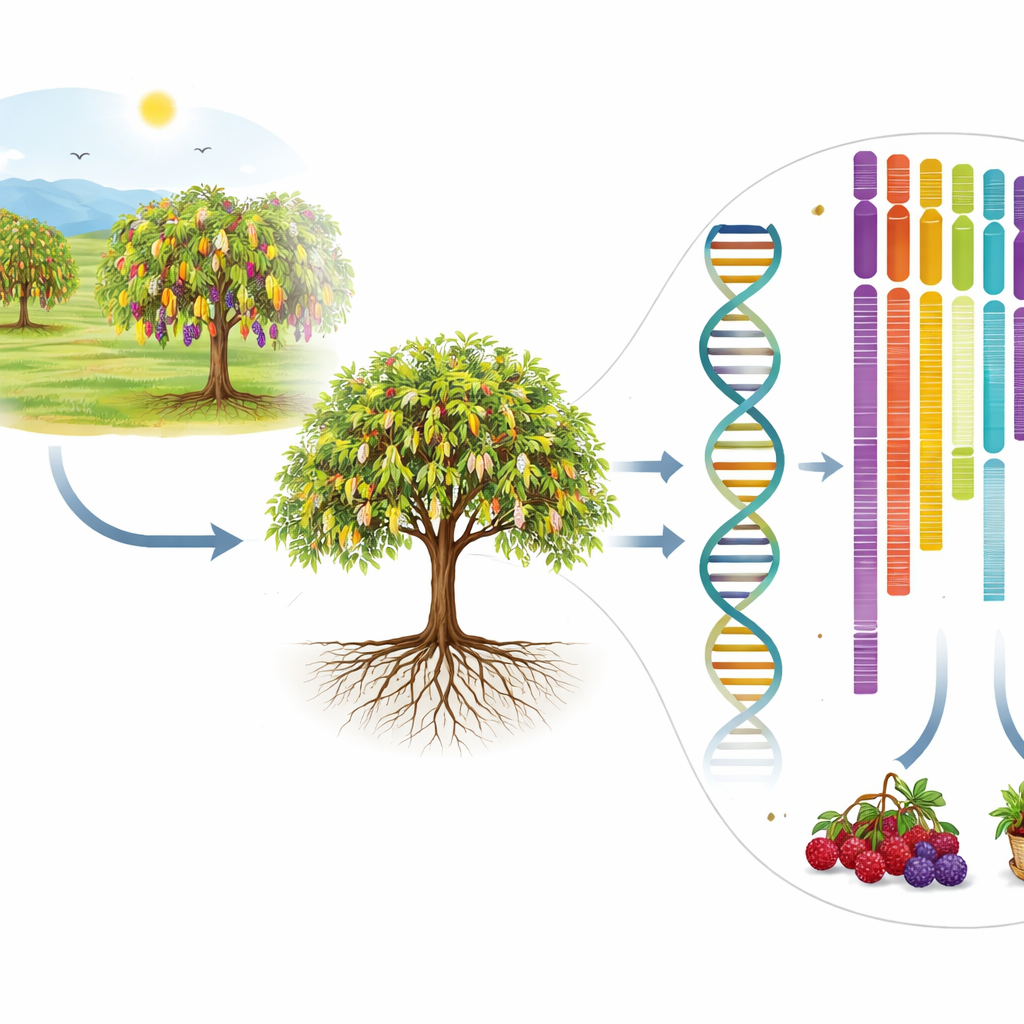
Vom Obstgarten zum DNA-Bauplan
Die Forscher konzentrierten sich auf eine kultivierte Sorte namens „Sijiguo 72C“, die für besonders lange Früchte und einen geringen Kältereizbedarf bekannt ist. Sie sammelten junge Blätter von einem einzelnen gesunden Baum, der auf Hainan, einer tropischen Insel Chinas, kultiviert wird, und isolierten sehr reine, lange DNA-Stränge. Zusätzlich gewannen sie RNA aus Blättern, Stängeln, Blüten und Früchten, um abzubilden, welche Gene in den verschiedenen Pflanzenteilen aktiv sind. Mit modernen Sequenziergeräten lasen sie die DNA und RNA der Maulbeere in riesigen Mengen an kurzen Fragmenten und erzeugten damit ausreichend Daten, um das gesamte Genom mehr als fünfzigfach abzudecken.
Das genetische Puzzle zusammensetzen
Milliarden von DNA-Buchstaben in ein nutzbares Genom zu verwandeln, ist wie ein riesiges Puzzle ohne das Bild auf der Schachtel zusammenzufügen. Das Team nutzte lange, hochpräzise DNA-Lesungen, um große, zusammenhängende Sequenzabschnitte, sogenannte Contigs, zu erzeugen und dadurch Lücken und Fehler zu minimieren. Anschließend setzten sie eine zweite Methode namens Hi-C ein, die erkennt, welche DNA-Stücke im Zellkern räumlich nahe beieinanderliegen. Diese weitreichenden Kontakte halfen dabei, die Contigs zu ordnen und auszurichten und sie in 14 große Einheiten zu überführen, die den Chromosomen der Maulbeere entsprechen. Im Endergebnis wurden über 99 % des Genoms sauber auf diese Chromosomen platziert, und Qualitätsprüfungen ergaben eine Fehlerrate von weniger als einem Fehler pro Million DNA-Basen.
Was das Maulbeer-Genom enthält
Mit der physischen Karte in der Hand machten sich die Wissenschaftler daran, die funktionalen Teile des Genoms zu identifizieren. Sie fanden heraus, dass etwas mehr als die Hälfte der DNA aus wiederholten Elementen besteht, wie springenden Genen und anderen repetitiven Sequenzen, die Größe und Struktur des Genoms prägen. Innerhalb dieses Rahmens sagten sie 21.824 protein-codierende Gene voraus und bestätigten die Funktionen von mehr als 97 % davon durch Vergleiche mit umfangreichen öffentlichen Datenbanken. Außerdem katalogisierten sie fast 3.000 nicht-codierende RNAs – kleine RNA-Moleküle, die keine Proteine bilden, aber dabei helfen, wie Gene ein- und ausgeschaltet werden. Gemeinsam bilden diese Merkmale die Grundlage, um Eigenschaften wie Fruchtgröße, Farbe, Geschmack sowie die Fähigkeit der Pflanze, mit geringem Winterkältereiz zu blühen und Früchte zu tragen, zu verstehen.
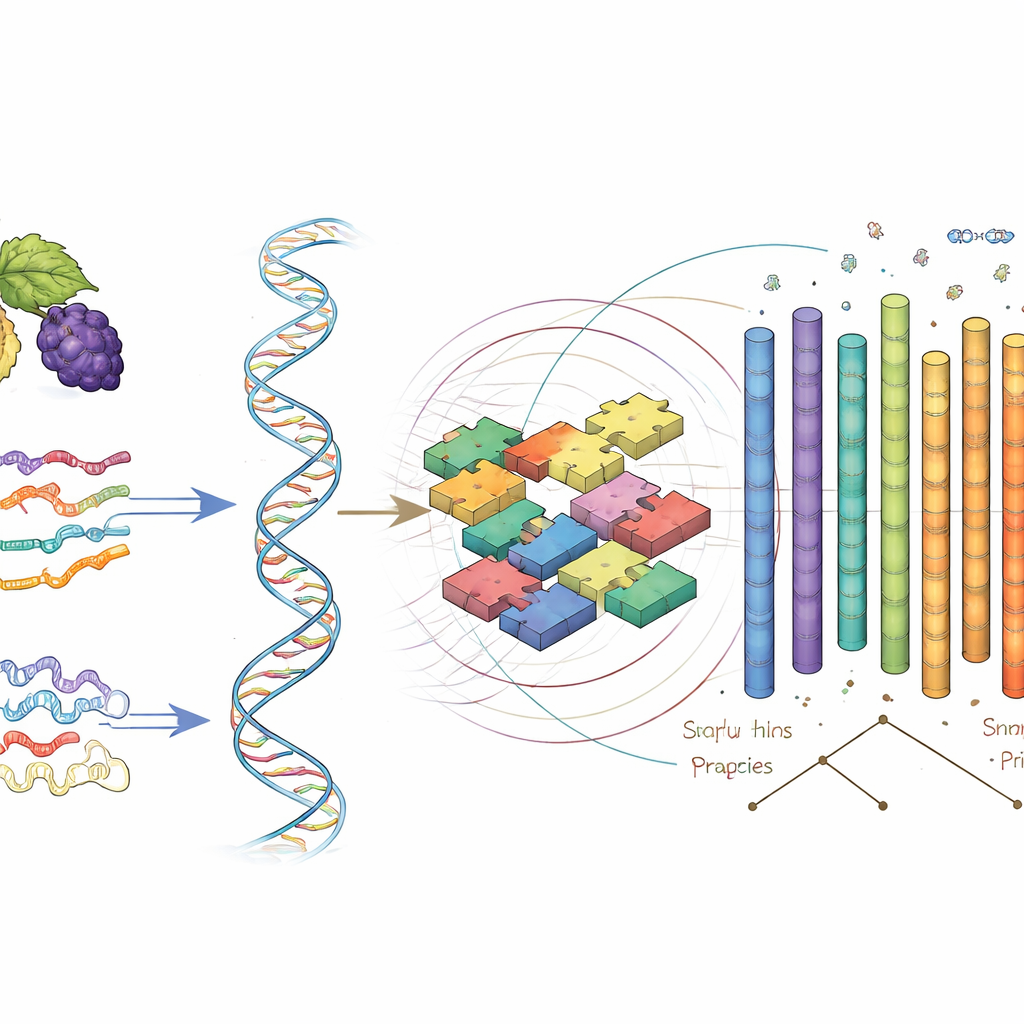
Die Maulbeere im Baum des Lebens verorten
Um zu sehen, wie diese Art in die größere Maulbeer-Familie passt, verglich das Team ihre Gene mit denen von acht verwandten Pflanzen, darunter andere Maulbeerarten und Pfirsich. Sie fassten Gene zu familienübergreifenden Gruppen zusammen und verfolgten, welche Gene sich im Laufe der Zeit vergrößerten oder verkleinerten. Die Ergebnisse deuten darauf hin, dass sich Morus macroura vor etwa vier Millionen Jahren vom gemeinsamen Vorfahren mit der weißen Maulbeere, Morus alba, abspaltete und besonders eng mit einer anderen kultivierten Form, Morus atropurpurea, verwandt ist. Die Studie zeigte außerdem Chromosomenabschnitte, die sich im Verlauf der Evolution umgeordnet haben, und liefert damit Hinweise darauf, wie sich verschiedene Maulbeerarten an ihre Umgebungen und Nutzung angepasst haben.
Was das für künftige Früchte bedeutet
Für jemanden, der eine Schale Maulbeeren genießt, mögen die feinsinnigen Details von DNA-Sequenzen weit entfernt erscheinen. Doch dieses hochwertige Genom liefert Züchtern und Wissenschaftlern ein kraftvolles Nachschlagewerk für die Kulturpflanze. Es wird ihnen helfen, die Netzwerke von Genen zu entschlüsseln, die Winterruhe, Blühzeitpunkte und kontinuierliche Fruchtbildung in warmen Klimaten steuern. Praktisch könnte das die Entwicklung neuer Maulbeersorten beschleunigen, die in einer wärmer werdenden Welt verlässlich ernten, außerhalb der Saison Früchte für den Markt liefern und die ernährungs‑ sowie medizinisch wertvollen Eigenschaften bewahren, die Maulbeeren seit Jahrhunderten schätzen lassen.
Zitation: Wu, H., Wang, J., Geng, T. et al. A high-quality chromosome-level genome assembly of the low chilling requirement mulberry, Morus macroura. Sci Data 13, 458 (2026). https://doi.org/10.1038/s41597-026-07117-2
Schlüsselwörter: Maulbeer-Genom, Sortenentwicklung, Klimaanpassung, Chromosomenassemblierung, Pflanzen‑Genetik