Clear Sky Science · de
Eine hochwertige Chromosomen‑Ebene-Genomassemblierung von Gynostemma guangxiense (Cucurbitaceae)
Eine Waldranke mit verborgener Heilwirkung
Tief in den Kalksteinwäldern Südchinas wächst eine wenig bekannte Kletterpflanze, Gynostemma guangxiense. Die Einheimischen verwenden diese Pflanze seit langem als traditionelle Arznei gegen Leberbeschwerden und chronischen Husten, und sie ist reich an natürlichen Verbindungen, die denen im Ginseng ähneln. Während die Nachfrage nach ihrem bekannteren Verwandten Gynostemma pentaphyllum stark gestiegen ist, sind Wildbestände unter Druck geraten. Um diese wertvollen Pflanzen zu schützen und ihr medizinisches Potenzial besser zu verstehen, haben Wissenschaftler nun das vollständige genetische Bauplan von G. guangxiense auf Chromosomen‑Ebene entschlüsselt.

Warum diese kleine Ranke wichtig ist
Gynostemma‑Pflanzen nehmen in der Kräutermedizin eine besondere Stellung ein, weil sie neben Ginseng zu den wenigen Gruppen gehören, die dammaran‑artige Saponine produzieren—Moleküle, die mit Immununterstützung, Herzgesundheit und antitumoraler Aktivität in Verbindung gebracht werden. G. guangxiense ähnelt optisch stark G. pentaphyllum, schmeckt aber süßer und soll hohe Gehalte an Saponinen, Flavonoiden sowie essenziellen Spurenelementen wie Eisen, Mangan, Zink und Kupfer enthalten. Diese Eigenschaften machen sie sowohl als alternative medizinische Ressource interessant als auch als Modell, um zu verstehen, wie solche gesundheitsfördernden Verbindungen in Pflanzen entstehen. Bislang lagen den Forschern jedoch nur Bruchstücke ihrer genetischen Information, etwa das Chloroplasten‑DNA, vor, was eingehendere Studien einschränkte.
Das Bedienungsbuch der Pflanze lesen
Um diese verborgenen Informationen zu entschlüsseln, sammelte das Forschungsteam gesunde Blätter von einer wilden weiblichen Pflanze in der Provinz Guangxi und isolierte DNA und RNA. Anschließend nutzten sie eine Kombination moderner Sequenzierverfahren, die sowohl kurze als auch lange DNA‑Abschnitte erfassen, sowie eine Methode namens Hi‑C, die zeigt, wie diese Abschnitte innerhalb der Zelle gefaltet und verknüpft sind. Durch sorgfältiges Zusammenfügen dieser unterschiedlichen Datenströme und Abgleich mit RNA‑Auslesungen aus mehreren Geweben—Knospen, Blättern, Stängeln, Blüten und Früchten—stellten sie eine hochvollständige Version des Pflanzen‑Genoms zusammen und überprüften dessen Genauigkeit mit etablierten Qualitätsprüfungen.
Chromosomen aus unzähligen Fragmenten bauen
Das Endergebnis ist ein Genom von etwa 565 Millionen DNA‑Bausteinen, organisiert in 11 Pseudochromosomen, die mehr als 99 Prozent der zusammengebauten Sequenz abdecken. Qualitätsmessungen zeigen, dass fast alle Standardreferenzgene für Pflanzen vorhanden und intakt sind, was darauf hindeutet, dass nur sehr wenig Information fehlt. Die Forscher kartierten zudem, wo sich wiederholte DNA‑Abschnitte entlang der Chromosomen befinden, und fanden heraus, dass mehr als zwei Drittel des Genoms aus solchen Wiederholungen bestehen, insbesondere aus einer Gruppe, die als Long Terminal Repeat‑Elemente bekannt ist. Sie katalogisierten 27.527 proteinkodierende Gene, und bemerkenswerterweise ließen sich fast 98 Prozent dieser Gene durch Vergleiche mit internationalen Datenbanken bekannten Funktionen oder Familien zuordnen.
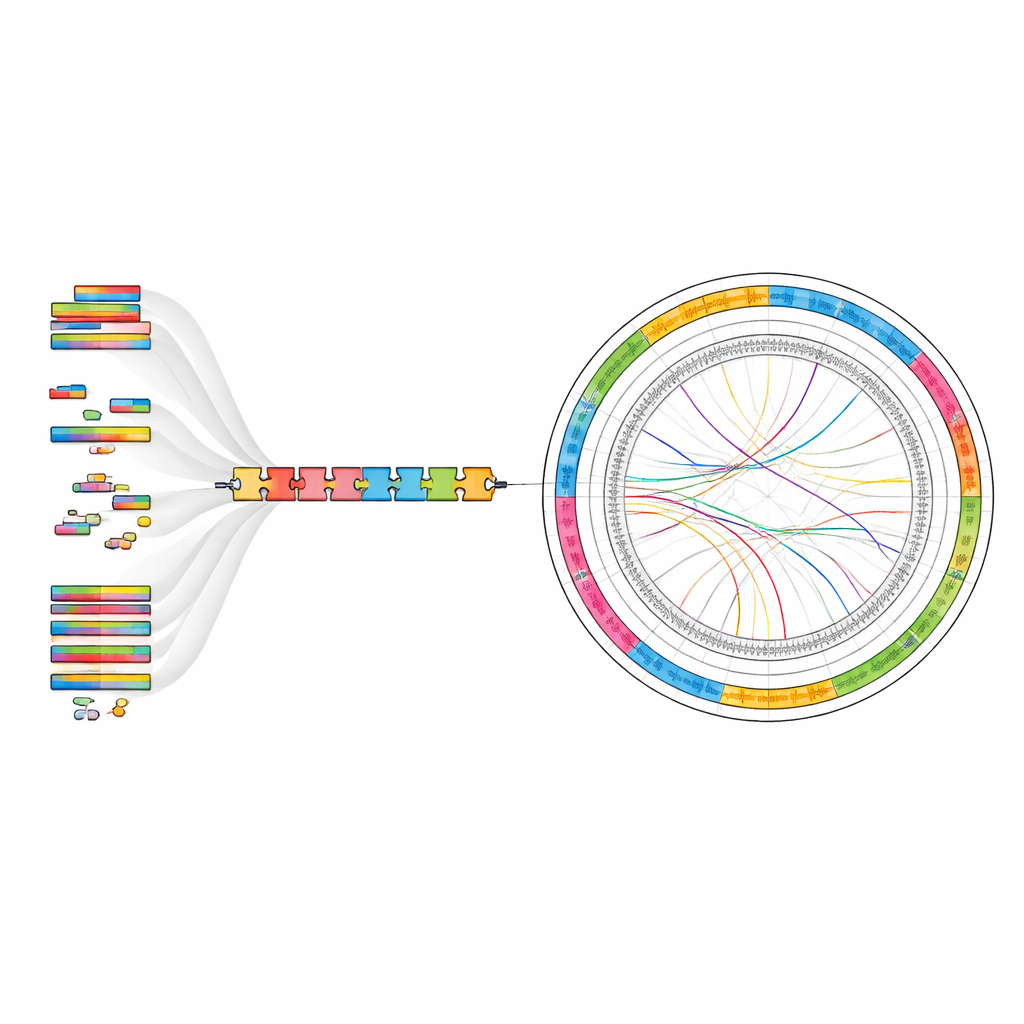
Was das Genom über diese Pflanze verrät
Über die bloße Auflistung von Genen hinaus zeigt die Genomkarte, wie verschiedene Merkmale—Gene, Wiederholungen und nicht‑kodierende RNAs—entlang jedes Chromosoms angeordnet sind und wie Regionen im Genom zueinander korrespondieren. Das liefert Hinweise auf frühere Chromosomen‑Umordnungen und die Kräfte, die die Evolution der Pflanze geprägt haben. Das Team identifizierte außerdem Tausende nicht‑kodierender RNA‑Stücke, einschließlich Transfer‑RNAs und ribosomaler RNAs, die die zelluläre Proteinfabrikation unterstützen. Zusammen bieten diese Befunde eine detaillierte Referenz, um zu erforschen, wie G. guangxiense sein reiches Spektrum an Saponinen und anderen bioaktiven Molekülen produziert und wie es sich an seinen felsigen Waldboden anpasst.
Eine neue Basis für Medizin und Naturschutz
Mit der Bereitstellung eines sorgfältig geprüften Genoms auf Chromosomen‑Ebene für G. guangxiense liefert diese Arbeit Wissenschaftlern ein mächtiges Nachschlagewerk für eine vielversprechende Heilranke. Mit diesem Bauplan können Forschende Gene, die an wertvollen Verbindungen beteiligt sind, leichter identifizieren, Züchtungsprogramme zur Verbesserung gewünschter Eigenschaften leiten und G. guangxiense mit verwandten Arten vergleichen, um ihre Beziehungen zu klären. Ebenso wichtig unterstützt das Genom eine bessere Schutzplanung in einer Zeit, in der Überernte einige Vertreter der Gattung bedroht. Kurz gesagt verwandelt diese detaillierte genetische Karte eine wenig bekannte Waldranke in eine gut dokumentierte Ressource für zukünftige Medizin, Landwirtschaft und Biodiversitätsschutz.
Zitation: Zhang, X., Zhang, H., Chen, C. et al. A high-quality Chromosome-level genome assembly of Gynostemma guangxiense (Cucurbitaceae). Sci Data 13, 503 (2026). https://doi.org/10.1038/s41597-026-06889-x
Schlüsselwörter: Heilpflanzen, Pflanzen‑Genom, Gynostemma, genetische Ressourcen, Erhaltungsbiologie