Clear Sky Science · de
Metabolomische und transkriptomische Profilierung von zwei eng verwandten Arten der Gattung Oldenlandia
Warum diese bescheidenen Kräuter wichtig sind
Zwei kleine, unerwünschte Pflanzen, die in der traditionellen asiatischen Medizin verwendet werden — Oldenlandia diffusa und Oldenlandia corymbosa — werden häufig gegen Beschwerden von Entzündungen bis hin zu Lebererkrankungen und Krebs eingesetzt. Trotz ihrer langen Verwendung in Kräuteranwendungen und ihrer häufigen Vermischung auf dem Markt wissen wir jedoch überraschend wenig darüber, wie sie sich innerlich tatsächlich unterscheiden: welche chemischen Inhaltsstoffe sie produzieren, in welchen Pflanzenteilen und welche Gene diese Inhaltsstoffe steuern. Diese Studie öffnet diese verborgene Welt, indem sie eine detaillierte Karte sowohl der Moleküle als auch der Genaktivität in verschiedenen Geweben der beiden Arten liefert.
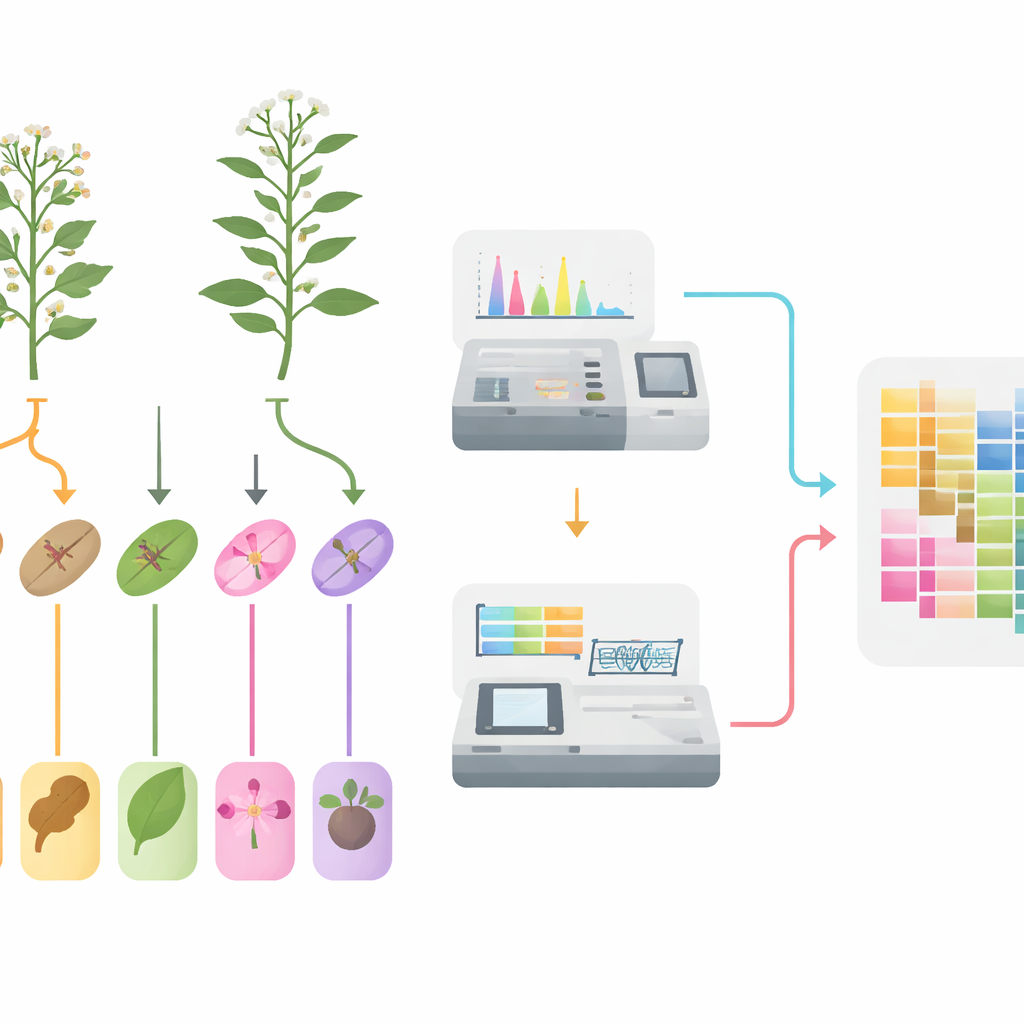
Vom Feld zu eingefrorenen Proben
Die Forschenden begannen damit, beide Arten nebeneinander unter gleichen Feldbedingungen anzubauen, um Umweltverzerrungen zu vermeiden. Während der Blütezeit trennten sie sorgfältig fünf Gewebe — Wurzeln, Stängel, Blätter, Blüten und Früchte — von mehreren Pflanzen jeder Art. Um ein zuverlässiges Bild der natürlichen Variation zu erhalten, wurden Materialien vieler Individuen zusammengeführt und für jeden Gewebetyp sechs biologische Replikate erstellt. Jede Gewebeprobe wurde dann geteilt: ein Teil zur Messung kleiner Moleküle und ein Teil zur Erfassung der aktiven Gene.
Bestandsaufnahme von Tausenden Pflanzenchemikalien
Um das chemische Profil der Pflanzen zu erfassen, verwendete das Team einen empfindlichen, massenspektrometriebasierten Ansatz, der in einem Durchgang eine sehr große Anzahl bekannter Pflanzenmetabolite nachverfolgen kann. In 60 Proben entdeckten sie 1.342 verschiedene kleine Moleküle, dominiert von Gruppen, denen bereits eine medizinische Bedeutung zugeschrieben wurde: fast ein Viertel waren Flavonoide, gefolgt von phenolischen Säuren, Alkaloiden und Terpenoiden. Statistische Analysen zeigten, dass sich Proben klar nach Gewebetyp gruppierten, und Qualitätskontrollen bestätigten, dass die Messungen stabil und reproduzierbar waren. Der Vergleich desselben Gewebes zwischen den beiden Arten offenbarte zahlreiche Moleküle, die in einer Art deutlich häufiger vorkamen als in der anderen, insbesondere in Stoffwechselwegen, die mit Farbpigmenten, Abwehrverbindungen und anderen spezialisierten Pflanzenstoffen verbunden sind.
Die Bedienungsanleitung der Pflanzen lesen
Parallel dazu extrahierten die Wissenschaftler RNA aus denselben Geweben, um zu sehen, welche Gene aktiv waren, und erfassten so die inneren Anweisungen der Pflanzen zum Zeitpunkt der Probenahme. Hochdurchsatzsequenzierung erzeugte über 500 Gigabasen an qualitativ hochwertigen Daten und führte zur Identifizierung von 37.644 Genen in Oldenlandia diffusa und 20.825 Genen in Oldenlandia corymbosa. Auch hier gruppierten sich Proben desselben Gewebes, was die Zuverlässigkeit der Daten unterstreicht. Durch den Vergleich der Gewebe fanden die Forschenden Tausende von Genen, die sich zwischen Wurzeln und oberirdischen Teilen oder zwischen Stängeln, Blättern, Blüten und Früchten unterschiedlich verhielten. Viele dieser Gene sind an Energiegewinnung, Grundstoffwechsel und Enzymen beteiligt, die Pflanzenverbindungen modifizieren — genau die Aktivitäten, die bestimmen, wo medizinisch relevante Verbindungen gebildet und gespeichert werden.
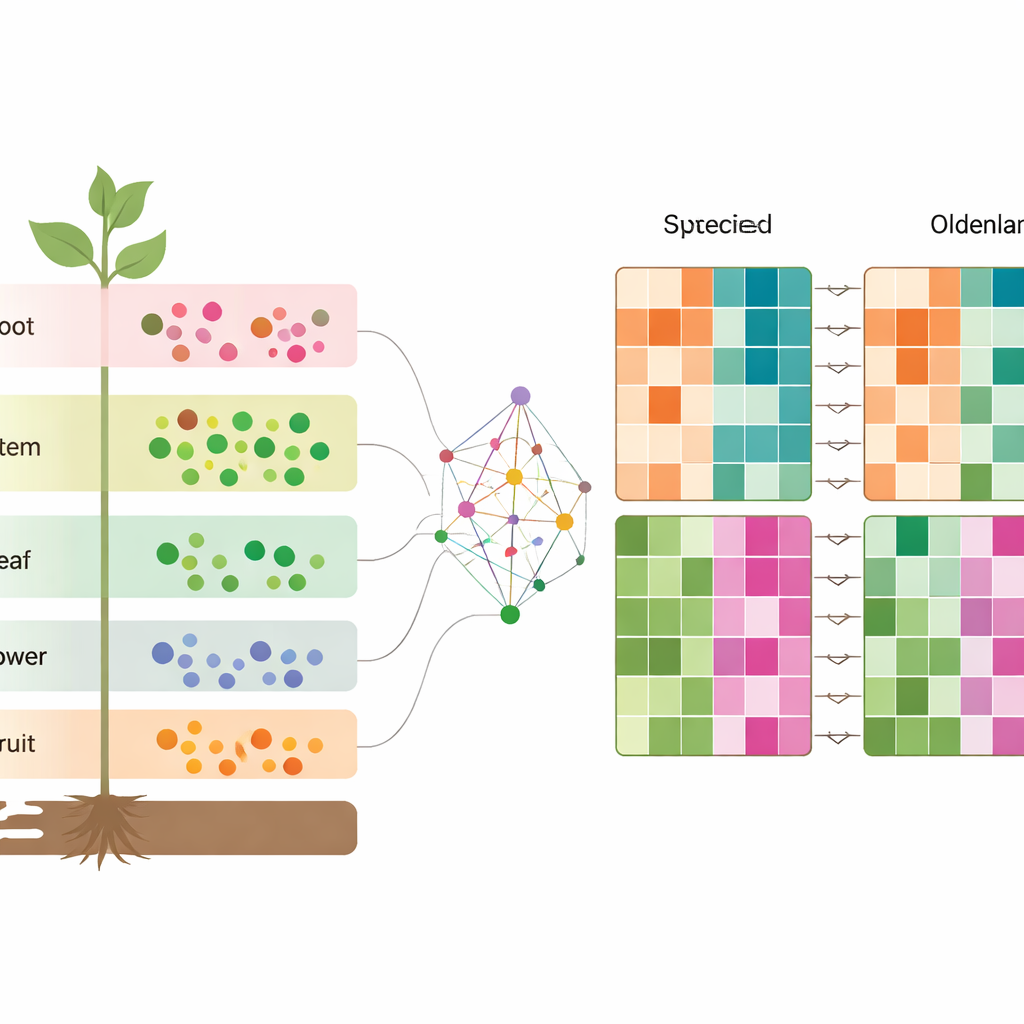
Unterschiede zwischen den beiden Arten genauer betrachtet
Um zu verstehen, was die Arten wirklich unterscheidet, ordneten die Autorinnen und Autoren Gene in O. diffusa und O. corymbosa einander als direkte Gegenstücke zu und verglichen dann deren Aktivität in jedem Gewebe. Sie entdeckten Tausende von Genen, die in einer Art gegenüber der anderen in Wurzeln, Stängeln, Blättern, Blüten und Früchten hoch- oder herunterreguliert waren. Diese Gene gehörten zu Stoffwechselwegen, die Schlüsselsubstanzen herstellen und verarbeiten, einschließlich Terpenoiden, Phenylpropanoiden und verschiedenen stickstoffhaltigen Molekülen. In Verbindung mit den Metabolitendaten ergibt sich so ein vielschichtiges Bild: Jedes Gewebe besitzt einen eigenen chemischen und genetischen Fingerabdruck, und diese Fingerabdrücke verändern sich auf charakteristische Weise zwischen den beiden eng verwandten Kräutern.
Was das für Medizin und zukünftige Forschung bedeutet
Für Nichtfachleute lautet die wichtigste Erkenntnis, dass diese beiden äußerlich ähnlichen Heilpflanzen nicht austauschbar sind. Hinter ihrer ähnlichen Erscheinung unterscheiden sich ihre Wurzeln, Stängel, Blätter, Blüten und Früchte sowohl in der Menge wichtiger kleiner Moleküle als auch in der Aktivität der Gene, die diese Moleküle herstellen. Mit der Veröffentlichung dieses großen, sorgfältig validierten Datensatzes stellt die Studie ein Referenzatlas zur Verfügung, den andere Wissenschaftler nutzen können, um genau zu bestimmen, welche Inhaltsstoffe bestimmte gesundheitliche Wirkungen hervorrufen könnten und welche Gene als Ziel für Züchtung oder gentechnische Verbesserung dienen könnten, um Pflanzen mit konsistenteren und potenteren Eigenschaften zu erzeugen. Langfristig kann diese Art der tiefgehenden Kartierung dazu beitragen, traditionelle Kräutermischungen in besser verstandene, gezielter einsetzbare Arzneimittel zu überführen.
Zitation: Chen, P., Huang, Z., Wen, Y. et al. Metabolomic and Transcriptomic Profiling of Two Closely Related Species within the Genus Oldenlandia. Sci Data 13, 378 (2026). https://doi.org/10.1038/s41597-026-06745-y
Schlüsselwörter: Oldenlandia, Heilpflanzen, Metabolomik, Transkriptomik, sekundäre Pflanzenstoffe