Clear Sky Science · de
Chromosomengenaue Genomassembly des Maulbeerfransenflüglers Pseudodendrothrips mori (Thysanoptera: Thripidae)
Kleine Schädlinge mit großer Wirkung
Maulbeerfransenflügler sind kaum länger als ein Sandkorn, können jedoch ganze Plantagen silbrig und krankhaft erscheinen lassen, wenn sie Blätter durchbohren und Pflanzensäfte aussaugen. Landwirte tun sich schwer mit der Bekämpfung dieser Insekten, weil sie sich schnell vermehren, sich gut verbergen und häufig Resistenzen gegen Pestizide entwickeln. Diese Studie liefert den ersten detaillierten genetischen Bauplan des Maulbeerfransenflüglers und bietet ein kraftvolles neues Werkzeug, um zu verstehen, wie dieser winzige Schädling gedeiht — und wie er nachhaltiger bekämpft werden könnte.
Warum die DNA eines blattverformenden Insekts kartieren?
Maulbeerfransenflügler ernähren sich von Maulbeerbäumen und anderen Pflanzen und verursachen Blattverformungen sowie Ertragsminderungen. Ihre geringe Größe erschwert die Forschung: Ein einzelnes Tier liefert nicht genug DNA oder RNA für die meisten modernen Sequenzierverfahren, weshalb Forschende sorgfältig gepoolte Proben verwenden müssen. Bislang hat das Fehlen eines vollständigen Referenzgenoms tiefere Fragestellungen blockiert, etwa wie sich diese Insekten auf bestimmte Pflanzen spezialisieren, wie sie so schnell Resistenzen gegen chemische Behandlungen entwickeln und wie sich ihre ungewöhnlichen Fortpflanzungssysteme entwickeln. Ein chromosomenebenes Genom bietet nun eine Grundlage, um all diese Fragen zu untersuchen — von der Grundlagenforschung bis zur praxisnahen Schädlingsbekämpfung.
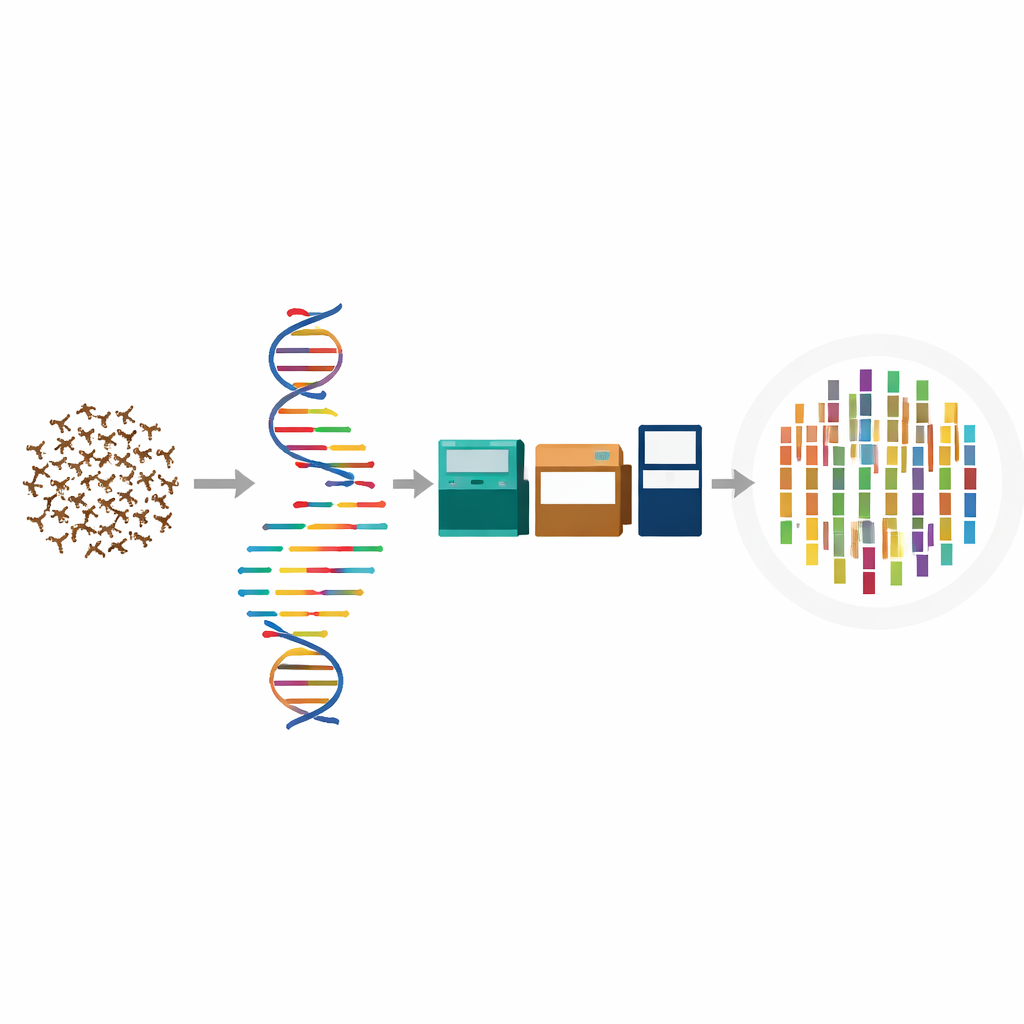
Ein qualitativ hochwertiges Genom aus vielen winzigen Körpern erstellen
Um die Größenordnung zu überwinden, sammelte das Team Hunderte ausgewachsener Fransenflügler in einem Maulbeergarten in Südchina und poolte sie für verschiedene Sequenzierungstypen. Lange DNA-Abschnitte wurden mit PacBio-HiFi-Technologie gelesen, die besonders gut darin ist, schwierige Regionen des Genoms zu überbrücken. Kurze, hochpräzise DNA-Fragmente von einer Illumina-Plattform dienten anschließend dazu, kleine Fehler zu korrigieren. Ein dritter Datentyp, Hi‑C, erfasste, wie DNA‑Stücke im Zellkern gefaltet und verbunden sind, sodass die Forschenden die Fragmente zu vollständigen Chromosomen anordnen konnten. RNA aus zusätzlichen gepoolten Fransenflüglern half dabei, die Grenzen von Genen zu bestimmen, sodass die zusammengefügte Sequenz in eine funktionale genetische Karte überführt werden konnte.
Von verstreuten Fragmenten zu vollständigen Chromosomen
Mithilfe dieser sich ergänzenden Datenströme setzten die Forschenden ein Genom von etwa 281 Millionen DNA-Buchstaben zusammen. Fast die gesamte Sequenz — mehr als 98 % — wurde in 19 lange Strukturen organisiert, die den Chromosomen des Insekts entsprechen. Qualitätsmaße der Assembly zeigen, dass diese Abschnitte für ein kleines Insektengenom ungewöhnlich zusammenhängend und präzise sind. Bei der Suche nach tausenden standardisierter Insektengene, die in nahezu jeder Art einmal vorkommen sollten, fanden sie etwa 98 % davon vollständig, ein starkes Indiz dafür, dass nur sehr wenig wichtige Information fehlt. Im Vergleich zu anderen sequenzierten Fransenflüglern ist das Genom des Maulbeerfransenflüglers ähnlich groß, sticht jedoch durch seine Vollständigkeit und die sorgfältige Validierung hervor.
Versteckte Wiederholungen und ein reichhaltiger Genkatalog
Das Team ging dann von der Rohsequenz zur biologischen Bedeutung über. Sie durchsuchten das Genom nach repetitiven DNA‑Abschnitten, die beeinflussen können, wie Gene sich entwickeln und wie Genome sich im Laufe der Zeit umstrukturieren. Etwa ein Fünftel des Maulbeerfransenflügler-Genoms besteht aus solchen Wiederholungen, viele davon ließen sich nicht bekannten Familien zuordnen, was auf linienspezifische Elemente dieser Insektengruppe hinweist. Nachdem diese Regionen maskiert waren, kombinierten die Forschenden Hinweise aus bekannten Proteinen, RNA‑Daten und computergestützten Vorhersagen, um über 13.000 proteinkodierende Gene zu identifizieren. Fast alle diese Gene konnten durch Abgleich mit bestehenden Datenbanken einer wahrscheinlichen Funktion zugewiesen werden, wodurch ein weites Spektrum der molekularen Werkzeuge dieses Schädlings beschrieben wurde — zum Fressen, Entgiften von Pflanzenchemikalien, Reagieren auf Pestizide und Entwickeln.
Ein neues Toolkit für intelligentere Schädlingsbekämpfung
Indem ein schwer zu untersuchendes Insekt zu einem der am besten charakterisierten Fransenflügler‑Genome gemacht wurde, schafft diese Arbeit die Grundlage für künftige Durchbrüche. Mit einem zuverlässigen Referenzgenom in der Hand können Wissenschaftler jetzt verfolgen, wie Maulbeerfransenflügler‑Populationen sich ausbreiten, genetische Signaturen von Insektizidresistenz entdecken und Schwachstellen in wichtigen biologischen Wegen suchen. Mit der Zeit kann dieses Wissen gezieltere, umweltfreundlichere Kontrollmethoden unterstützen — von verbesserten Überwachungswerkzeugen bis zu biologischen Bekämpfungsstrategien — und so Ernteverluste reduzieren bei gleichzeitig geringerem Einsatz breit wirkender Chemikalien.
Zitation: Guan, DL., Li, YM., Zhang, SH. et al. A chromosome-level genome assembly for the mulberry thrips Pseudodendrothrips mori (Thysanoptera: Thripidae). Sci Data 13, 330 (2026). https://doi.org/10.1038/s41597-026-06697-3
Schlüsselwörter: Maulbeerfransenflügler, Genomassembly, landwirtschaftliche Schädlinge, Insektengenomik, Insektizidresistenz