Clear Sky Science · de
Eine kuratierte Ressource von chemolithoautotrophen Genomen und Markergenen zur Vorhersage von CO₂-Fixierungswegen
Mikroben, die das globale Kohlenstoffkonto ausgleichen
Verborgen in Böden, Ozeanen und extremen Lebensräumen können bestimmte Mikroben ihre eigene Biomasse mithilfe von Kohlendioxid (CO₂) als Hauptkohlenstoffquelle aufbauen. Diese mikroskopischen Chemiker sind entscheidend, um den Kohlenstoffkreislauf der Erde im Gleichgewicht zu halten, und könnten neue Ansätze zur Abscheidung industriellen CO₂ inspirieren. Bislang fehlte Forschern jedoch eine einfache, verlässliche Methode, die anhand der DNA eines Mikroben erkennt, welche CO₂-fixierende Strategie es nutzt. Diese Studie stellt einen kuratierten Genkatalog und ein neues Computerwerkzeug namens AutoFixMark vor, das diese Lücke schließen soll.
Viele Wege, Luft in Biomasse zu verwandeln
Nicht alle Organismen, die CO₂ fixieren, tun dies auf dieselbe Weise. Mikroben haben mindestens sieben natürliche Wege entwickelt, um CO₂ in organische Materie umzuwandeln. Einige, wie der Calvin–Benson–Bassham-Zyklus, der in Pflanzen und vielen Bakterien verbreitet ist, sind gut bekannt; andere, etwa der erst 2020 entdeckte reduktive Glycinweg, sind noch schlecht untersucht. Diese Wege finden sich über viele Zweige des Lebensbaums verteilt und verwenden oft ähnliche Enzyme, was es überraschend schwer macht, sie allein aus Genomsequenzen zu unterscheiden. Bestehende Software kann breite Stoffwechselfähigkeiten vorhersagen, wurde aber nicht speziell optimiert oder umfassend getestet, um die genauen CO₂-Fixierungsrouten zu bestimmen.
Aufbau einer sauberen Referenzkarte CO₂-fixierender Mikroben
Die Forschenden begannen damit, zwei sorgfältig geprüfte Genomkollektionen zusammenzustellen. Zuerst wählten sie 15 gut untersuchte Mikroben aus, deren CO₂-Fixierungswege im Detail aufgeklärt sind. Diese Referenzorganismen, die mehrere bakterielle und archaeale Gruppen abdecken, dienten als Vorlage zur Definition der Schlüsselenzyme, die für jeden Weg tatsächlich charakteristisch sind. Anschließend erstellten sie einen Benchmark-Satz von 347 chemolithoautotrophen Genomen — Mikroben, die Energie aus anorganischen Stoffen gewinnen und Biomasse aus CO₂ aufbauen. Jedes Genom in diesem größeren Satz wurde manuell aus der Literatur mit spezifischen CO₂-Fixierungswegen verknüpft, wodurch ein solides Wahrheitsset für die Bewertung von Vorhersagen entstand.
Markergene und einfache Regeln statt Black-Box-Methoden
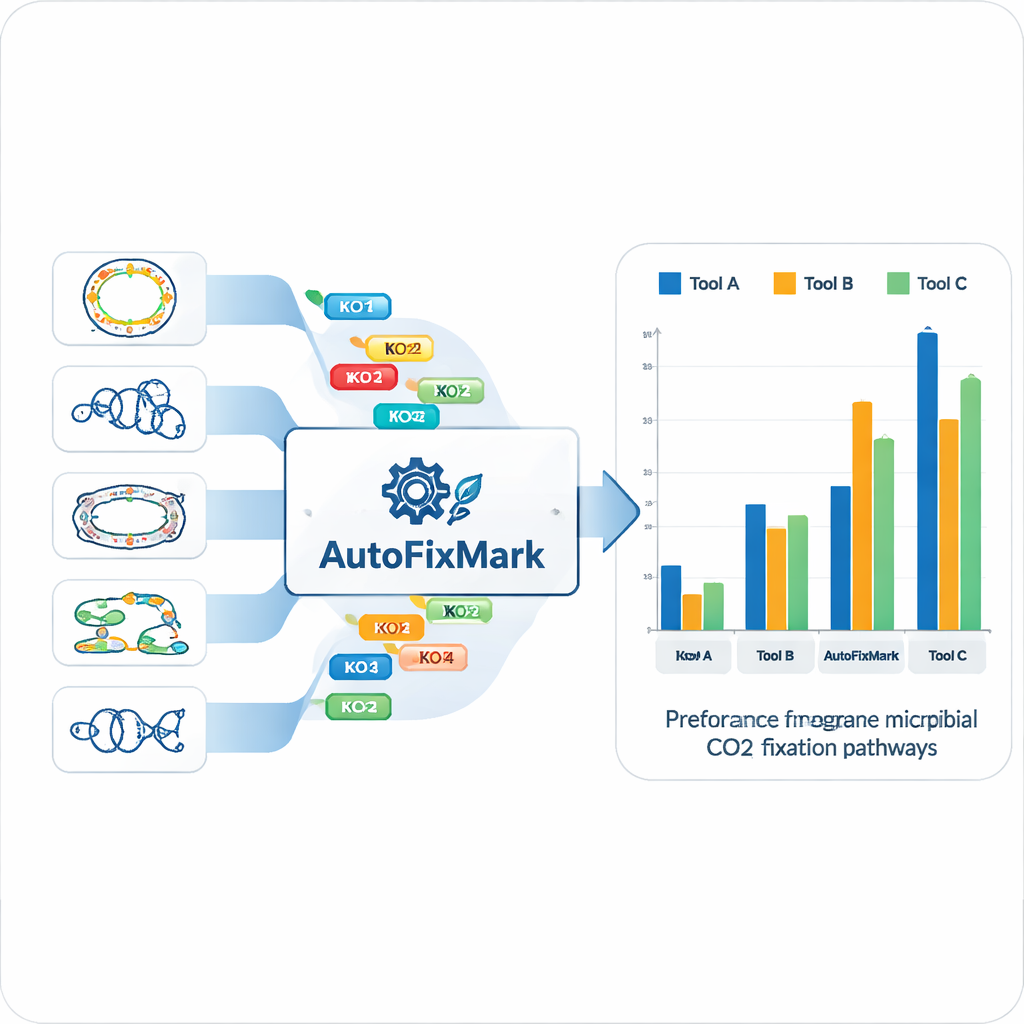
Mithilfe der 15 Referenzgenome identifizierte das Team „Markergene“ für jeden der sieben CO₂-Fixierungswege und wies sie standardisierten KEGG-Orthologie-(KO)-Kennungen zu. Anstatt auf undurchsichtige maschinelle Lernverfahren zu setzen, kodierten sie transparente Regeln darüber, wie sich diese Marker kombinieren. Einige Reaktionen können von mehreren alternativen Enzymen katalysiert werden, was durch eine „one_of“-Regel abgebildet wird. Andere beruhen auf Multisubunit-Komplexen und erfordern, dass „all_of“ eine definierte Menge von KOs vorhanden ist. Für den reduktiven Glycinweg, dessen Komponenten nicht vollständig verstanden sind, verwendet das Tool „at_least“-Regeln, die eine Mindestanzahl an Untereinheiten voraussetzen. Diese logischen Regeln werden in einer maschinenlesbaren JSON-Datei gespeichert, die die zentrale Wissensbasis von AutoFixMark bildet.
Ein leichtgewichtiges Werkzeug, das etablierte Software übertrifft
AutoFixMark selbst ist ein kleines, regelbasiertes Programm in Python. Es nimmt als Eingabe eine Liste von KO-IDs der Gene eines Mikrobengenoms, typischerweise erzeugt von einem separaten Tool namens KofamScan, und prüft dann, welche Markerregeln für jeden der sieben Wege erfüllt sind. Die Autoren verglichen AutoFixMark mit zwei weitverbreiteten Tools zur Stoffwechselannotation, METABOLIC und gapseq, unter Verwendung ihres 347-Genom-Benchmark-Satzes. Alle drei Werkzeuge lieferten gute Ergebnisse für klassische Wege wie den Calvin-Zyklus, den reduktiven Tricarbonsäurezyklus und den Wood–Ljungdahl-Weg. AutoFixMark hob sich jedoch deutlich ab bei neueren oder weniger verbreiteten Wegen wie dem 3‑Hydroxypropionat/4‑Hydroxybutyrat-Zyklus, dem Dicarboxylat/4‑Hydroxybutyrat-Zyklus und dem reduktiven Glycinweg, von denen einige in der Konkurrenzsoftware gar nicht abgedeckt sind.
Welche Bedeutung diese Ergebnisse für Klima- und Ökologie‑Studien haben
Die kuratierten Gen-Sets, das AutoFixMark-Programm und die vollständige Benchmark-Genomkollektion sind öffentlich zugänglich. Forschende können damit nun sowohl isolierte Mikroben als auch aus Metagenomen rekonstruierte Genome daraufhin durchsuchen, welche CO₂-Fixierungsstrategien sie genetisch besitzen. Wichtig ist, dass die Autoren betonen, dass AutoFixMark das genetische Potenzial vorhersagt, nicht ob ein Weg unter realen Bedingungen aktiv ist. Viele dieser biochemischen Routen können abhängig vom Energiehaushalt der Zelle auch in umgekehrter Richtung laufen. Dennoch wird eine robuste, transparente Methode zur Kennzeichnung CO₂-fixierender Mikroben Wissenschaftlern helfen, aufzuzeigen, wo und wie Leben Kohlenstoff aus der Atmosphäre entzieht, Experimente zu neuen Wegen zu leiten und die Konzeption künftiger CO₂-basierter Biotechnologien zu unterstützen.
Zitation: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Schlüsselwörter: mikrobielle Kohlenstoff-Fixierung, autotropher Stoffwechsel, Genom-Annotation, CO2-Abscheidung, Metagenomik