Clear Sky Science · de
Ein annotierter Datensatz von Gram-Färbungen aus positiven Blutkulturen
Warum schnelle Befunde bei Infektionen wichtig sind
Wenn Bakterien oder Pilze in die Blutbahn gelangen, kann jede Stunde ohne die richtige Behandlung über Leben und Tod entscheiden. Ärztinnen und Ärzte verlassen sich auf einen schnellen Labortest, die Gram-Färbung, um zu erkennen, welche Art von Erreger vorliegt und welche frühen Antibiotika geeignet sein könnten. Das Lesen dieser gefärbten Mikroskoppräparate ist jedoch eine qualifizierte, manuelle Aufgabe, die Zeit kostet und von Technologe zu Technologe variieren kann. Die vorliegende Studie beschreibt eine neu erstellte, sorgfältig annotierte Bildsammlung realer Krankenhaus-Blutkulturpräparate, die Computern helfen soll, Gram-Färbungen automatisch zu lesen und so schnellere, zuverlässigere Versorgung zu unterstützen.
Reale Krankenhauspräparate als Daten
Die Forschenden sammelten 57 verschiedene Bakterien- und Pilzarten, die aus positiven Blutkulturflaschen von Patientinnen und Patienten im Rahmen der Routine im Krankenhaus angezüchtet worden waren. Von Januar bis Mai 2024 bereiteten Mitarbeitende nach positivem Signal einer Blutkultur Gram-gefärbte Ausstriche auf Glasobjektträgern vor und bestätigten die genaue Art mit einem hochpräzisen Identifikationsverfahren, der MALDI-TOF-Massenspektrometrie. Ohne die normalen Abläufe zu ändern oder zusätzliche Proben zu entnehmen, erfasste das Team hochauflösende digitale Bilder typischer Sichtfelder unter einem 100×-Ölimmersi‑onsobjektiv, was zu 505 großen Farbbildern führte, die dem entsprechen, was Technologinnen und Technologen in der Praxis sehen.
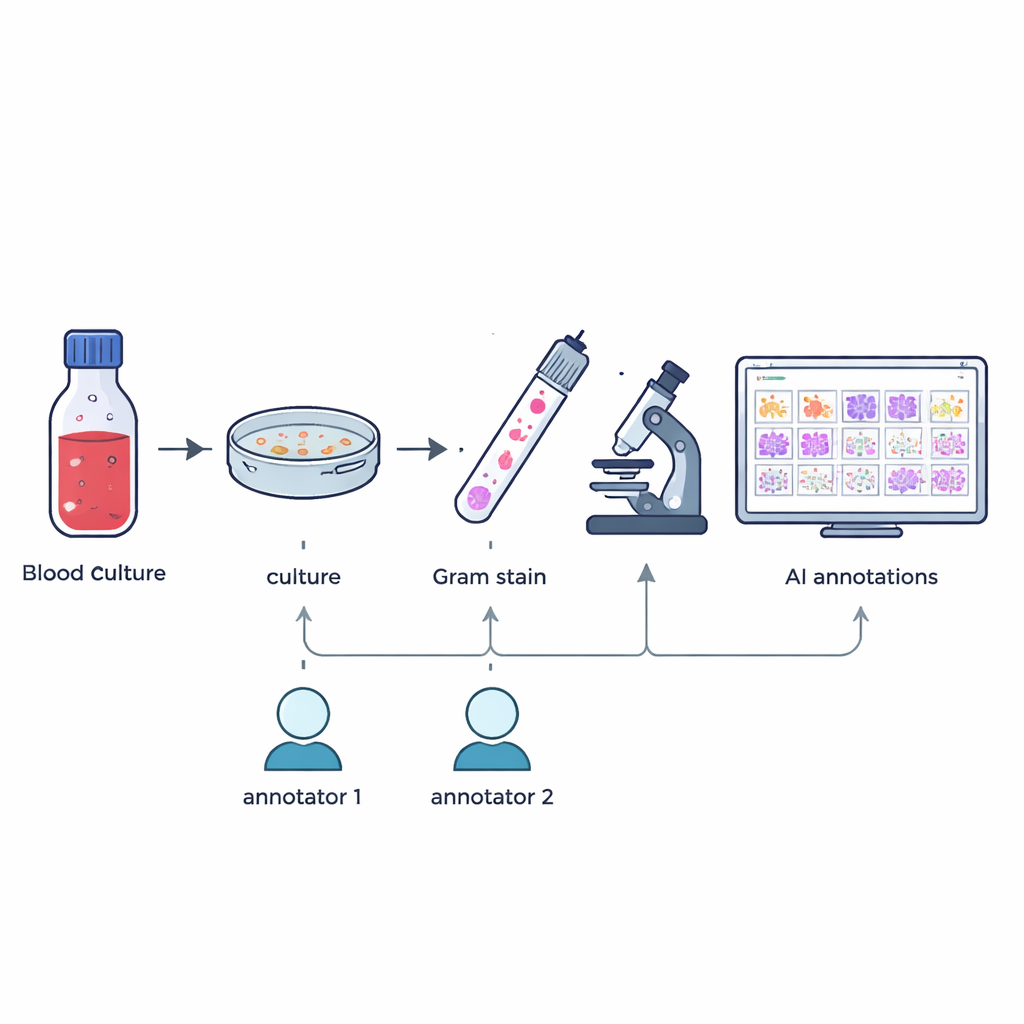
Sorgfältige Kennzeichnung winziger Formen
Ein nützliches Trainingsset für künstliche Intelligenz setzt voraus, genau zu wissen, wo sich jeder Mikroorganismus in jedem Bild befindet. Zwei erfahrene mikrobiologische Technologinnen zeichneten unabhängig voneinander Boxen um einzelne mikrobielle Zellen oder Cluster in jedem Bild, geleitet nur von dem, was sie im Mikroskop sahen. Ein maßgeschneidertes Softwarewerkzeug verglich die beiden Markierungssätze: Boxen mit ausreichender Überlappung wurden zusammengeführt, und Unstimmigkeiten oder Meinungsverschiedenheiten wurden markiert. Ein leitender Experte mit mehr als 20 Jahren Erfahrung überprüfte diese Fälle anschließend von Hand. Dieser mehrstufige Prozess ergab 7.528 geprüfte Annotationen, die Kokken (runde Zellen), Bazillen (stabförmige Zellen) und Pilze hervorheben, während partielle oder zweifelhafte Objekte ausgeschlossen wurden.
Was der Datensatz enthält
Die fertige Ressource kombiniert mehrere Informationsebenen. Alle 505 Bilder werden als hochauflösende JPEG-Dateien bereitgestellt, und die finalen, expertengeprüften Boxen sind im standardisierten COCO-JSON-Format gespeichert, das in der Computer-Vision-Forschung weit verbreitet ist. Zusätzliche Dateien verknüpfen jedes Bild mit der Mikrobenart, ob es sich um Gram-positiv oder Gram-negativ handelt, mit der übergeordneten Formklasse, dem Typ der Blutkulturflasche, aus der es stammte, und der Zeit bis zum Positivsignal der Kultur. Da jedes Bild nur eine Art enthält, teilen alle Boxen innerhalb eines Bildes dieselben biologischen Merkmale. Nutzerinnen und Nutzer können zwischen einer einzigen großen Annotationsdatei oder separaten Dateien pro Bild wählen; ein einfaches Python-Skript ist enthalten, um jedes Bild mit darübergelegten Boxen darzustellen.
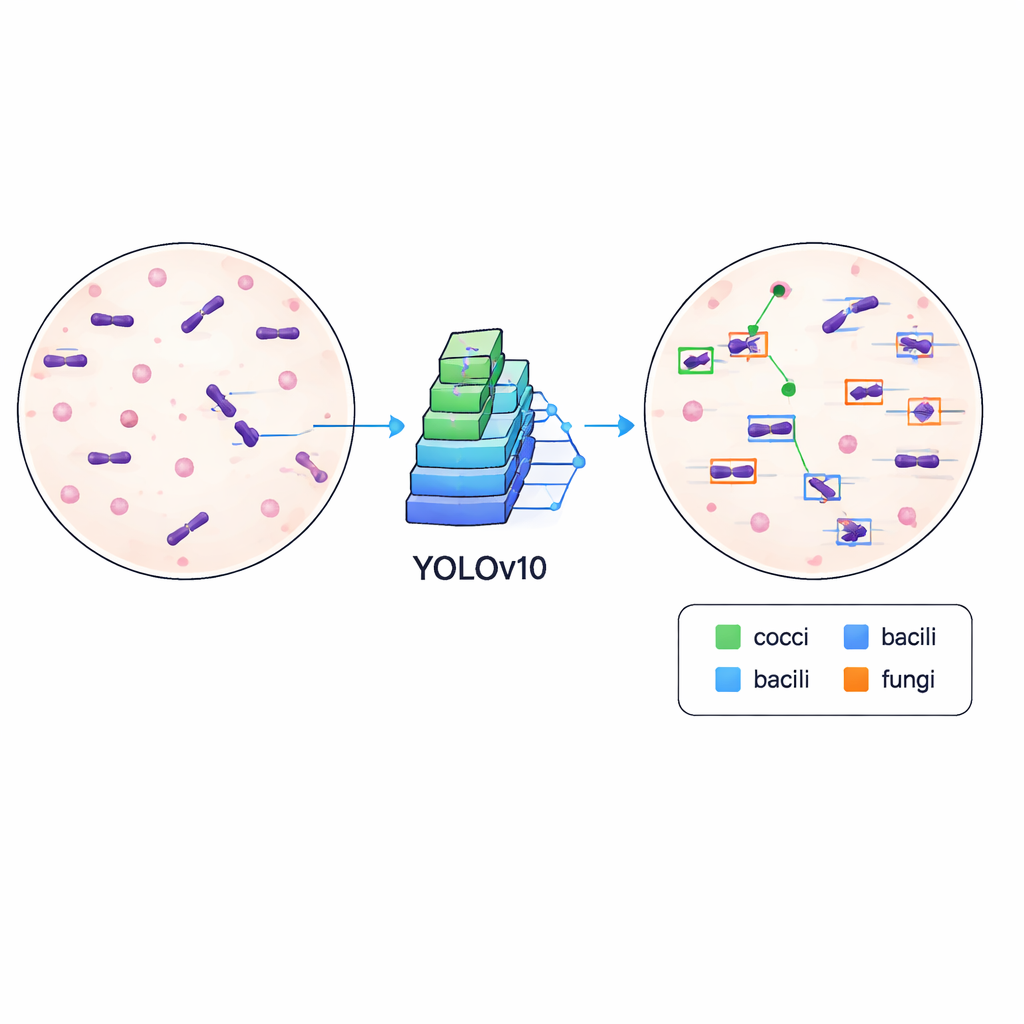
Computern das Erkennen von Keimen beibringen
Um zu zeigen, dass der Datensatz nicht nur ordentlich, sondern auch praktisch ist, trainierten die Autorinnen und Autoren einen modernen Objekterkennungsalgorithmus, bekannt als YOLOv10, um Mikroben in den Bildern zu finden und zu klassifizieren. Sie teilten die Daten in Trainings- und Validierungssets und ließen das Modell 500 Trainingsdurchläufe auf einer Hochleistungs-Grafikkarte laufen, wobei sie verfolgten, wie gut es lernte, genaue Boxen zu zeichnen und zwischen Zelltypen zu unterscheiden. Das trainierte System erreichte eine mittlere Durchschnittsgenauigkeit von etwa 84,6 % bei einem üblichen Übereinstimmungs-Schwellenwert, was darauf hindeutet, dass es Mikroben zuverlässig lokalisieren und beschriften kann trotz variierender Präparatansichten, unterschiedlicher Färbeintensitäten, Hintergrundpartikeln und Schärfegrade.
Wie diese Ressource genutzt werden kann
Weil die Daten gängigen Formaten folgen, lassen sie sich in viele bestehende Computer-Vision-Pipelines einfügen. Forschende könnten zunächst ein System trainieren, das echte Mikroben von Schmutz unterscheidet und Labore dabei unterstützt, falsch-positive Kulturhinweise herauszufiltern. Sie können Mikroben auch in grobe Formgruppen einteilen, passend zu dem, was Klinikerinnen und Kliniker für einen frühen, sogenannten „Tier‑1“-Bericht benötigen, der die initiale Antibiotikawahl leitet. Ein ambitionierteres Ziel ist die Unterscheidung einzelner Arten anhand subtiler visueller Hinweise. Die Autorinnen und Autoren nennen Grenzen: Einige Zellen liegen gruppiert vor, einige Präparate stammen pro Art nur aus einer Quelle, und die Schärfe kann variieren — wie im echten Leben. Dennoch wurde jede enthaltene Box sorgfältig geprüft, wodurch der Datensatz einen verlässlichen Ausgangspunkt bietet.
Was das für Patientinnen und Patienten bedeutet
Einfach gesagt verwandelt diese Arbeit Routine-Blutkulturpräparate in ein gemeinsames Trainingsfeld für intelligente Software. Indem sowohl die Bilder als auch die Expertenmarkierungen öffentlich zugänglich gemacht werden, senkt die Studie die Hürde für Teams weltweit, KI‑Werkzeuge zu entwickeln und zu testen, die Gram-Färbungen schnell und konsistent lesen können. Solche Systeme werden menschliche Mikrobiologen zwar nicht ersetzen, könnten aber helfen, gefährliche Infektionen früher zu erkennen, Interpretationsfehler zu reduzieren und die bessere Nutzung von Antibiotika zu unterstützen. Für Patientinnen und Patienten könnte das schnellere, präzisere Behandlungen bedeuten, wenn es am meisten darauf ankommt.
Zitation: Yi, Q., Gou, X., Zhu, R. et al. An annotated dataset of Gram stains from positive blood cultures. Sci Data 13, 294 (2026). https://doi.org/10.1038/s41597-026-06651-3
Schlüsselwörter: Blutstrominfektionen, Gram-Färbung, medizinischer Bilddatensatz, künstliche Intelligenz, mikrobiologische Diagnostik