Clear Sky Science · de
Chromosomenaufgelöste Genomassemblierung von Schmalblättrigem Binsenkraut (Sparganium angustifolium Michx., Typhaceae)
Eine unauffällige Seepflanze mit großer genomischer Geschichte
Das Schmalblättrige Binsenkraut ist eine eher zurückhaltend wirkende Wasserpflanze, an der man beim Paddeln leicht vorbeiziehen könnte, die aber in vielen nördlichen Seen und Teichen das Leben entscheidend mitgestaltet. Sie bietet Schutz für kleine Fische, dient Wasservögeln als Nahrung und bedeckt mit ihren schwimmenden Blättern die Wasseroberfläche. In dieser Studie legen Forschende einen detaillierten genetischen Bauplan dieser Pflanze vor, der neue Einblicke liefert, wie Pflanzen sich an ein Leben unter Wasser anpassen, und eine wertvolle Referenz für Naturschutz und Grundlagenforschung darstellt. 
Warum diese Bewohnerin des Wassers wichtig ist
Das Schmalblättrige Binsenkraut (wissenschaftlicher Name Sparganium angustifolium) ist in den gemäßigten Regionen der nördlichen Hemisphäre weit verbreitet. Im Gegensatz zu Schilf- oder rohrartigen Pflanzen, die größtenteils über der Wasseroberfläche stehen, wächst diese Art in tieferem Wasser; ihre langen, schlanken Blätter sind größtenteils untergetaucht oder schwimmend. Dichte Bestände bilden unterwasserliche Wälder, die aquatischen Tieren Verstecke bieten, und ihre Früchte und Blätter dienen Enten und anderen Wasservögeln als Nahrung. Da sie nahe der Basis eines wichtigen Zweigs des Gras- und Getreide-Stammbaums (die Ordnung Poales, zu der auch Kulturpflanzen wie Reis und Mais gehören) steht, liefert sie einen entscheidenden Vergleichspunkt, um zu verstehen, wie Pflanzen den Übergang von Land zu Wasser vollzogen haben.
Aufbau eines hochauflösenden genetischen Bauplans
Um das Genom der Pflanze zu entschlüsseln, sammelten die Forschenden ein Exemplar aus einem Fluss in der Inneren Mongolei, China, und nutzten mehrere moderne DNA-Sequenzierverfahren. Sie kombinierten lange, sehr präzise DNA-Lesungen, Kurzlese-Sequenzierung und eine Methode namens Hi-C, die erfasst, wie unterschiedliche DNA-Regionen im dreidimensionalen Raum innerhalb der Zelle zueinander liegen. Durch das Verweben dieser Daten stellten sie die DNA der Pflanze in 15 Chromosomen zusammen und deckten damit nahezu das gesamte Genom ab — etwa 487 Millionen „Buchstaben“ des genetischen Codes. Qualitätsmaße der Assemblierung zeigten, dass große DNA-Abschnitte lückenlos zusammengefügt wurden und dass mehr als 96 % der erwarteten Kernpflanzengene vorhanden sind, was auf ein sehr vollständiges und verlässliches Referenzgenom hinweist.
Repetitive DNA und Tausende Gene
Nachdem das Genom zusammengesetzt war, ermittelte das Team dessen wesentliche Merkmale. Sie identifizierten 23.767 proteinkodierende Gene — DNA-Abschnitte, die in Proteine übersetzt werden können und den Aufbau und die Funktion der Pflanzenzellen steuern. Um mögliche Funktionen dieser Gene zu bestimmen, verglichen sie sie mit mehreren großen wissenschaftlichen Datenbanken und konnten mehr als 96 % der Gene wahrscheinlichen Funktionen zuordnen. Die Forschenden fanden außerdem heraus, dass der Großteil des Genoms — etwas mehr als 70 % — aus repetitiver DNA besteht, viel davon in Form von springenden genetischen Elementen, sogenannten Retrotransposons. Diese Abschnitte kodieren nicht direkt für Proteine, prägen aber stark die Genomgröße und -struktur und können die Aktivität benachbarter Gene beeinflussen. 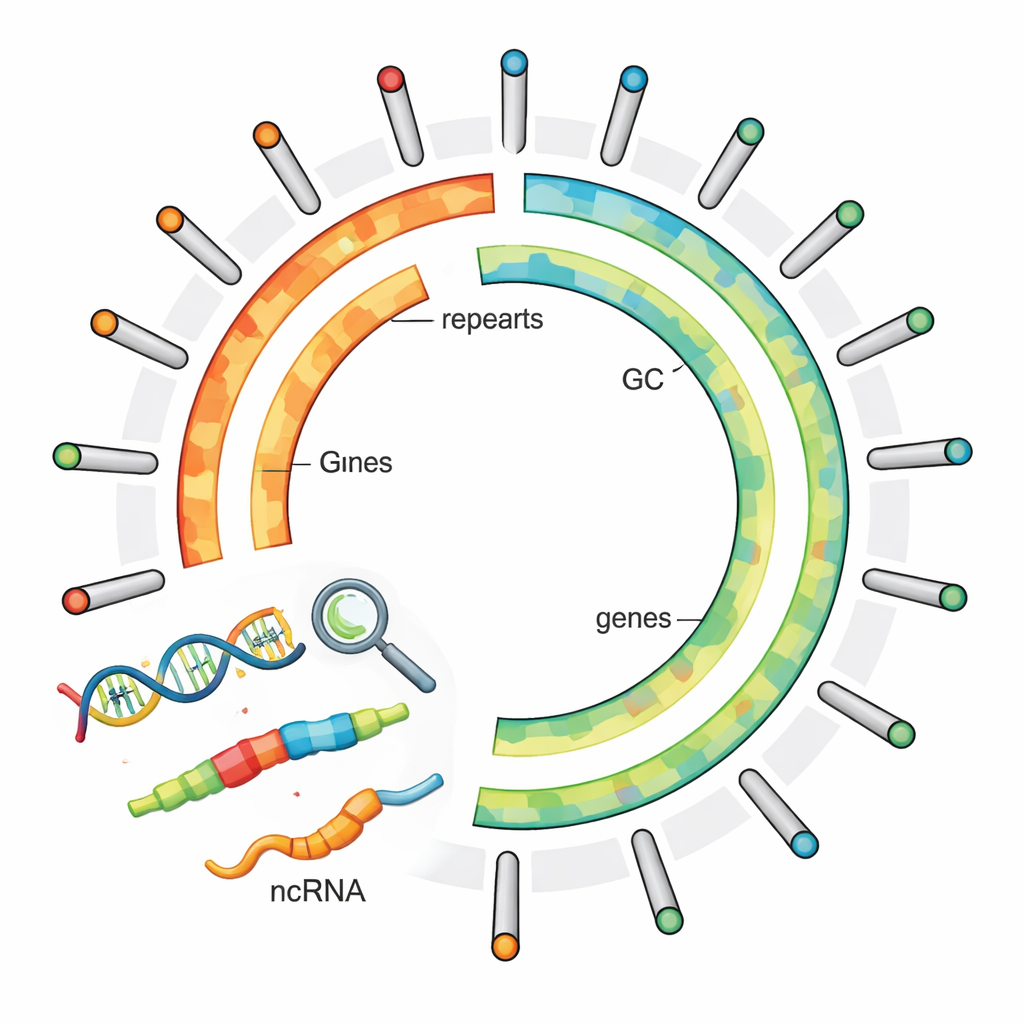
Das verborgene RNA-Werkzeug der Pflanze
Jenseits der proteinkodierenden Gene enthält das Genom zahlreiche nichtkodierende RNAs, Moleküle, die helfen, die Genaktivität zu steuern und feinabzustimmen. Die Forschenden identifizierten mehr als 3.300 solcher Elemente, darunter tausende ribosomale RNAs, die den Kern der zellulären Proteinfabriken bilden, hunderte Transfer-RNAs, die Bausteine für neue Proteine liefern, sowie kleine RNAs, die steuern können, welche Gene an- oder ausgeschaltet werden. Dieses umfangreiche RNA-Werkzeug deutet darauf hin, dass das Schmalblättrige Binsenkraut mehrere Regulationsebenen besitzt, um auf Veränderungen von Licht, Sauerstoff, Temperatur und Wasserbewegung in seinem aquatischen Lebensraum zu reagieren.
Von einer Pflanze zu einem breiteren evolutiven Bild
Indem die Autoren dieses chromosomenaufgelöste Genom in internationalen Datenbanken öffentlich verfügbar machen, stellen sie Forschenden ein mächtiges neues Werkzeug zur Verfügung, um zu untersuchen, wie Pflanzen sich an das Leben im Wasser anpassen. Der Vergleich dieses Genoms mit denen verwandter Arten, die am Wasserufer oder an Land leben, kann offenlegen, welche Gene und DNA-Merkmale geteilt werden und welche speziell für ein vollständig aquatisches Leben sind. Für Nicht-Spezialisten lautet die Kernaussage einfach: Durch das Entschlüsseln des genetischen Skripts einer scheinbar gewöhnlichen Seepflanze haben Forschende eine Grundlage geschaffen, um zu verstehen, wie Pflanzen sich selbst so gestalten, dass sie unter Wasser gedeihen — Wissen, das letztlich den Schutz von Feuchtgebieten unterstützen und sogar zur Züchtung widerstandsfähigerer Kulturpflanzen beitragen könnte.
Zitation: Shi, X., Xue, J. & Xu, X. Chromosome-level genome assembly of narrow-leaf bur-reed (Sparganium angustifolium Michx., Typhaceae). Sci Data 13, 284 (2026). https://doi.org/10.1038/s41597-026-06640-6
Schlüsselwörter: Wasserpflanzen, Genomassemblierung, Feuchtgebietökologie, Pflanzenentwicklung, Sparganium