Clear Sky Science · de
Chromosomenaufgelöste Genomassemblierung der agarproduzierenden Rotalge Gracilaria vermiculophylla
Warum das Genom einer Rotalge wichtig ist
Agar, die geleeartige Substanz, die unsere Desserts erstarren lässt, Suppen andickt und im Labor als Nährboden für Mikroben dient, stammt häufig von einer unscheinbaren Rotalge namens Gracilaria vermiculophylla. Diese Alge ist nicht nur ein industrieller Nutzstoff, sondern auch eine invasive Art, die sich an Küsten in Nordamerika und Europa ausbreitet. Bislang fehlte der Wissenschaft ein vollständiger, hochwertiger Genomplan dieser Art, was Bemühungen zur Verbesserung der Agarproduktion, zum Verständnis ihrer Invasivität oder zur Erforschung gesundheitsrelevanter Verbindungen einschränkte. Diese Studie liefert den fehlenden genetischen Bauplan auf Chromosomenebene und eröffnet damit sowohl praktische Anwendungen als auch neue Grundlagenforschung.

Pflanze der Küste mit vielen Rollen
Gracilaria vermiculophylla ist eine Rotalge, die in Teilen Asiens und im nordwestlichen Pazifik heimisch ist und heute in Ästuaren weltweit gedeiht — mitunter auch problematisch. Züchter nutzen sie als Quelle für Agar und andere wertvolle Moleküle mit potenziellen medizinischen und ernährungsphysiologischen Vorteilen, etwa zur Erhöhung des Jodgehalts in Aquakultur oder zur Unterstützung von Organismen bei Stress. Gleichzeitig dient sie Ökologen als Modell dafür, wie marine Arten sich schnell an neue Lebensräume und erwärmende Meere anpassen. Da diese Alge einen komplexen Lebenszyklus hat und eine auffällige genetische Vielfalt zeigt, ist ein vollständiges Genomkartierung entscheidend, um zu verstehen, wie ihre Biologie funktioniert und wie sie auf sich verändernde Meere reagiert.
Vom Meer zum Sequenzierer
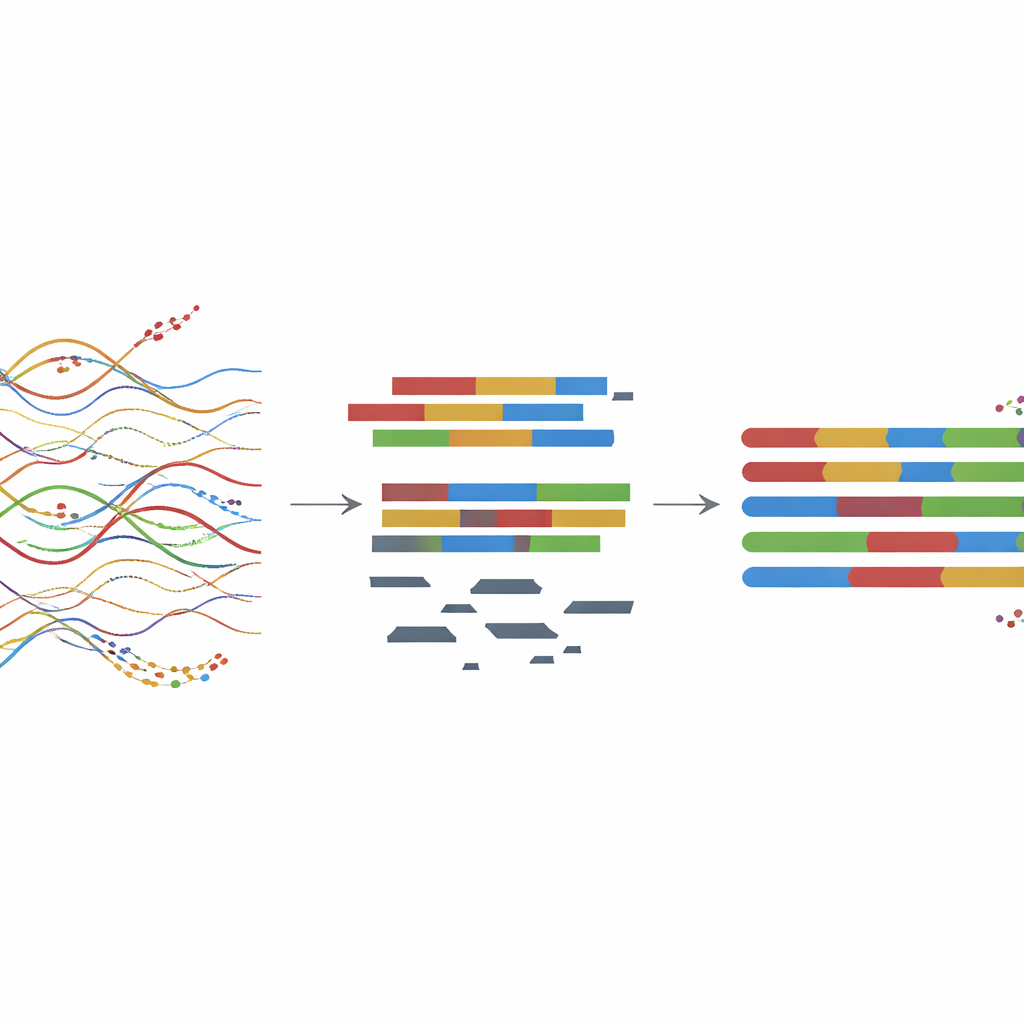
Um diese Karte zu erstellen, sammelten die Forschenden Algen an Chinas Ostküste und reinigten sowie konservierten das Material sorgfältig, um hochqualitative DNA zu gewinnen. Anschließend kombinierten sie drei moderne Sequenzierverfahren: kurze, sehr genaue DNA-Fragmente; deutlich längere, aber rauschärmere bzw. fehleranfälligere Reads, die Lücken überbrücken; und eine spezielle Methode namens Hi-C, die erfasst, welche DNA-Stücke innerhalb des Zellkerns räumlich nahe beieinander liegen. Zusammen erlauben diese Methoden den Forschenden nicht nur, den genetischen Code der Alge zu lesen, sondern ihn auch zu langen Abschnitten zusammenzusetzen, die ganzen Chromosomen entsprechen, während fremde DNA von Bakterien und anderen auf der Pflanze lebenden Mitfahrern herausgefiltert wird.
Das genetische Puzzle zusammensetzen
Mithilfe dieser Daten stellte das Team ein Kerngenomen von etwa 77,5 Millionen „Basen“ zusammen, organisiert in 22 große Einheiten, sogenannte Pseudochromosomen. Das ist ein großer Fortschritt gegenüber früheren Entwürfen, die kleiner, stärker fragmentiert und in ganzen Chromosomenregionen lückenhaft waren. Die neue Assemblierung weist deutlich weniger Brüche und viel längere zusammenhängende Abschnitte auf, sodass Forschende nun Gene und größere Muster über ganze Chromosomen hinweg verfolgen können. Sorgfältige Prüfungen der Sequenzgenauigkeit, der Abdeckung und der Basenzusammensetzung zeigten, dass Kontaminationen erfolgreich entfernt wurden und die meisten Kern-Gene, die in ähnlichen Organismen erwartet werden, vorhanden und vollständig sind.
Verborgene Wiederholungen und aktive Gene
Die Studie tat mehr, als nur DNA-Teile zusammenzufügen. Das Team durchsuchte das Genom nach wiederholten Sequenzen und fand heraus, dass fast 60 Prozent aus mobilen genetischen Elementen bestehen, insbesondere aus sogenannten Long-Terminal-Repeats. Diese wiederholten Abschnitte, oft als genomische „Springende Gene“ bezeichnet, können die Evolution von Genomen über die Zeit mitgestalten. Die Forschenden identifizierten außerdem 10.689 proteinkodierende Gene, von denen über 86 Prozent durch den Abgleich mit mehreren biologischen Datenbanken bekannten Funktionen zugeordnet werden konnten. Viele dieser Gene sind an grundlegenden Zellprozessen, am Stoffwechsel von Zuckern und anderen Molekülen sowie an Reaktionen auf Umweltbedingungen beteiligt — Merkmale, die direkt relevant für die Agarproduktion und die Anpassung an Stress sind.
Eine neue Grundlage für zukünftige Arbeiten
Indem diese Arbeit ein genomisches Referenzwerk auf Chromosomenebene für Gracilaria vermiculophylla liefert, verwandelt sie ein zuvor unscharfes genetisches Bild in einen detaillierten Atlas. Für die Industrie bietet sie eine Karte, um Gene zu identifizieren, die an Agarqualität und -ausbeute beteiligt sind, und damit potenziell gezielte Züchtung oder biotechnologische Verbesserungen zu ermöglichen. Für Ökologen und Evolutionsbiologen liefert sie die Werkzeuge, um zu erforschen, wie diese Alge in neuen Lebensräumen und unter sich verändernden klimatischen Bedingungen gedeiht. Kurz: Diese Genomassemblierung macht G. vermiculophylla aus einer nützlichen, aber genetisch rätselhaften Alge zu einem gut kartierten Modellorganismus für Ernährung, Industrie und Umweltwissenschaften.
Zitation: Jian, J., Luo, Y., Xu, J. et al. Chromosome-level genome assembly of agar-producing red seaweed Gracilaria vermiculophylla. Sci Data 13, 334 (2026). https://doi.org/10.1038/s41597-026-06635-3
Schlüsselwörter: Genom der Rotalge, Agarproduktion, marine invasive Art, chromosomenaufgelöste Assemblierung, Gracilaria vermiculophylla