Clear Sky Science · de
Chromosomenebene Genomassemblierung der Steinfliege Rhopalopsole triangulispina Mo und Li, 2025 (Plecoptera: Leuctridae)
Warum ein winziges Bachinsekt wichtig ist
In rauschenden Bergbächen weltweit signalisieren kleine, zarte Insekten, die Steinfliegen genannt werden, still und deutlich den Zustand des Wassers. Ihre Larvenstadien, die Nymphen, sind so empfindlich gegenüber Verschmutzung, dass ihr Vorhandensein oft bedeutet, dass der Bach sauber und gut mit Sauerstoff versorgt ist. Trotz dieser ökologischen Bedeutung wussten Wissenschaftler überraschend wenig über die detaillierte genetische Ausstattung vieler Steinfliegenarten. Diese Studie liefert eine hochwertige Genomkarte auf Chromosomenebene für eine solche Art, Rhopalopsole triangulispina, und eröffnet damit neue Einblicke in die Evolution dieser Insekten sowie in ihre Nutzung zum besseren Schutz von Süßwasserökosystemen.
Leben in klarem, schnell fließendem Wasser
Steinfliegen der Überfamilie Nemouroidea gehören zu den artenreichsten und reichsten Gruppen dieser Insekten und leben in kalten, sauberen Bächen, Seen und Teichen – oft versteckt zwischen Steinen oder Sedimenten. Ihre Nymphen sind auf gute Wasserqualität angewiesen: Temperatur, Sauerstoffgehalt, chemische Belastung und sogar die Beschaffenheit des Bachbetts können den Unterschied zwischen gedeihen und Verschwinden bedeuten. Aufgrund dieser Empfindlichkeit werden sie von Wissenschaftlern als natürliche „Umweltfühler“ bei der Bewertung von Fluss- und Bachgesundheit eingesetzt. Innerhalb der Nemouroidea sind die Familie Leuctridae und die Gattung Rhopalopsole besonders häufig in asiatischen Bergregionen, einschließlich China, vertreten, das mehr als 60 bekannte Rhopalopsole-Arten beherbergt. Trotz dieser Vielfalt fehlen jedoch genetische Referenzkarten, insbesondere vollständig annotierte Genome, was unsere Möglichkeiten einschränkt, ihre Evolution zu untersuchen oder genomische Werkzeuge im Wasserqualitätsmonitoring einzusetzen.
Ein genetischer Lageplan von Grund auf
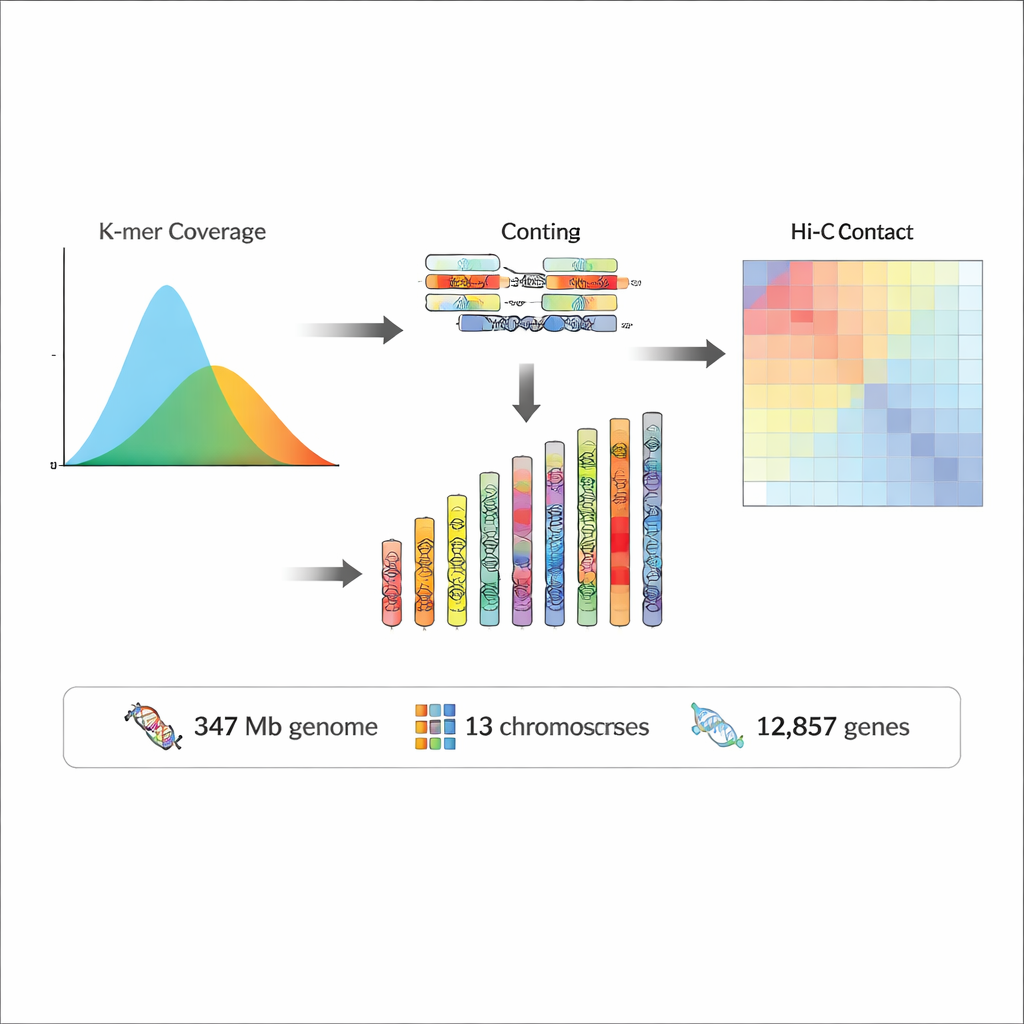
Um diese Lücke zu schließen, sammelten die Forschenden adulte Rhopalopsole triangulispina in einem geschützten Bergreservat im Süden Chinas. Nach sorgfältiger Konservierung der Exemplare isolierten sie hochwertige DNA und RNA (das Molekül, das widerspiegelt, welche Gene aktiv sind). Mithilfe mehrerer moderner Sequenzierungstechnologien erzeugten sie unterschiedliche Sichten auf das Genom: sehr genaue lange DNA-Lesungen (PacBio HiFi), große Mengen kurzer Lesungen (Illumina) und spezielle Daten, die erfassen, wie DNA-Stücke im Zellkern gefaltet sind und miteinander interagieren (Hi-C). Zusammen ermöglichten diese Datentypen dem Team, das genetische Material der Art in lange, zusammenhängende Sequenzen zu assemblieren und die Hi-C-Informationen zu nutzen, um diese in 13 chromosomenähnliche Strukturen, sogenannte Pseudochromosomen, anzuordnen.
Was das Genom enthüllt
Das fertige Genom umfasst etwa 347 Millionen „Buchstaben“ der DNA, wobei fast 97 % davon auf die 13 Pseudochromosomen platziert wurden. Qualitätsprüfungen zeigten, dass die Assemblierung sowohl sehr vollständig als auch außerordentlich genau ist, mit geschätzten Fehlerraten von weniger als eins pro zehn Millionen Basen und über 95 % aller Sequenzierungslesungen, die wieder auf das Genom abbilden. Fast die Hälfte des Genoms besteht aus repetitiver DNA – Abschnitten, die vielfach vorkommen und oft mobile genetische Elemente oder „springende Gene“ widerspiegeln, die das Genom im Verlauf der Evolution geprägt haben. Auf dieser Grundlage sagte das Team 12.857 protein-codierende Gene sowie mehr als 2.400 nicht-kodierende RNA-Gene voraus, zu denen Moleküle gehören, die am Aufbau von Ribosomen beteiligt sind, RNA verarbeiten und die Proteinproduktion steuern. Durch den Vergleich dieser Gene mit großen internationalen Datenbanken konnten sie wahrscheinliche Funktionen für die Mehrheit ableiten und viele Gene mit bekannten biologischen Stoffwechselwegen verknüpfen.
Eine neue Ressource für Evolution und Ökologie
Über die bloße Katalogisierung von Genen hinaus dient dieses Genom als Nachschlagewerk für zukünftige Studien. Forschende können nun untersuchen, welche Gene Steinfliegen helfen, sich an kaltes, schnell strömendes Wasser anzupassen, wie sie auf molekularer Ebene auf Verschmutzung oder Klimawandel reagieren und wie verschiedene Steinfliegenlinien zueinander verwandt sind. Bisher basierten die meisten evolutionären Untersuchungen an Nemouroidea auf Merkmalen des Körpers, mitochondrialer DNA oder Teilgensets. Dieses vollständige, annotierte Genom bietet eine viel reichere und präzisere Grundlage, um den Stammbaum der Steinfliegen zu rekonstruieren und Genome über Insekten hinweg zu vergleichen, einschließlich solcher mit sehr unterschiedlichen Lebensweisen. Da alle Rohdaten und Annotationen öffentlich verfügbar sind, können Forschende weltweit die Informationen neu analysieren, mit anderen Datensätzen integrieren und neue Werkzeuge für das Biomonitoring entwickeln.
Vom DNA-Plan zu saubereren Bächen
Für Nichtfachleute ist die zentrale Erkenntnis, dass wir nun einen detaillierten Genomplan auf Chromosomenebene für eine Steinfliegenart haben, die als Wächter der Süßwasserqualität fungiert. Dieses Genom wird Wissenschaftlern helfen zu verstehen, wie diese Insekten leben und sich anpassen, ihre tiefe evolutionäre Geschichte nachzuzeichnen und empfindlichere, DNA-basierte Methoden zu entwickeln, um sie in Flüssen und Bächen nachzuweisen. In der Praxis bedeutet das bessere Frühwarnsysteme für Verschmutzung und Umweltveränderungen. Indem die genetischen Grundlagen eines kleinen Insekts aus Bergbächen entschlüsselt werden, trägt diese Arbeit letztlich zum Schutz des sauberen Wassers bei, von dem Menschen und Ökosysteme abhängen.
Zitation: Lin, A., Cao, J., Murányi, D. et al. Chromosome-level genome assembly of the stonefly Rhopalopsole triangulispina Mo and Li, 2025 (Plecoptera: Leuctridae). Sci Data 13, 292 (2026). https://doi.org/10.1038/s41597-026-06631-7
Schlüsselwörter: Genom der Steinfliege, Süßwasser-Bioindikatoren, Assemblierung auf Chromosomenebene, Insektenentwicklung, Umwelt-DNA