Clear Sky Science · de
Metagenome und metagenomisch-assemblierte Genome von globalen Tiefsee‑Hydrothermalerzen im Zeit‑ und Raumverlauf
Leben in den dunkelsten Teilen des Ozeans
Tief unter der Reichweite des Sonnenlichts schaffen Tiefsee‑Quellen, sogenannte Hydrothermalquellen, Oasen des Lebens auf dem sonst kargen Meeresboden. An diesen Orten gedeihen ungewöhnliche, hitzeliebende Mikroben, die wichtige globale Stoffkreisläufe antreiben und möglicherweise einigen der frühesten Lebensformen der Erde ähneln. Die hier beschriebene Studie konzentriert sich nicht auf ein einzelnes neues Organismus, sondern liefert einen umfangreichen, langfristigen genetischen Katalog der Mikroben, die in diesen extremen Lebensräumen vorkommen — eine offene Ressource, die Entdeckungen in den Bereichen Evolution, Biotechnologie und den möglichen künftigen Auswirkungen des Tiefseebergbaus befeuern wird.
Verborgene heiße Quellen rund um die Welt
Hydrothermalquellen entstehen, wenn Meerwasser in die ozeanische Kruste eindringt, sich erhitzt und als metal‑ und gasbeladene Flüssigkeit zum Meeresboden zurücksteigt. Wenn diese heiße Flüssigkeit auf kaltes Meerwasser trifft, bilden sich schornsteinähnliche Mineralkörper, die schnell von Mikroben besiedelt werden, die statt Sonnenlicht Chemikalien zur Energiegewinnung nutzen können. Bis vor Kurzem waren die meisten dieser thermophilen Bakterien und Archaeen nur anhand von Fragmenten eines einzelnen Gens bekannt, sodass die Wissenschaft weitgehend im Dunkeln darüber tappte, welche Funktionen sie wirklich erfüllen. Dieser neue Ansatz vereint Proben, die über 16 Jahre hinweg aus 21 Schloten in Atlantik, Pazifik und Indik gesammelt wurden, und verwandelt verstreute Expeditionen in eine kohärente globale Zeitreihe. 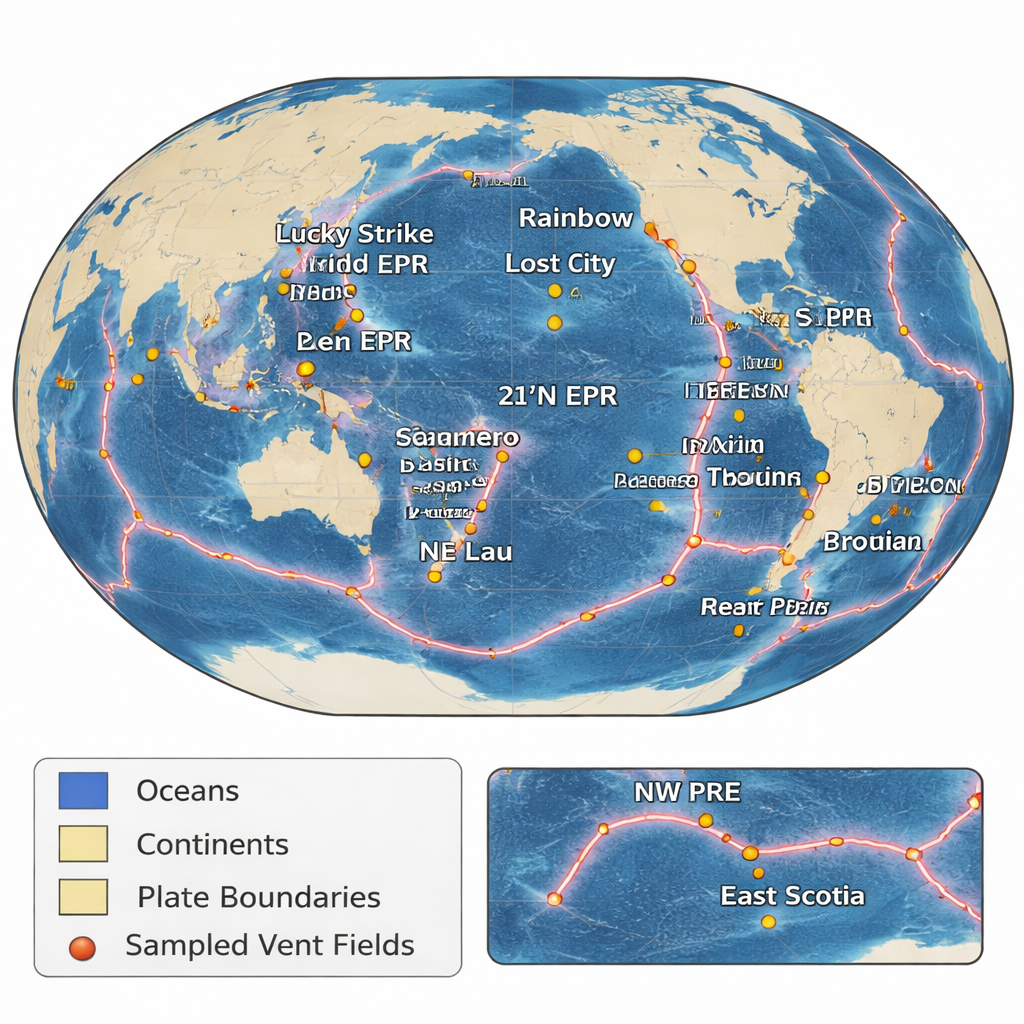
Vom Meeresbodenmineral zu Genomen
Um herauszufinden, welche Mikroben in diesen Ablagerungen leben und welche Funktionen sie ausüben, nutzte das Team einen metagenomischen Ansatz: Statt zu versuchen, jede Art im Labor zu kultivieren, extrahierten sie die gesamte DNA direkt aus den Schlottmineralien. Hochdurchsatzsequenzierung erzeugte enorme 3,56 Billionen Basenpaare Rohdaten aus 70 Proben. Nach sorgfältiger Qualitätskontrolle zur Entfernung minderwertiger und kontaminierender Sequenzen setzten spezialisierte Software‑Tools die verbleibenden DNA‑Stücke zu längeren Fragmenten zusammen und gruppierten sie anschließend zu Tausenden von Entwurfsgenomen, sogenannten metagenomisch assemblierte Genome (MAGs). Dieser stufenweise Prozess — vom Schloten‑Sampling über DNA‑Sequenzierung bis zur Genomrekonstruktion — schafft eine Art molekularen Zensus jeder Schlottgemeinschaft.
Ein umfangliches Familienalbum für Tiefseemikroben
Das Ergebnis ist der DSV70‑Datensatz: 7.422 Genome mittlerer bis hoher Qualität von hitzeliebenden Bakterien und Archaeen. Diese Genome decken mindestens 16 archäische Gruppen und 85 bakterielle Gruppen ab, einschließlich vieler Linien, die in bestehenden Datenbanken schlecht vertreten oder völlig fehlend sind. Manche mikrobiellen Gruppen, die an Schloten häufig vorkommen, wie Campylobacterota und bestimmte Proteobacteria, sind besonders gut repräsentiert, doch erweitert der Datensatz auch erheblich die genomische Abdeckung wenig erforschter archäischer Zweige wie Thermoproteota und der kleinzelligen DPANN‑Linien. Insgesamt wurden mehr als 29 Millionen vorhergesagte Proteine identifiziert, von denen viele bekannten metabolischen Funktionen zugeordnet sind. Das bietet einen reichen Fundus zum Verständnis, wie Schlottmikroben chemische Energie nutzen, Elemente recyceln und miteinander sowie mit der Schlottchemie interagieren. 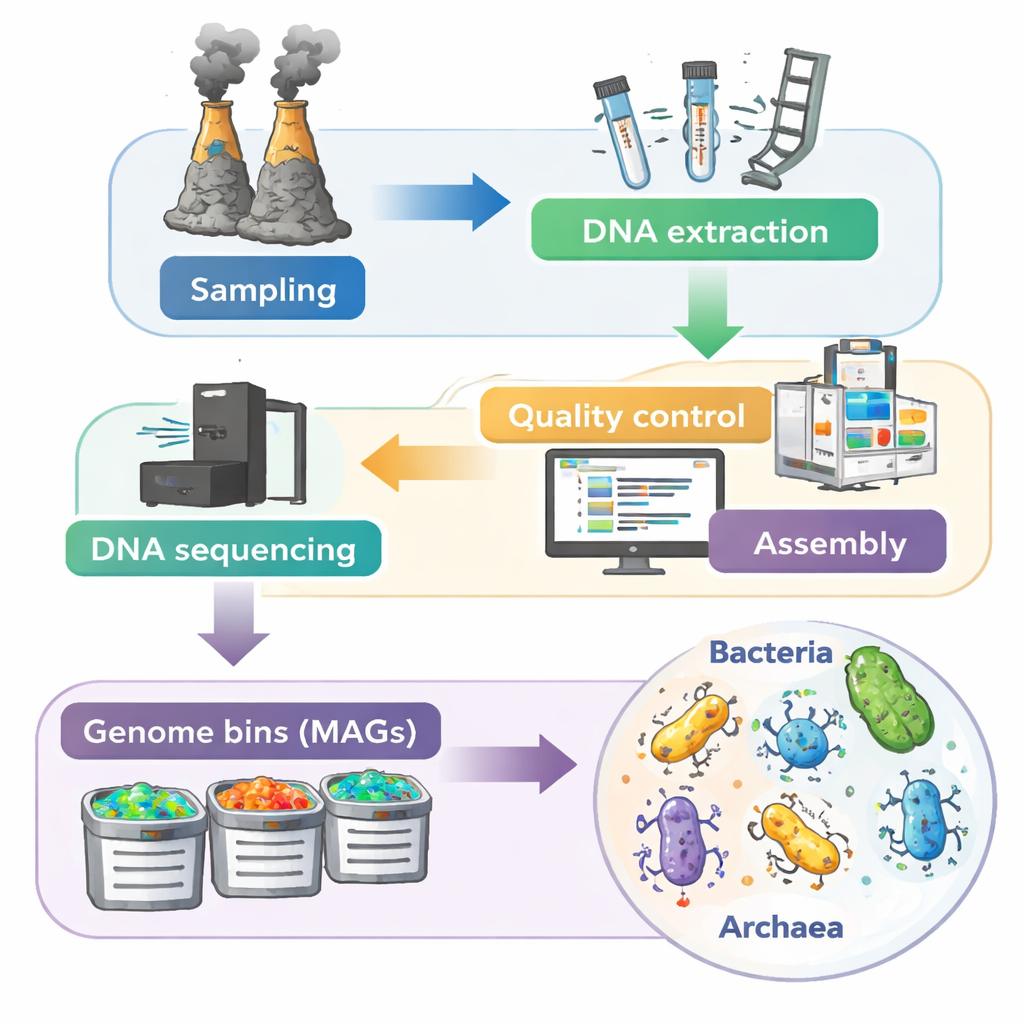
Veränderungen über Raum, Zeit und Temperatur verfolgen
Da die Proben aus vielen Standorten stammen und sich über mehr als ein Jahrzehnt erstrecken, ermöglicht der Datensatz Wissenschaftlern, zu untersuchen, wie sich Schlottmikrobengemeinschaften im Laufe der Zeit und in unterschiedlichen geologischen Umgebungen verändern. Die Autoren kombinierten ihre neuen Sequenzen mit früheren Metagenom‑Sammlungen aus ähnlichen Habitaten, um eine statistisch fundierte Basis für den Vergleich von Schloten an verschiedenen Rücken und Back‑Arc‑Becken zu schaffen. Forschende können nun Fragen untersuchen wie: Welche Mikroben kommen überall vor und welche nur an bestimmten Schloten? Wie eng verwandt sind Tiefseemikroben mit denen terrestrischer heißer Quellen? Und wie könnte sich die Gemeinschaftsstruktur auf Ereignisse wie Ausbrüche, natürliche Klimaschwankungen oder menschliche Aktivitäten wie Tiefseebergbau reagieren?
Warum dieser genomische Atlas wichtig ist
Alle Rohsequenzen, zusammengefügten DNA‑Fragmente und rekonstruierten Genome wurden in öffentlichen Repositorien hinterlegt und schaffen damit praktisch eine globale Referenzbibliothek für hydrothermale Tiefsee‑Mikroben. Für Nicht‑Spezialisten ist die zentrale Erkenntnis, dass Wissenschaftlern nun ein detaillierter genetischer Schnappschuss des Lebens in einigen der extremsten — und zunehmend bedrohten — Umgebungen der Erde vorliegt. Diese Ressource wird Forschende dabei unterstützen, neue Enzyme für industrielle und medizinische Anwendungen zu identifizieren, die mikrobiellen Äste im Stammbaum des Lebens zu verfeinern und eine Grundlage für die Überwachung möglicher Veränderungen von Tiefseeökosystemen zu schaffen, wenn sich der Ozean erwärmt und Bergbauinteressen bis in die Tiefen vordringen.
Zitation: St. John, E., Reysenbach, AL. Global deep-sea hydrothermal deposit metagenomes and metagenome-assembled genomes over time and space. Sci Data 13, 283 (2026). https://doi.org/10.1038/s41597-026-06612-w
Schlüsselwörter: Tiefsee‑Hydrothermalquellen, mikrobielle Genome, Metagenomik, Extremophile, ozeanische Biodiversität