Clear Sky Science · de
Neubestimmung des gesamten Genoms und genetische Vielfalt von fünf einheimischen Rinderrassen aus China
Warum lokale Rinder uns alle betreffen
In der chinesischen Provinz Sichuan sind Kleinbauern auf robuste gelbe Rinder angewiesen, die steile Hänge, heiße, feuchte Sommer und karge Fütterung verkraften. Diese Tiere sichern stillschweigend die Nahrungsvorsorge und ländliche Lebensgrundlagen, doch ihre einzigartigen Eigenschaften sind bedroht, weil moderne Rassen und Kreuzungen sich ausbreiten. Diese Studie liest nahezu jeden Buchstaben der DNA mehrerer Sichuan-Rinderrassen und erstellt eine detaillierte genetische Karte, die helfen kann, diese Tiere zu schützen, die Rindfleischproduktion zu verbessern und das Vieh auf einen sich wandelnden Klimazustand vorzubereiten.
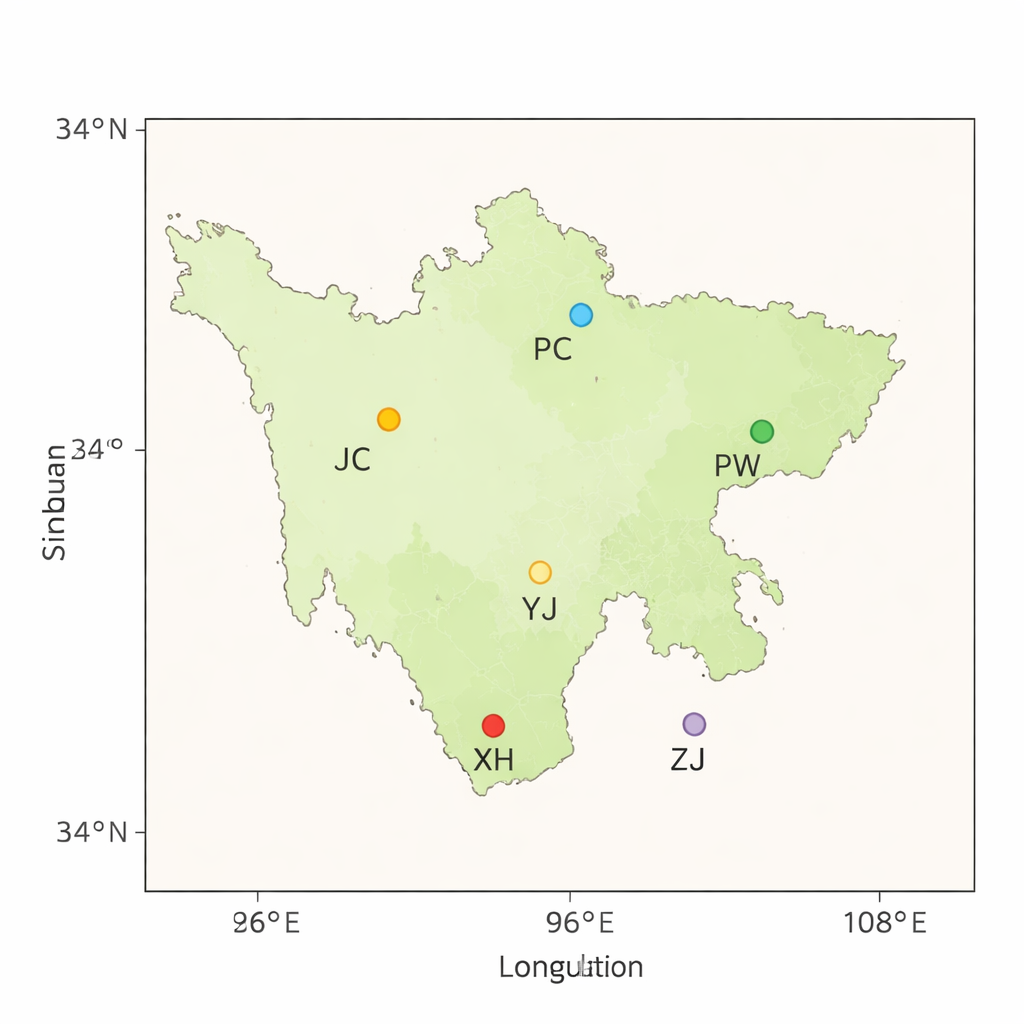
Rinder für raue Landschaften
Sichuan ist einer der Hotspots der Rinderdiversität Chinas, mit Millionen von Tieren, die sich über Becken, Hügel und Hochländer verteilen. Die lokalen gelben Rinder wurden durch Jahrhunderte des Überlebens in rauen Umgebungen und durch die sorgfältige Auswahl von Bauern geprägt, die Wert auf Kraft, Krankheitsresistenz und die Fähigkeit legten, von grobem Futter zu leben. Trotzdem sehen sich diese Rassen heute schrumpfenden Beständen und genetischer Erosion gegenüber. Unkontrollierte Kreuzungen, saisonale Wanderungen der Herden, Krankheitsausbrüche, Überschwemmungen und die schnelle Durchmischung der Tiere über den Handel verwischen die Grenzen zwischen traditionellen Rassen. Ohne gezielte Erhaltungsmaßnahmen könnten die ausgeprägten biologischen Stärken dieser Rinder verloren gehen.
Die gesamte genetische Geschichte lesen
Um diese Vielfalt zu verstehen und zu schützen, sammelten die Forscher Blutproben von 56 gelben Rindern aus fünf Landkreisen Sichuans, wobei jeder Landkreis eine lokale Rasse repräsentierte. Außerdem bezogen sie DNA von 10 hochalpinen Yaks als Vergleichsgruppe (Outgroup), um die Genetik der Rinder in einen breiteren evolutiven Kontext zu stellen. Mit modernen Hochdurchsatz-Sequenziermethoden erzeugten sie etwa 2,3 Terabyte an DNA-Daten und lasen das Genom jedes Tieres etwa 13-fach, um Genauigkeit zu gewährleisten. Die Reads wurden dann an ein Standard-Rinderreferenzgenom ausgerichtet; mehr als 99 % landeten an der richtigen Stelle, ein Hinweis auf sehr hohe Datenqualität.
Millionen Unterschiede im DNA-Code
Nachdem die Genome ausgerichtet waren, durchsuchte das Team sie nach verschiedenen Arten genetischer Variation. Sie fanden etwa 31 Millionen Einzelbasenveränderungen in der DNA-Sequenz sowie mehr als zwei Millionen kleine Einfügungen und Deletionen, zehntausende größere strukturelle Veränderungen und über 240.000 Regionen, in denen DNA-Abschnitte fehlen oder dupliziert sind. Die meisten dieser Unterschiede liegen außerhalb der protein-kodierenden Bereiche von Genen, aber eine erhebliche Zahl fällt innerhalb oder in der Nähe von Genen, die wichtige Merkmale beeinflussen könnten. Das Muster der Veränderungen über die Chromosomen hinweg, insbesondere das auffällige Verhalten des X-Chromosoms, spiegelt sowohl die Biologie der Rinder als auch die evolutionären Kräfte wider, denen sie im Laufe der Zeit ausgesetzt waren.
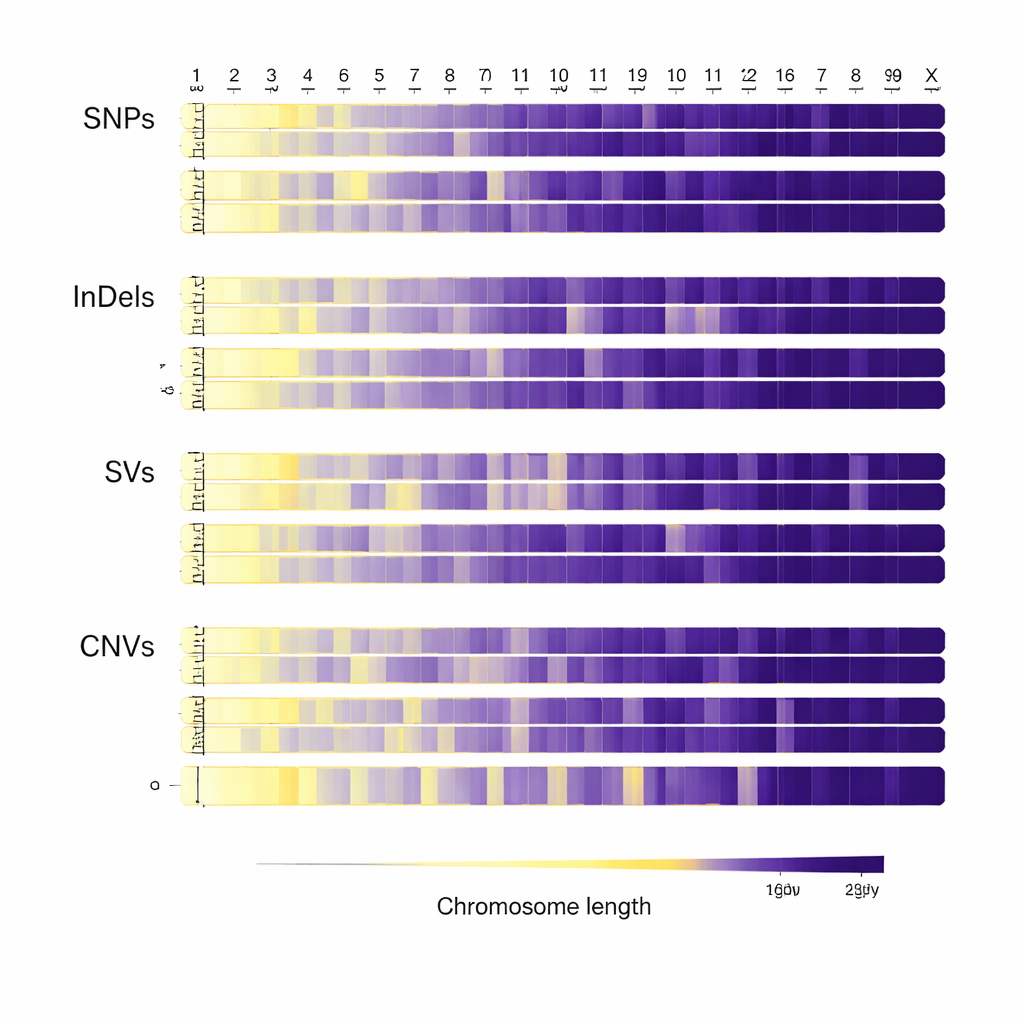
Rohdaten in biologischen Erkenntnisgewinn verwandeln
Entscheidend ist, dass die Forscher mehr taten, als nur DNA-Veränderungen zu zählen — sie annotierten diese, um mögliche Auswirkungen auf die Genfunktion vorherzusagen. Mit weit verbreiteten Bioinformatik-Tools verknüpften sie jede Variante mit ihrer Position in oder nahe bei Genen und hoben Veränderungen hervor, die Proteine stören oder die Genregulation verändern könnten. Anschließend stellten sie alle Rohsequenzdaten und verarbeiteten Variantenlisten frei in internationalen Datenbanken zur Verfügung. Diese Offenheit ermöglicht es Wissenschaftlern weltweit, die Daten zu durchsuchen, um Gene zu finden, die mit Hitze‑ und Feuchtigkeitstoleranz, Krankheitsresistenz, effizienter Nutzung minderwertigen Futters und Fleischqualität in Verbindung stehen, oder um Sichuan-Rinder mit anderen Rassen zu vergleichen.
Vom verborgenen Code zum praktischen Nutzen
Für Nichtfachleute lässt sich diese Arbeit als hochauflösende genetische Momentaufnahme einiger der härtesten Rinder Chinas betrachten. Indem sie die DNA-Unterschiede detailliert katalogisiert und die Ergebnisse offen geteilt hat, legt die Studie die wesentlichen Grundlagen für Zuchtprogramme, die die Widerstandsfähigkeit traditioneller Tiere bewahren und gleichzeitig die Produktivität verbessern. In einer Zukunft mit klimatischem Stress und veränderten Krankheitsmustern wird diese Information Landwirten und Züchtern helfen, robuste, lokal angepasste Rinder zu erhalten, die eine nachhaltige Rindfleischproduktion unterstützen und ein unersetzliches Stück landwirtschaftlichen Erbes schützen.
Zitation: Wang, W., Li, L., Chen, Y. et al. Whole-genome resequencing and genetic diversity of five indigenous cattle breeds from China. Sci Data 13, 282 (2026). https://doi.org/10.1038/s41597-026-06610-y
Schlüsselwörter: Rindergenetik, einheimische Rassen, genetische Vielfalt, Whole-Genome-Sequencing, Tierbestandserhaltung