Clear Sky Science · de
Chromosomenebene Genomassemblierung und Annotation des tropischen Seegurke Holothuria fuscocinerea
Warum eine unscheinbare Seegurke wichtig ist
Seegurken mögen auf dem Meeresboden wie sandbedeckte Würste aussehen, doch sie sind stille Arbeitspferde tropischer Riffe und werden zunehmend Gegenstand von Fischerei und medizinischer Forschung. Da die Nachfrage nach diesen Tieren steigt und wilde Bestände unter Druck geraten, benötigen Wissenschaftler genaue genetische Informationen, um sie verantwortungsvoll zu bewirtschaften und ihre biochemischen Potenziale zu nutzen. Diese Studie liefert die erste Genomkarte auf Chromosomenebene von Holothuria fuscocinerea, einer weit verbreiteten tropischen Seegurke, und schafft damit einen Referenzbauplan, den künftige Ökologen, Züchter und Wirkstofffinder verwenden können.
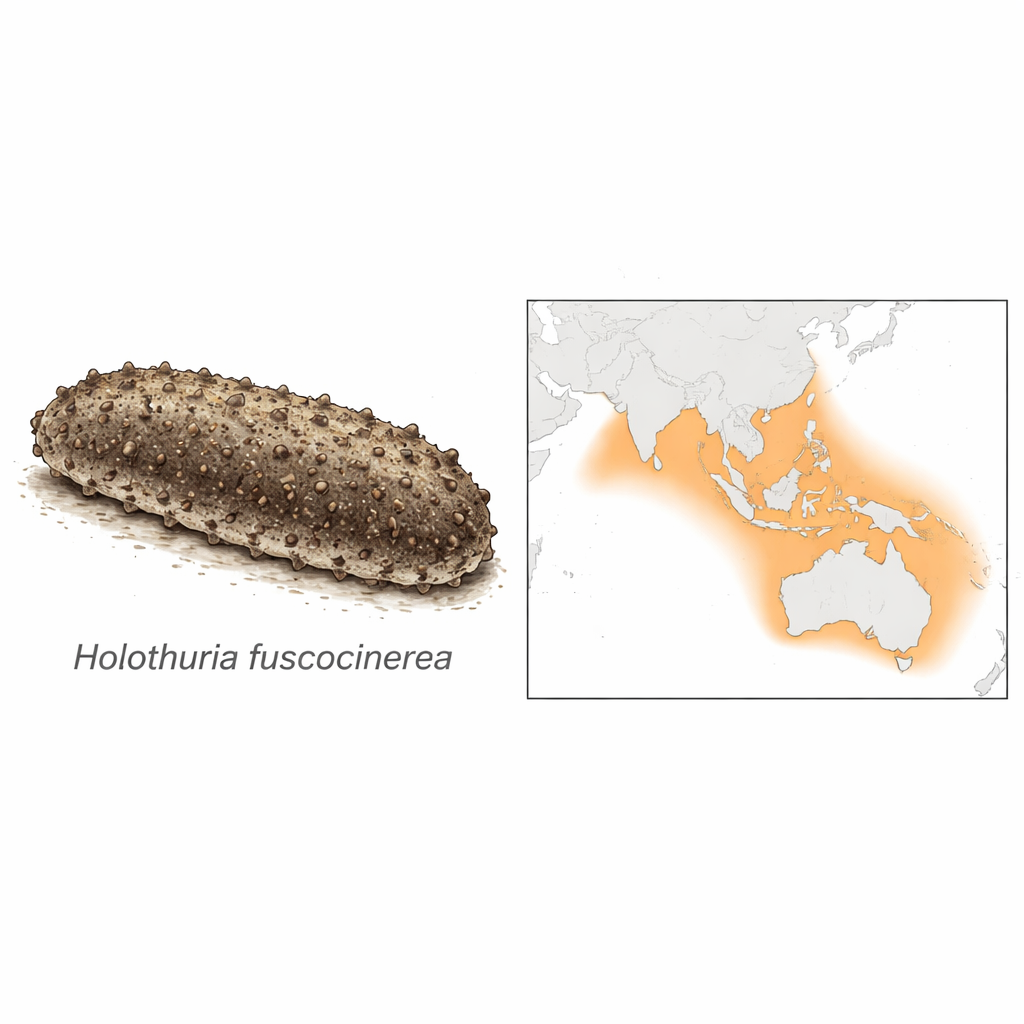
Ein weit verbreiteter Reiniger tropischer Meere
Holothuria fuscocinerea kommt auf warmen Riffen vom Roten Meer und Ostafrika über den Indischen und Pazifischen Ozean bis nach China, Südjapan, Nordaustralien und entfernte Pazifikinseln vor. Sie wird typischerweise etwa einen halben Meter lang, hat einen ovalen, leicht abgeflachten Körper, dessen grob braun-graue Oberseite oft eine Sandschicht trägt, die ihm hilft, sich in den Meeresboden einzufügen. Wie viele Verwandte besitzt sie spezielle Abwehrstrukturen, die Cuvier’schen Tubuli, die bei Bedrohung ausgestoßen werden können. Obwohl ihr kommerzieller Wert derzeit im Vergleich zu einigen begehrten „Seegurken“-Arten moderat ist, wird erwartet, dass sie mit dem Rückgang höherwertiger Bestände vermehrt Ziel der Fischerei wird; zudem produziert sie bioaktive Verbindungen mit antimikrobiellen, immunstimulierenden und anticanceren Potenzial.
Der Bedarf an einem vollständigen genetischen Bauplan
Seegurken erfüllen mehrere ökologische Funktionen: Sie durchmischen und reinigen Sedimente, recyceln Stickstoff, helfen, die Chemie des Meerwassers zu regulieren, und stützen Nahrungsnetze auf Korallenriffen und anderen Küstenhabitaten. Gleichzeitig werden viele Arten intensiv befischt und erholen sich nur langsam, weshalb Zuchtanstalten Jungtiere zur Auswilderung aufziehen und Tiere zwischen Regionen verlagern. Ohne ein vollständiges Genom war es jedoch schwierig, Populationsstrukturen zu verfolgen, verborgene Durchmischung zwischen wildlebenden und gezüchteten Beständen zu erkennen oder nachzuvollziehen, wie diese Tiere ihre ungewöhnlichen Eigenschaften entwickelt haben — etwa weiche Gewebe, die rasch ihre Festigkeit ändern können, und abwerfbare Abwehrorgane. Bisher konzentrierte sich die Forschung an H. fuscocinerea auf lokale Häufigkeit, Identifikation, Nahrung und einzelne chemische Verbindungen, während genetische Studien überwiegend auf kurzen mitochondrialen Sequenzen beruhten, sodass die stammesgeschichtlichen Beziehungen der Art teilweise ungeklärt blieben.
Das Genom der Seegurke aufbauen
Die Forschenden kombinierten mehrere moderne DNA-Sequenzierungsstrategien, um das Genom in nahezu chromosomaler Auflösung zu assemblieren. Kurzlese-Sequenzierung lieferte große Mengen genauer, kleiner DNA-Schnipsel; Langlese-Sequenzierung erzeugte fortlaufende Abschnitte, die repetitive Regionen überbrücken; und Hi-C-Mapping erfasste die dreidimensionale Faltung der DNA im Zellkern und zeigte, welche Fragmente zu demselben Chromosom gehören. Mit spezieller Software setzten sie diese Daten zu 541 zusammenhängenden Stücken zusammen und ordneten und orientierten sie anschließend zu 23 Pseudochromosomen, die zusammen etwa 1,56 Milliarden DNA-Basenpaare abdecken. Qualitätsprüfungen zeigten, dass die Assemblierung sehr vollständig und genau ist, mit wenigen Lücken und starker Bestätigung durch unabhängige Messungen von Geninhalt und Fehlerrate.
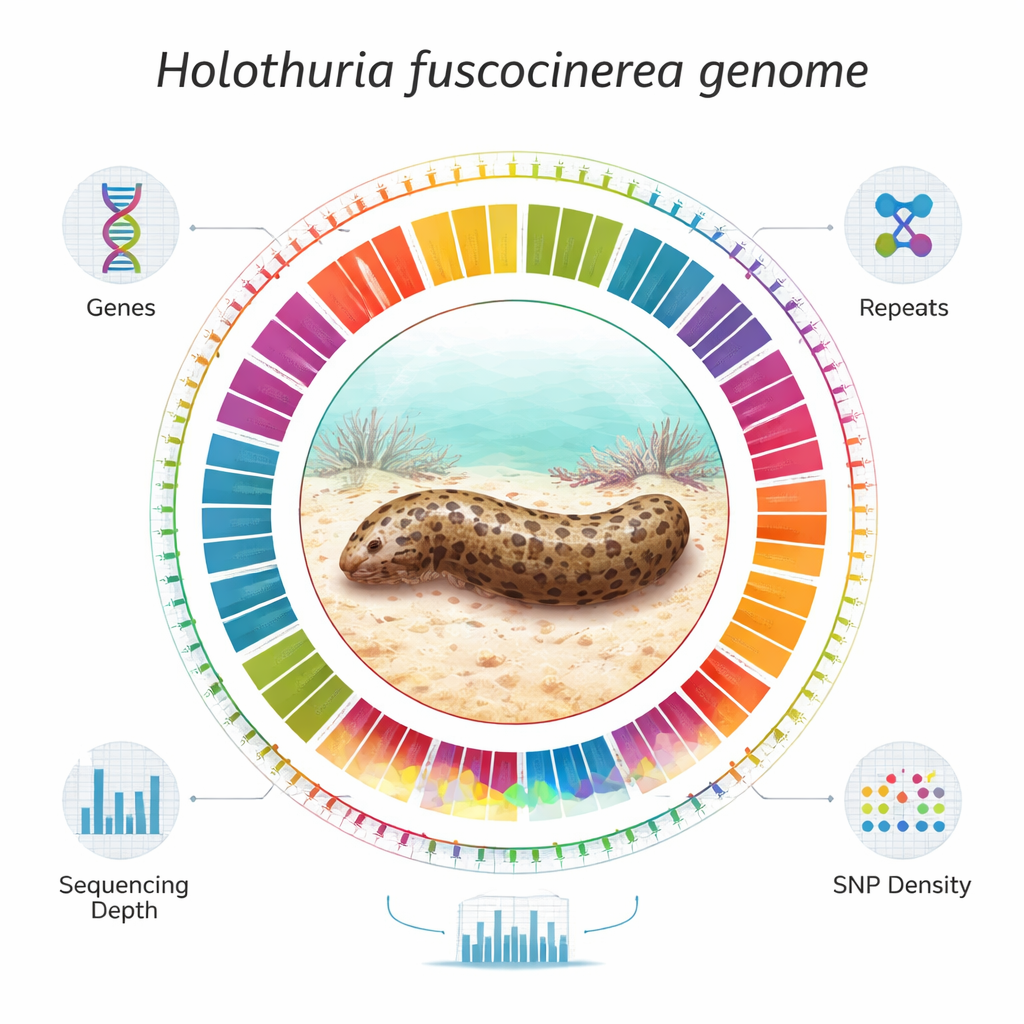
Was das Genom im Inneren offenbart
Mit den zusammengesetzten Chromosomen katalogisierte das Team systematisch die genetischen Elemente. Sie identifizierten fast 30.000 proteinkodierende Gene und überprüften deren Strukturen mithilfe von RNA aus zehn verschiedenen Geweben, darunter Haut, Darm, Tentakel, Abwehrorgane und Fortpflanzungsorgane. Etwa 95 Prozent dieser Gene ließen sich über große biologische Datenbanken bekannten Funktionen oder Familien zuordnen. Ungefähr die Hälfte des Genoms besteht aus repetitiver DNA, vor allem mobilen genetischen Elementen, sogenannten Transposons, die die Größe und Evolution des Genoms prägen können. Die Forschenden kartierten zudem tausende nichtkodierende RNAs und lokalisierte viele Chromosomenden (Telomere) sowie wahrscheinliche Zentromerregionen, was zeigt, dass große Teile des Genoms end-zu-end zusammengefügt sind. Sie rekonstruierten sogar das vollständige mitochondriale Genom als separates, kompaktes zirkuläres Molekül.
Eine Grundlage für Schutz und Entdeckung
Für Nichtfachleute ist die zentrale Botschaft: Wir verfügen jetzt über eine hochwertige, nahezu vollständige genetische Referenz für eine ökologisch wichtige und zunehmend ausgebeutete tropische Seegurke. Diese Referenz ermöglicht es Wissenschaftlern, die genetische Vielfalt in wilden und gezüchteten Beständen zu verfolgen, bessere Zucht- und Wiedereinbürgerungsprogramme zu entwickeln und H. fuscocinerea mit anderen Seegurken zu vergleichen, um die Gene hinter ihrer flexiblen Körperstruktur, ungewöhnlichen Abwehrmechanismen und medizinisch vielversprechenden Chemie zu entschlüsseln. Praktisch dient das Genom wie ein Atlas für diese Art, der Bemühungen leitet, Riffökosysteme zu schützen, küstennahe Lebensgrundlagen zu erhalten, die von Seegurken abhängen, und neue, aus dem Meer gewonnene Arzneimittel zu erforschen.
Zitation: Wang, X., Huang, Q., Qin, Z. et al. Chromosome-level genome assembly and annotation of the tropical sea cucumber Holothuria fuscocinerea. Sci Data 13, 281 (2026). https://doi.org/10.1038/s41597-026-06609-5
Schlüsselwörter: Genom der Seegurke, Holothuria fuscocinerea, Meeresnaturschutz, Assemblierung auf Chromosomenebene, Ökologie tropischer Riffe