Clear Sky Science · de
Telomer-zu-Telomer lückenfreie Genomassemblierung von Opsariichthys evolans (Cypriniformes: Cyprinidae)
Ein Bachfisch mit genomischer Geschichte
Stürmische Gebirgsbäche im Südosten Chinas und auf Taiwan sind die Heimat eines kleinen, farbenprächtigen Fisches namens Opsariichthys evolans. Außerhalb der Region wenig bekannt, ist diese Art ein ökologischer Schlüsselspieler und ein Naturkunstwerk: leuchtende Streifen und auffällige Laichfarben zeichnen sie aus. Seit mehr als einem Jahrhundert streiten Wissenschaftler darüber, wie sie einzuordnen ist und wo sie in den Stammbaum der Süßwasserfische gehört. Diese Studie liefert ein wesentliches Puzzlestück: das erste vollständige, lückenfreie Genom von O. evolans, gelesen von einem Chromosomenende bis zum anderen.
Warum dieser Fisch wichtig ist
O. evolans lebt in klaren, fließenden Bächen, wo er zur Stabilität von Nahrungsnetzen beiträgt und als empfindlicher Indikator für Wasserqualität dient. Männchen entwickeln während der Laichzeit auffällige Seitenstreifen und granuläre Höcker am Kopf und um die Augen sowie eine dunkle, schwärzlich-violette Schnauze. Diese markanten Merkmale, kombiniert mit der Vorliebe der Art für schnell fließendes Wasser, machen sie zu einem idealen Modell, um zu untersuchen, wie Tiere sich an ihre Lebensräume anpassen. Gleichzeitig schrumpfen die Bestände durch menschengemachte Veränderungen – Verschmutzung, Habitatfragmentierung und invasive Arten – weshalb das Verständnis ihrer Biologie für den Schutz wichtig ist.
Ein langwieriges Namenswirrwarr
Jahrzehntelang rangen Biologen um die Frage, ob O. evolans zur Gattung Opsariichthys oder zu Zacco gehört. Frühe Taxonomen beschrieben die Art als Zacco evolans und stützten sich vor allem auf äußere Merkmale wie Flossenform und Körperstreifen. Spätere, detailliertere Untersuchungen zeigten, dass das Streifenmuster und die Laichhöcker sich von denen des ähnlich aussehenden Zacco platypus unterscheiden. Mitochondriale DNA-Studien deuteten darauf hin, dass O. evolans am besten in Opsariichthys passt, doch einige nukleare Gen-Daten ließen eine nähere Verbindung zu Zacco vermuten. Ohne ein vollständiges Genom blieb das evolutionäre Bild unscharf, und die Debatte über die richtige Einordnung in den Fischstammbaum ging weiter.

Jeden Buchstaben des Genoms lesen
Um diese Fragen zu klären, sammelten die Forschenden ein wildes Männchen aus einem Fluss in der Provinz Anhui, China, und konservierten neun verschiedene Gewebe sorgfältig. Sie kombinierten mehrere hochmoderne DNA-Sequenzierungstechnologien, die jeweils eigene Stärken haben, um den genetischen Code des Tieres zu lesen. Kurze, sehr genaue Fragmente halfen beim Polieren der Sequenz, während lange und ultralange Reads von PacBio- und Oxford-Nanopore-Plattformen schwierige Regionen überspannten und Chromosomen von einem Ende zum anderen zusammenfügten. Hi-C-Technologie, die erfasst, wie DNA im Zellkern gefaltet ist, wurde verwendet, um die Teile zu vollständigen Chromosomen zu ordnen. Das Endergebnis ist ein telomer-zu-telomer lückenfreies Genom von etwa 0,89 Milliarden Basenpaaren, sauber organisiert in 39 Chromosomen mit je einem durchgehenden DNA-Stück pro Chromosom.
Was das Genom offenbart
Das fertige Genom bestand strenge Qualitätsprüfungen, erfasste mehr als 99 % der erwarteten konservierten Gene und ordnete sich eng an bekannten DNA-Sequenzen verwandter Fische an. Fast die Hälfte des Genoms besteht aus repetitiven Sequenzen, von denen viele „springende Gene“ sind, die sich bewegen und das Genom über evolutionäre Zeiträume umgestalten können. Das Team identifizierte nahezu 30.000 proteinkodierende Gene und tausende nichtkodierende RNAs, von denen die meisten über große biologische Datenbanken mit bekannten Funktionen verknüpft werden konnten. Durch den Vergleich dieses neuen Genoms mit denen zweier naher Verwandter – Opsariichthys bidens und Zacco platypus – fanden die Wissenschaftler, dass die Gesamtstruktur der Chromosomen sehr ähnlich ist, was enge evolutionäre Verbindungen bestätigt. Innerhalb dieses Rahmens identifizierten sie Kandidatengene und Signalwege, die wahrscheinlich an der Körperstreifenfärbung und an Anpassungen an das Leben in schnellen Strömungen beteiligt sind, und lieferten damit Hinweise darauf, wie das markante Aussehen und der Lebensstil entstanden sein könnten.
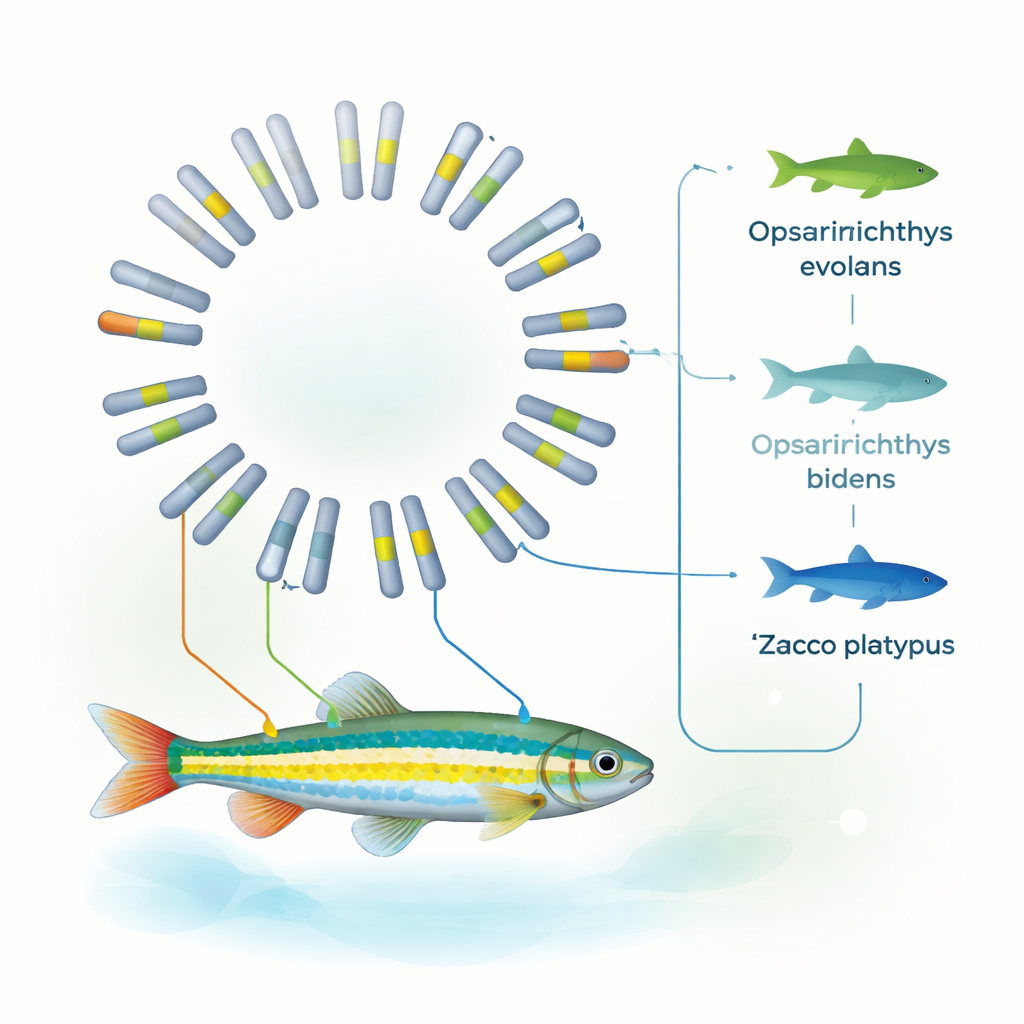
Ihren Platz im Fischstammbaum klären
Mithilfe von Genfamilien, die bei zehn verschiedenen Fischarten gemeinsam vorkommen, rekonstruierten die Forschenden einen detaillierten Evolutionsbaum. Ihre Analyse deutet darauf hin, dass sich O. evolans vor etwa 8 bis 19 Millionen Jahren von Z. platypus abspaltete und dass seine Genomstruktur besonders nahe an der von O. bidens liegt. Zusammen mit früheren mitochondrialen Befunden stützen diese Muster die Einordnung von O. evolans eindeutig in die Gattung Opsariichthys, nicht Zacco. Anders gesagt: Das vollständige Genom bestätigt, was sorgfältige Beobachtungen von Streifen, Schnauzenfarbe und Laichstrukturen nahegelegt hatten — das Aussehen kann täuschen, aber wenn Morphologie und ein komplettes Genom übereinstimmen, werden taxonomische Grenzen deutlich klarer.
Warum ein vollständiges Genom die Spielregeln ändert
Für Nicht-Fachleute ist die Leistung hier wie der Wechsel von einer verschwommenen, zerrissenen Karte zu einem gestochen scharfen Atlas einer Art. Mit einem vollständigen, lückenfreien Genom können Forschende nun die Ursprünge der auffälligen Farben von O. evolans, seine stromlinienförmige Gestalt für das Leben in schnellen Strömungen und seine Verwandtschaft zu anderen ostasiatischen Köcherfischen mit beispielloser Präzision zurückverfolgen. Diese Ressource wird helfen, die Fischklassifikation zu verfeinern, Naturschutzmaßnahmen für gefährdete Bachökosysteme zu lenken und unser Verständnis zu vertiefen, wie kleine Unterschiede in der DNA die reiche Vielfalt der Süßwasserfische erzeugen können.
Zitation: Wang, P., Wang, X., Yin, D. et al. Telomere-to-telomere gap-free genome assembly of the Opsariichthys evolans (Cypriniformes: Cyprinidae). Sci Data 13, 263 (2026). https://doi.org/10.1038/s41597-026-06588-7
Schlüsselwörter: Genomassemblierung, Süßwasserfisch, Telomer-zu-Telomer, Fischevolution, vergleichende Genomik