Clear Sky Science · de
Metabarcoding- und Metagenomikdaten entlang aquatischer Umweltgradienten an den Küsten von Frankreich und Chile
Verborgenes Leben in sich verändernden Meeren
An den Küsten der Welt, von ruhigen Lagunen bis zu dramatischen Fjorden, passt sich mikroskopisches Leben ständig an wechselnde Bedingungen an. Diese winzigen Organismen treiben die Kohlenstoff- und Nährstoffkreisläufe, die Fischbestände, Wasserqualität und sogar das Klima stützen. Dennoch sind viele Küstengewässer, besonders komplexe Lebensräume wie Lagunen und Fjorde, auf genetischer Ebene kaum erforscht. Diese Studie will das ändern, indem sie einen umfangreichen, offenen Datensatz zu Küstenmikroben aus Frankreich und Chile bereitstellt und damit neue Einblicke liefert, wie Meereslebewesen auf eine sich beständig verändernde Umwelt reagieren.
Küsten als natürliche Versuchslabore
Küstengewässer sind selten stabil. Regenfälle, Flusszuflüsse, Verdunstung und Gezeiten können Temperatur und Salzgehalt über kurze Distanzen und Zeiträume stark schwanken lassen. Nährstoffe, die mikroskopische Algen nähren, können plötzlich ansteigen oder versiegen, und menschliche Aktivitäten sorgen für zusätzliche Störungen. Solche Variationen erzeugen ein Mosaik von Lebensräumen, das unterschiedliche mikrobielle Gemeinschaften selektiert und neue Anpassungen begünstigt. Um diese Komplexität zu erfassen, beprobte das Forschungsteam 26 Standorte entlang der französischen und chilenischen Küsten, darunter Lagunen, Flussmündungen, Fjorde, Häfen, Strände, küstennahe Gewässer und einen Offshore-Standort. Einige französische Orte wurden monatlich über ein Jahr hinweg besucht, um die Jahreszeiten zu verfolgen, während die chilenischen Proben im südlichen Herbst entnommen wurden, was einen breiten Schnappschuss kontrastierender Küstenwelten liefert. 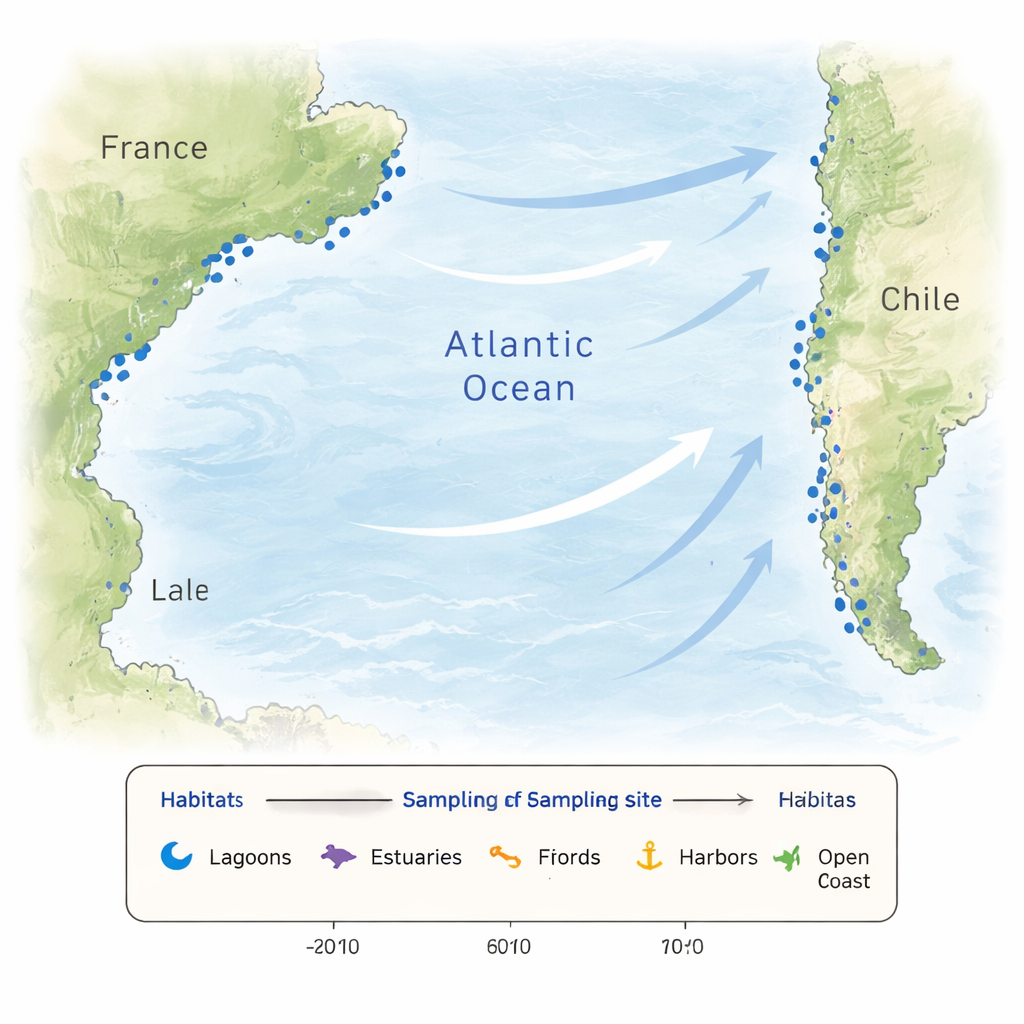
Von Eimern voller Wasser zu DNA-Fingerabdrücken
An jedem Standort sammelte das Team große Wassermengen, überwiegend aus der lichtdurchfluteten Oberfläche, aber auch aus tieferen Schichten in ausgewählten Fjorden und Offshore-Gewässern. Sie maßen grundlegende Umweltbedingungen wie Temperatur, Salzgehalt und Nährstoffe sowie Indikatoren biologischer Aktivität wie Chlorophyll (als Proxy für Algen), gelöste organische Substanz, bakterielle Produktion und Atmung. Im Labor wurden Mikroben auf feinen Filtern konzentriert und deren DNA extrahiert. Ein Satz von Tests konzentrierte sich auf ein standardisiertes Markergen (16S rRNA), das wie ein Barcode zur Identifizierung von Bakterien und Archaeen dient. Dieser Metabarcoding-Ansatz enthüllte mehr als 53.000 unterschiedliche DNA-Varianten und zeigte, dass einige Proben lediglich drei gemeinsame Varianten aufwiesen — ein Hinweis darauf, wie unterschiedlich benachbarte Gemeinschaften sein können.
Genome aus einem genetischen Gemisch rekonstruieren
Die zweite Analyseebene ging einen ambitionierteren Weg: Shotgun-Metagenomik, bei der alle DNA in einer Probe gleichzeitig sequenziert wird. Mit fortschrittlichen Assemblierungs- und Binning-Methoden rekonstruierte das Team 1.372 Entwurfsgenome, sogenannte metagenomisch assemblierte Genome (MAGs). Viele dieser Genome ließen sich nicht bekannten Arten zuordnen, und nur etwa 4 % stimmten mit formell beschriebenen mikrobiellen Arten überein. In manchen Gruppen, etwa bei bestimmten Bakterien und Archaeen, die an ungewöhnliche Bedingungen angepasst sind, hatten mehr als die Hälfte der vorhergesagten Proteine keine bekannte Funktion. Die Forschenden erstellten außerdem einen riesigen Genkatalog mit über 23 Millionen nicht-redundanten Genen und fanden, dass etwa 31 % keine Übereinstimmungen in wichtigen Referenzdatenbanken aufwiesen. Das deutet auf ein tiefes Reservoir uncharakterisierter Biologie in Küstengewässern hin.
Extreme Lebensräume, neuartige Werkzeuge
Einige Standorte, besonders hyper-salzige Lagunen in Frankreich, stachen als Hotspots genetischer Neuheit hervor. Dort schwankte der Salzgehalt innerhalb weniger Monate von nahezu normalem Meerwasser bis zu mehr als dem Doppelten der Meereskonzentration. Solche stressigen Bedingungen könnten sogenannten extremotoleranten Mikroben einen Vorteil verschaffen, die über Enzyme verfügen, die auch bei hohem Salz- oder Temperaturstress funktionieren. Solche Enzyme werden zunehmend für industrielle Anwendungen in Waschmitteln, Biokraftstoffen, Schadstoffsanierung und Lebensmittelverarbeitung gesucht. Indem detaillierte Umweltmessungen mit Gen- und Genomdaten verknüpft werden, hilft dieser Datensatz dabei, Orte zu identifizieren, an denen ungewöhnliche Organismen und biochemische Werkzeuge am wahrscheinlichsten zu finden sind. 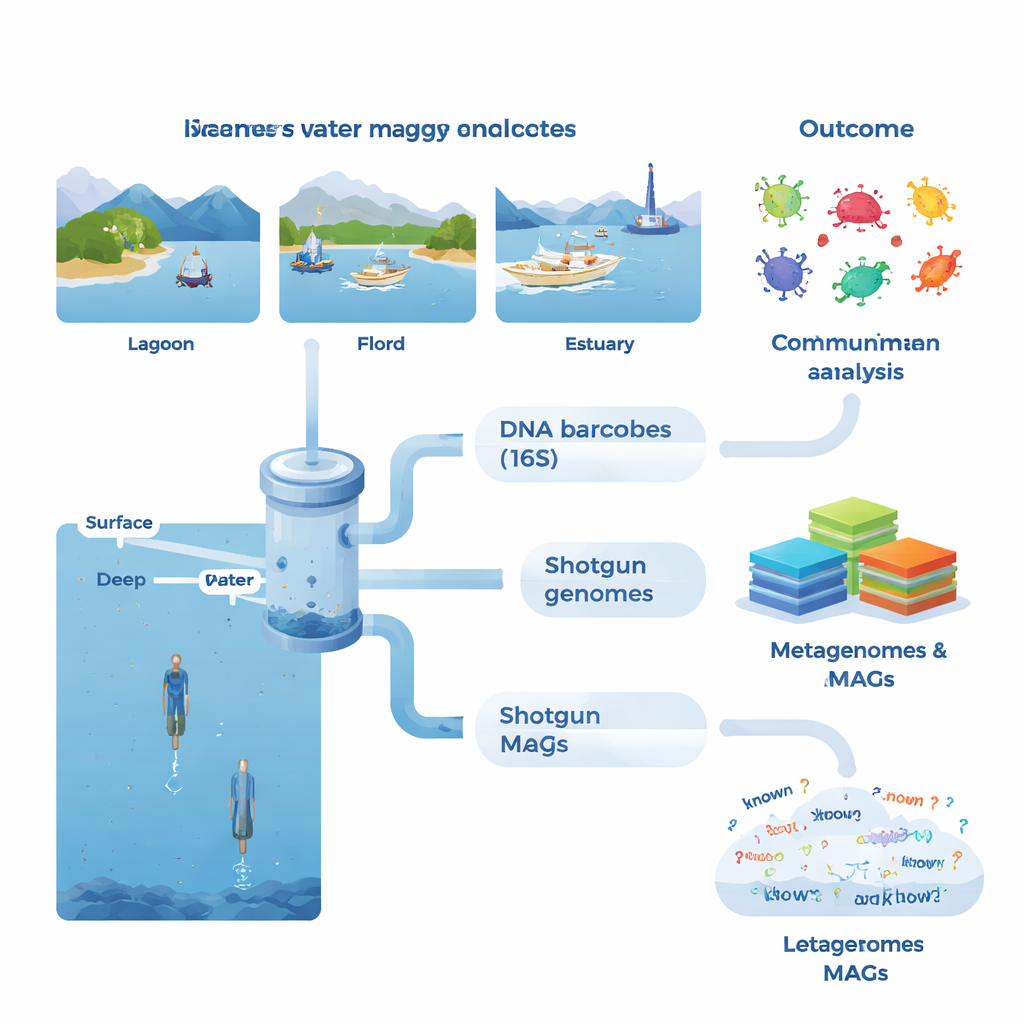
Eine öffentliche Ressource für die Zukunft der Ozeane
Anstatt eine einzelne Entdeckung zu präsentieren, liefert diese Arbeit eine sorgfältig validierte, offene Ressource, die andere Wissenschaftler nutzen können. Alle DNA-Sequenzen, Genomrekonstruktionen, Genkataloge und Umweltmessungen sind öffentlich archiviert, ebenso wie der verwendete Computer-Code zur Datenverarbeitung. Für Nicht-Spezialisten ist die Kernbotschaft, dass Küstenmikroben sowohl vielfältig als auch voller Überraschungen sind, insbesondere in übersehenen Lebensräumen wie Lagunen und Fjorden. Wenn Forschende diese Daten erschließen, werden sie besser gerüstet sein, zu verstehen, wie mikroskopisches Leben an unseren Küsten auf Erwärmung, Verschmutzung und Störungen reagiert — und neuartige Gene zu nutzen, die der Biotechnologie und dem Umweltmanagement nützen könnten.
Zitation: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
Schlüsselwörter: küstennahe Mikrobiome, Metagenomik, Lagunen und Fjorde, marine Biodiversität, Umwelt-DNA