Clear Sky Science · de
Hochauflösende Bildsequenzen von Blättern mit geometrischer Ausrichtung für die dynamische Phänotypisierung von Blattkrankheiten
Die Entfaltung von Pflanzenkrankheiten in Echtzeit beobachten
Bäuerinnen, Bauern und Gärtnerinnen bemerken Pflanzenkrankheiten meist erst, wenn braune Flecken und gelbe Streifen bereits sichtbar sind. Aber was wäre, wenn wir diese Symptome stundenweise beobachten und genau nachvollziehen könnten, wie Wetter, Pflanzensorte und verschiedene Erreger einen Ausbruch beeinflussen? Dieser Artikel stellt einen öffentlichen Datensatz vor, der genau das für Weizen — eine der wichtigsten Nahrungspflanzen der Welt — ermöglicht. Indem einzelne Blätter über Tage und Wochen mit einer Kamera verfolgt werden, eröffnen die Autoren ein neues Fenster darauf, wie Blattkrankheiten beginnen, sich ausbreiten und miteinander interagieren.
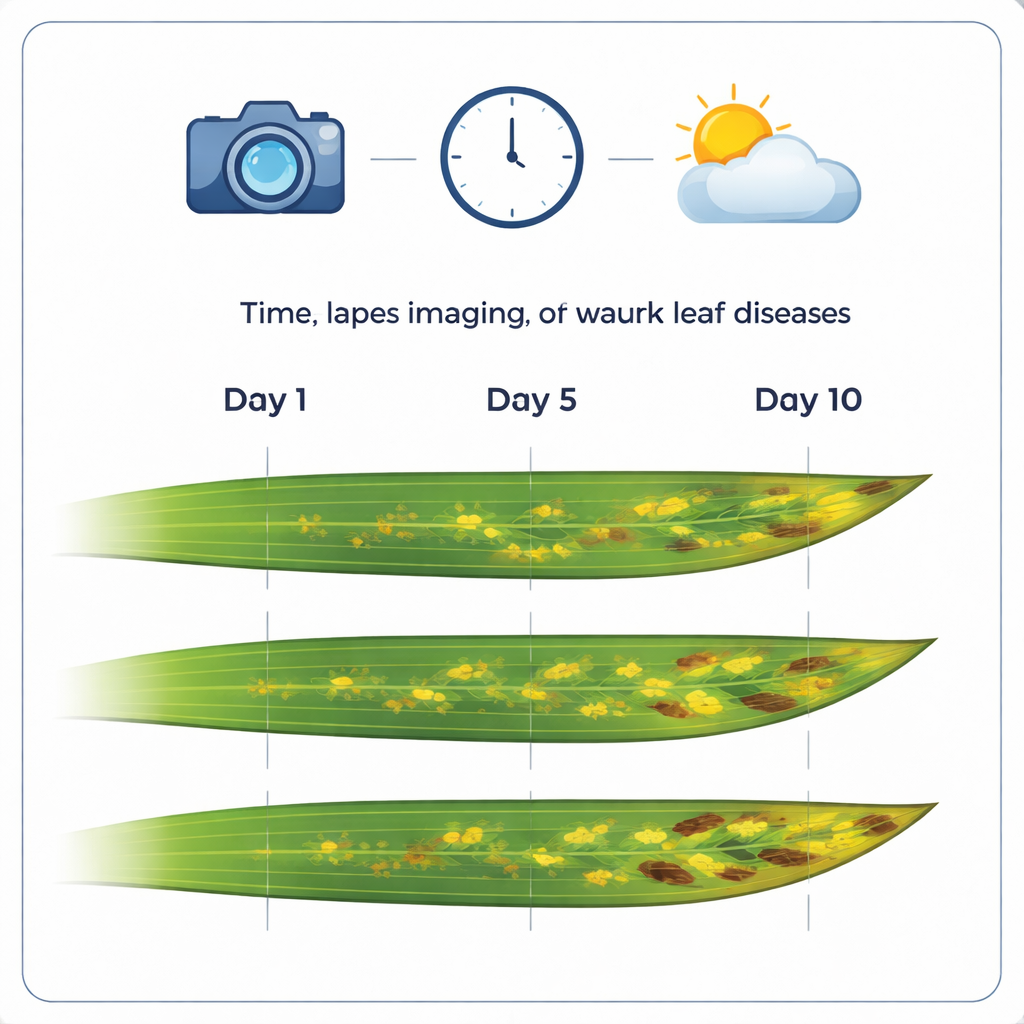
Eine neue Fotobibliothek kranker Blätter
Kern der Arbeit ist eine sorgfältig zusammengestellte Sammlung von 12.520 hochauflösenden Farbbildern von Weizenblättern. Diese Bilder sind in 1.032 Zeitraffersequenzen gruppiert, die jeweils dasselbe Blatt über etwa zwei Wochen mit nahezu täglichen Aufnahmen verfolgen. Viele Blätter zeigen verbreitete Weizenerkrankungen wie Braunrost, Gelbrost und Septoria tritici-Blattflecken. Durch die sehr feine Bildauflösung (etwa drei Hundertstel Millimeter pro Pixel) erfasst der Datensatz kleine Details wie einzelne Läsionen, Rostpusteln und winzige Fruchtkörper, an denen Pilze Sporen produzieren.
Jedes Blatt an derselben Stelle halten
Eines der größten technischen Probleme beim Studium solcher Zeitreihen besteht darin, dass Blätter sich bewegen und ihre Form verändern. Um das zu lösen, haben die Forschenden jedes Blatt vorsichtig gegen eine transparente Platte flachgedrückt und kleine weiße Tintenpunkte als Referenz hinzugefügt. Computer-Vision-Software nutzte diese Markierungen, um alle Bilder einer Sequenz so auszurichten, dass derselbe Gewebeausschnitt von Tag zu Tag an derselben Position erscheint. Der mediane Ausrichtungsfehler beträgt nur 0,16 Millimeter — ausreichend, um die meisten Läsionen beim Wachsen zu verfolgen. Neben den Bildern stellt das Team auch die mathematischen Transformationen zur Ausrichtung bereit, sodass andere Forscher alternative Methoden testen oder die vorhandenen verbessern können.
Von Bildern zu messbarer Krankheit
Nach der Ausrichtung setzten die Autoren Deep-Learning-Modelle ein, um Symptome auf jedem Blatt zu lokalisieren und zu umreißen. Die Verarbeitungskette erkennt Schlüsselpunkte, segmentiert befallene Bereiche und verknüpft dieselbe Läsion über mehrere Tage anhand der Überlappung der umrahmten Regionen. So lässt sich messen, wie schnell einzelne Flecken wachsen, wann neue Pusteln erscheinen und wie viele Fruchtkörper sich entwickeln. Der Datensatz enthält außerdem Wetteraufzeichnungen, Angaben zu Fungizid- und Inokulationstreatments sowie Details zu 15 Weizensorten mit unterschiedlichen Blattformen und Widerstandsniveaus. Diese Zusatzdaten ermöglichen es Wissenschaftlern, zu untersuchen, wie sich die Krankheitsentwicklung von der Pflanzengeetik, Managemententscheidungen und wechselnden Feldbedingungen beeinflussen lässt.
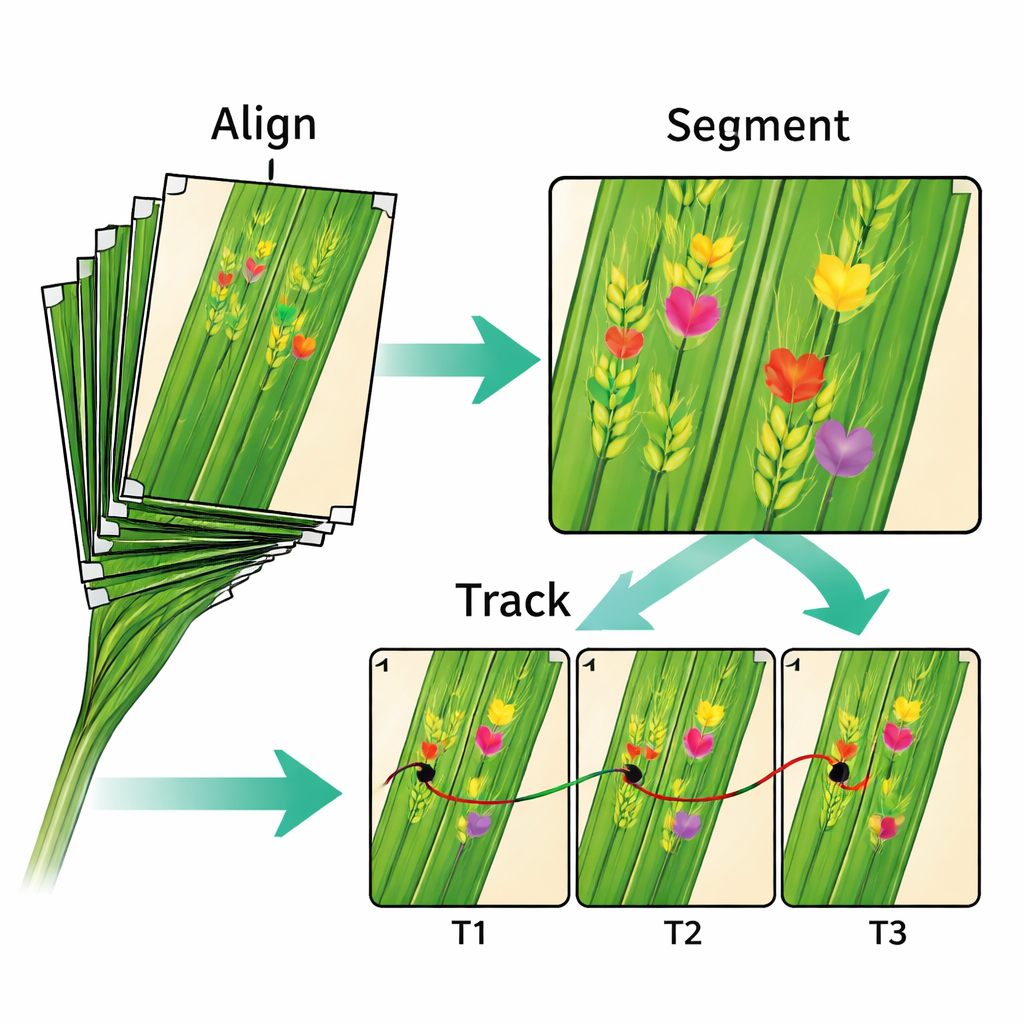
Intelligentere Bildwerkzeuge testen
Über die Pflanzenkrankheit selbst hinaus ist der Datensatz ein Spielplatz für Informatiker und Ingenieure. Die Autoren zeigen, dass ihr aktueller schrittweiser Ansatz — erst ausrichten, dann segmentieren, dann verfolgen — ziemlich gut funktioniert, aber Kontext vermissen lässt und manuelle Qualitätskontrollen erfordert. Sie argumentieren, dass die eigentliche Chance in stärker integrierten „End-to-End“-Systemen liegt, die Ausrichtung, Symptomerkennung und Tracking gleichzeitig erlernen, angelehnt an ähnliche Fortschritte in der medizinischen Bildgebung. Da die Daten sowohl Rohbilder als auch verarbeitete Ausgaben wie Masken und Markierungskoordinaten enthalten, können Forschende neue Algorithmen benchmarken und direkt mit der bestehenden Pipeline vergleichen.
Was das für künftige Ernten bedeutet
Für Nichtfachleute ist die praktische Botschaft, dass wir lernen, Pflanzenkrankheiten mit derselben Präzision und Kontinuität zu überwachen wie in der modernen Medizin. Indem Blätter zu Zeitraffergeschichten statt zu Einzelschnappschüssen werden, hilft dieser Datensatz Wissenschaftlern zu bestimmen, welche Arten von Resistenz auf dem Feld wirklich relevant sind und unter welchen Wetterlagen Ausbrüche beschleunigen oder abklingen. Obwohl die aktuellen Daten von einem Standort stammen und sich auf Weizen konzentrieren, lassen sich die Methoden und Werkzeuge auf andere Kulturpflanzen und Stressfaktoren übertragen. Langfristig könnte eine derart detaillierte Nachverfolgung Züchter zu dauerhafterer Krankheitsresistenz führen und Frühwarnsysteme unterstützen, die Erträge schützen, bevor Schäden mit bloßem Auge sichtbar werden.
Zitation: Anderegg, J., McDonald, B.A. High-Resolution Leaf Image Sequences with Geometric Alignment for Dynamic Phenotyping of Foliar Diseases. Sci Data 13, 247 (2026). https://doi.org/10.1038/s41597-026-06567-y
Schlüsselwörter: Getreideblattkrankheiten, Zeitrafferaufnahmen, Pflanzenphänotypisierung, digitale Pflanzenpathologie, Resistenz gegen Pflanzenkrankheiten