Clear Sky Science · de
MaAsLin 3: Verfeinerung und Erweiterung generalisierter multivariabler linearer Modelle zur Entdeckung von Assoziationen in Meta-Omics
Warum winzige Darmbewohner wichtig sind
Unser Körper beherbergt Billionen von Mikroben, die bei der Verdauung helfen, das Immunsystem schulen und möglicherweise sogar unsere Stimmung beeinflussen. Mit der Verbreitung der DNA-Sequenzierung, die das Erfassen dieser mikrobiellen Gemeinschaften erleichtert hat, ist eine zentrale Frage aufgetaucht: Welche spezifischen Mikroben gehen mit Erkrankungen wie entzündlichen Darmerkrankungen oder mit alltäglichen Merkmalen wie Alter und Ernährung einher? Die Beantwortung erweist sich als überraschend schwierig. Die Daten sind laut, voller Nullen und werden häufig als Prozentsätze statt als echte Zählwerte angegeben. Dieser Artikel stellt MaAsLin 3 vor, ein neues statistisches Werkzeug, das darauf ausgelegt ist, aus unordentlichen Mikrobiomdaten klarere Signale zu extrahieren, sodass Forscher Mikroben zuverlässiger mit menschlicher Gesundheit und Umwelt in Verbindung bringen können.
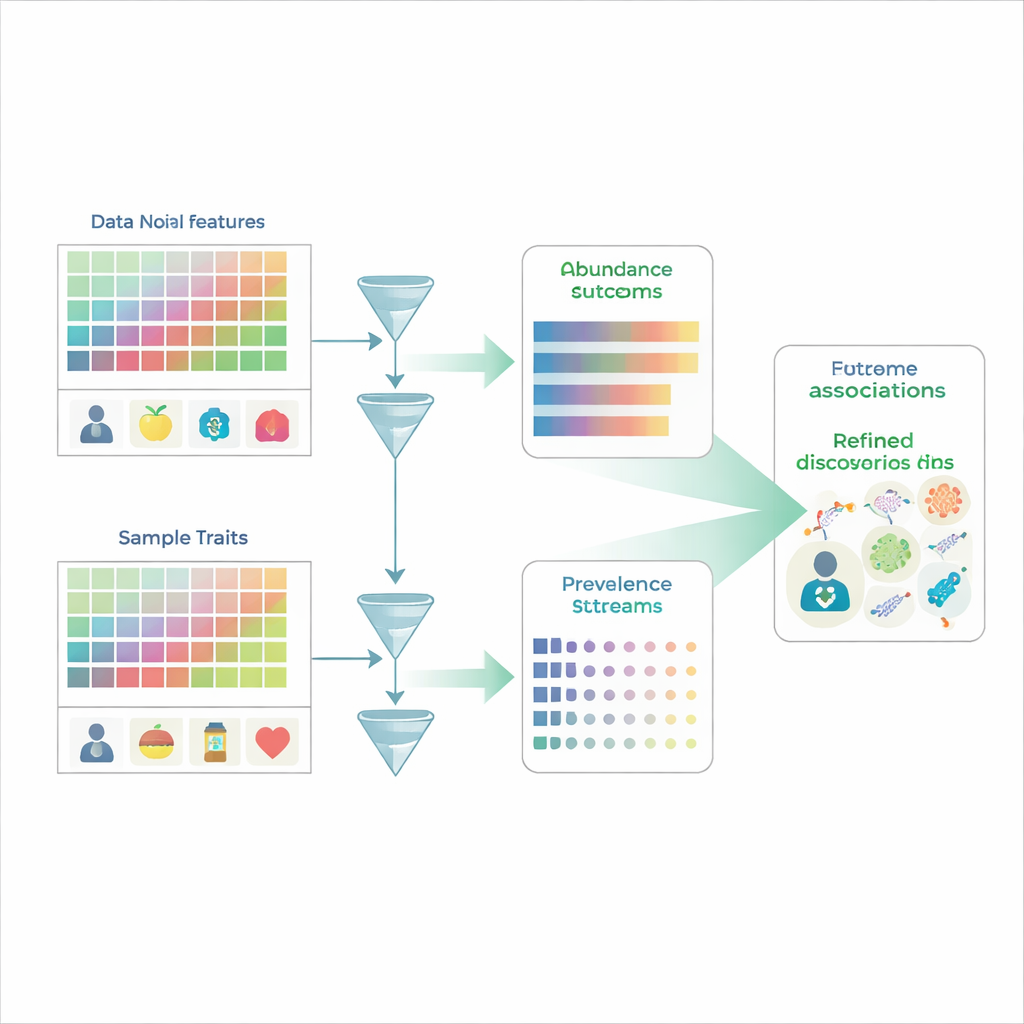
Nach Mustern in einer lauten Menge suchen
Traditionelle Mikrobiomstudien funktionieren ein wenig wie das Zählen von Gesichtern in einer Menge: Forscher messen die relative Häufigkeit von Hunderten oder Tausenden mikrobieller Arten bei vielen Personen und fragen dann, welche Arten sich beispielsweise zwischen kranken und gesunden Gruppen unterscheiden. Mikrobiomdaten sind jedoch auf Prozentsätze beschränkt, die sich zu 100 % summieren müssen. Steigt daher eine Art, scheint mindestens eine andere zu sinken, auch wenn sich deren tatsächliche Menge nicht verändert hat. Hinzu kommt, dass viele Arten in einer Probe schlicht nicht nachgewiesen werden, wodurch zahlreiche Nullen entstehen, die entweder auf echtes Fehlen oder auf Detektionsgrenzen hinweisen können. Übliche Analysemethoden vermischen häufig zwei verschiedene Fragen – ob ein Mikroorganismus überhaupt vorhanden ist und wie viel davon vorhanden ist, wenn er vorhanden ist – wodurch das zugrundeliegende biologische Bild leicht falsch interpretiert werden kann.
Präsenz von Menge trennen
MaAsLin 3 begegnet diesen Problemen, indem es Präsenz und Menge explizit als getrennte, aber verwandte Phänomene behandelt. Für jedes mikrobiologische Merkmal – etwa eine Art, ein Gen oder einen Stoffwechselweg – baut es parallel zwei Modelle auf. Ein Modell betrachtet die Prävalenz und fragt, wie häufig das Merkmal in Proben mit unterschiedlichen Merkmalen nachgewiesen wird. Das andere Modell konzentriert sich auf die Abundanz und untersucht, wie sich das Niveau des Merkmals nur in den Proben verändert, in denen es nachweisbar ist. Durch diese Aufteilung vermeidet MaAsLin 3 die übliche Abkürzung, Nullen durch beliebig kleine Zahlen zu ersetzen, was Ergebnisse verzerren kann. Anschließend kombiniert es die beiden Effekte zu einem Gesamtbild darüber, wie jedes Merkmal mit jedem untersuchten Merkmal zusammenhängt, und erlaubt gleichzeitig zu sehen, ob eine Assoziation hauptsächlich die Präsenz, die Menge oder beides betrifft.
Näher an reale Größen kommen
Eine weitere Komplikation in der Mikrobiomforschung ist, dass die meisten Messungen relativ sind: Sie geben an, welchen Anteil an der Gesamtgemeinschaft eine Art einnimmt, nicht wie viele Zellen tatsächlich vorhanden sind. Biologische Fragestellungen hängen jedoch oft von absoluter Häufigkeit ab – beispielsweise davon, ob die Zellzahl eines Krankheitserregers eine Schwelle überschreitet, die eine Krankheit auslösen könnte. MaAsLin 3 bietet zwei komplementäre Lösungen. Wenn Experimente zusätzliche Informationen enthalten, etwa bekannte Mengen einer Referenzorganismus oder Schätzungen der gesamten mikrobiellen Last, kann die Methode relative Prozentsätze in Schätzungen absoluter Zählwerte umwandeln und diese direkt modellieren. Wenn solche Daten nicht vorliegen, vergleicht MaAsLin 3 stattdessen das Verhalten jedes Merkmals mit dem typischen Muster über alle Merkmale hinweg, was unter realistischen Annahmen eine Annäherung an das ergibt, was auf absoluter Skala beobachtet würde. Umfangreiche Computersimulationen und Tests an realen Datensätzen mit experimentell gemessenen absoluten Abundanzen zeigen, dass diese Strategie zugrundeliegende Trends genau rekonstruiert und mehrere weit verbreitete Werkzeuge übertrifft.
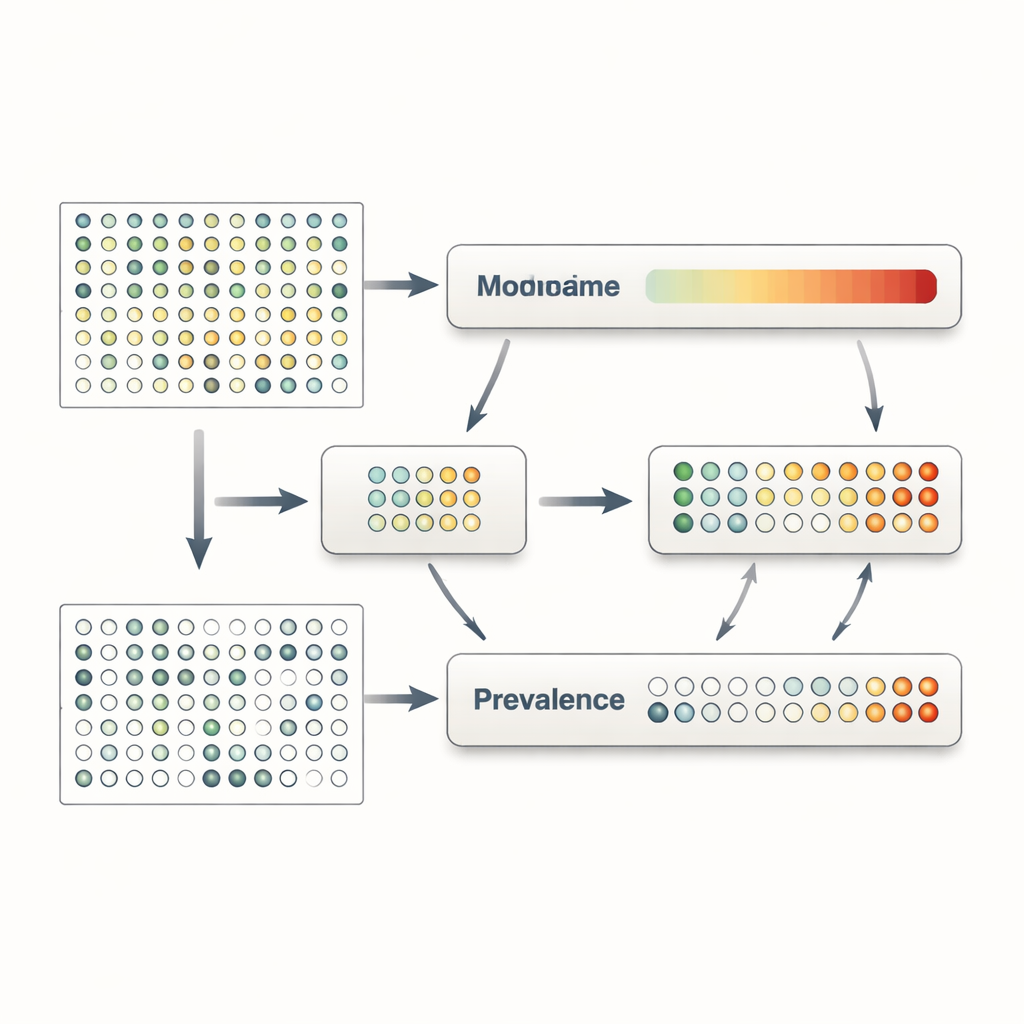
Verborgene Signale bei Darmerkrankungen aufdecken
Um zu zeigen, was diese Fortschritte in der Praxis bedeuten, wendeten die Autoren MaAsLin 3 auf eine große, gut untersuchte Kohorte von Personen mit und ohne entzündliche Darmerkrankungen wie Morbus Crohn und Colitis ulcerosa an. Früheren Arbeiten waren bereits viele mikrobielle Veränderungen in diesen Zuständen aufgefallen, doch MaAsLin 3 fügte mehrere Nuancen hinzu. Es bestätigte die meisten bekannten Verbindungen und machte deutlich, dass etwa drei Viertel der Assoziationen Änderungen betrafen, ob Mikroben überhaupt vorhanden waren, statt Änderungen der Abundanz, wenn sie vorhanden waren. Anders gesagt: Darmentzündungen gingen oft mit dem vollständigen Verlust bestimmter nützlicher Mikroben oder deren Nichterkennung einher, statt nur mit einem leichten Rückgang ihrer Mengen. Die Methode identifizierte außerdem Mikroben, deren bloße Präsenz – unabhängig von ihrer Menge – stark mit krankheitsbedingten Störungen der Darmgemeinschaft korrespondierte.
Was das für künftige Studien und Versorgung bedeutet
Für Nicht-Spezialisten ist die Kernbotschaft, dass die Art und Weise, wie wir Mikrobiomdaten analysieren, entscheidend beeinflusst, welche Mikroben wir für gesundheitlich relevant halten. Durch ein besseres Handling von Nullen, die Trennung von Präsenz und Menge sowie die Annäherung an echte Zellzahlen bietet MaAsLin 3 eine schärfere Linse zur Entdeckung zuverlässiger mikrobieller Marker für Krankheit, Ernährung und Umwelt. Die Ergebnisse zu entzündlichen Darmerkrankungen deuten darauf hin, dass viele klinisch relevante Veränderungen Mikroben betreffen, die verschwinden oder neu auftreten, nicht nur solche, die allmählich in ihrer Häufigkeit steigen oder fallen. Diese Unterscheidung ist wichtig für die Entwicklung von Therapien: Wenn eine Erkrankung mit dem vollständigen Verlust nützlicher Arten verbunden ist, könnten Strategien, die diese Mikroben wieder einführen oder schützen, wirksamer sein als Ansätze, die lediglich versuchen, das Gesamtgleichgewicht der Gemeinschaft leicht zu verschieben. MaAsLin 3 stattet Forscher somit mit einem präziseren und flexibleren Werkzeugkasten aus, um komplexe Mikrobiommessungen in verwertbare biologische Erkenntnisse zu überführen.
Zitation: Nickols, W.A., Kuntz, T., Shen, J. et al. MaAsLin 3: refining and extending generalized multivariable linear models for meta-omic association discovery. Nat Methods 23, 554–564 (2026). https://doi.org/10.1038/s41592-025-02923-9
Schlüsselwörter: Mikrobiom, entzündliche Darmerkrankung, statistische Modellierung, absolute Häufigkeit, mikrobielle Prävalenz