Clear Sky Science · de
Die HUNT-Studie identifiziert genetische Wirtsfaktoren, die reproduzierbar mit der Zusammensetzung des menschlichen Darmmikrobioms assoziiert sind
Warum Ihre Gene und Darmbakterien wichtig sind
Jeder von uns trägt Billionen Mikroben im Darm, die bei der Verdauung helfen, das Immunsystem schulen und möglicherweise sogar unser Krankheitsrisiko beeinflussen. Diese Studie stellt eine auf den ersten Blick einfache Frage: Wie viel dieses inneren Ökosystems ist in unserer DNA festgeschrieben? Indem die Forschenden die Genome von Zehntausenden Menschen mit der detaillierten Zusammensetzung ihrer Darmmikroben verglichen, zeigen sie, dass bestimmte menschliche Gene das Mikrobiom beständig in bestimmte Richtungen lenken – und dass diese Verschiebungen mit Erkrankungen wie Zöliakie, Hämorrhoiden und Herz-Kreislauf-Problemen sowie mit dem Körpergewicht verknüpft sind.
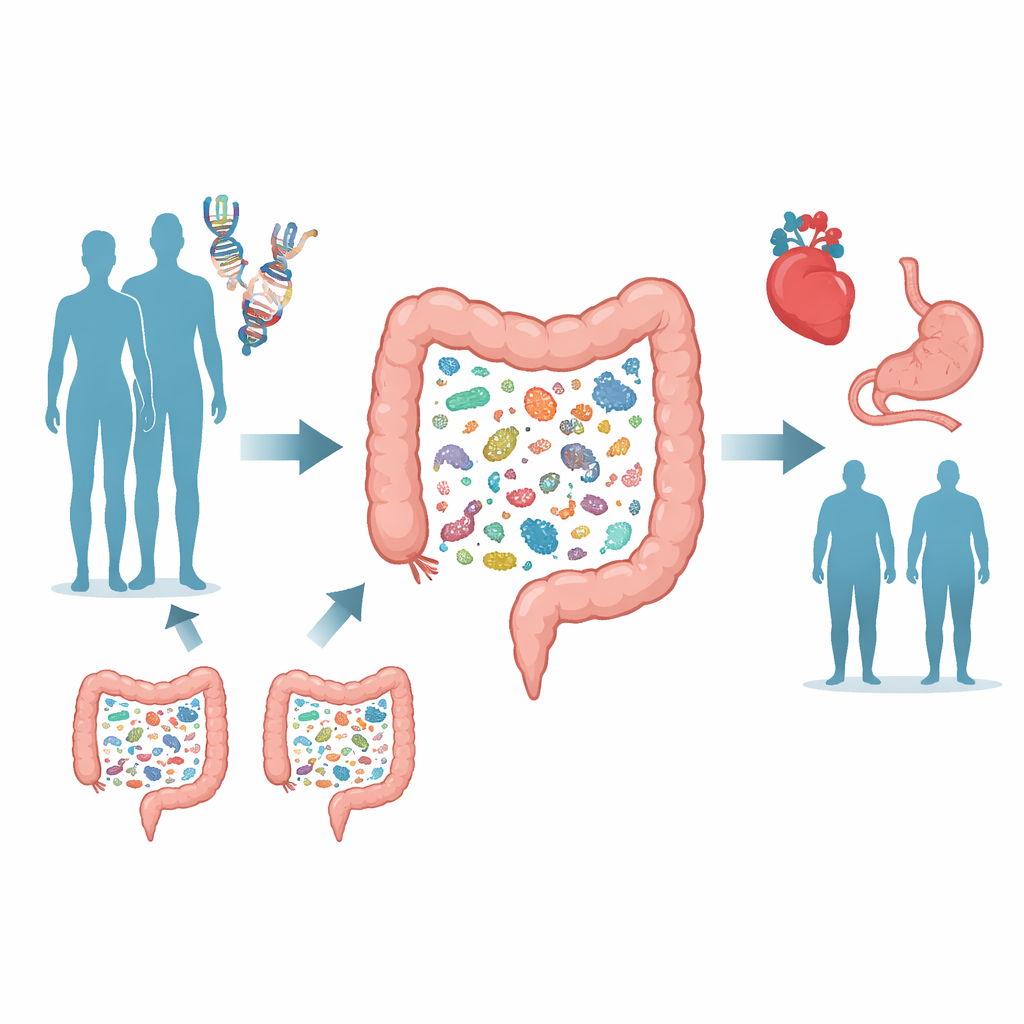
Nach Mustern in der Masse suchen
Um Gen–Mikroben-Verknüpfungen aufzuspüren, griff das Team auf die Trøndelag-Gesundheitsstudie in Norwegen zurück, in der über 12.000 Erwachsene sowohl Blut für die DNA-Analyse als auch Stuhlproben zur mikrobiellen Profilierung bereitstellten. Im Gegensatz zu vielen früheren Projekten, die relativ grobe bakterielle Fingerabdrücke nutzten, beruhte diese Arbeit auf tiefer metagenomischer Sequenzierung, die einen großen Teil der DNA jeder Probe liest und Hunderte verschiedene Bakterienarten sowie deren Stoffwechselfähigkeiten unterscheiden kann. Die Wissenschaftler führten anschließend eine genomweite Assoziationsstudie durch und durchsuchten fast acht Millionen menschliche genetische Varianten, um zu sehen, welche mit Unterschieden in der relativen Häufigkeit von 546 häufigen Darmarten und mit Messgrößen der gesamten mikrobiellen Diversität einhergingen.
Sechs genetische Hotspots, die den Darm formen
Die Analyse offenbarte einen überraschend starken genetischen Einfluss. Zwölf robuste Assoziationen traten zutage zwischen menschlichen DNA-Varianten und spezifischen bakteriellen Arten, die sich auf sechs Regionen des Genoms konzentrierten. Zwei dieser Regionen, nahe dem LCT-Gen, das an der Laktoseverdauung beteiligt ist, und dem ABO-Blutgruppengen, waren bereits zuvor genannt worden, doch vier – in der Nähe von HLA-DQB1, MUC12, SLC37A2 und FUT2 – waren neu oder wurden neu bestätigt. Beispielsweise neigten Menschen mit der laktasepersistenten Variante von LCT dazu, weniger Bifidobacterium adolescentis zu tragen, eine Art, die auf Milchzucker gedeiht, der im Darm verbleibt, wenn Laktose nicht vollständig abgebaut wird. Die FUT2-Region, die beeinflusst, ob Blutgruppenzucker auf der Darmoberfläche dargestellt werden, stand in Verbindung mit mehreren bakteriellen Arten, die offenbar von diesen zuckerbeschichteten Oberflächen leben.
Von Mikroben zum Krankheitsrisiko
Die Geschichte wurde noch interessanter, als die Forschenden diese genetischen Ergebnisse mit großen Datenbanken zu menschlichen Krankheiten überlagerten. Varianten in der HLA-DQB1-Region, die mit höheren Niveaus einer Agathobacter-Art verbunden waren, standen auch mit einem geringeren Risiko für Autoimmunerkrankungen, einschließlich Zöliakie, in Zusammenhang. Menschen mit Zöliakie in der norwegischen Kohorte wiesen tendenziell besonders niedrige Werte dieses Mikroorganismus auf, was nahelegt, dass die Krankheit teilweise die Darmgemeinschaft umgestalten könnte. Eine andere Region, in der Nähe des MUC12-Gens, war sowohl mit der Häufigkeit eines Bakteriums namens Coprobacillus cateniformis als auch mit einem verringerten Risiko für Hämorrhoidalleiden verbunden. Laboruntersuchungen zeigten, dass MUC12 in den Zellen, die den Dickdarm auskleiden, stark produziert wird, was darauf hindeutet, dass subtile Veränderungen dieser Schleimhautschicht beeinflussen könnten, welche Bakterien gedeihen und wie diese wiederum empfindliche Blutgefäße und Gewebe im Rektum beeinflussen.
Mikrobielle Funktionen, Herzgesundheit und Körpergewicht
Über einzelne Arten hinaus untersuchte das Team, wozu die Mikroben fähig sind, indem es deren Gene in funktionelle Module gruppierte, wie Transportsysteme und Regulationskreise. Dieselben menschlichen Genregionen – LCT, ABO und FUT2 – beeinflussten auch diese mikrobiellen Funktionen, was darauf hindeutet, dass unsere DNA nicht nur bestimmt, wer im Darm vorhanden ist, sondern auch, was diese Organismen tun. An der FUT2-Stelle etwa gingen Varianten, die mit dem "Non-Secretor"-Status verbunden sind, Hand in Hand mit Bakterien, die potenziell schädliche Metaboliten produzieren, und mit einem erhöhten Risiko für hohen Cholesterinspiegel und Bluthochdruck. Schließlich fanden die Forschenden mithilfe einer Technik namens Mendelsche Randomisierung, die genetische Varianten als natürliche Experimente nutzt, Hinweise darauf, dass ein höherer Body-Mass-Index ursächlich das Mikrobiom verändert: Menschen, die genetisch zu höherem Gewicht disponiert sind, zeigten tendenziell eine geringere gesamte mikrobielle Diversität und konsistente Veränderungen über viele Arten hinweg.
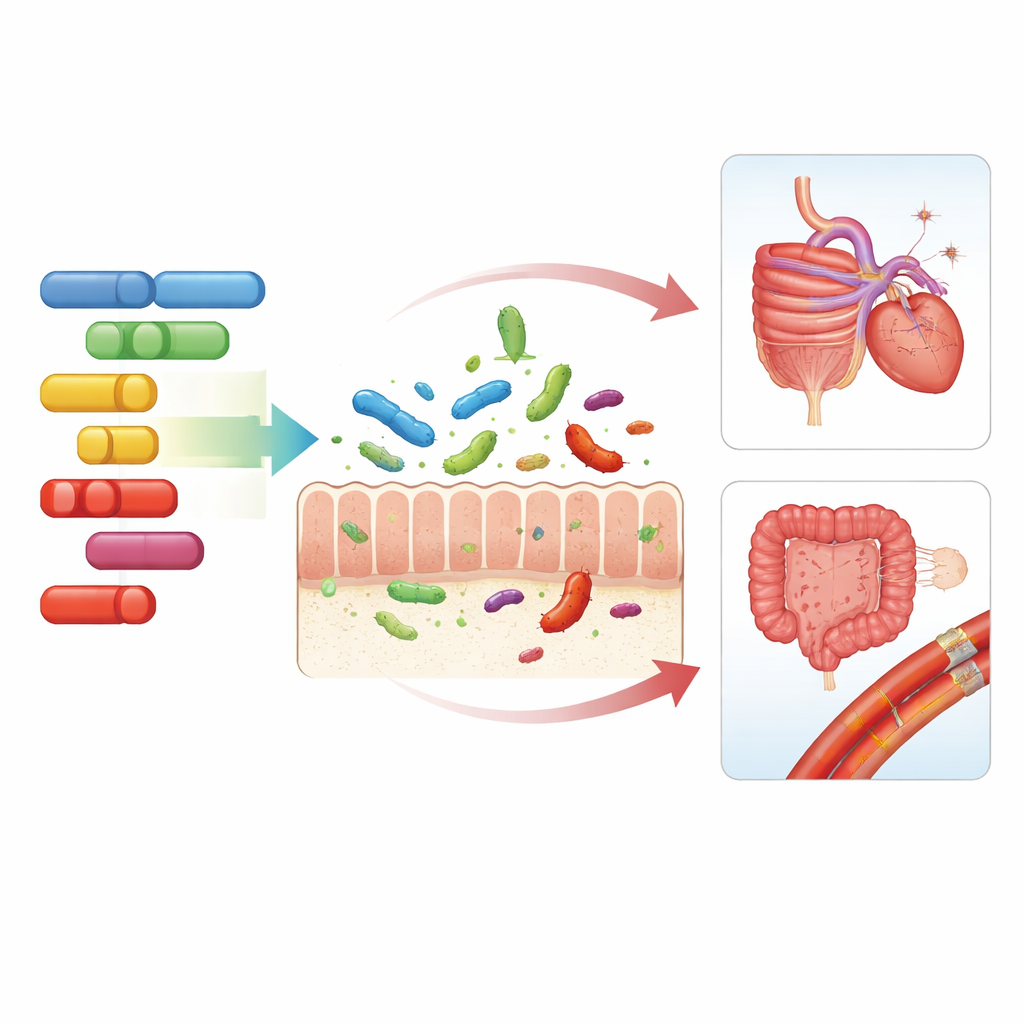
Was das für die tägliche Gesundheit bedeutet
Insgesamt zeichnen diese Befunde ein Bild eines dreiseitigen Gesprächs zwischen unseren Genen, unseren Darmmikroben und unserer Gesundheit. Bestimmte Abschnitte der menschlichen DNA begünstigen oder entmutigen subtil bestimmte bakterielle Bewohner und mikrobielle Aktivitäten, die sich dann mit Risiken für Verdauungserkrankungen, Herz-Kreislauf-Problemen und den Folgen von Übergewicht überschneiden. Obwohl diese genetischen Einflüsse nur einen Teil der enormen Variabilität in Darmgemeinschaften erklären – und noch nicht in klinische Tests übersetzt sind – helfen sie zu klären, warum Menschen unterschiedlich auf dieselbe Ernährung oder Umgebung reagieren, und weisen auf personalisiertere Ansätze für Ernährung und Krankheitsprävention hin, die sowohl Genom als auch Mikrobiom berücksichtigen.
Zitation: Moksnes, M.R., Coward, E., Nethander, M. et al. The HUNT study identifies host genetic factors reproducibly associated with human gut microbiota composition. Nat Genet 58, 530–539 (2026). https://doi.org/10.1038/s41588-026-02502-4
Schlüsselwörter: Darmmikrobiom, Menschliche Genetik, Mikrobiota und Krankheit, Körpergewicht und Mikroben, Genomweite Assoziation