Clear Sky Science · de
Aufbau komplexer und vielfältiger DNA-Sequenzen mithilfe von DNA-Dreiwegverzweigungen
Neue genetische Geschichten schreiben
Die moderne Biologie kann DNA mit erstaunlicher Geschwindigkeit lesen und editieren, doch das eigentliche Schreiben langer, maßgeschneiderter genetischer Sequenzen hinkt noch hinterher. Diese Lücke verlangsamt alles, von der Entwicklung neuer Medikamente bis zur Herstellung umweltfreundlicherer Materialien. Diese Studie stellt „Sidewinder“ vor, eine neue Methode, DNA-Stücke zusammenzufügen, die darauf abzielt, das Erstellen komplexer, kundenspezifischer Gene genauso zuverlässig und skalierbar zu machen wie ihr Lesen.
Warum der DNA-Zusammenbau neu gedacht werden muss
Jede Zelle läuft auf DNA, einer langen Kette chemischer Buchstaben, die die Anweisungen des Lebens kodieren. Wissenschaftler können chemisch nur kurze DNA-Abschnitte herstellen, daher müssen längere Gene aus vielen kleinen Stücken zusammengesetzt werden, wie Sätze aus zerschnittenen Wörtern. Bestehende Methoden nutzen passende Ränder an diesen Stücken, um zu steuern, welche Teile zusammenkleben. Diese passenden Ränder werden jedoch Teil des endgültigen DNA-Produkts, was bedeutet, dass sie nicht frei für einen fehlerlosen Zusammenbau optimiert werden können, ohne das Gen selbst zu verändern. Mit zunehmender Länge und Komplexität der Designs führt dieser eingebettete Kompromiss zu mehr Fehlern, geringeren Ausbeuten und praktischen Grenzen dessen, was gebaut werden kann.
Ein Seitenpfad, der führt, ohne Spuren zu hinterlassen
Sidewinder löst dieses Problem, indem ein dritter Hilfsstrang aus DNA hinzugefügt wird, der im Endprodukt niemals auftaucht. Die DNA-Stücke werden an ihren Enden mit zwei Merkmalen vorbereitet: kurzen „Toeholds“, die später die nahtlose finale Verbindung bilden, und längeren „Barcodes“, die nur dazu entworfen sind, mit ihren vorgesehenen Partnern zu interagieren. Wenn man die Teile bei kontrollierter Temperatur mischt, finden die Barcodes benachbarter Stücke zueinander und wickeln sich zu einer temporären Seitenhelix ein, wodurch eine Dreiwegverzweigung entsteht, die die passenden Toeholds an ihren Platz zieht. Ein Enzym versiegelt dann die Haupt-DNA-Stücke. Schließlich werden die Hilfsbarcodes entfernt, sodass eine saubere, durchgehende Sequenz ohne zusätzliche Narben oder Tags zurückbleibt. 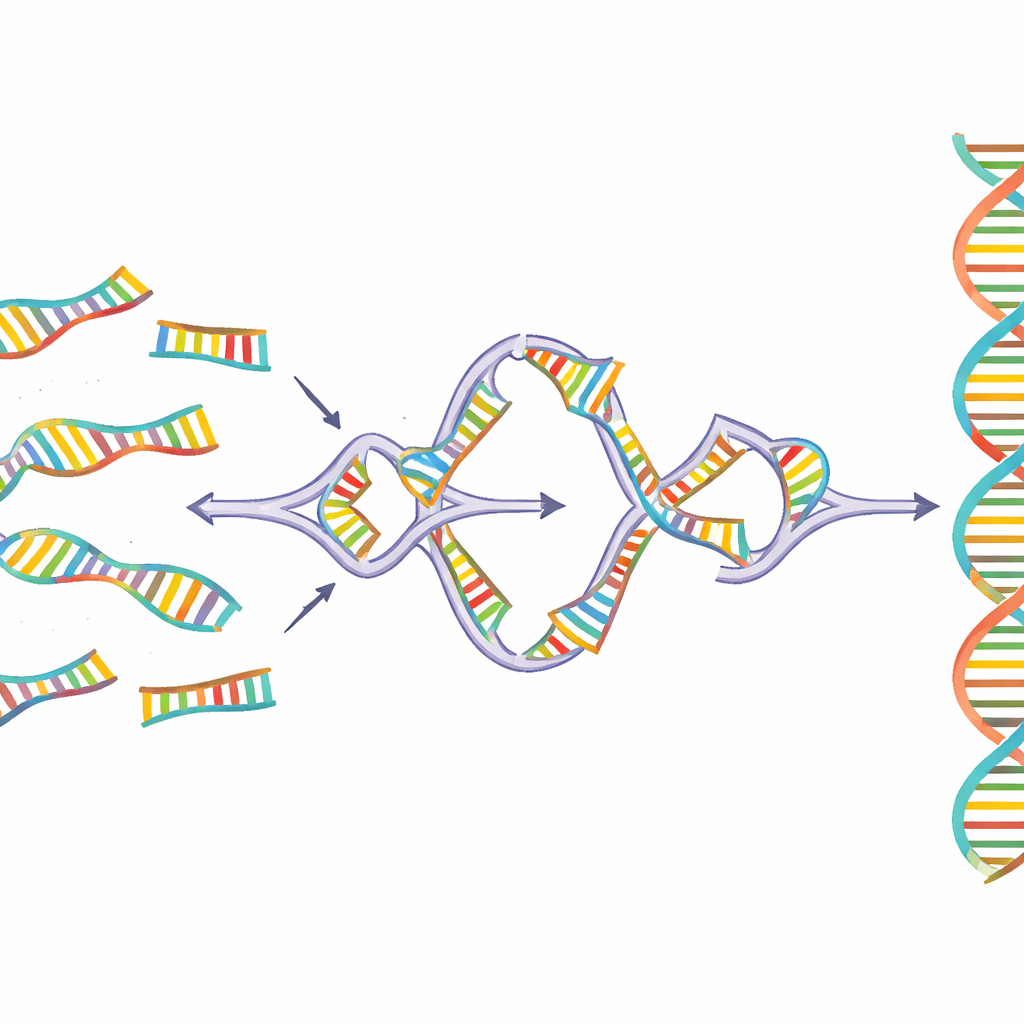
Von Dutzenden von Fragmenten zu schwierigen Genen
Um zu zeigen, was Sidewinder leisten kann, bauten die Autoren DNA-Konstrukte aus 5, 10, 20 und sogar 40 einzelnen Fragmenten in einer einzigen Reaktion. Vergleichbare, hochmoderne Methoden versagten bereits nach wenigen Fragmenten, lieferten chaotische Gemische oder scheiterten ganz, während Sidewinder konsequent ein einzelnes, korrekt großes Produkt ergab. Long-Read-Sequenzierung bestätigte, dass in einem 40-Fragment-Test mehr als 96 % der Reads echte Sidewinder-Produkte waren und jedes dieser Produkte in der perfekten Reihenfolge assembliert worden war. Das Team testete die Methode anschließend an „Hard‑Mode“-Sequenzen: einem menschlichen Gen mit extrem hohem G‑ und C‑Anteil und einem seidenähnlichen Proteinabschnitt, der aus vielen Wiederholungen besteht. Solche Sequenzen scheitern oft an Standardzusammenbauten, weil sie sich auf verwirrende Weise an sich selbst anlagern. Sidewinder erzeugte dennoch nahezu perfekte Assemblierungen, selbst wenn alle Verknüpfungen absichtlich denselben Toehold-Abschnitt teilten — etwas, das mit älteren Techniken nahezu unmöglich zu kontrollieren wäre.
Viele Gene zugleich und Ozeane von Varianten
Da Sidewinders Barcodes eindeutig festlegen, wer mit wem paaren darf, können mehrere Gene im selben Gefäß ohne Kreuzkontamination gebaut werden. Die Forschenden mischten Fragmente für drei unterschiedlich gefärbte Markerproteine und setzten sie in einem Ansatz zusammen. Mit den richtigen Primern konnten sie gezielt jedes einzelne Gen oder die Mischung amplifizieren, und die Sequenzierung zeigte, dass falsche Kreuzungen zwischen den Designs äußerst selten waren. 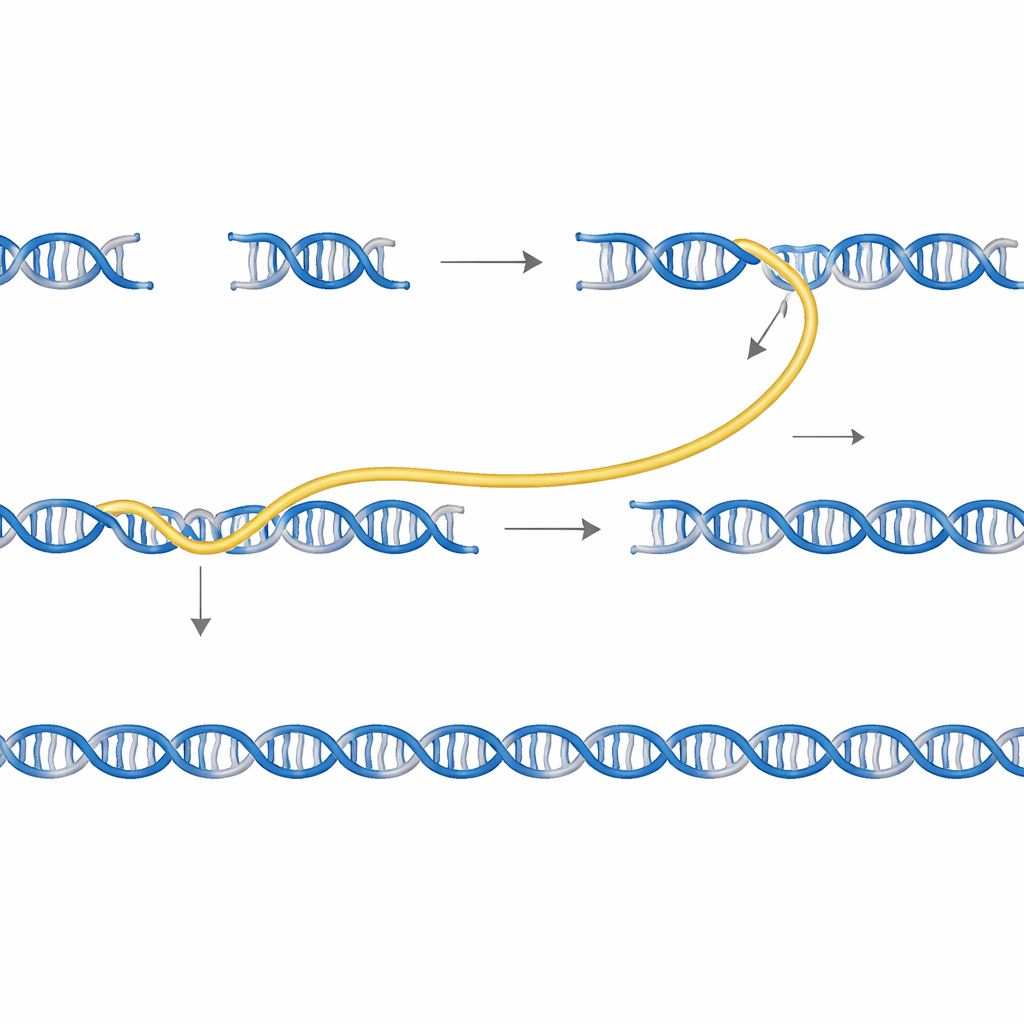
Was das für die zukünftige Bioengineering-Praxis bedeutet
Der wichtigste Erfolg von Sidewinder besteht darin, die „Montageanweisungen“ vom endgültigen DNA-Text zu trennen. Indem die leitende Information auf einen entfernbaren Seitenstrang verlagert wird, können Forschende Verbindungen entwerfen, die außergewöhnlich spezifisch und zuverlässig sind, ohne das Gen selbst kompromittieren zu müssen. Das Ergebnis ist eine universell einsetzbare Methode, um lange, schwierige und stark variierte DNA-Sequenzen mit einer Genauigkeit zu bauen, die der Qualität der Ausgangsstücke ebenbürtig ist und sie in manchen Bereichen sogar übertrifft. Da Werkzeuge wie KI zunehmend mutige neue genetische Entwürfe vorschlagen, könnten Techniken wie Sidewinder entscheidend werden, um diese Entwürfe in echte Moleküle für Medizin, Materialien, Landwirtschaft und darüber hinaus zu verwandeln.
Zitation: Robinson, N.E., Zhang, W., Ghosh, R. et al. Construction of complex and diverse DNA sequences using DNA three-way junctions. Nature 651, 491–500 (2026). https://doi.org/10.1038/s41586-025-10006-0
Schlüsselwörter: DNA-Zusammenbau, synthetische Biologie, Genbibliotheken, DNA-Nanotechnologie, Proteinengineering