Clear Sky Science · de
TONSOKU verhindert die Entstehung großer tandemförmiger Duplikationen und bremst die ATR–WEE1-Checkpoint-Aktivierung
Wenn DNA-Reparatur bei Pflanzen schiefgeht
Unsere Genome – ebenso die von Kulturpflanzen und Tumoren – werden ständig beim Kopieren der DNA belastet. Normalerweise beseitigen Reparatursysteme Störungen unauffällig, bevor sie Probleme verursachen. Diese Studie untersucht, was passiert, wenn eines dieser Systeme, das um das Protein TONSOKU (TSK) aufgebaut ist, in einer kleinen, häufig in der Forschung verwendeten Unkrautpflanze fehlt. Das Resultat ist ein überraschender Anstieg großer DNA-Duplikationen und ausgefallener Wuchsmuster – Befunde, die sowohl für Pflanzenzüchtung als auch für das Verständnis menschlicher Erkrankungen von Bedeutung sein könnten.
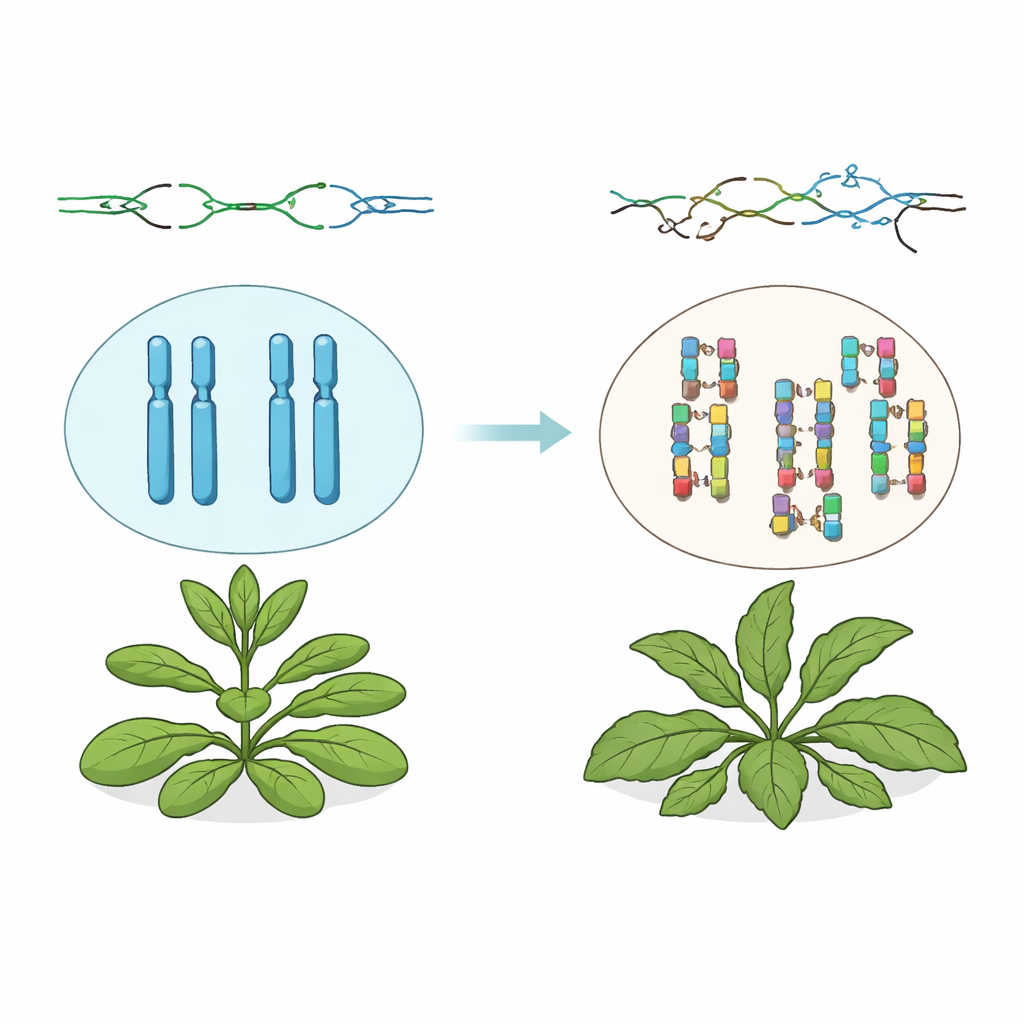
Zusätzliche DNA-Kopien häufen sich an
Die Autorinnen und Autoren arbeiteten mit Arabidopsis thaliana-Pflanzen, denen ein funktionierendes TSK-Gen fehlt. Obwohl diese Pflanzen lebens- und fortpflanzungsfähig sind, erzählen ihre Genome eine dramatische Geschichte. Mit Hilfe von Ganzgenomsequenzierung fanden die Forschenden heraus, dass während kleine Mutationen weitgehend im normalen Bereich blieben, große DNA-Abschnitte häufig direkt hintereinander kopiert wurden – sogenannte tandemförmige Duplikationen. Diese zusätzlichen Stücke reichten von unter tausend Basenpaaren bis zu nahezu eineinhalb Millionen, was oft eine Erhöhung der Gesamtgenomgröße um etwa sieben Prozent bewirkte. Viele dieser Duplikationen waren individuell einzigartig, was zeigt, dass sie wiederholt und unabhängig während des Pflanzenwachstums und über Generationen hinweg entstehen.
Duplikationen verändern Gene und ihre Aktivität
Diese zusätzlichen DNA-Segmente sind keine leere Fracht. Wenn die duplizierten Regionen Gene enthalten, sind diese Gene tendenziell stärker aktiv, schlicht weil mehr Kopien vorhanden sind. Durch die Kombination von DNA-Sequenzierung mit Messungen der RNA (dem Abbild der Genaktivität) zeigten die Forschenden, dass Gene innerhalb duplizierter Regionen häufig mehrere Male mehr RNA produzierten als ihre Gegenstücke in normalen Pflanzen. Dieser Schub kann sich auch auf Gene außerhalb der duplizierten Zonen auswirken. Im Laufe der Zeit können solche Änderungen der Kopienzahl Merkmale erheblich verändern – etwas, das lange bei der Domestikation von Kulturpflanzen genutzt wurde und das man oft in menschlichen Tumoren beobachtet.
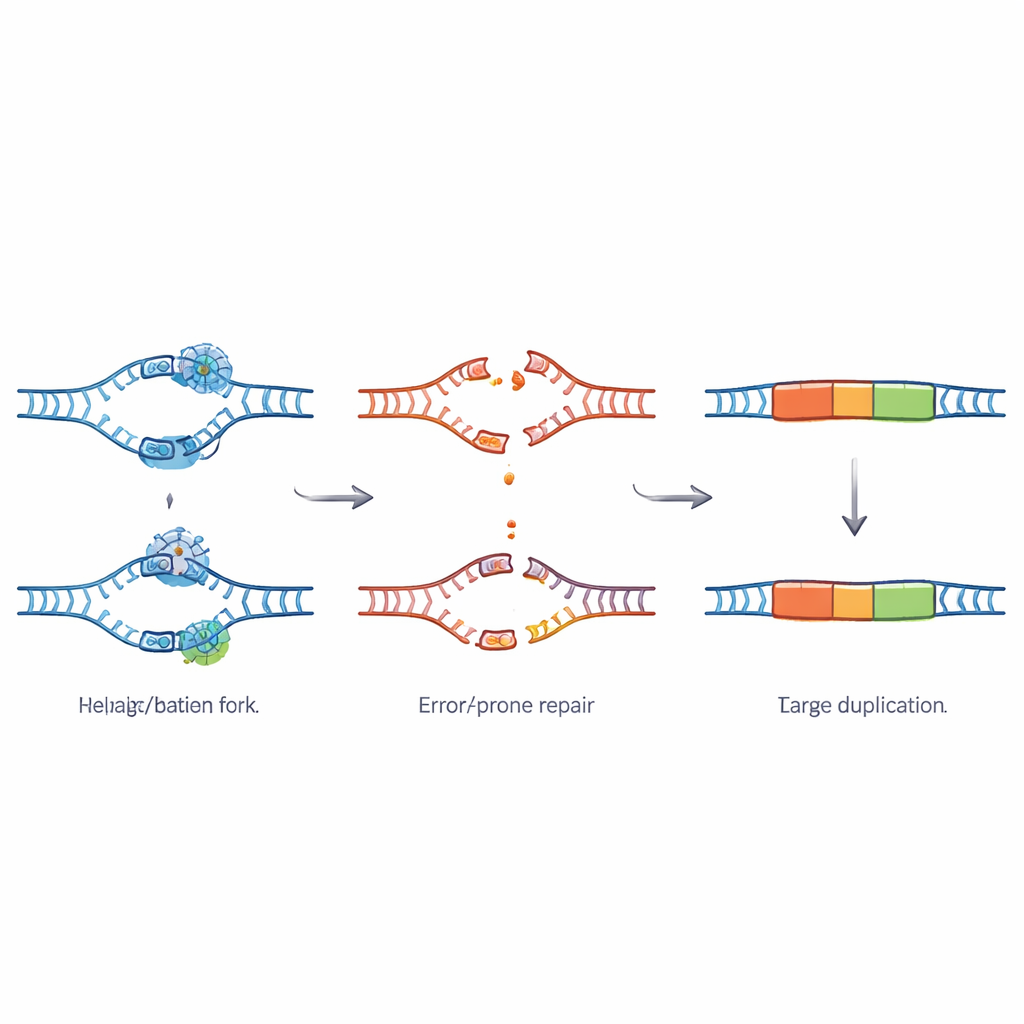
Ein Backup-Reparaturweg erzeugt den Schaden
Um herauszufinden, wie diese Duplikationen entstehen, untersuchte das Team die Enden der duplizierten Segmente. Die beobachteten Muster passten zu den Fingerabdrücken eines Ausweichreparaturwegs, der als theta-vermittelte End-Joining bezeichnet wird und auf einem Enzym namens Polymerase theta beruht. Wenn das übliche hochpräzise Reparatursystem, das von TSK abhängt, versagt, greift dieser Backup-Weg ein, um gebrochene DNA zu kleben. Er verwendet dazu winzige übereinstimmende Sequenzen als „Klebstoff“, was leicht dazu führen kann, dass ein DNA-Stück doppelt kopiert wird. Optische Kartierung sehr langer DNA-Moleküle bestätigte, dass die zusätzlichen Stücke direkt neben ihren ursprünglichen Gegenstücken auf den Chromosomen liegen und echte tandemförmige Duplikationen bilden, statt separater DNA-Kreise.
Stress-Hotspots im Genom
Die duplizierten Regionen sind nicht zufällig verteilt. Sie treten gehäuft in Teilen des Genoms auf, die während der Zellteilung spät repliziert werden und die als dicht verpackte, repetitive DNA – Heterochromatin – vorliegen. Diese Bereiche sind reich an speziellen Wiederholungsmotiven und mobilen DNA-Elementen, die für die Replikationsmaschinerie problematisch sind. Die Grenzen der Duplikationsstellen zeigen ebenfalls Anzeichen chronischen Stresses: Sie enthalten mehr natürliche Variation, längere Wiederholungsstrecken, mehr Transposons und mehr Initiationsstellen für die DNA-Replikation als typische Regionen. All das deutet darauf hin, dass diese Zonen Hotspots sind, an denen die DNA-Kopie häufig ins Stocken gerät oder bricht, besonders wenn TSK fehlt.
Von beschädigter DNA zu seltsam geformten Pflanzen
Arabidopsis-Pflanzen ohne TSK tragen nicht nur gezeichnete Genome, sie sehen auch äußerlich ungewöhnlich aus. Viele zeigen verdrehte Blatt- und Blütenmuster, dicke oder gespaltene Stängel und ungewöhnliche Verzweigungen. Die Forschenden prüften, ob diese sichtbaren Auffälligkeiten von den Duplikationen selbst oder von der Alarmsignalisierung der Zelle als Reaktion auf anhaltende DNA-Schäden herrühren. Durch Deaktivieren zentraler Akteure der pflanzlichen DNA-Schadensantwort – Proteine, die gestoppte DNA-Replikation erkennen und den Zellzyklus anhalten – stellten sie weitgehend die normale Pflanzenform wieder her, obwohl die Duplikationen weiterhin entstanden. Das zeigt, dass die Entwicklungsdefekte hauptsächlich durch chronische Aktivierung der DNA-Schadensantwort verursacht werden und nicht direkt durch die zusätzlichen DNA-Kopien.
Warum das über ein Unkraut hinaus relevant ist
Diese Arbeit offenbart einen zuvor verborgenen Weg, über den große DNA-Duplikationen entstehen können, wenn ein konservierter Reparaturweg versagt, und verknüpft Replikationsstress, fehleranfällige Reparatur und sichtbare Veränderungen der Organismenform. Ähnliche TONSOKU-ähnliche Proteine und Reparatursysteme gibt es auch bei Tieren, einschließlich des Menschen. In einigen Krebserkrankungen sind Genome mit großen tandemförmigen Duplikationen durchsetzt, deren Größen striking an die in diesen Pflanzen erinnerten, und die stark von demselben Stress-Erkennungsweg abhängig sind, den die Autorinnen und Autoren untersucht haben. Zu verstehen, wie der Verlust von TSK-ähnlichen Funktionen das Gleichgewicht von stabiler DNA-Erhaltung hin zu ungehemmter Duplikation verschiebt, kann daher sowohl beim gezielten Gestalten neuer Pflanzenmerkmale als auch beim Verständnis, wie bestimmte Tumoren evolvieren und auf Therapien reagieren, Aufschluss geben.
Zitation: Thomson, G., Poulet, A., Huang, YC. et al. TONSOKU prevents the formation of large tandem duplications and restrains ATR–WEE1 checkpoint activation. Nat Commun 17, 2874 (2026). https://doi.org/10.1038/s41467-026-70906-1
Schlüsselwörter: Genomstabilität, tandemförmige Duplikationen, DNA-Replikationsstress, DNA-Reparaturwege, Pflanzenentwicklung