Clear Sky Science · de
Löslichkeitsbasierte mechanistische Profilerstellung kombinatorischer Medikamententherapien
Warum die Kombination von Medikamenten wichtig sein kann
Die moderne Krebsbehandlung beruht häufig auf Medikamentenkombinationen, doch welche Wirkstoffe am besten zusammenwirken, wird weiterhin weitgehend durch Ausprobieren ermittelt. Diese Studie konzentriert sich auf die akute myeloische Leukämie, eine aggressive Blutkrebserkrankung, die nach der Behandlung oft zurückkehrt. Die Forschenden stellen eine neue Methode vor, mit der sich in hoher Durchsatzrate beobachten lässt, wie die Proteine in Zellen auf die gleichzeitige Gabe zweier Wirkstoffe reagieren. Ihr Ansatz hilft zu erklären, warum bestimmte Kombinationen wirksamer und weniger toxisch sind, und liefert einen Fahrplan für die Entwicklung gezielterer, präziserer Kombinationstherapien bei schwer behandelbaren Krebserkrankungen.
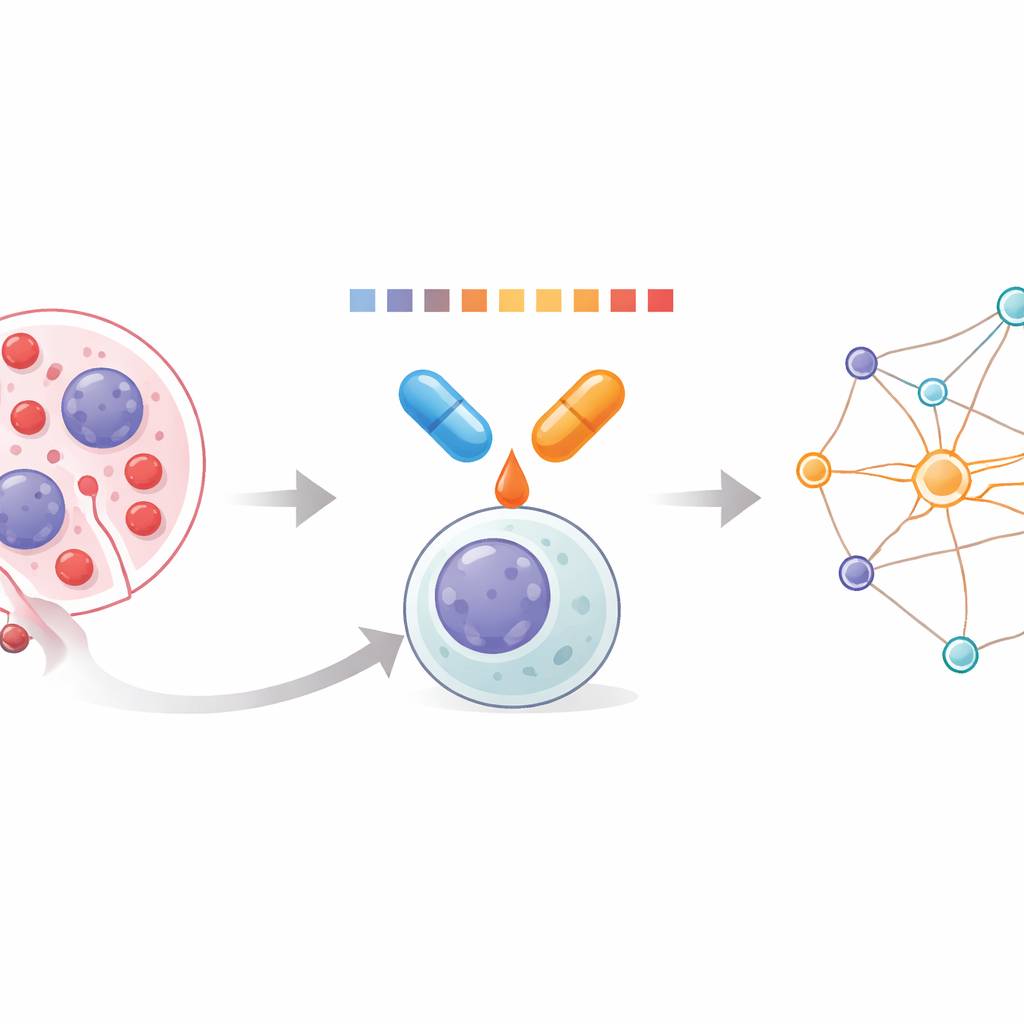
Ein Blick in Leukämiezellen
Die akute myeloische Leukämie (AML) entsteht, wenn unreife weiße Blutzellen im Knochenmark unkontrolliert wachsen und die gesunde Blutbildung verdrängen. Da AML durch viele verschiedene genetische Veränderungen getrieben wird, wirken Einzelmedikamente selten dauerhaft. Kombinationen können erfolgreicher sein, aber Ärztinnen und Ärzte hatten bislang nur begrenzte Werkzeuge, um zu sehen, wie Medikamentpaare auf der Ebene von Tausenden von Proteinen innerhalb der Zelle zusammenwirken. Das Team dieser Arbeit setzte sich zum Ziel, diese kombinierten Effekte direkt zu messen, mithilfe einer Methode, die abliest, wie leicht Proteine sich beim Erhitzen lösen oder verklumpen. Änderungen in der Löslichkeit zeigen, welche Proteine durch die Behandlung stabilisiert oder destabilisiert werden und geben so Einblick in die tatsächliche Wirkung der Wirkstoffe.
Eine neue Methode zur Profilierung von Medikamentpaaren
Die Forschenden entwickelten einen Arbeitsablauf, den sie Combinatorial Proteome Integral Solubility/Stability Alteration analysis beziehungsweise CoPISA nennen. Zellen oder deren Proteinextrakte werden mit Wirkstoff A, Wirkstoff B, der Kombination aus A und B oder ohne Wirkstoff behandelt. Jede Probe wird dann kurz über eine Reihe von Temperaturen erhitzt, und die verbleibenden gelösten Proteine werden erfasst und mittels Massenspektrometrie quantifiziert. Anstatt für jedes Protein komplexe Kurven zu fitten, nutzt die Methode die gesamte Fläche unter dem Schmelzprofil jedes Proteins als kompakte Maßzahl für dessen Verhalten. Der Vergleich dieser Flächen über die Behandlungen hinweg zeigt, welche Proteine unter welchen Bedingungen mehr oder weniger löslich werden und offenbart Muster, die Einzelwirkstoffen gegenüber Kombinationen einzigartig sind.
Finden von Zielen, die nur bei beiden Wirkstoffen erscheinen
CoPISA wurde auf zwei gezielt ausgewählte AML‑Wirkstoffpaare angewendet: LY3009120 mit Sapanisertib (genannt LS) und Ruxolitinib mit Ulixertinib (RU). Diese Paare hatten bereits in Patientenproben, Zelllinien und Zebrafischmodellen starke Aktivität bei vergleichsweise geringer Toxizität gezeigt. CoPISA deckte nicht nur Proteine auf, die durch jeden Wirkstoff allein betroffen waren, sondern auch eine eigene Gruppe von Proteinen, deren Löslichkeit sich nur änderte, wenn beide Wirkstoffe gemeinsam vorlagen. Die Autoren beschreiben dies als „konjunktionale Zieladressierung“, ähnlich einem UND‑Gatter in der Logik: Das Protein reagiert nur, wenn beide Eingänge (Wirkstoffe) aktiv sind. Bei LS konzentrierten sich diese ausschließlich bei der Kombination auftretenden Effekte auf Prozesse wie DNA‑Verpackung, kleine Proteinanhängsel namens SUMO, die die Genomstabilität steuern, und die Haftung der Leukämiezellen an ihr umgebendes Gewebe. Bei RU deuteten die einzigartigen Ziele auf abgeschwächte DNA‑Schadensprüfstellen, gestörte Energieproduktion in Mitochondrien und beeinträchtigte RNA‑Verarbeitung hin.
Die Schwachstellen des Krebses kartieren
Indem sie ihre Löslichkeitsdaten auf große Karten AML‑relevanter Gene und Signalwege überlagerten, konnten die Forschenden sehen, wie jede Behandlung die innere Verschaltung des Krebses umgestaltet. Viele bekannte AML‑Gene – wie DNMT3A, NPM1 und TP53 – wurden in Formen beeinflusst, die nur unter Kombinationstherapie auftraten, was die Idee stützt, dass gepaarte Wirkstoffe Verwundbarkeiten offenbaren können, die Einzelwirkstoffen verborgen bleiben. Das Team untersuchte auch chemische Modifikationen von Proteinen, etwa Acetylierung, Methylierung und Phosphorylierung, die als molekulare Schalter fungieren. Sie fanden, dass bestimmte modifizierte Formen von Schlüsselproteinen, darunter NPM1 und der DNA‑Reparaturfaktor BLM, spezifisch von den Kombinationen betroffen wurden, was nahelegt, dass veränderte Proteinlokalisation und Signalübertragung zum verstärkten Effekt beitragen.
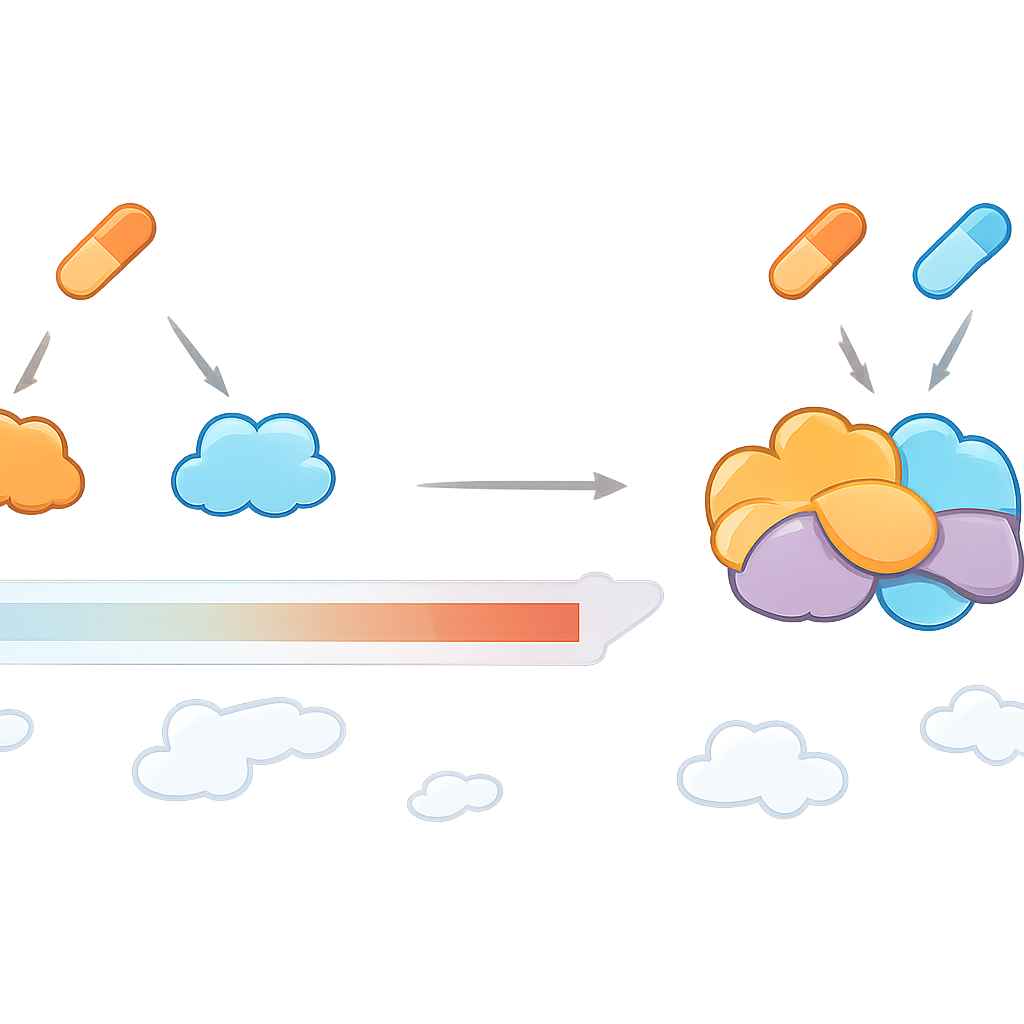
Was das für künftige Behandlungen bedeutet
Insgesamt zeigt die Studie, dass Medikamentkombinationen eine eigene, einzigartige Landschaft von Proteinzielen erzeugen können, statt die Effekte der Einzelwirkstoffe einfach zu addieren. CoPISA bietet einen praktischen Weg, diese Landschaft zu kartieren und Proteine sowie Signalwege hervorzuheben, die erst verwundbar werden, wenn zwei Wirkstoffe gemeinsam wirken. Für Patientinnen und Patienten könnte das bedeuten, dass Kombinationstherapien nicht nur wegen ihrer Wirkung in Zellkulturen ausgewählt werden, sondern weil sie die tieferen Schwachstellen des Krebses adressieren und gleichzeitig unnötige Toxizität begrenzen. Obwohl hier an AML demonstriert, ist der Ansatz generell anwendbar und kann helfen, die rationale Gestaltung von Kombinationstherapien bei vielen komplexen Erkrankungen zu leiten.
Zitation: Gholizadeh, E., Zangene, E., Vadadokhau, U. et al. Solubility based mechanistic profiling of combinatorial drug therapy. Nat Commun 17, 2744 (2026). https://doi.org/10.1038/s41467-026-70394-3
Schlüsselwörter: akute myeloische Leukämie, Arzneimittelkombinationen, Proteomik, Proteinlöslichkeit, zielgerichtete Therapie