Clear Sky Science · de
Identifizierung cis-regulatorischer Elemente liefert Einblicke in die gewebespezifische Genregulation im Schafgenom
Warum das Schafgenom im Alltag wichtig ist
Schafe ernähren Millionen von Menschen und stützen ländliche Ökonomien, doch wir wissen immer noch überraschend wenig darüber, wie ihre Gene in verschiedenen Körperregionen an- und ausgeschaltet werden. Diese Studie erstellt eine detaillierte Karte der Kontrollschalter, die die Genaktivität in 24 Geweben eines einzelnen Schafs feinjustieren — vom Gehirn und der Lunge bis zu Muskel und Euter. Durch das Kartieren dieser verborgenen Schalter legt die Arbeit die Grundlage für gesündere Tiere, bessere Produktionsmerkmale wie Milchfett und ein tieferes Verständnis dafür, wie Säugetierkörper, einschließlich unseres eigenen, Gene regulieren.
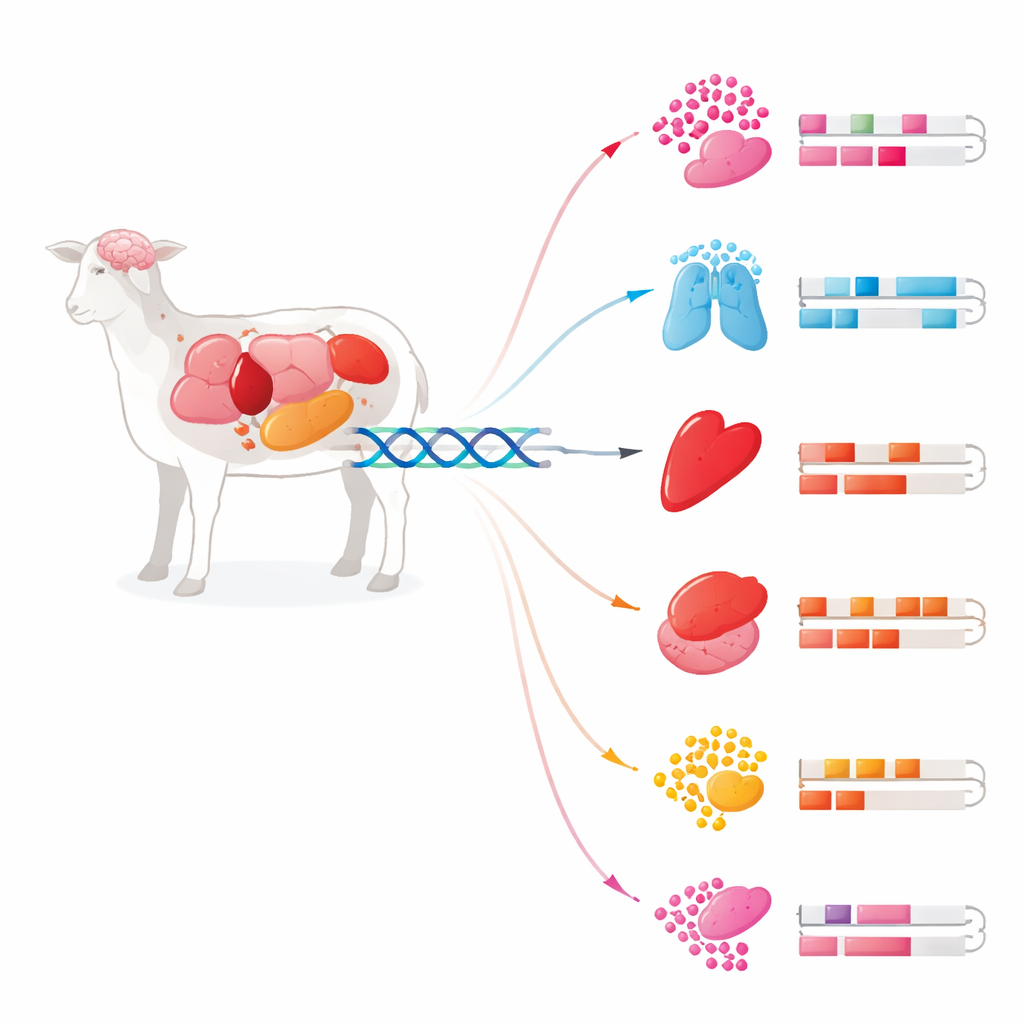
Verborgene Schalter in der DNA
Unsere DNA enthält nicht nur Gene; sie birgt auch riesige Abschnitte regulatorischen Codes, die wie Dimmerknöpfe wirken und entscheiden, wann und wo Gene aktiv werden. Zwei wesentliche Elementtypen sind Promotoren, direkt neben Genen, und Enhancer, die weit entfernt liegen können und dennoch Kontrolle ausüben. Die Forscher kombinierten sechs hochmoderne Methoden, die unterschiedliche Aspekte genomischer Aktivität erfassen: Proteinmarkierungen auf DNA-verpackenden Proteinen, offene Chromatinbereiche, Transkriptionsstartstellen, DNA-Methylierung und RNA-Ausstoß. Mit Hilfe dieser überlappenden Hinweise identifizierten sie mehr als 270.000 Enhancer und nahezu 26.000 Promotoren in 24 Geweben derselben Rambouillet-Schäfin, die auch für das aktuelle Schaf-Referenzgenom verwendet wurde. Diese einheitliche Karte zeigt, wo das Genom für Regulation verdrahtet ist, nicht nur welche Gene vorhanden sind.
Unterschiedliche Gewebe, unterschiedliche Steuerlogik
Obwohl fast jede Zelle dieselbe DNA trägt, verhalten sich Gewebe sehr unterschiedlich, weil sie verschiedene Mengen an Enhancern nutzen. Die Studie zeigte, dass Promotoren relativ stabil sind: Viele werden über Gewebe hinweg geteilt, und ihre Muster sind zwischen Arten konserviert. Enhancer dagegen sind hochvariabel und deutlich gewebespezifischer. Gehirngewebe wie das Kleinhirn und die Großhirnrinde zeichneten sich durch besonders reiche und vielfältige Enhancer-Landschaften aus. Einige neuronale Gene besaßen mehr als zehn Enhancer, was darauf hindeutet, dass zentrale Funktionen wie Nervenwachstum und Kommunikation durch dicht geschichtete regulatorische Kontrolle gesteuert werden und nicht durch einen einzigen Ein-/Ausschalter.
Genauer Blick auf Gehirn- und Organ‑Spezialisierung
Durch die Korrelation von Enhancer-Aktivität mit Genexpressionsniveaus verbanden die Autorinnen und Autoren beinahe 9.000 Enhancer mit etwa 4.300 Genen und entdeckten viele gewebespezifische Steuerpaare. Im Kleinhirn etwa scheint eine einzigartige Enhancer‑Region den Gehirnfaktor BDNF anders zu steuern als die benachbarte Großhirnrinde, was hilft, subtile Unterschiede zwischen Hirnregionen zu erklären, die dasselbe Gen teilen. Ähnliche Muster zeigten sich in Herz-, Darm- und Nebennierengewebe: Organe können überlappende Gen-Sets nutzen, doch unterschiedliche Enhancer in jedem Gewebe justieren, wann und wie stark diese Gene eingesetzt werden. Die Analyse der DNA‑Methylierung zeigte, dass chemische Markierungen auf Enhancern generell die Genaktivität dämpfen, was ihre Rolle als empfindliche Regulatoren statt passiver DNA‑Abschnitte unterstreicht.
Was Schafe und andere Säugetiere unterscheidet
Um zu sehen, wie sich Schafe zu anderen Säugetieren verhalten, verglich das Team seine Karte mit regulatorischen Daten von Menschen, Mäusen, Schweinen und Rindern. Promotoren erwiesen sich als hochkonserviert, während Enhancer zwischen den Arten viel stärker variierten — ein Befund, der die Idee stützt, dass die Evolution die Genregulation häufiger umverdrahtet als die Gene selbst verändert. Die Autorinnen und Autoren identifizierten Sets von Enhancer–Promotor‑Paaren, die nur bei Wiederkäuern wie Schafen und Rindern vorkommen und für Prozesse wie Zuckerabbau im Pansen und den Umgang mit langkettigen Fettsäuren angereichert sind. Das legt nahe, dass spezialisierte Verdauungssysteme und Stoffwechsel dieser Tiere teilweise durch einzigartige regulatorische Verschaltungen angetrieben werden und nicht allein durch einzigartige Gene.
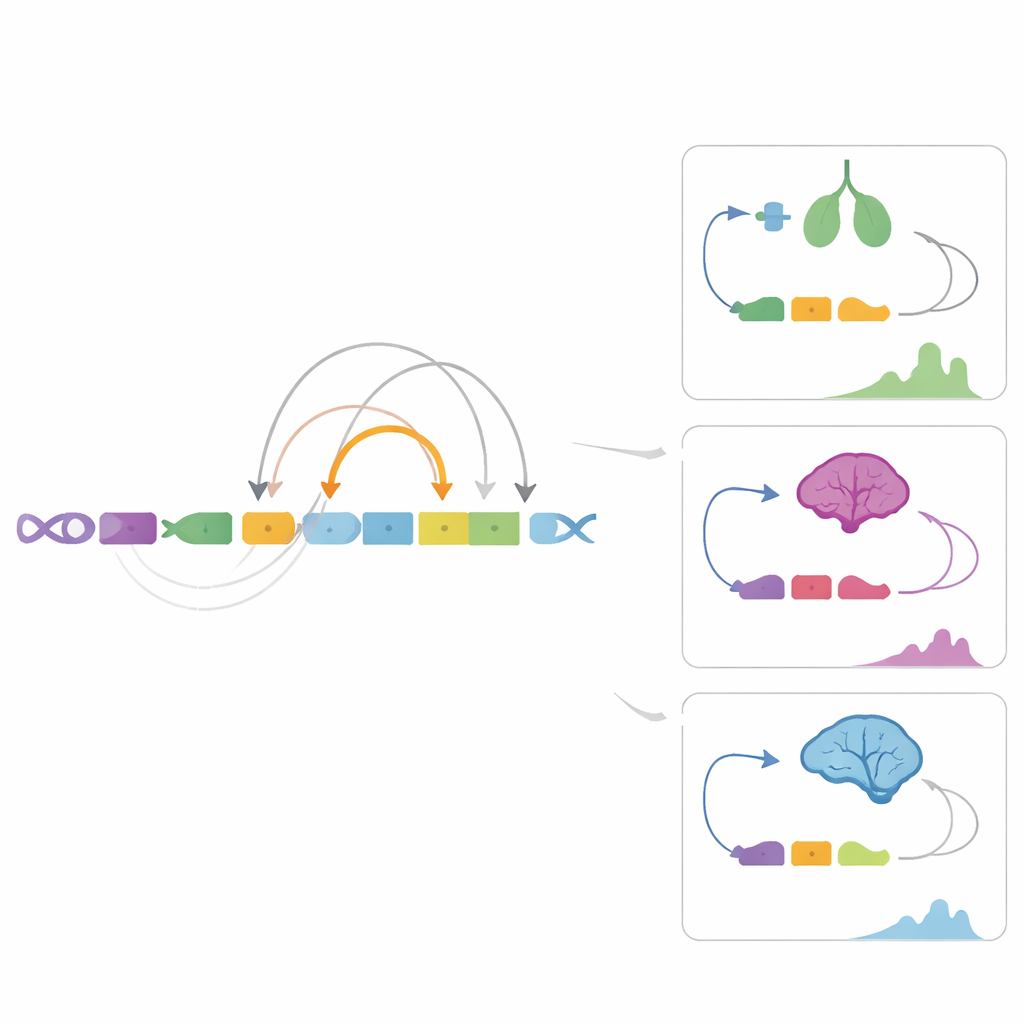
Verbindungen zu Merkmalen, die Landwirte interessieren
Da viele wirtschaftlich wichtige Merkmale von subtilen Veränderungen in der Genregulation abhängen, legte das Team Millionen genetischer Varianten und bekannte regionsweise trait‑assoziierte Bereiche über ihre Regulatorkarte. Sie entdeckten Varianten innerhalb von Enhancern, die wahrscheinlich die Milchfettproduktion beeinflussen, indem sie die Kontrolle eines Gens verändern, das an Kupfer‑ und Fettstoffwechsel beteiligt ist, COMMD1. Außerdem fanden sie mit dem Geburtsgewicht assoziierte Varianten in einem kleinhirnspezifischen Enhancer, der das Gen XKR4 regulieren dürfte — ein plausibler Weg von DNA‑Veränderung zu Wachstumsmerkmalen. Diese Beispiele zeigen, wie Enhancer‑Karten anonyme Signale aus genomweiten Assoziationsstudien in konkrete biologische Hypothesen darüber verwandeln können, wie Merkmale entstehen.
Was das für die Zukunft bedeutet
Für Laien lautet die Kernbotschaft, dass diese Studie das Schafgenom von einer statischen Teileliste in ein Verdrahtungsdiagramm verwandelt und zeigt, wie und wo Gene in echten Geweben gesteuert werden. Indem sie Hunderttausende regulatorischer Schalter katalogisiert, ihre Aktivität in verschiedenen Organen klärt und sie mit Merkmalen und Artunterschieden verbindet, bietet die Arbeit eine starke Grundlage für die Zucht gesünderer, produktiverer Tiere und für das Verständnis, wie komplexe Merkmale aus Genregulation entstehen. Ähnliche Karten in anderen Arten, einschließlich des Menschen, werden unser Verständnis von Gesundheit, Krankheit und Evolution vertiefen, indem sie den Fokus auf die Verwaltung von Genen legen und nicht nur auf deren bloße Existenz.
Zitation: Xie, S., Davenport, K.M., Salavati, M. et al. Identification of cis-regulatory elements provides insights into tissue-specific gene regulation in the sheep genome. Nat Commun 17, 2413 (2026). https://doi.org/10.1038/s41467-026-70382-7
Schlüsselwörter: gewebespezifische Genregulation, Schafgenomik, Enhancer und Promotoren, funktionelle Genomik bei Nutztieren, Wiederkäuer-Evolution