Clear Sky Science · de
Die dynamische Verteilung genetischer Tandemverstärkungen in einer heteroresistenten Escherichia-coli-Population, aufgedeckt durch ultra-tiefes Long-Read-Sequencing
Verborgene Überlebensnischen
Wenn Ärztinnen und Ärzte bakterielle Infektionen mit Antibiotika behandeln, gehen sie meist davon aus, dass sich der gesamte Bakterienverband einheitlich verhält. Doch manchmal widersteht ein winziger Teil der Population stillschweigend, überlebt die Behandlung und legt damit den Grundstein für ein Therapieversagen oder ein Rezidiv. Diese Studie zeigt, wie solche seltenen Überlebenden bei Escherichia coli entstehen und sich im Laufe der Zeit verschieben, und stellt eine leistungsfähige Methode vor, um diese genetischen Veränderungen Zelle für Zelle zu verfolgen.
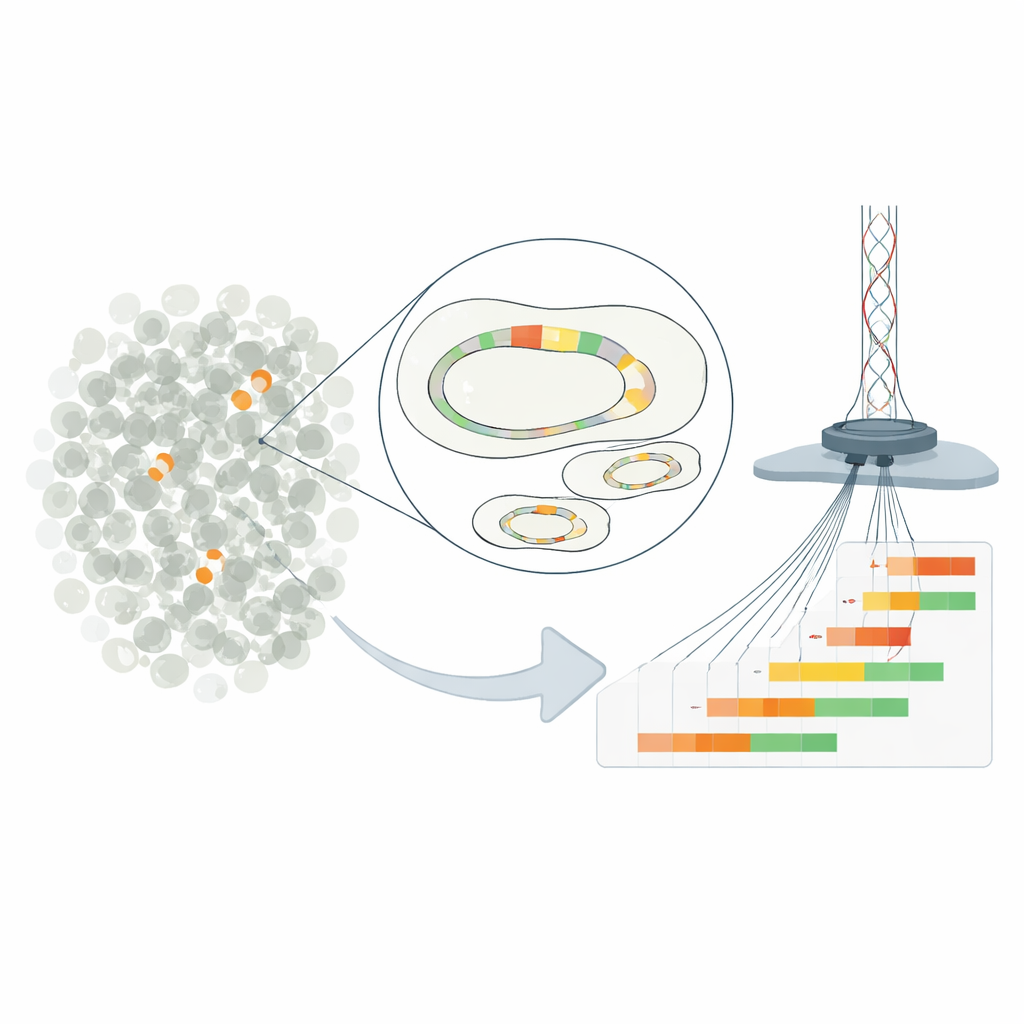
Kleine genetische Wiederholungen, große Wirkung
Die Arbeit konzentriert sich auf „Heteroresistenz“, ein Phänomen, bei dem die Mehrheit der Bakterien in einer Probe anfällig für ein Medikament erscheint, während eine kleine Minderheit deutlich höhere Dosen übersteht. In dem untersuchten E.-coli-Stamm beruht dieses Verhalten auf mehrfachen Kopien eines Resistenzgens, das auf einem Plasmid sitzt — einem kleinen DNA-Kreis getrennt vom Hauptchromosom. Durch die Duplizierung eines kurzen DNA-Abschnitts, der ein Beta-Lactamase-Gen enthält, können die Bakterien die Produktion eines Enzyms steigern, das das Antibiotikum Piperacillin-Tazobactam abbaut. Je mehr Wiederholungen eine Zelle trägt, desto mehr Enzym produziert sie und desto höher sind ihre Überlebenschancen in Anwesenheit des Arzneimittels.
DNA-Kreise in nie dagewesener Detailtiefe lesen
Traditionelle Methoden können nur die durchschnittliche Anzahl von Genkopien über eine gesamte Bakterienpopulation schätzen und überdecken dadurch die reiche Vielfalt zwischen einzelnen Zellen. Um dem zu entgehen, veränderten die Forschenden das klinische Plasmid so, dass es an einer präzisen Stelle geschnitten und anschließend vom übrigen Genom isoliert werden konnte. Sie nutzten ultra-tiefes Nanopore-Long-Read-Sequencing, um komplette Plasmidmoleküle von Ende zu Ende zu lesen und exakt zu zählen, wie viele wiederholte Resistenz-Einheiten jede einzelne enthielt. Mit dieser Methode erreichten sie eine Auflösung bis hinunter zu einer Zelle pro 100.000 und entdeckten Plasmide mit null bis mehr als einem Dutzend Genkopien, die in derselben Kultur koexistierten. Kontrollen mit anderen Techniken bestätigten, dass die neue Methode im Mittel korrekte Kopienzahlen angab.
Wie Antibiotika die Population umformen
Mit diesem Werkzeug verfolgte das Team, was geschah, als sie E.-coli-Kulturen steigenden Konzentrationen von Piperacillin-Tazobactam aussetzten und das Medikament danach wieder entfernten. Mit zunehmenden Antibiotikaspiegeln verschob sich die Gesamtverteilung zugunsten von Plasmiden mit mehr Kopien des Resistenzgens, doch Zellen mit weniger Kopien verschwanden nie vollständig. Nachdem das Medikament entzogen wurde und die Bakterien über Hunderte von Generationen weiterkultiviert wurden, driftete die Population nur langsam zurück zu niedrigeren Kopienzahlen und kehrte nie vollständig in ihren Ausgangszustand zurück. Getrennte Wachstumstests zeigten, dass jede zusätzliche Genkopie eine messbare Erhöhung der Medikamententoleranz bewirkte, wodurch die beobachteten genetischen Verteilungen eng mit dem sichtbaren Heteroresistenz-Muster in Standardlabortests verknüpft wurden.

Schutz durch Nachbarn und stille Kosten
Um zu erklären, warum Zellen mit wenigen Kopien selbst unter starker Behandlung persistent blieben, konstruierten die Autorinnen und Autoren ein mathematisches Modell, das Bakterienwachstum, Antibiotikabeseitigung und die zufälligen Ereignisse integrierte, die Genkopien hinzufügen oder entfernen. Die Simulationen zeigten, dass „indirekte Resistenz“ eine Schlüsselrolle spielt: Hochresistente Zellen pumpen genügend Beta-Lactamase aus, um die Wirkstoffkonzentration in der geteilten Umgebung zu senken und damit weniger resistente Nachbarn beiläufig zu schützen. Solange die zusätzlichen Genkopien nur geringe Wachstumskosten verursachen, wenn kein Medikament vorhanden ist, trägt dieser Schutz dazu bei, eine breite Verteilung von Kopienzahlen aufrechtzuerhalten und verlangsamt die Rückkehr zu einer vollständig anfälligen Population. Das Modell zeigte auch, wie gewöhnliche Anpassungen an das Nährmedium — unabhängige Mutationen, die das Wachstum verbessern — bestimmte Kopienzahlzustände zementieren können, indem sie einige Subpopulationen fitter machen als andere.
Warum das für Patientinnen, Patienten und darüber hinaus wichtig ist
Für Nicht-Fachleute lautet die Botschaft: Eine Bakterienkultur ist kein einheitlicher Gegner, sondern ein sich ständig wandelnder Mix von Individuen mit unterschiedlichen Fähigkeiten, Antibiotika zu überleben. Indem diese Studie Genkopien direkt auf tausenden einzelner DNA-Moleküle zählt, verbindet sie diese verborgene Vielfalt quantitativ mit behandlungsrelevantem Resistenzverhalten. Solche Erkenntnisse könnten verbessern, wie Genomsequenzierung verwendet wird, um schwer erkennbare Heteroresistenz vorherzusagen, helfen, Bakterienstämme zu identifizieren, die besonders wahrscheinlich Therapieversagen verursachen, und bessere Diagnosetests leiten. Da Tandem-Genamplifikationen auch schnelle Anpassung in Viren, Tumoren und anderen Organismen antreiben, könnte dieselbe Strategie weit über E. coli hinaus angewendet werden und ein neues Fenster dafür öffnen, wie wiederholte DNA-Abschnitte dem Leben helfen, Bedrohungen zu überlisten.
Zitation: Jonsson, S., Guliaev, A., Berryhill, B.A. et al. The dynamic distribution of genetic tandem amplifications in a heteroresistant Escherichia coli population revealed by ultra-deep long read sequencing. Nat Commun 17, 2113 (2026). https://doi.org/10.1038/s41467-026-70044-8
Schlüsselwörter: antibiotische Heteroresistenz, Genamplifikation, Escherichia coli, Long-Read-Sequenzierung, Beta-Lactamase