Clear Sky Science · de
Artübergreifende Gen-Neuentwürfe mithilfe von Orthologeninformationen und generativem Modellieren
Warum Gen-Neuentwürfe zwischen Arten wichtig sind
Die moderne Biotechnologie muss häufig Gene von einem Mikroorganismus in einen anderen übertragen, um Medikamente, Enzyme oder Werkzeuge zur Umweltreinigung herzustellen. Ein Gen, das in seinem ursprünglichen Wirt gut funktioniert, kann in einem neuen Wirt jedoch schlecht exprimiert werden und nur wenig Protein produzieren. Dieser Artikel stellt ein neues System der künstlichen Intelligenz vor, OrthologTransformer, das aus der Evolution selbst lernt, Gene so umzuschreiben, dass sie in einer anderen Spezies „heimisch“ wirken, ihre Leistung steigern und neue Möglichkeiten für grüne Technologien und die Industrie eröffnen.
Grenzen heutiger Gen-Tuning-Tricks
Seit Jahrzehnten vertrauen Wissenschaftler auf eine Strategie namens Codon-Optimierung, um fremde Gene in neuen Wirten funktionsfähig zu machen. Die Idee ist einfach: Der genetische Code hat mehrere dreibuchstabige „Codons“, die dieselbe Aminosäure kodieren können, und verschiedene Spezies bevorzugen unterschiedliche Codons. Traditionelle Werkzeuge tauschen seltene Codons gegen bevorzugte aus, ohne die Aminosäuresequenz des Proteins zu verändern. Das hilft oft, ignoriert aber viele andere Faktoren, die für die Genleistung wichtig sind, wie RNA-Faltung, regulatorische Signale und das Timing der Proteinsynthese. In einigen Fällen kann übermäßige Codon-Optimierung sogar die Proteinausbeute verschlechtern. Die Natur löst artübergreifende Anpassung hingegen auf reichhaltigere Weise: Verwandte Gene in verschiedenen Spezies, sogenannte Orthologe, zeigen häufig Aminosäureänderungen sowie kleine Insertionen oder Deletionen neben Codonänderungen, während die Gesamtfunktion erhalten bleibt.
Das Spielbuch der Natur für Gen-Umschreibungen lernen
OrthologTransformer betrachtet Gen-Neuentwurf als eine Art Sprachübersetzung: Gegeben eine DNA-Sequenz aus einem Bakterium „übersetzt“ es diese in die Form, wie dieses Gen wahrscheinlich in einer anderen Spezies aussehen würde. Das Modell basiert auf der Transformer-Architektur, die in modernen Sprachwerkzeugen verwendet wird, arbeitet hier jedoch mit Codons statt mit Wörtern. Es wird an Millionen natürlicher Paare orthologer Gene aus über zweitausend bakteriellen Spezies trainiert, mit speziellen Tokens, die angeben, von welcher und in welche Spezies konvertiert wird. Indem es beobachtet, wie die Evolution bereits Funktion und Wirtanpassung austariert hat, lernt das System, wann einfache Codonwechsel ausreichen und wann subtile Aminosäureänderungen oder Längenanpassungen toleriert werden. In Tests über 45 bakterielle Spezies und Hunderte von Quell–Ziel-Kombinationen ähnelten die vom KI-System neu entworfenen Gene den nativen Orthologen der Zielspezies stärker als sowohl konventionelle Codon-Optimierung als auch ein führender neuronaler Codon-Optimierer, während sie auf Proteinebene weiterhin hohe Ähnlichkeit bewahrten. 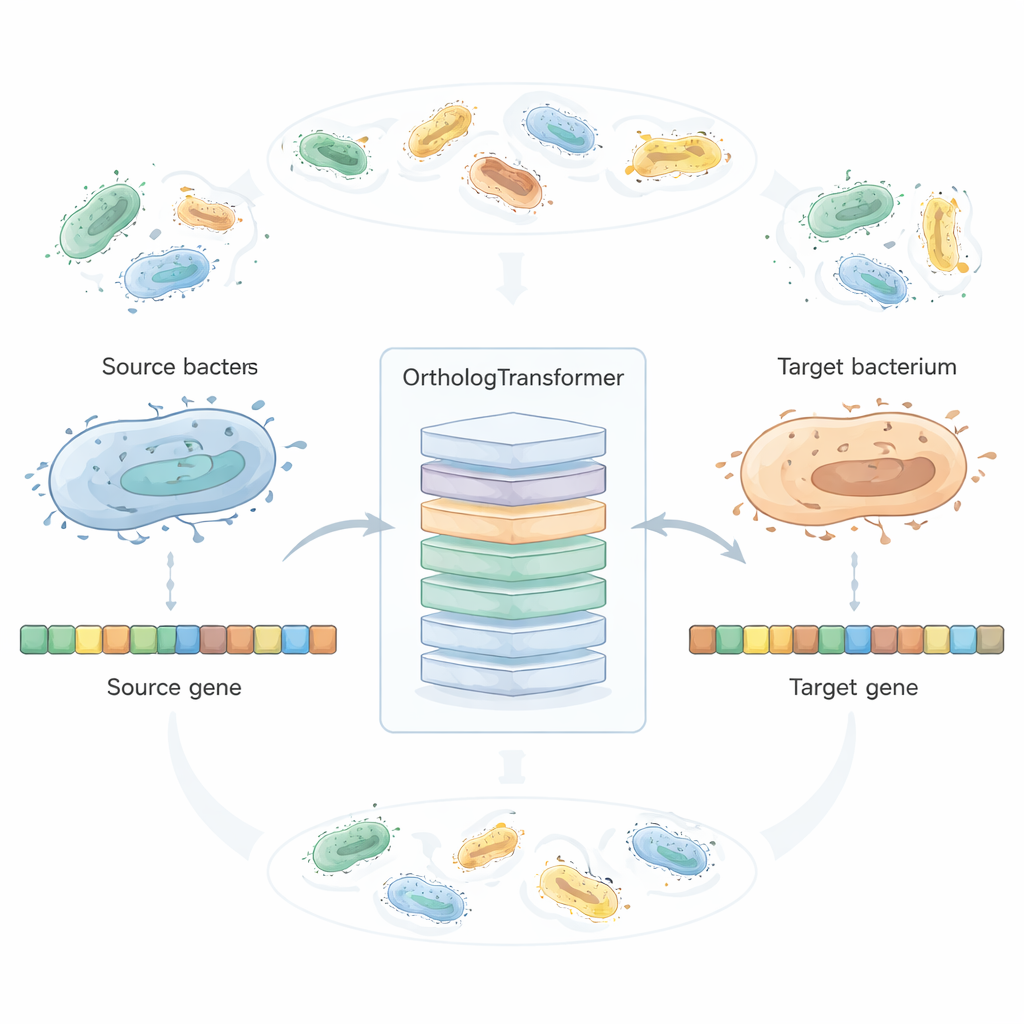
KI-entworfene, plastikabbauende Enzyme in der Praxis
Um zu zeigen, dass dies mehr als ein rein rechnerischer Trick ist, konzentrierte sich das Team auf PETase, ein Enzym des Bakteriums Ideonella sakaiensis, das PET-Kunststoff abbauen kann, das Material, aus dem die meisten Getränkeflaschen bestehen. Ideonella wächst langsam und ist industriell nicht ideal, daher baten die Forschenden den OrthologTransformer, das PETase-Gen für einen schneller wachsenden Wirt, Bacillus subtilis, umzuschreiben. Sie erzeugten ein Panel von zwölf neu entworfenen Genvarianten, erkundeten verschiedene Trainingskonfigurationen und ein zusätzliches Suchverfahren, das Sequenzen in Richtung bacillusähnlicher DNA-Zusammensetzung und günstiger RNA-Strukturen lenkte. Trotz einiger Varianten mit vielen DNA-Änderungen und wenigen Aminosäuresubstitutionen sagten Computermodelle voraus, dass die grundlegende 3D-Form des Enzyms erhalten blieb. Als diese Entwürfe gebaut und in lebenden Bacillus-Zellen getestet wurden, produzierten mehrere große Mengen sekretierter PETase, und alle zeigten messbare plastikabbauende Aktivität.
Ein KI-Entwurf, der Standardoptimierung übertrifft
Eine KI-entworfene Sequenz, genannt AI-L2, stach besonders hervor. Bacillus-Zellen mit diesem Gen sezernierten besonders große Mengen PETase und erzeugten in einem siebentägigen Test etwa dreimal mehr Abbauprodukt als jeder andere Stamm und etwa zehnmal mehr als typische codonoptimierte Kontrollen, gemessen an den Reaktionsprodukten. Mikroskopische Aufnahmen von PET-Folien, die AI-L2-Zellen ausgesetzt wurden, zeigten tiefe Gruben und Löcher, wo der Kunststoff abgetragen worden war — deutlich dramatischer als unter anderen Bedingungen. Detaillierte Enzymtests zeigten, dass die AI-L2-Version von PETase nicht nur effizienter produziert wurde, sondern ihr Substrat auch schneller verarbeitete, wodurch sie eine höhere katalytische Effizienz als das Original und die codonoptimierten Enzyme aufwies. Ein paralleles Experiment in Escherichia coli zeigte, dass eine vom OrthologTransformer entworfene PETase-Version, selbst wenn sie nur die Codon-Verwendung änderte und nicht die Aminosäuresequenz, dennoch eine Häufigkeits-basierte Codon-optimierte Variante übertraf — ein Hinweis darauf, dass das Modell subtile, wirtsspezifische Präferenzen erfasst, die traditionelle Methoden übersehen. 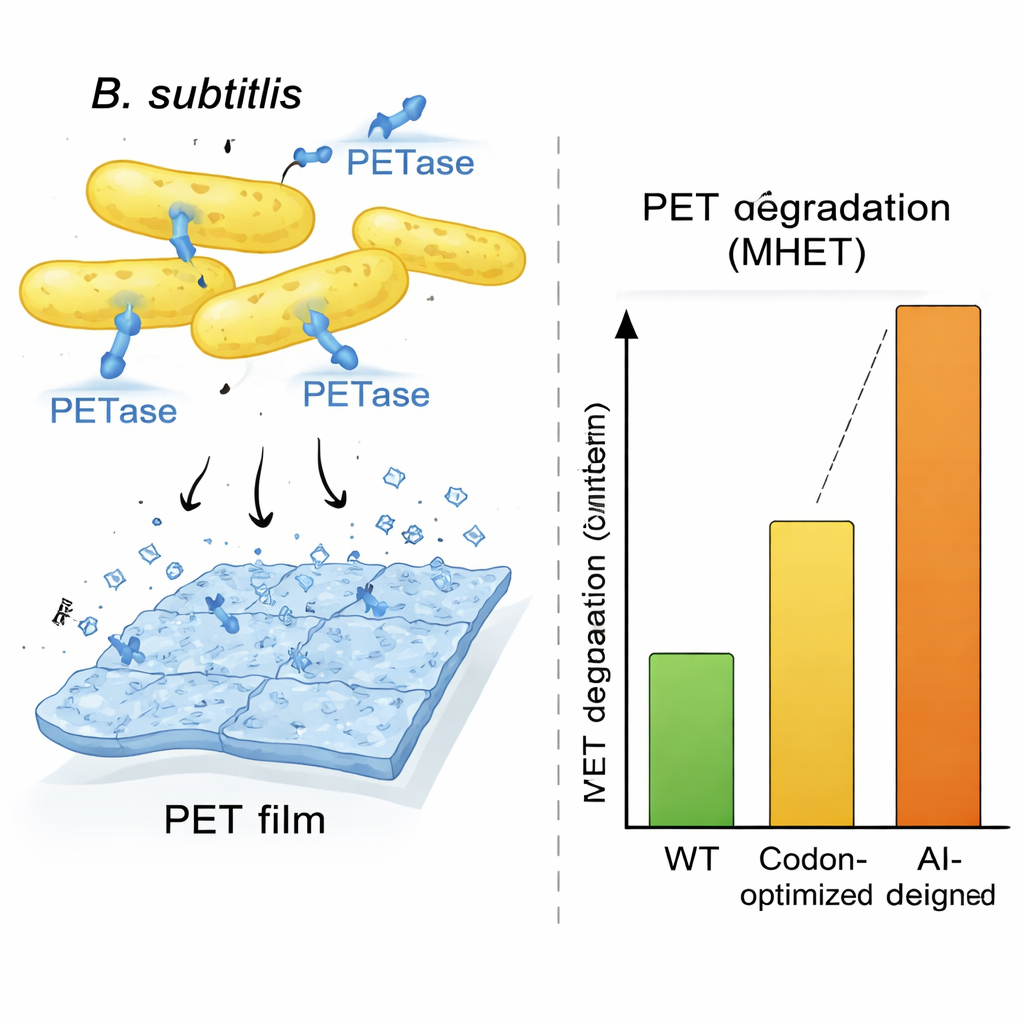
Was das für zukünftige Biologie und Technologie bedeutet
Alltäglich ausgedrückt ist OrthologTransformer wie ein erfahrener Übersetzer, der nicht nur die „Rechtschreibung“ eines Gens für einen neuen Mikrobenwirt umschreibt, sondern auch kleine, evolutionsinformierte Änderungen am „Satz“ selbst vornimmt, wenn er weiß, dass sie sicher oder vorteilhaft sind. Indem es direkt von der natürlichen Anpassung von Genen über Tausende bakterieller Spezies lernt, kann es neu entworfene DNA vorschlagen, die in neuen Wirten besser funktioniert als Designs, die auf reinen Codonwechseln beruhen. Die erfolgreiche Erzeugung eines leistungsfähigeren, plastikabbauenden Enzyms in Bacillus subtilis deutet darauf hin, dass eine solche KI-gesteuerte Gen-Neuentwurfsstrategie die Entwicklung industrieller Biokatalysatoren, mikrobieller Umweltreinigungswerkzeuge und möglicherweise sogar medizinischer Gentherapien beschleunigen könnte, indem sie Organismen hilft, fremde Gene zu lesen und zu nutzen, als wären sie ihre eigenen.
Zitation: Akiyama, M., Tashiro, M., Huang, Y. et al. Cross-species gene redesign leveraging ortholog information and generative modeling. Nat Commun 17, 2120 (2026). https://doi.org/10.1038/s41467-026-69966-0
Schlüsselwörter: Gen-Neuentwurf, synthetische Biologie, orthologe Gene, KI in der Biotechnologie, plastikabbauende Enzyme