Clear Sky Science · de
Rechen- und ressourceneffiziente genomweite Assoziationsanalyse für groß angelegte Bildgebungsstudien
Einblick in den genetischen Bauplan des Gehirns
Warum altern die Gehirne mancher Menschen anmutiger, widerstehen psychischen Erkrankungen oder unterstützen bessere Gedächtnis- und Lernleistungen? Moderne Gehirnscans und Gentests versprechen Antworten, doch das schiere Datenvolumen war überwältigend. Diese Studie stellt einen neuen Weg vor, winzige DNA-Unterschiede mit hochauflösenden Hirnbildern zu verknüpfen und macht es damit endlich praktikabel, das gesamte Genom gegen Millionen von Messpunkten im Gehirn zu untersuchen. Der Ansatz reduziert nicht nur Rechen- und Speicherbedarf drastisch, er fördert auch verborgene genetische Muster zutage, die bestimmte Hirnregionen mit Merkmalen wie Bildungsniveau, Depression und Schizophrenie verbinden.
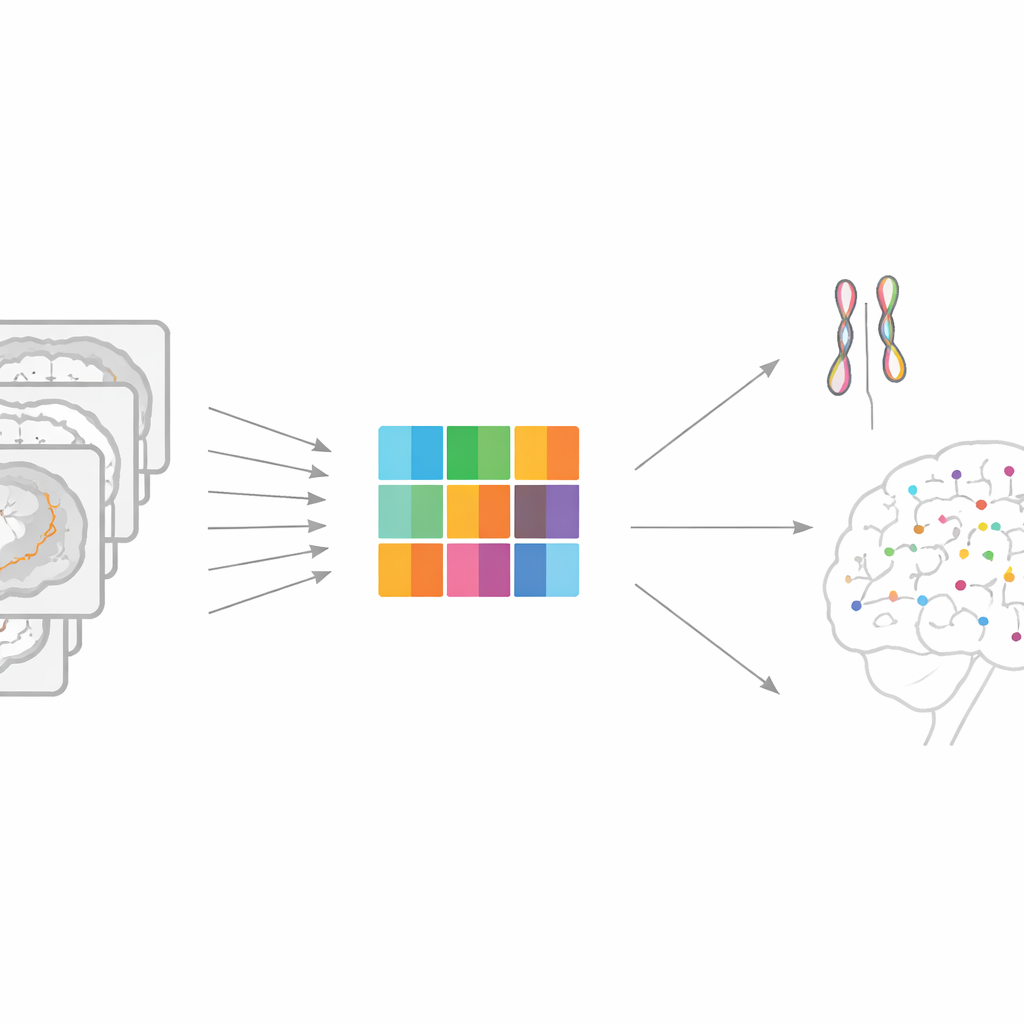
Von unscharfen Mittelwerten zu detaillierten Gehirnkarten
Die meisten großen genetischen Gehirnstudien vereinfachen Bilder zu einigen hundert zusammenfassenden Messwerten, etwa dem Gesamtvolumen einer Region. Diese Abkürzung macht die Analyse möglich, verwischt aber feine Details. Jeder Scan enthält tatsächlich Zehntausende winziger Orte, sogenannte Voxel, an denen Struktur und Verschaltungen variieren können. Ein direkter „Voxel-für-Voxel“-Abgleich über das ganze Genom wäre wissenschaftlich ideal, würde in der Praxis jedoch in Billionen von Tests explodieren, enormen Rechenaufwand erfordern und Zusammenfassungsdateien erzeugen, die zu groß sind, um sie zu teilen oder wiederzuverwenden.
Ein intelligenter Weg zur Kompression von Hirnbildern
Die Autorinnen und Autoren schlagen ein Framework namens Representation learning-based Voxel-level Genetic Analysis (RVGA) vor, um diesen Engpass zu überwinden. RVGA bereinigt zunächst jedes Hirnbild, indem es glatte, bedeutungsvolle Strukturen vom zufälligen Scannerrauschen trennt. Anschließend lernt es eine kleine Menge zugrunde liegender Muster – wie grundlegende Bausteine von Form und Textur –, die kombiniert werden können, um das ursprüngliche Bild zu rekonstruieren. Das Gehirn jedes Einzelnen wird somit nicht durch alle Voxel, sondern durch Werte auf diesen Mustern zusammengefasst, wodurch die Datengröße um ein bis drei Größenordnungen reduziert wird, während das meiste Signal erhalten bleibt. Diese Musterscores werden dann als Traits in einer standardmäßigen genomweiten Assoziationsstudie behandelt, die deutlich schneller läuft.
Das vollständige Bild aus kleinen Teilen rekonstruieren
Entscheidend ist, dass RVGA nicht bei diesen komprimierten Traits stehen bleibt. Mithilfe der gelernten Muster projiziert es die genetischen Befunde mathematisch vom Musterlevel zurück auf jeden Voxel im Bild. Dieser Trick erlaubt es Forschenden, detaillierte Assoziationskarten auf Voxel-Ebene zu rekonstruieren, ohne je Milliarden separater Modelle anpassen zu müssen. Alles, was gespeichert und geteilt werden muss, sind drei kompakte Bestandteile: die genetischen Ergebnisse für die Muster, die Bildmuster selbst und die Art, wie die Musterscores über Personen variieren. Aus diesem minimalen „Triplet“ kann RVGA vollständige hochauflösende Karten genetischer Effekte rekonstruieren, abschätzen, wie viel Genetik zur Variation an jedem Voxel beiträgt, und berechnen, wie Genetik zwischen Voxeln und mit externen Traits geteilt wird.
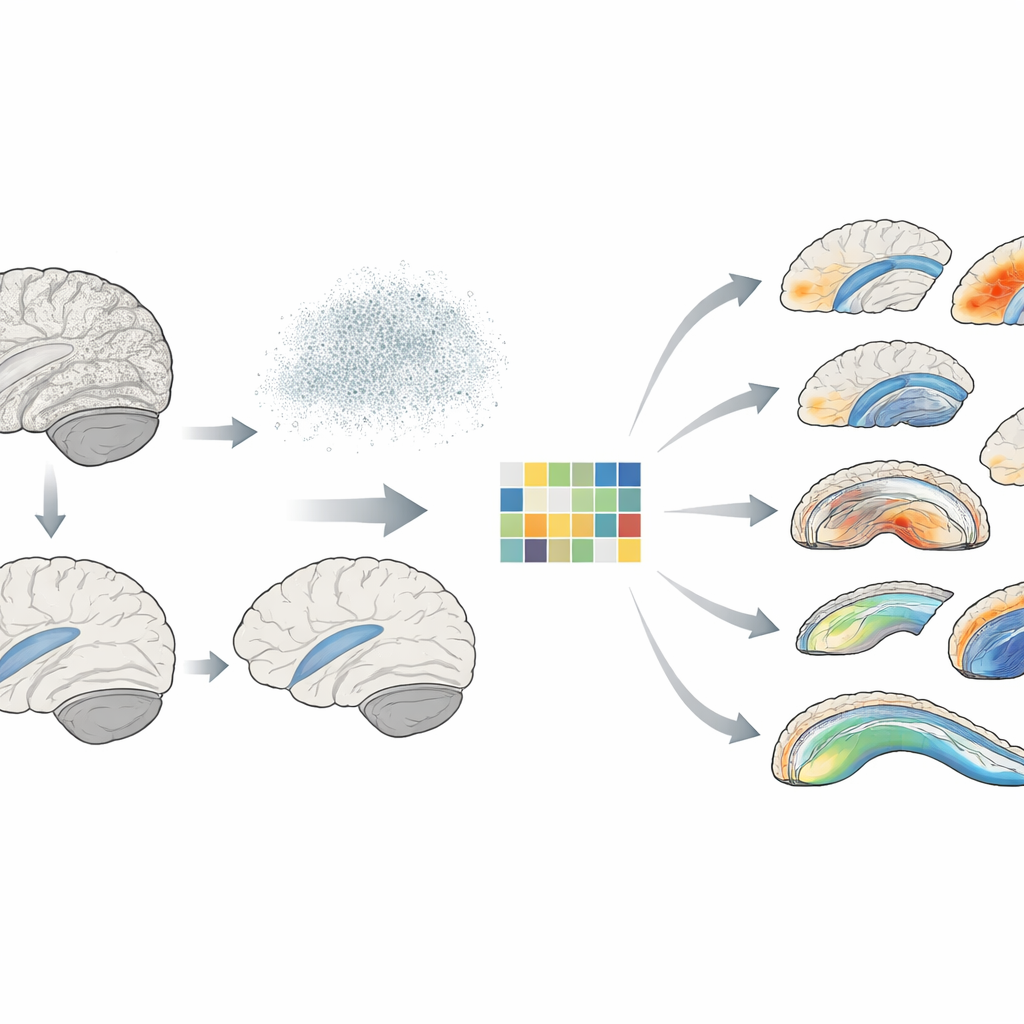
Was die neue Methode in realen Gehirnen enthüllt
Das Team wandte RVGA auf Gehirnscans und genetische Daten von mehr als 53.000 Teilnehmenden der UK Biobank an. Sie konzentrierten sich auf die detaillierte Form des Hippokampus – entscheidend für das Gedächtnis – und die feine Struktur wichtiger weißer Substanzbahnen, die verschiedene Hirnregionen verbinden. Mit RVGA identifizierten sie 39 zuvor nicht berichtete genetische Regionen, die die Hippokampusform beeinflussen, und 275 neue Regionen, die die Mikrostruktur der weißen Substanz beeinflussen, während gleichzeitig viele bekannte Befunde repliziert wurden. Die Methode verringerte die Größe der resultierenden genetischen Zusammenfassungsdateien um etwa das 229-Fache, wodurch sie deutlich leichter zu teilen sind. Außerdem zeigte sich, dass genetischer Einfluss alles andere als gleichmäßig verteilt ist: Einige Hippokampus-Subregionen wiesen deutlich höhere Erblichkeit auf als andere, und bestimmte Segmente der weißen Substanz trugen besonders starke genetische Signaturen.
Verknüpfungen zu Bildung, Stimmung und psychischen Erkrankungen
Da RVGA mit genetischen Ergebnissen aus anderen Studien kombiniert werden kann, erstellten die Autorinnen und Autoren „Atlanten“ darüber, wie Hirnvoxel genetische Wurzeln mit Gehirnerkrankungen und verwandten Merkmalen teilen. Sie fanden zum Beispiel, dass Teile des Hippokampus-Schwanzes und benachbarte Strukturen positive genetische Verbindungen mit Bildungserfolg aufwiesen, während eine andere Subregion, das Presubiculum, eine negative Verbindung zeigte. In der weißen Substanz teilten bestimmte Segmente der anterioren Corona radiata genetische Einflüsse mit Schizophrenie, und Teile des Corpus callosum zeigten negative genetische Verknüpfungen mit bipolarer Störung. Viele dieser Muster bestätigen frühere Regionenbefunde, doch RVGA verfeinert sie zu präzisen Subregionen und deutet so auf gezieltere biologische Pfade hin.
Warum das für die Gehirngesundheit wichtig ist
Indem es ultradetaillierte genetische Scans des Gehirns praktikabel und teilbar macht, öffnet RVGA die Tür zu einer neuen Generation bildgebungsgenetischer Studien. Forschende können nun genau sehen, welche winzigen Hirngewebspatches von bestimmten genetischen Varianten beeinflusst werden, wie stark und auf welche Weise diese Patches genetische Gemeinsamkeiten mit kognitiven Funktionen und psychischen Erkrankungen teilen. Mit der Zeit könnten solche Karten biologische Schaltkreise lokalisieren, die überwacht, geschützt oder sogar in personalisierten Behandlungen gezielt adressiert werden können. Die Methode verallgemeinert sich außerdem über das Gehirn hinaus auf andere bildgebungsreiche Organe und verspricht einen breiteren Wandel von unscharfen Mittelwerten hin zu genetischen Einsichten in hoher Auflösung.
Zitation: Jiang, Z., Stein, J., Li, T. et al. Computation and resource efficient genome-wide association analysis for large-scale imaging studies. Nat Commun 17, 3313 (2026). https://doi.org/10.1038/s41467-026-69816-z
Schlüsselwörter: Bildgebungsgenetik, Gehirn-MRT, genomweite Assoziation, Hippokampus, weiße Substanz