Clear Sky Science · de
Heterogene Multikopie von blaCTX-M-Varianten auf demselben Plasmid erhöht die evolutionäre Anpassungsfähigkeit bei klinischen Klebsiella pneumoniae
Warum das für die moderne Medizin wichtig ist
Antibiotikaresistente Infektionen sind in Krankenhäusern weltweit eine wachsende Bedrohung, und Ärztinnen und Ärzte sind zunehmend auf Reservemedikamente angewiesen, um Patientinnen und Patienten zu retten. Diese Studie erklärt, wie ein in Krankenhäusern häufig vorkommendes Bakterium, Klebsiella pneumoniae, einen subtilen genetischen Trick nutzen kann, um leistungsstarke Antibiotikakombinationen zu überstehen, die eigentlich zur Überwindung von Resistenzen entwickelt wurden. Durch die Aufklärung dieser Strategie liefert die Forschung Hinweise darauf, warum manche Infektionen trotz aggressiver Behandlung immer wieder auftreten — und zeigt Ansätze auf, wie Ärztinnen und Ärzte einen Schritt voraus bleiben könnten.
Ein Krankenhauskeim unter Druck
Die Geschichte beginnt auf einer Intensivstation, wo zwei Patientinnen bzw. Patienten von nahezu identischen Stämmen von K. pneumoniae infiziert wurden. Ein Stamm ließ sich leicht mit dem modernen Arzneimittelpaar Ceftazidim/Avibactam behandeln, während der andere stark resistent war. Genetische Vergleiche zeigten, dass beide Stämme dieselbe breite Familie von Resistenzenzymen trugen, sogenannte β-Laktamasen, auf einem gemeinsamen Plasmid — einem kleinen, mobilen DNA-Kreis im Inneren der Bakterien. Im resistenten Stamm hatte sich jedoch eines dieser Enzyme dezent verändert; diese Variante, CTX-M-249 genannt, ermöglichte dem Bakterium, die Kombination zu überstehen, die es eigentlich hätte abtöten sollen.
Eine kleine Veränderung mit großen Folgen
Genauere biochemische Tests zeigten, dass CTX-M-249 eine Art Schutz gegen einen anderen tauscht. Die übliche Version, CTX-M-65, ist hervorragend darin, bestimmte Antibiotika wie Cefotaxim zu spalten, bleibt aber gegenüber dem Inhibitor Avibactam verwundbar. CTX-M-249, das an nur zwei Positionen im Protein verändert ist, wird gut darin, mit Ceftazidim plus Avibactam fertigzuwerden, verliert aber einen Großteil seiner Wirksamkeit gegen Cefotaxim. Auf dem Papier sieht das wie ein klassischer evolutionärer Zielkonflikt aus: Man gewinnt eine Verteidigung, verliert dafür eine andere. Trotzdem umging der klinische Stamm diesen Nachteil, indem er mehrere eng verwandte Kopien des Gens gleichzeitig trug, sodass unterschiedliche Versionen des Enzyms in derselben bakteriellen Linie koexistieren konnten.
Viele Kopien, viele Optionen
Mithilfe von Langzeit-DNA-Sequenzierung und präzisen Zählmethoden fanden die Forschenden heraus, dass das Plasmid im resistenten Stamm zwei getrennte blaCTX-M-Stellen trug, und eine davon in mehreren, leicht unterschiedlichen Versionen vorliegen konnte. Ohne Antibiotikadruck trug etwa die Hälfte der Population die ältere CTX-M-65-Version und nahezu die andere Hälfte CTX-M-249, mit einem kleinen Anteil intermediärer Formen. Wurden die Bakterien zunehmenden Dosen von Ceftazidim/Avibactam ausgesetzt, stiegen sowohl die Kopienzahl des Gens als auch der Anteil von CTX-M-249 stark an. Manchmal geschah dies durch eine Erhöhung der Plasmidzahl pro Zelle; bei höheren Wirkstoffkonzentrationen bildete das Plasmid selbst kurze Tandemwiederholungen des Resistenzgens. Effektiv nutzten die Bakterien DNA-Duplikation als ein Einstellrad, das sie auf- oder abdrehen konnten, um sich an die umgebenden Antibiotika anzupassen.
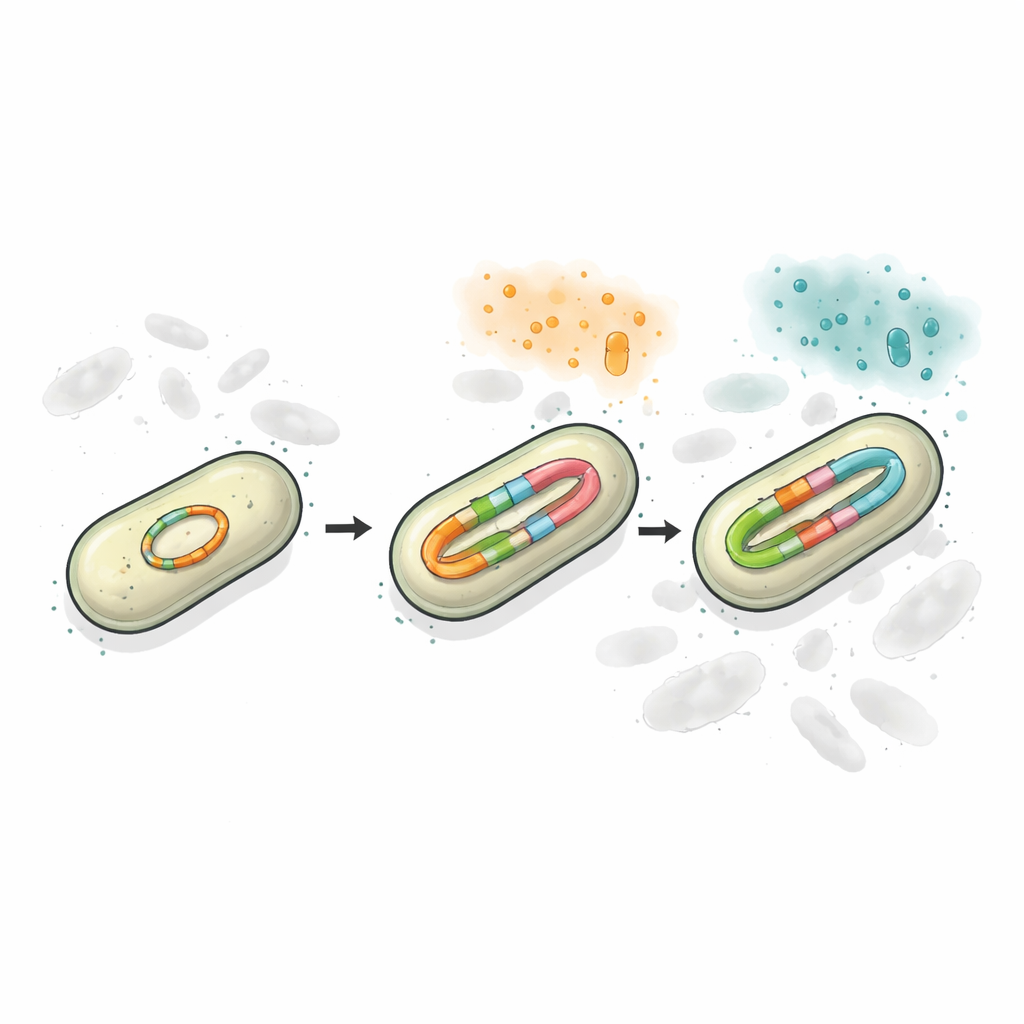
Vielfalt auf einem DNA-Kreis bewahren
Um zu testen, wie diese Anordnung das Überleben beeinflusst, erstellte das Team vereinfachte Labor‑Modelle, in denen Bakterien entweder eine Resistenzversion, zwei Versionen auf separaten Plasmiden oder beide Versionen zusammen auf einem einzigen Plasmid trugen. Unter Belastung mit zwei verschiedenen Cephalosporin‑Medikamenten schnitten die gemischten Systeme besser ab als Ein-Gen-Stämme, weil mindestens eine Enzymversion mit jedem der Medikamente zurechtkam. Am stabilsten erwies sich jedoch die Konfiguration, in der beide Genvarianten auf demselben Plasmid saßen. Wurden Antibiotika über mehrere Tage angewendet oder von einem Wirkstoff auf einen anderen umgestellt, verloren Zellen mit zwei separaten Plasmiden oft eines davon und opferten damit einen Teil ihres Schutzes. Im Gegensatz dazu wurde das „Zwei‑in‑Eins“-Plasmid als Paket vererbt und bewahrte beide Resistenzoptionen, selbst wenn es kurzfristig ein Wachstumskost verursachte.
Ein größeres Muster bei gefährlichen Bakterien
Mathematische Modelle rekonstruierten diese Experimente und zeigten, dass oberhalb bestimmter Antibiotikaspiegel Bakterien mit einem einzelnen Plasmid, das mehrere Resistenzvarianten trägt, letztlich gemischte Populationen dominieren. Die Forschenden durchsuchten dann Tausende von K. pneumoniae‑Genomen aus Krankenhäusern, landwirtschaftlichen Betrieben, Lebensmitteln und der Umwelt. Häufig fanden sie mehrere, leicht unterschiedliche Kopien von Schlüsselresistenzgenen — besonders in menschlichen klinischen Isolaten, die starkem Arzneimitteldruck ausgesetzt sind. Das deutet darauf hin, dass das Aufbauen von „multikopierter Heterogenität“ in Plasmiden keine seltene Ausnahme ist, sondern eine verbreitete Taktik, mit der Bakterien ihr Risiko gegen wechselnde Behandlungen streuen.
Was das für Patientinnen, Patienten und Therapien bedeutet
Für Nichtfachleute ist die Kernbotschaft, dass manche Bakterien nicht einfach nur ein einzelnes Resistenzgen tragen; sie tragen Familien verwandter Versionen, gebündelt auf demselben mobilen DNA‑Element, und verfügen so über ein flexibles Werkzeugarsenal gegen verschiedene Medikamente. Diese Anordnung erlaubt es ihnen, Resistenz über lange Zeiträume aufrechtzuerhalten, selbst wenn Ärztinnen und Ärzte die Therapien wechseln, und hilft zu erklären, warum bestimmte Infektionen so schwer zu beseitigen sind. Gleichzeitig zeigt die Studie, dass sorgfältig gewählte Wirkstoffkombinationen — etwa die Kombination von Ceftazidim/Avibactam mit Cefotaxim — Schwachstellen in diesem System ausnutzen und sogar diese gut bewaffneten Stämme unterdrücken können. Das Verständnis dafür, wie Bakterien solche multikopierten Plasmide konstruieren und nutzen, ist daher entscheidend für die Entwicklung klügerer Antibiotika‑Strategien und die Verlangsamung des Vormarschs der Resistenzen.
Zitation: Weng, R., Zhu, J., Wu, X. et al. Heterogeneous multicopy of blaCTX-M variants on the same plasmid enhances evolutionary adaptability in clinical Klebsiella pneumoniae. Nat Commun 17, 2460 (2026). https://doi.org/10.1038/s41467-026-69266-7
Schlüsselwörter: antibiotikaresistenz, Klebsiella pneumoniae, Plasmide, Beta-Laktamasen, Mehrfachtherapie