Clear Sky Science · de
TANGO: Analyse und Kuratierung von Partikeln in der Kryo-Elektronentomographie
Zellen in 3D sehen und dann die Menschenmenge verstehen
Kryo-Elektronentomographie ermöglicht es Forschern, lebende Zellen in Aktion einzufrieren und sie in drei Dimensionen einzufangen, fast so, als würde man einen Film auf atomarer Ebene anhalten. Sobald jedoch Tausende winziger molekularer „Pünktchen“ innerhalb einer Zelle kartiert sind, taucht ein neues Problem auf: Wie verstehen wir, wer neben wem sitzt, wer Teams bildet und wo sich wichtige Muster in dieser überfüllten molekularen Stadt verbergen? Diese Studie stellt TANGO vor, ein Software-Framework, das rohe 3D-Partikelkarten in lesbare Geschichten darüber verwandelt, wie Moleküle angeordnet sind und zusammenarbeiten.
Von Punkten im Eis zur Karte molekularer Nachbarn
Die Kryo-Elektronentomographie beginnt damit, die gefrorene Probe im Mikroskop zu kippen, um viele 2D-Bilder aufzunehmen. Diese werden zu einem 3D-Volumen kombiniert, dem Tomogramm, in dem einzelne molekulare Komplexe als verschwommene Flecken erscheinen. Bestehende Methoden nutzen diese Daten bereits, um die Formen von Molekülen durch Mittelung vieler Exemplare zu schärfen, ignorieren dabei aber weitgehend einen ebenso wertvollen Schatz: die exakten Positionen und Orientierungen jedes Partikels. TANGO ist darauf ausgelegt, diese bislang vernachlässigten Informationen auszubeuten. Es behandelt alle Partikel als Punkte im Raum, jeweils mit einer Richtung, und analysiert, wie sie relativ zueinander positioniert und orientiert sind. Damit geht es über die einfache Frage „Wie sieht dieses Molekül aus?“ hinaus und fragt: „Wie sind diese Moleküle gemeinsam in der Zelle organisiert?“ 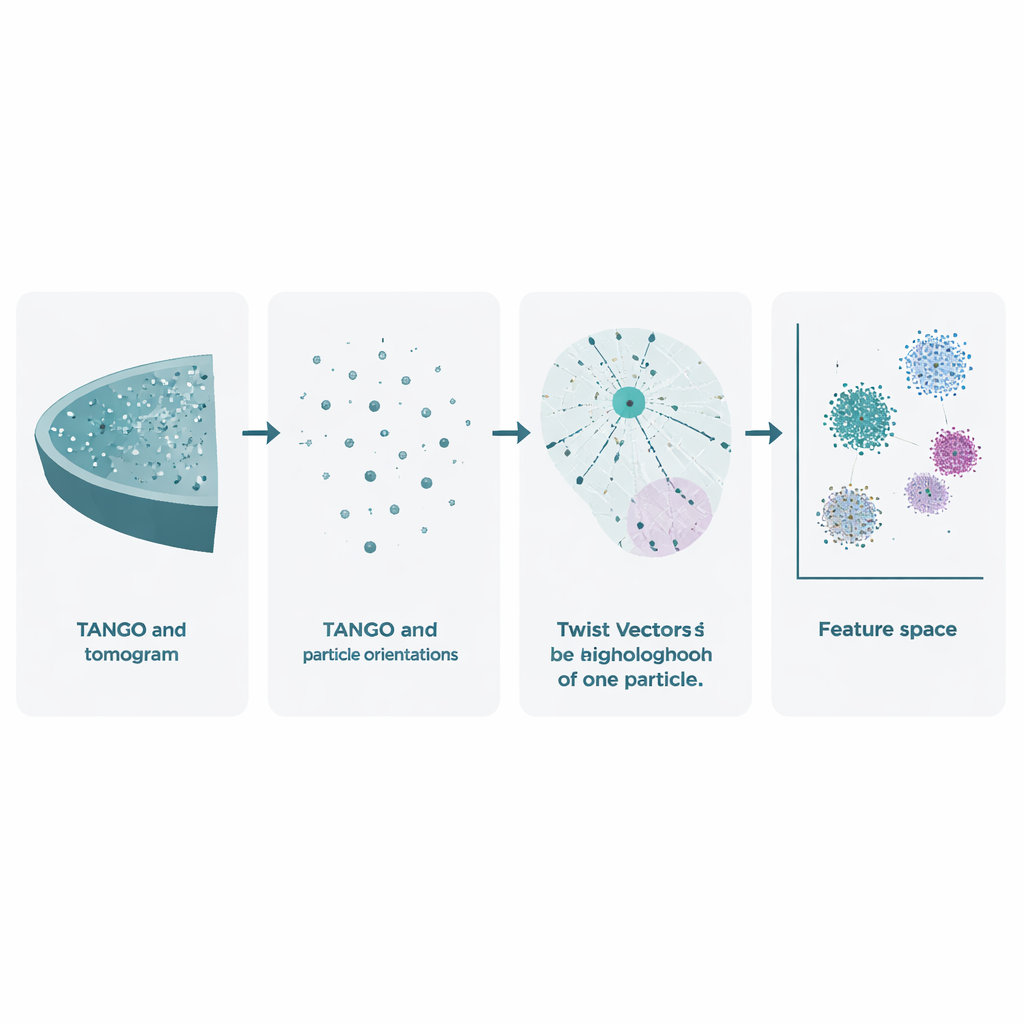
Drehungen und Wendungen mit einem neuen Deskriptor erfassen
Im Kern von TANGO steht die Idee der „Twist-Vektoren“. Für ein gegebenes Partikel betrachtet die Software alle Nachbarn innerhalb eines gewählten Radius und erfasst zwei Dinge: wo sich jeder Nachbar im 3D-Raum befindet und wie er relativ zum zentralen Partikel rotiert ist. Diese kombinierten Positions- und Winkelbeziehungen werden als prägnante numerische Beschreibungen kodiert, die als Twist-Deskriptoren bekannt sind. Weil TANGO Nachbarschaften immer in einen gemeinsamen Referenzrahmen überführt, sind diese Deskriptoren unempfindlich gegenüber der Rotation der gesamten Probe im Mikroskop. Das macht es möglich, lokale Nachbarschaften konsistent über verschiedene Tomogramme und Experimente hinweg zu vergleichen.
Rauschige Daten säubern und molekulare Assemblagen wieder aufbauen
Echte experimentelle Daten sind unordentlich: automatische Picking-Methoden können viele falsche Partikel einschließen und verlieren, welche kleinen Teile zu welchen größeren Strukturen gehören. TANGO geht dieses Problem an, indem es das Netzwerk von Twist-Beziehungen in einen Graphen überführt, bei dem Partikel Knoten und Nachbarschaftsverbindungen Kanten sind. Durch Analyse, wie Knoten verbunden sind, kann TANGO Partikel wieder ihren korrekten übergeordneten Assemblagen zuordnen und Ausreißer verwerfen, die nicht zur erwarteten Geometrie passen. Die Autoren zeigen, dass dieser Ansatz die ringförmige Architektur der Kernporen in der Kernhülle, die röhrenförmige Anordnung von Mikrotubuli und die annähernd kugelförmigen Hüllen unreifer HIV-Virus-ähnlicher Partikel genau rekonstruieren kann. In jedem Fall säubert TANGO sowohl die Partikellisten als stellt wieder her, welche Teile zusammengehören, und erreicht dabei oft Ergebnisse, die mit sorgfältiger manueller Kuratierung übereinstimmen oder diese verbessern.
Feine Defekte und Muster in Gittern erkennen
Viele Viren und zelluläre Strukturen bilden sich wiederholende Gitter, ähnlich molekularen Fliesen auf gekrümmten Flächen. TANGO nutzt seine Twist-Deskriptoren, um zu messen, wie regelmäßig diese Muster sind, und um Stellen zu erkennen, an denen sie sich biegen oder brechen. Ein zentraler Bestandteil ist ein „Winkelscore“, der Orientierungen vergleicht und eingebaute Symmetrien respektiert, wie etwa die sechsfache Symmetrie von Hexameren. Auf reife HIV-Kapside angewendet, detektiert TANGO Pentamere — fünfteilige Einheiten, die notwendig sind, um die konische Hülle zu schließen — versteckt in großen Feldern von Hexameren. In unreifen HIV-Gittern trennt es gut geordnete Regionen von verzerrten und verknüpft niedrige Winkelscores mit unregelmäßigen, gebrochenen Bereichen der Hülle. Ähnliche Analysen an synthetischem Chromatin- und Ribosom-Datenmaterial zeigen gestapelte Nukleosomen, helikale DNA–Protein-Anordnungen und wiederkehrende Ribosomenpaare, die zuvor beschriebene Translationszustände ähneln. 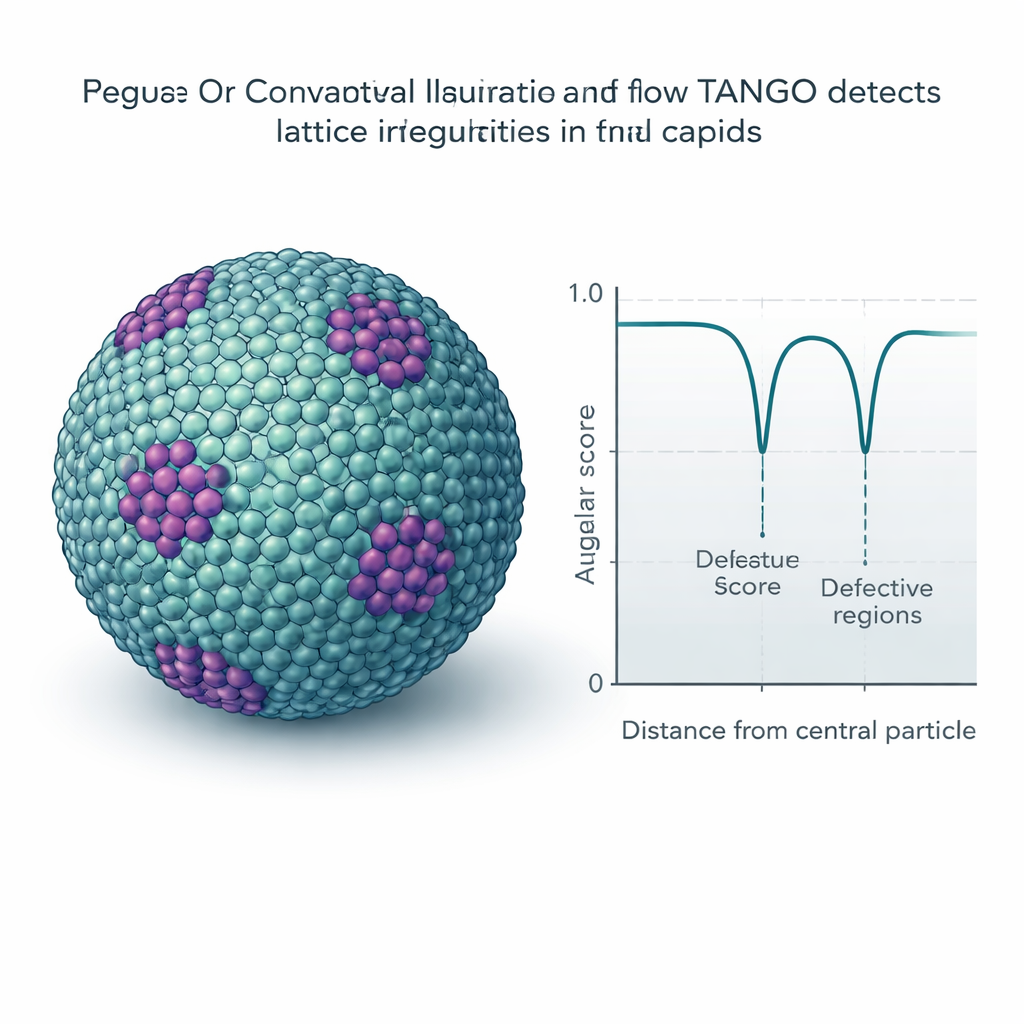
Ein flexibles Werkzeugkasten zur Erkundung zellulärer Architektur
TANGO ist als Open-Source-Python-Software implementiert und enthält eine grafische Oberfläche, sodass Anwender verschiedene Nachbarschaftsformen, Filter und Merkmale ohne große Programmierkenntnisse testen können. Da es modular aufgebaut ist, können Forschende eigene geometrische Maße oder Musterdeskriptoren einstecken und sofort im selben Arbeitsablauf verwenden. Für Einsteiger senkt das die Hürde, räumliche Organisation zu erkunden; für Expertinnen und Experten bietet es ein Framework, das mit neuen Ideen und Datensätzen mitwachsen kann.
Warum das für das Verständnis lebender Zellen wichtig ist
Einfach gesagt bietet diese Arbeit Biologen eine Möglichkeit, von statischen Bildern einzelner Moleküle zu dynamischen Karten darüber zu gelangen, wie diese Moleküle angeordnet sind und innerhalb der Zellen zusammenwirken. Indem die Beziehungen „wer ist neben wem“ und „wie sind sie orientiert“ in robuste numerische Merkmale kodiert werden, verwandelt TANGO rauschende 3D-Mikroskopiedaten in Muster, die geclustert, verglichen und statistisch getestet werden können. Das kann versteckte Assemblagen offenlegen, Defekte in viralen Hüllen lokalisieren und seltene molekulare Anordnungen aufdecken, die mit Krankheit oder Arzneimittelwirkung verknüpft sind. Während die Kryo-Elektronentomographie weiter verbreitet wird, werden Werkzeuge wie TANGO dichte Partikelwolken in klare Einsichten über die innere Choreographie des Lebens verwandeln.
Zitation: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
Schlüsselwörter: Kryo-Elektronentomographie, räumliche Organisation, molekulare Gitter, virale Kapside, Ribosomen