Clear Sky Science · de
PRICE: direkte und robuste Erkennung von microRNAs mit Einzelnukleotid‑Auflösung
Warum winzige genetische Botschaften wichtig sind
In jeder Zelle gibt es ein Schwarm winziger RNA‑Moleküle, sogenannte microRNAs, die helfen, fein zu steuern, welche Gene ein- oder ausgeschaltet werden. Eine Änderung von nur einem „Buchstaben“ in diesen kurzen Molekülen kann das Gleichgewicht in Richtung Gesundheit oder Krankheit verschieben, einschließlich Krebs. Ärztinnen, Ärzte und Forschende würden diese winzigen Unterschiede gern direkt aus Blut oder Gewebe ablesen, doch die heute üblichen Methoden sind oft langsam, teuer und nicht genau genug, um zuverlässig eine einzelne Buchstabenänderung zu erkennen. Diese Arbeit stellt eine neue Labormethode vor, PRICE genannt, die verspricht, diese mikroskopischen Tippfehler in microRNAs einfacher und genauer zu lesen und damit früheren Krebsnachweis und bessere Verfolgung des Tumorverhaltens zu ermöglichen.
Eine neue Möglichkeit, ähnlich aussehende Moleküle zu unterscheiden
MicroRNAs sind extrem kurz, was es schwierig macht, sie auseinanderzuhalten, wenn ihre Sequenzen sich nur um einen Baustein unterscheiden. Viele der derzeitigen Werkzeuge, etwa PCR und RNA‑Sequenzierung, zählen microRNAs insgesamt gut, haben aber Probleme, wenn zwei Varianten fast identisch sind, oder sie erfordern aufwändige Probenvorbereitung und teure Geräte. Die Autorinnen und Autoren kombinieren zwei leistungsfähige Ideen, um das zu überwinden: eine programmierbare molekulare „Schere“ aus der CRISPR‑Familie und synthetische, DNA‑ähnliche Stücke namens Peptidnukleinsäuren (PNAs). Das CRISPR‑Enzym Cas13a kann so programmiert werden, dass es eine bestimmte RNA erkennt, und sobald es sein Ziel gefunden hat, beginnt es in der Nähe befindliche Reporter‑Moleküle zu zerschneiden, wodurch ein starkes fluoreszierendes Signal entsteht. PNAs wiederum sind kurze Stränge, die besonders fest an passende RNA‑Sequenzen binden, aber ihre Bindung scharf verlieren, wenn auch nur ein Buchstabe falsch ist.
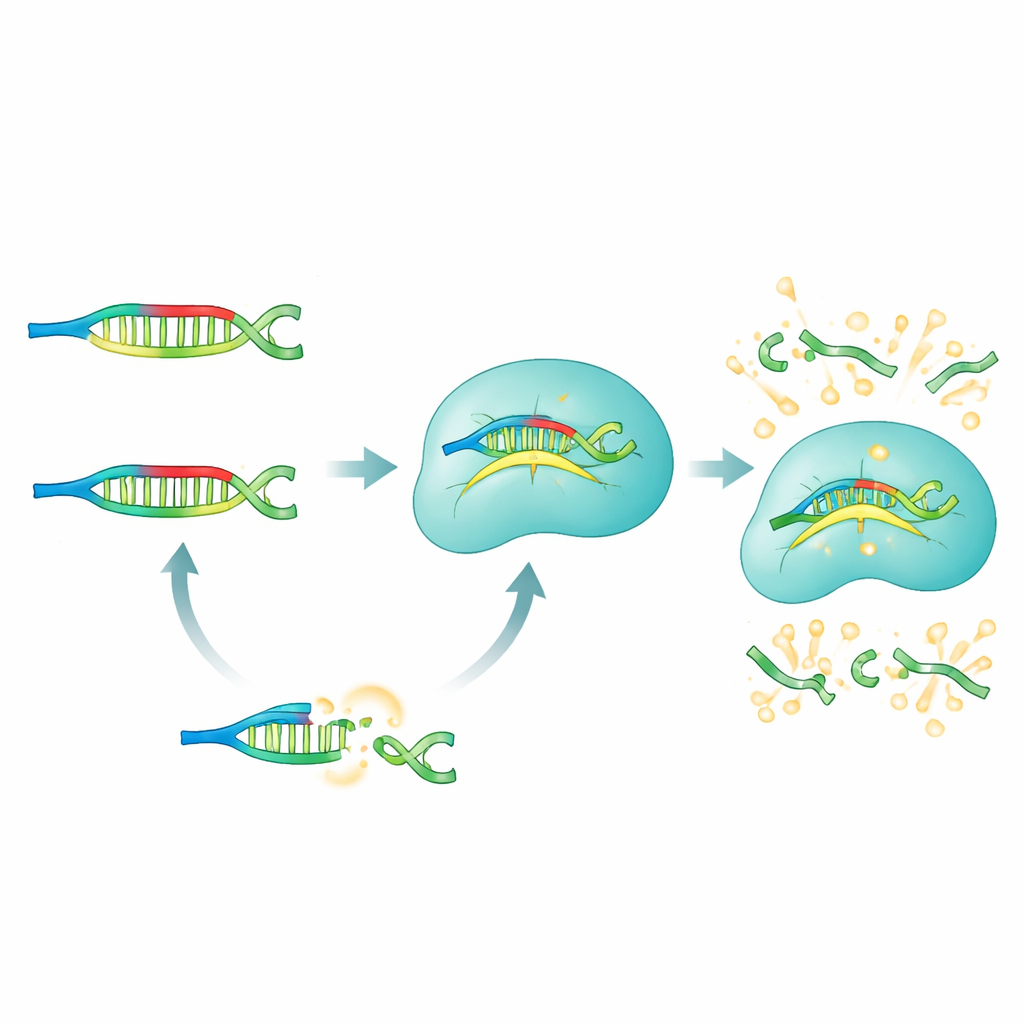
Wie die PRICE‑Methode funktioniert
Im PRICE‑System fungieren PNAs als selektive Blocker, die alles stummschalten, was Forschende nicht sehen wollen. Für eine gegebene microRNA des Interesses entwirft das Team ein Panel von PNA‑Blockern, die perfekt zu allen „falschen“ Versionen passen—also denen mit unerwünschten Einzelbuchstabenänderungen—während sie absichtlich nicht exakt zum ausgewählten Ziel passen. Wird eine biologische Probe (aus Serum, Zellen oder Gewebe) mit diesen PNAs gemischt, binden die nicht‑zielgerichteten microRNAs fest und werden effektiv maskiert. Die wahre Ziel‑microRNA bleibt ungebunden und kann mit dem Cas13a‑Komplex interagieren, der zuvor mit einer Guide‑RNA programmiert wurde, die diese microRNA erkennt. Nur dieses unmaskierte Ziel kann Cas13a in den aktiven Schneidemodus versetzen, wodurch fluoreszierende Reporter‑Moleküle gespalten werden und ein starkes, leicht messbares Leuchten entsteht.
Feinabstimmung auf Einzelbuchstabenpräzision
Die Autorinnen und Autoren untersuchten systematisch, wie PNA‑Blocker so entworfen werden können, dass sie stark genug sind, die falsche microRNA zu fassen, aber gleichzeitig schwach genug, das gewünschte Molekül zu ignorieren, das sich nur um einen Buchstaben unterscheidet. Sie stellten fest, dass zwei temperaturähnliche Gestaltungsregeln entscheidend sind: Das PNA sollte mit dem unerwünschten Mutanten bei oder über Körpertemperatur ein stabiles Paar bilden, aber mit dem Ziel eine deutlich schwächere Bindung eingehen, die schon deutlich unter dieser Temperatur auseinanderfällt. Mit diesen Regeln, gestützt durch ein einfaches Vorhersagemodell, bauten sie PNAs, die falsche Signale von mutanten microRNAs um mehr als 70 Prozent reduzierten, während das wahre Signal nahezu ungestört blieb. Wichtig ist, dass die zusätzlich eingesetzten PNAs die Gesamtsensitivität nicht beeinträchtigten: PRICE konnte weiterhin microRNAs in Konzentrationen von nur wenigen Dutzend Femtomolar nachweisen, vergleichbar mit den besten amplifikationsbasierten Tests, jedoch ohne die zusätzlichen Kopierschritte.
Praktische Anwendung in Krebsproben
Um zu zeigen, dass PRICE mehr als ein theoretisches Gerät ist, konzentrierte sich das Team auf die let‑7‑Familie der microRNAs, die stark in der Krebsbiologie involviert ist. Sie demonstrierten, dass PRICE Ziel‑microRNAs aus Gemischen mit vielen nahezu identischen Familienmitgliedern herausfiltern kann und sogar seltene Varianten nachweist, die nur 5 Prozent einer Probe ausmachen. Die Forschenden wandten die Methode dann auf klinisches Material an: Leberkrebs‑Zelllinien, Gewebebiopsien und Patientenserum. Sowohl im Tumorgewebe als auch im Blut erkannte PRICE konsistent geringere Mengen spezifischer let‑7‑microRNAs bei Patientinnen und Patienten im Vergleich zu Nicht‑Krebs‑Kontrollen, in Übereinstimmung mit früheren Studien. Im direkten Vergleich mit dem Standard RT‑qPCR zeigte PRICE mindestens eine ähnliche und oft bessere Fähigkeit, Krebsfälle von Nicht‑Krebs‑Fällen zu unterscheiden, besonders in Serumproben mit geringer Häufigkeit, in denen PCR‑Ergebnisse unruhig wurden.
Warum das für zukünftige Diagnostik wichtig ist
Kern dieser Arbeit ist der Nachweis, dass es möglich ist, Einzelbuchstabenunterschiede in winzigen regulatorischen RNAs direkt, praktisch und skalierbar zu lesen. Indem PNAs unerwünschte, ähnlich aussehende Sequenzen fixieren und die abschließende Ablesung einem CRISPR‑Enzym überlassen, bietet PRICE einen flexiblen Werkzeugkasten für die Entwicklung von Tests, die sich einfach neu ausrichten lassen, indem man das Blocker‑Panel und die Guide‑RNA austauscht. Über Leberkrebs und die let‑7‑Familie hinaus ließe sich dieselbe Strategie auf viele andere Krankheiten ausdehnen, bei denen kleine RNA‑Veränderungen eine Rolle spielen, und sogar auf DNA‑Varianten, wenn sie mit verwandten CRISPR‑Enzymen kombiniert wird. Die Autorinnen und Autoren zeigen außerdem einen kompakten Mehrkanal‑Leser, der PRICE‑Assays außerhalb großer Zentrallabore betreiben kann, was auf zukünftige Tests am Point‑of‑Care hindeutet. Bei weiterer Entwicklung könnte PRICE zu einem praktikablen Weg werden, subtile genetische Verschiebungen zu überwachen, die Krebs und andere Krankheiten lange vor dem Auftreten von Symptomen ankündigen.
Zitation: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Schlüsselwörter: microRNA-Diagnostik, CRISPR Cas13a, Peptidnukleinsäure, Einzelnukleotid‑Variante, Biomarker für Leberkrebs