Clear Sky Science · de
dHyperCas12a ermöglicht multiplexe CRISPRi-Screens
Den Lautstärkeregler der Zelle programmieren
Unsere Zellen entscheiden ständig, welche Gene hochgeregelt, welche heruntergeregelt und welche stummgeschaltet werden sollen. Viele Krankheiten entstehen, wenn dieses empfindliche Gleichgewicht gestört ist, doch die meisten Werkzeuge zur Untersuchung der Genregulation können jeweils nur einen einzelnen Schalter betätigen. Diese Arbeit stellt eine leistungsfähige Methode vor, aufgebaut auf einem CRISPR-Protein namens dHyperCas12a, die es Forschenden ermöglicht, viele genetische Schalter gleichzeitig hoch- oder herunterzudrehen. Indem dies effizient und sicher gelingt, eröffnet sie Möglichkeiten, Kartierungen vorzunehmen, wie Netzwerke von DNA-Kontrollelementen zusammenwirken — in Gesundheit, Krankheit und bei zellulären Therapien. 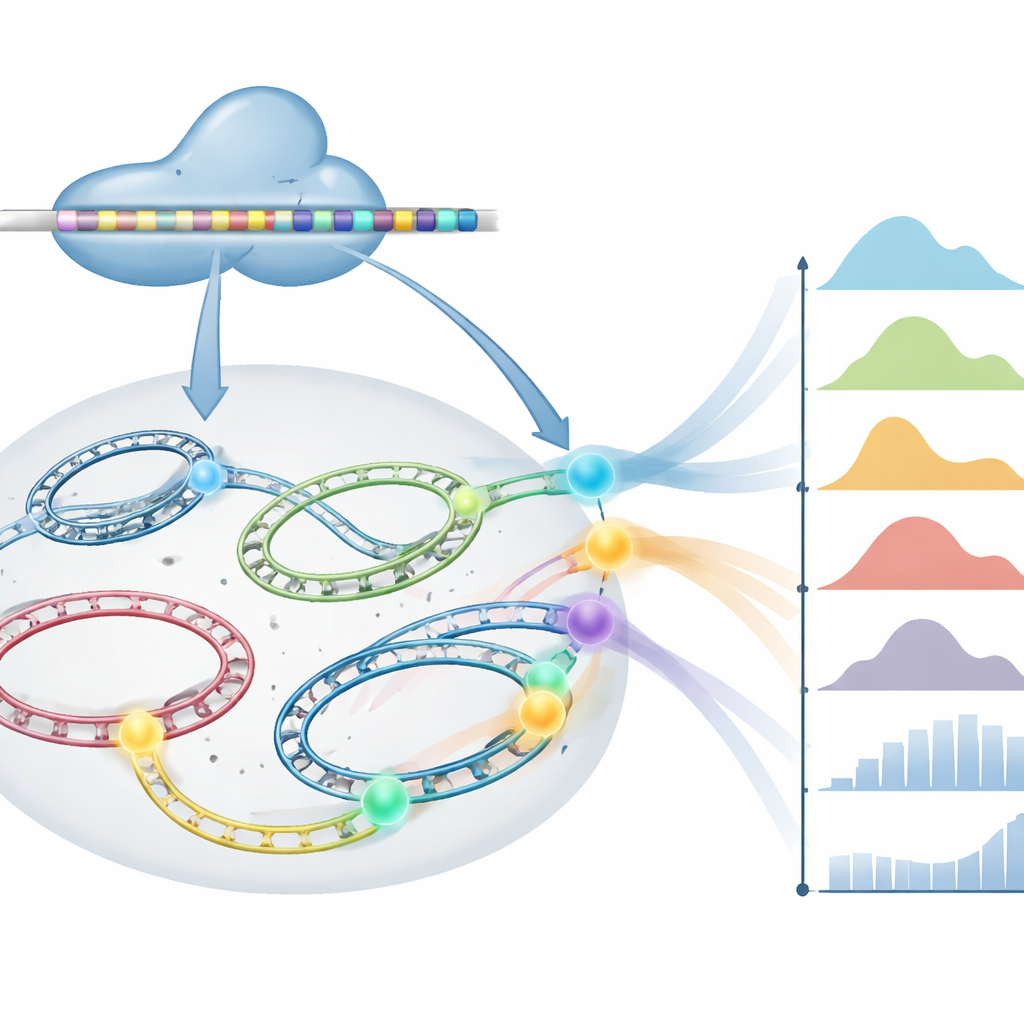
Viele Schalter, ein Bedienfeld
Die meisten Gene werden nicht von einem einzigen Ein-/Aus-Schalter gesteuert, sondern von mehreren kurzen DNA-Abschnitten, sogenannten regulatorischen Elementen. Diese wirken zusammen, um zu bestimmen, wann, wo und in welcher Stärke ein Gen genutzt wird. Traditionelle CRISPR-Werkzeuge können Gene an- oder ausschalten, aber das Studium von Kombinationen war schwierig, weil jedes Ziel normalerweise seine eigene Guide-RNA und sein eigenes Lieferkonstrukt benötigt. Das Handling von Dutzenden nahezu identischer Guides führt häufig zu Bruchstücken in den DNA-Konstrukten, auf die Forschende angewiesen sind, und macht umfassende Tests von Gen–Gen- oder Element–Element-Interaktionen unpraktisch.
Warum Cas12a besser multitaskt
Die Forscher wandten sich Cas12a zu, einem Verwandten des bekannten Cas9-Enzyms, weil Cas12a natürlicherweise eine lange „Guide-RNA-Array“ liest und dieses Array im Inneren der Zelle in viele einzelne Guides zerschneidet. Sie verglichen mehrere gentechnisch veränderte Cas12a-Varianten und fanden, dass eine Variante, dHyperLbCas12a genannt, besonders gut darin war, Zielgene hoch- oder herunterzuregulieren, selbst bei niedrigen Guide-Niveaus. Anschließend verbesserten sie die Herstellung der Guide-Arrays in menschlichen Zellen, indem sie von einem kurzen, schwer verlängerbaren RNA-Promotor zu einem stärkeren Promotor wechselten, der lange Transkripte treiben kann. Diese Änderung erlaubte ihnen, einzelne RNAs mit bis zu 14 Guides zu bauen, die alle von Cas12a in separate Zielanweisungen prozessiert werden.
Ein flexibles Dimmer-System für Gene aufbauen
Um die Genaktivität zu steuern, fusionierte das Team dHyperCas12a mit sogenannten Effektor-Domänen, die in der Nähe der DNA entweder aktivieren oder reprimieren. Sie erzeugten Versionen, die Gene stark abschalten (mithilfe einer KRAB-Domäne), Versionen, die sanfter reprimieren (mithilfe einer SID-Domäne), und Versionen, die Gene einschalten (mithilfe der Aktivatoren VPR oder P300). In mehreren humanen Zelltypen — darunter Leberzellen, Lungenkrebszellen, immunologische T‑Zellen und Stammzellen, die sich zu Neuronen entwickeln — zeigten sie, dass ein einzelnes dHyperCas12a-Protein zusammen mit einem Multi-Guide-Array viele Gene gleichzeitig hoch- oder herunterregulieren kann. Sie demonstrierten außerdem ein hybrides Array, das Guides für zwei kompatible Cas12a-Proteine mischt, sodass ein Protein einige Gene aktiviert, während das andere andere Gene in derselben Zelle reprimiert.
Das System auf die Probe stellen
Mit diesen Werkzeugen führten die Wissenschaftler umfangreiche Screens durch. In einem untersuchten sie, welche Gene für das Zellwachstum essentiell sind, indem sie Hunderte von Zielen gleichzeitig leicht reprimierten, wobei jedes als Teil von Vier-Guide-Arrays kodiert war. Das dHyperCas12a in Kombination mit einer KRAB-Domäne zeigte die stärkste und verlässlichste Abschwächung bekannter essentieller Gene, selbst bei niedriger Kopienzahl nach Lentivirus-Lieferung — wichtig für realistische Krankheitsmodelle. In einem anderen Screen analysierten sie, wie zwei benachbarte regulatorische Elemente das Gen PER1 steuern, einen Schlüsselspieler der täglichen Körperrhythmen, der auf Stresshormone reagiert. Durch Konstruktion von über 8.000 Sechs-Guide-Arrays, die entweder einen Enhancer, den anderen oder beide in Tausenden von Kombinationen trafen, zeigten sie, dass bei sehr niedrigen Hormonspiegeln ein Enhancer dominiert, während bei steigender Dosis beide beitragen. 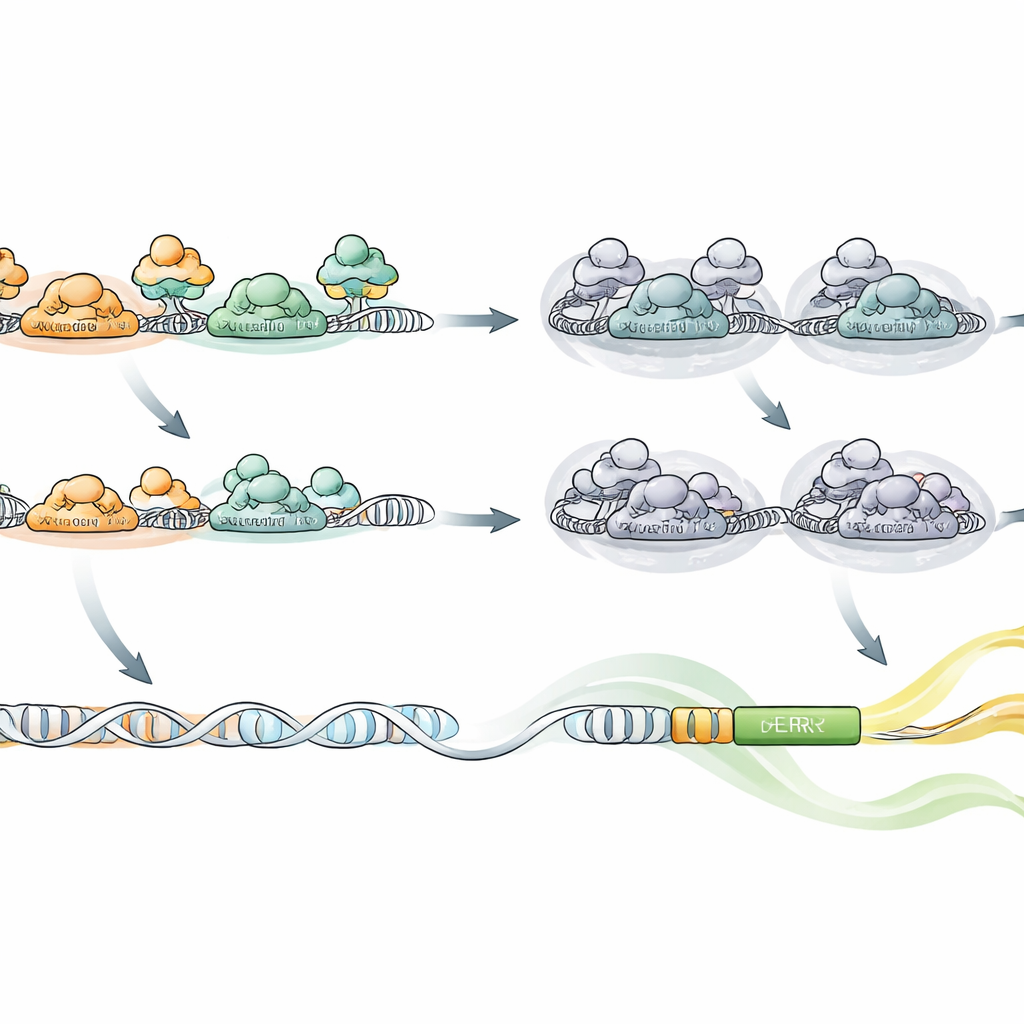
Was das für künftige Forschung bedeutet
Für Nicht-Spezialisten lässt sich der Fortschritt so beschreiben, als würde man vom Betätigen eines einzelnen Lichtschalters in einem Gebäude zu einer Steuerung ganzer Reihen von Dimmern von einem einzigen Smart-Panel aus wechseln. dHyperCas12a und seine Guide-Arrays ermöglichen Forschenden, viele genetische Kontrollpunkte gleichzeitig präzise abzuschwächen oder zu verstärken, in Kombinationen, die der realen Biologie näherkommen. Dadurch wird es möglich zu fragen, welche Gruppen von DNA-Elementen tatsächlich relevant sind für eine Arzneimittelantwort, einen Entwicklungsschritt oder ein Krankheitsmerkmal, ohne das Genom dauerhaft zu zerschneiden. Zwar sind weitere Arbeiten nötig, um Off-Target-Effekte zu kartieren und die Skalierung auf noch größere Kombinationen zu prüfen, doch diese Studie legt die Grundlage für leistungsfähige „Viele‑auf‑einmal“-CRISPR-Interferenz-Screens, die aufdecken können, wie komplexe Genkontrollsysteme wirklich funktionieren.
Zitation: Melore, S.M., McRoberts Amador, C.D., Hamilton, M.C. et al. dHyperCas12a enables multiplexed CRISPRi screens. Nat Commun 17, 2642 (2026). https://doi.org/10.1038/s41467-026-69090-z
Schlüsselwörter: CRISPRi, Cas12a, Genregulation, Enhancer, funktionelle Genomik