Clear Sky Science · de
FLASH-MM: schnelle und skalierbare Einzelzell-Differenzanalyse mit linearen gemischten Modellen
Warum winzige Zellen große Rechenhilfe brauchen
Die moderne Biologie kann inzwischen die Aktivität von Tausenden Genen in Hunderttausenden einzelner Zellen gleichzeitig ablesen. Diese Einzelzellperspektive verspricht schärfere Einsichten darin, wie unser Körper Infektionen bekämpft, wie sich Männer und Frauen unterscheiden oder wie Krankheiten entstehen. Doch aus diesen riesigen, unordentlichen Datensätzen verlässliche Entdeckungen zu gewinnen, ist mühsam langsam und kann bei naiver Vorgehensweise irreführend sein. Dieser Artikel stellt FLASH-MM vor, eine neue Methode zur Auswertung von Einzelzelldaten, die die Statistik korrekt hält und zugleich die Berechnungen so beschleunigt, dass sie für die größten aktuellen Studien praktisch einsetzbar sind.
Die Herausforderung lauter, dichter Zelldaten
Bei der Einzelzell-RNA-Sequenzierung wird gemessen, welche Gene in jeder Zelle „an“ oder „aus“ sind – über viele Personen und Bedingungen hinweg. Zellen derselben Person ähneln einander, weil sie Gene und Lebensgeschichte teilen, während sich Personen untereinander stark unterscheiden. Das erzeugt eine geschichtete Datenstruktur: viele Zellen pro Person und viele Personen pro Bedingung, etwa krank versus gesund. Werden diese Beziehungen ignoriert, können Standardmethoden fälschlich Tausende Gene als verändert ausweisen, weil sie jede Zelle als unabhängigen Datenpunkt behandeln. Gleichzeitig sind Einzelzelldatensätze auf hunderte von Probanden und bis zu Millionen Zellen angewachsen und überfordern konventionelle statistische Werkzeuge sowohl zeitlich als auch im Speicher.
Ein intelligenteres Modell für Personen und Zellen
Statistiker greifen in solchen Fällen oft auf lineare gemischte Modelle zurück, die systematische Unterschiede zwischen Bedingungen (beispielsweise Tuberkulose-Status oder Geschlecht) explizit von zufälligen Unterschieden zwischen Individuen trennen. Prinzipiell sind diese Modelle ideal für Einzelzellstudien, weil sie sowohl Ähnlichkeiten zwischen Zellen derselben Person als auch Variation zwischen Personen berücksichtigen können. In der Praxis jedoch bremsen weit verbreitete Softwarepakete für diese Modelle bei großen Einzelzellexperimenten stark aus oder laufen aus dem Speicher. Forscher greifen deshalb häufig zu Abkürzungen, etwa dem Mittelwertbilden der Zählungen über alle Zellen eines Typs pro Person, wodurch viele fein abgestuften Zell-zu-Zell-Informationen verloren gehen, die Einzelzelldaten so wertvoll machen.
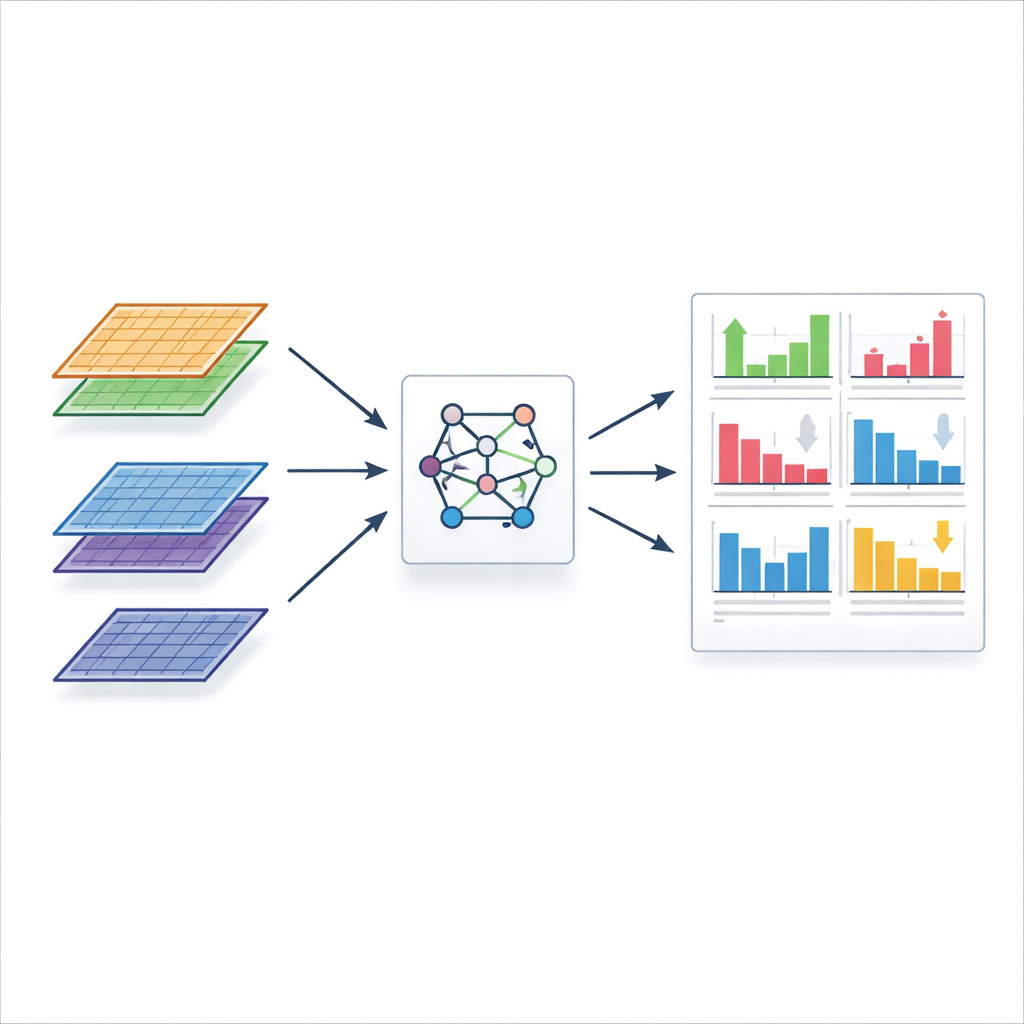
Wie FLASH-MM die schwere Rechnung beschleunigt
FLASH-MM bewahrt die Vorteile gemischter Modelle und überarbeitet zugleich die Rechenweise. Anstatt wiederholt riesige Tabellen mit Zelle-mal-Gen-Messungen zu durchlaufen, verdichtet FLASH-MM zunächst jeden Datensatz zu einer kompakten Menge von Zusammenfassungszahlen, die abbilden, wie Zellen zu bekannten Merkmalen wie Bibliotheksgröße, Zelltyp, Behandlung oder Spender in Beziehung stehen. Der Kernalgorithmus arbeitet dann nur noch mit diesen kleineren Matrizen und reduziert die Rechenlast von einer Skalierung mit jeder einzelnen Zelle auf eine Skalierung mit der deutlich kleineren Zahl von Modellkomponenten. Die Autorinnen und Autoren passen außerdem die Darstellung der Modellvarianz so an, dass Standardstatistiken gültig bleiben, sodass einfache t- und z-Statistiken sowohl Haupteffekte als auch den zusätzlichen Wert der Berücksichtigung personenbezogener Variation beurteilen können. Simulationen mit realistischen synthetischen Daten zeigen, dass FLASH-MM Ergebnisse liefert, die mit denen von Referenzsoftware bis auf mehrere Dezimalstellen übereinstimmen, dabei aber etwa 50- bis 140-mal schneller laufen und deutlich weniger Speicher benötigen.
Praktischer Einsatz an echten Geweben
Um die Relevanz zu demonstrieren, wendete das Team FLASH-MM auf zwei anspruchsvolle Einzelzelldatensätze an. In einer Karte von über 27.000 gesunden menschlichen Nierenzellen aus 19 Spendern suchte FLASH-MM innerhalb jedes Zelltyps nach Unterschieden in der Genaktivität zwischen männlichen und weiblichen Spendern und behandelte jede Person als zufälligen Faktor, um übermütige Befunde zu vermeiden. Die stärksten geschlechtsgebundenen Muster fand die Methode in einem spezifischen Nierentubulus-Zelltyp: männliche Zellen zeigten gehäuft Signalwege im Zusammenhang mit Säuretransport und Blutdruck, weibliche Zellen waren für Signalübertragung und Rezeptor-Recycling angereichert. FLASH-MM beendete diese Analyse in etwa einer Minute, verglichen mit fast zwei Stunden für ein Standardwerkzeug. Die Methode analysierte außerdem rund eine halbe Million Gedächtnis-T-Zellen von 259 Personen aus einer Tuberkulose-Kohorte und identifizierte Gen- und Signalwegsets, die mit dem Krankheitsstatus in verschiedenen aktivierten T-Zell-Zuständen verknüpft sind. Hier benötigte FLASH-MM weniger als anderthalb Stunden, gegenüber mehr als zwei Tagen beim herkömmlichen Ansatz.
Was das für künftige Einzelzellstudien bedeutet
Für Laien gesagt lautet die Botschaft: Wir können den Strom von Einzelzelldaten jetzt besser nutzen, ohne Abkürzungen zu machen. FLASH-MM berücksichtigt, welche Zellen von welcher Person und unter welcher Bedingung stammen, sodass erkannte Genänderungen eher echte biologische Signale als Stichproben- oder Batch-Effekte widerspiegeln. Zugleich ermöglichen die schlanken Berechnungen die Analyse von Hunderttausenden Zellen auf Standardrechnern und eröffnen so größere Studien zu subtilen Krankheitszeichen, Geschlechtsunterschieden und seltenen Zellzuständen. Da der Ansatz allgemein gehalten und sowohl in R als auch in Python verfügbar ist, lässt er sich auf neuere Technologien wie räumliche Genkartierung und mehrschichtige molekulare Messungen ausdehnen und hilft Forschenden, umfangreiche Einzelzelldatensätze in robuste, klinisch relevante Erkenntnisse zu verwandeln.
Zitation: Xu, C., Pouyabahar, D., Voisin, V. et al. FLASH-MM: fast and scalable single-cell differential expression analysis using linear mixed-effects models. Nat Commun 17, 2384 (2026). https://doi.org/10.1038/s41467-026-69063-2
Schlüsselwörter: Einzelzell-RNA-Sequenzierung, Differenzielle Expression, lineare gemischte Modelle, statistische Genomik, computationale Biologie