Clear Sky Science · de
AACRNL: Von Virulenzfaktor zum epigenetischen Parasiten, der die Genomexpansion bei freilebenden Eukaryoten antreibt
Wenn alte Toxine neue Tricks lernen
Unsere Genome sind keine stillen Bedienungsanleitungen. Sie sind belebte Arenen, in denen Gene, Viren und mobile DNA ständig um Raum und Kontrolle ringen. Diese Studie deckt einen überraschenden Mitspieler in diesem Kampf auf: ein Protein, das ursprünglich als von Mikroben eingesetztes Toxin diente, um Wirte anzugreifen, das aber in freilebenden Tieren als eine Art „epigenetischer Parasit“ umfunktioniert wurde und dazu beiträgt, seinen eigenen Fußabdruck im Genom zu vergrößern.
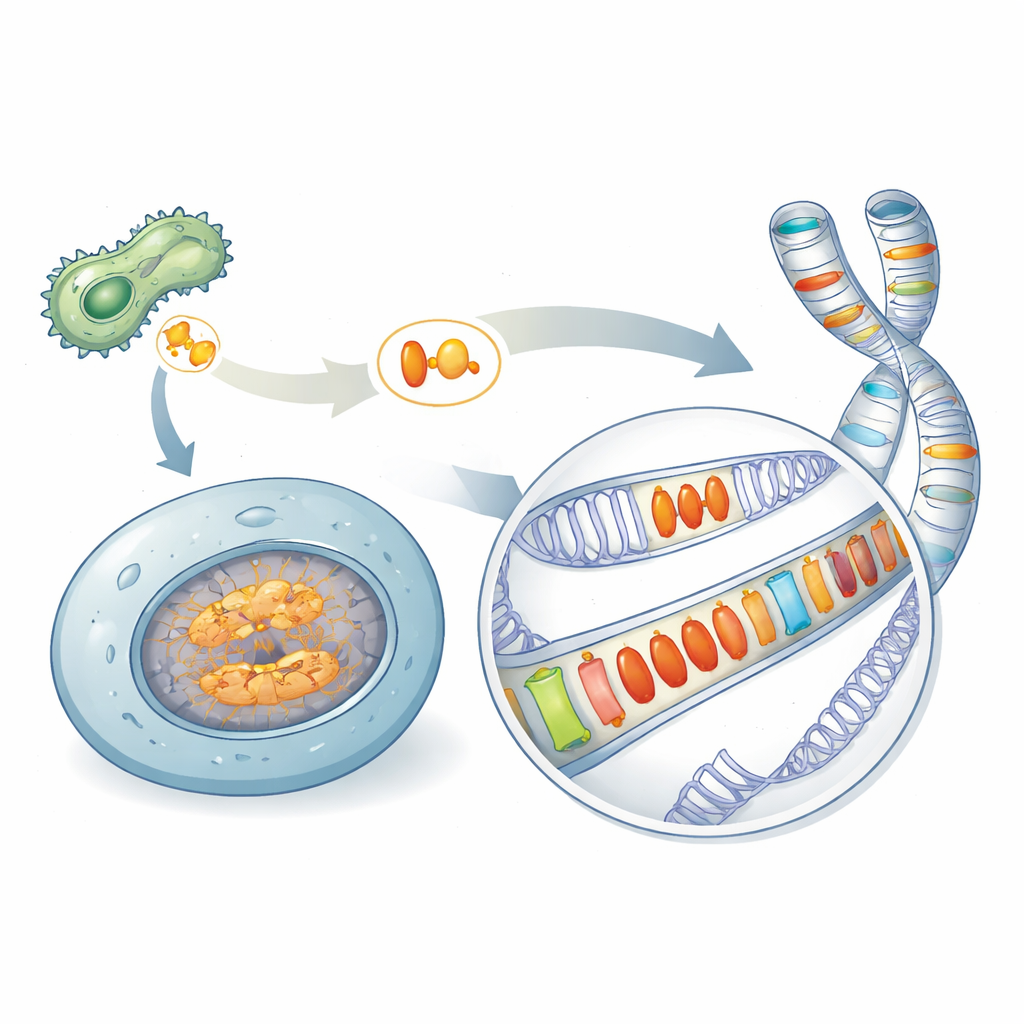
Ein verborgenes Erbe mikrobieller Waffen
Viele krankheitserregende Mikroben verwenden spezialisierte Proteine, sogenannte Effektorproteine, um die Abwehrmechanismen ihrer Wirte zu sabotieren. Eine bekannte Familie, die als Crinkler bekannt ist, galt bisher als auf Pathogene beschränkt. Durch das Durchsuchen einer breiten Vielfalt von Arten fanden die Autoren verwandte Proteine – hier unter dem Namen AACRNL zusammengefasst – an unerwarteten Orten, darunter Schwämme, Korallen, Seeigel und Knochenfische, die keine klassischen Erreger sind. Diese AACRNL‑Proteine behalten den toxinähnlichen Kern, der andere Proteine chemisch modifizieren kann, während ihr vorderer „Transport“‑Abschnitt, den Pathogene zur Invasion von Wirtszellen nutzen, weitgehend zerfallen ist. Diese strukturelle Veränderung deutet auf einen Wechsel hin: weg vom Angriff auf andere Organismen, hin zur Funktion innerhalb der Zellen des Wirts selbst.
Ein egoistischer Schalter im Genom
Bei Knochenfischen kommen AACRNL‑Gene in mehreren Kopien vor, verteilt auf verschiedene Chromosomen. Durch den Vergleich benachbarter DNA‑Abschnitte zeigten die Forschenden, dass einige AACRNL‑Linien aufgehört haben, sich selbst zu kopieren, während sich andere mithilfe benachbarter, springender DNA‑Segmente, sogenannter Transposons, vervielfältigt haben. Diese Transposons wirken wie genomische Shuttles: Wenn sie sich bewegen oder duplizieren, können sie AACRNL mit sich ziehen. Das Ergebnis ist ein Flickenteppich aus wiederholten AACRNL‑Kopien, eingebettet in Transposon‑Sequenzen — ein Kennzeichen eines Gens, das sich eher zu seinem eigenen Vorteil ausbreitet als zum Nutzen des Wirts.
Den stummen Knopf des Genoms außer Kraft setzen
Normalerweise halten Zellen solche mobilen DNA‑Elemente streng unter Kontrolle. Eine zentrale Schutzmaßnahme ist eine chemische Markierung auf den Proteinen, die die DNA verpacken, bekannt als H3K27me3, die gefährliche oder laute Regionen abgeschaltet hält. Die Autoren fanden heraus, dass eine aktive Version von AACRNL bei Fischen, genannt AACRNLβ, EZH2 chemisch modifizieren kann — das Enzym, das diese repressive Markierung anbringt. Wenn AACRNLβ EZH2 verändert, sinkt die Menge an H3K27me3 an seiner eigenen genetischen Position und an benachbarten Transposons, die lokale DNA öffnet sich, und sowohl AACRNLβ als auch seine Transposon‑Nachbarn werden stärker exprimiert. Effektiv drückt das Protein seinen eigenen „An“-Knopf und löst die Bremsen an den mobilen Elementen, die es zu neuen Stellen im Genom tragen können.
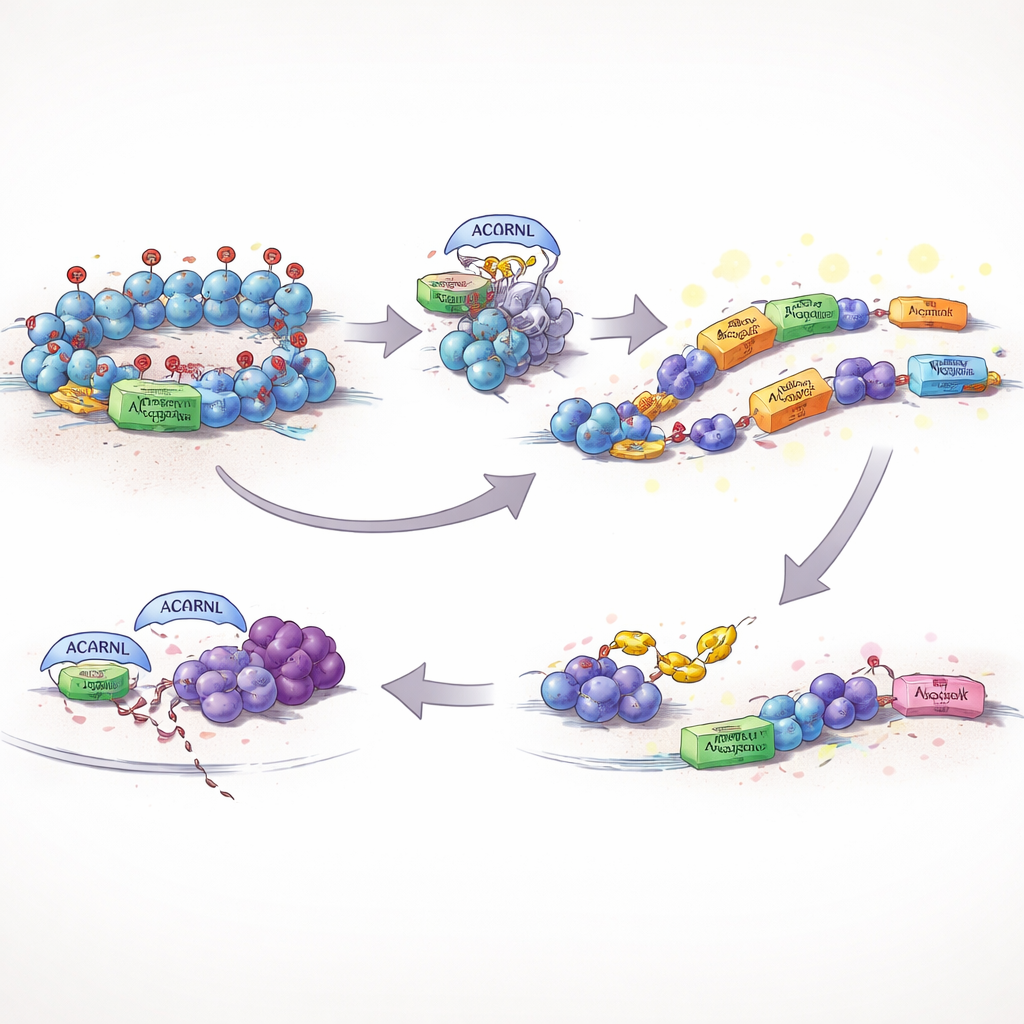
Den Immun‑Wächter ausweichen
Das Freisetzen von Transposons und ungewöhnlicher genetischer Aktivität läuft Gefahr, das Immunsystem aufmerksam zu machen. Die Studie zeigt, dass AACRNLβ auch dieses Problem angeht. Es heftet eine kleine chemische Markierung an TRAF6 an, ein zentrales Knotenprotein, das antivirale und entzündliche Signale einschaltet. Auf diese Weise markiert, wird TRAF6 weniger stabil und vermehrt für den Abbau durch die zellulären Entsorgungsmechanismen vorgesehen. Mit diesem geschwächten Signalzentrum schlagen wichtige Abwehrwege weniger intensiv an, wodurch ein toleranteres Umfeld entsteht, in dem AACRNLβ und seine assoziierten Transposons bestehen bleiben und sich mit geringeren Konsequenzen der Erkennung vervielfältigen können.
Ein empfindlicher Rüstungswettlauf innerhalb der Zelle
Die Geschichte endet nicht mit einem ungehinderten Lauf von AACRNLβ. Dasselbe TRAF6‑Protein, das von AACRNLβ angegriffen wird, kann seinerseits eigene Markierungen an AACRNLβ anbringen und das parasitenartige Protein zum Abbau kennzeichnen. Dieses Hin und Her gleicht einem molekularen Rüstungswettlauf: AACRNLβ nutzt toxinabgeleitete Chemie, um Chromatin und Immunität zu seinen Gunsten zu beeinflussen, während Wirtsproteine gegensteuern, indem sie es abbauen und seine Aktivität sporadisch und riskant halten. Die Autoren argumentieren, dass dieses Tauziehen es einer einst mikrobiellen Waffe ermöglichte, als egoistischer Bewohner freilebender Genome zu überdauern, DNA‑Inhalt zu vergrößern und die Regeln genetischer Konflikte von innen heraus umzugestalten.
Warum das unsere Sicht auf Genome verändert
Für Nicht‑Spezialisten ist die Kernbotschaft: Genome sind nicht nur Blaupausen, die für das Überleben des Wirts optimiert sind. Sie beherbergen auch Opportunisten. Diese Arbeit zeigt, dass sogar klassische Toxine domestiziert werden können und als solche Elemente ihre ursprüngliche destruktive Chemie nutzen, um epigenetische Sperren und Immunalarme zu umgehen und sich im Laufe der Evolution durch das Genom zu verbreiten. Das Verständnis dieses verborgenen Konflikts hilft zu erklären, warum Genome so groß, komplex und dynamisch sind — und legt nahe, dass andere „pensionierte“ Toxine in vielen Arten, möglicherweise auch in unserer eigenen, leise die DNA umschreiben könnten.
Zitation: Xu, T., Geng, S., Lv, X. et al. AACRNL evolved from virulence factor to epigenetic parasite driving genome expansion in free-living eukaryotes. Nat Commun 17, 2130 (2026). https://doi.org/10.1038/s41467-026-69012-z
Schlüsselwörter: egoistische genetische Elemente, Genom‑Evolution, epigenetische Regulation, Transposons, angeborene Immunität