Clear Sky Science · de
Hochdurchsatz-Methoden mit Robotik und Computer Vision zur Entwicklung therapeutischer Phagen-Cocktails
Warum das für alltägliche Infektionen wichtig ist
Antibiotikaresistenz verwandelt einst routinemäßig behandelbare Infektionen, wie Harnwegsinfektionen (HWI), in hartnäckige und mitunter lebensbedrohliche Probleme. Diese Studie beschreibt, wie Forscher Roboter, Kameras und Datenanalyse nutzen, um virusbasierte Medikamente—sogenannte Phagen-Cocktails—zu entwickeln, die gezielt gegen antibiotikaresistente Bakterien vorgehen, die HWIs verursachen. Die Arbeit zeigt, wie ein industriell geprägtes, automatisiertes Labor große Mengen an Virus–Bakterium-Kombinationen durchforstet, um eine einheitliche, gebrauchsfertige Behandlung zu entwerfen, die für die Mehrzahl der Patienten wirkt.
Eine verbreitete Infektion als Testfall
HWIs gehören zu den häufigsten Gründen für Antibiotikaverschreibungen, besonders bei Frauen, von denen viele wiederholt Infektionen erleben. Der Hauptverursacher ist eine Form von E. coli, die zunehmend gegenüber Standardmedikamenten resistent geworden ist. Traditionelle Antibiotika wirken breit und können die nützlichen Mikroben im Körper stören, während sie zugleich den Druck zur Evolution von Resistenzen erhöhen. Phagen—Viren, die Bakterien infizieren—bieten eine gezieltere Alternative, doch greift jeder Phage in der Regel nur bestimmte Bakterienstämme an. Die Herausforderung besteht darin, die richtige Mischung von Phagen zu finden, die gemeinsam die tatsächliche Diversität der HWI-verursachenden E. coli abdeckt.
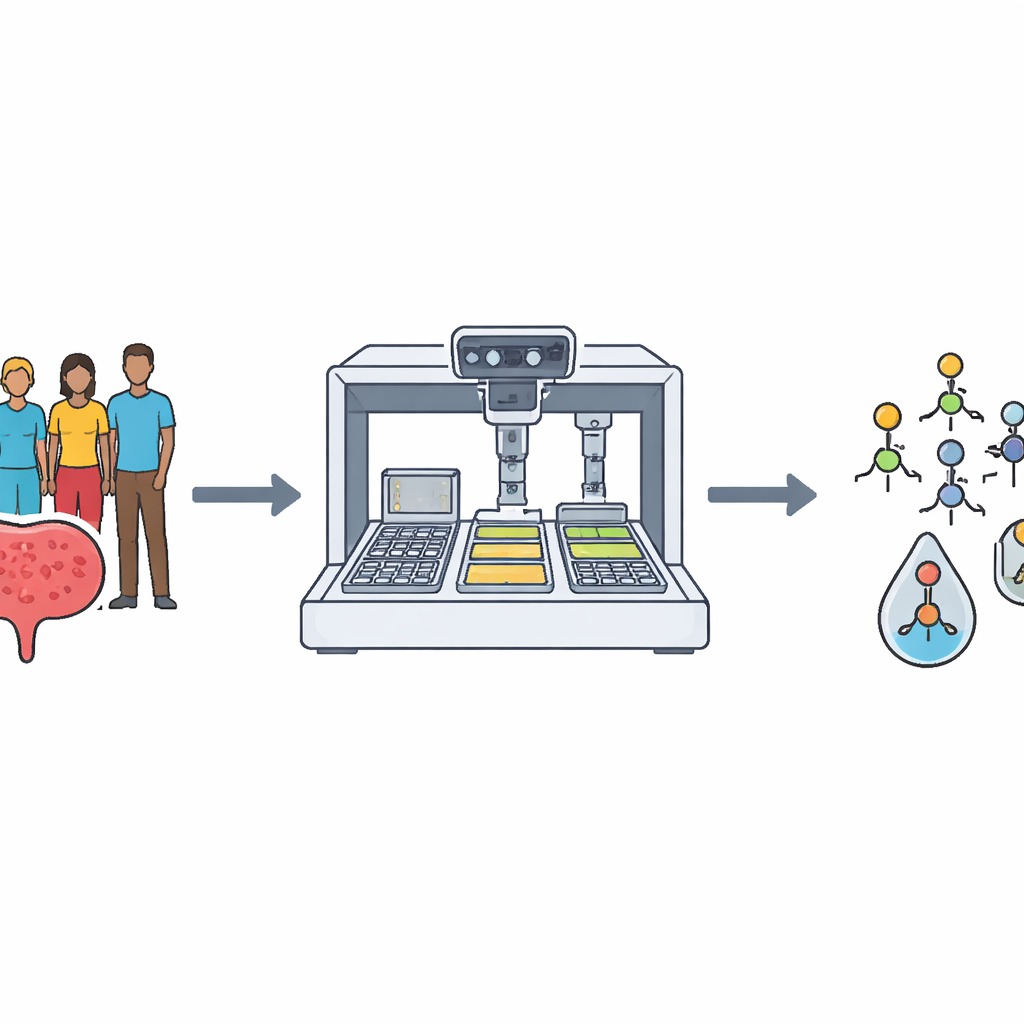
Aufbau einer realistischen Bibliothek problematischer Bakterien
Das Team stellte zunächst ein großes und vielfältiges Panel von HWI-verursachenden E. coli-Stämmen zusammen, das das klinische Geschehen widerspiegelt. Aus etwa 1.700 Isolaten, die von Patientinnen und kommerziellen Quellen stammten, und geleitet durch genetische Daten von rund 10.000 öffentlich verfügbaren E. coli-Genomen, wählten sie 356 Stämme für ein „Clinical Panel“ aus. Diese Stämme repräsentierten die wichtigsten genetischen Linien, stammten aus Patientinnen in 39 US-Bundesstaaten und umfassten viele mit Resistenz gegenüber mehreren Antibiotikaklassen. Jeder Stamm wurde sorgfältig kultiviert, portioniert, mit Barcodes versehen und in automatisierten Gefrierschränken gelagert, sodass Roboter sie wiederholt und zuverlässig für Tests entnehmen konnten.
Roboter und Kameras suchen die beste Viren-Mischung
Als Nächstes wandten sich die Forscher der anderen Seite der Gleichung zu: den Phagen. Sie sammelten über tausend Umweltproben, überwiegend aus Abwasser, und nutzten ihr Clinical Panel, um 1.143 E. coli-zielende Phagen zu isolieren, von denen 421 zu den zentralen Arbeitspferden wurden. Eine maßgeschneiderte Roboterplattform setzte Mehrkanalpipetten, Inkubatoren und Plattenleser ein, um Bakterien, Phagen und Nährmedium in winzigen Vertiefungen zu mischen und das bakterielle Wachstum über 20 Stunden zu verfolgen. Durch den Vergleich des Wachstums in phagenbehandelten Vertiefungen mit unbehandelten Kontrollen bestimmte das System, wie effektiv jeder Phage—oder Phagenkombinationen—das Bakterienwachstum unterdrückte. Im Verlauf entstanden so etwa 1,5 Millionen Wachstumskurven und mehr als 3,8 Millionen Phage–Bakterien-Reaktionsdatensätze, die in ein Cocktail-Vorhersagemodell einflossen, das neue, vielversprechende Kombinationen vorschlug.
Computer Vision zählt die Überlebenden
Optische Messungen liefern Hinweise auf die allgemeine Trübung, können aber schwer detektieren, wenn nur noch eine kleine Zahl von Bakterien übrig ist. Um tiefgehende Abtötung zu quantifizieren, ergänzte das Team ein zweites automatisiertes Assay. Roboter verdünnten Proben, punkteten sie auf Agarplatten und inkubierten diese, sodass einzelne bakterielle Überlebende sichtbare Kolonien bildeten. Hochauflösende Kameras fotografierten die Platten. Eine eigens entwickelte Bildanalyse-Pipeline nutzte drei verschiedene Algorithmen, um Kolonien und phageninduzierte Aufklarungen zu zählen, verglich die Ergebnisse und markierte Abweichungen zur menschlichen Nachprüfung. Über mehr als zwei Millionen Spots hinweg erreichte das automatisierte System die Genauigkeit ausgebildeter Analysten oder übertraf sie, während es auf deutlich größerer Skala arbeitete und verlässliche Zählungen lebender Bakterien und Phagenpartikel lieferte.
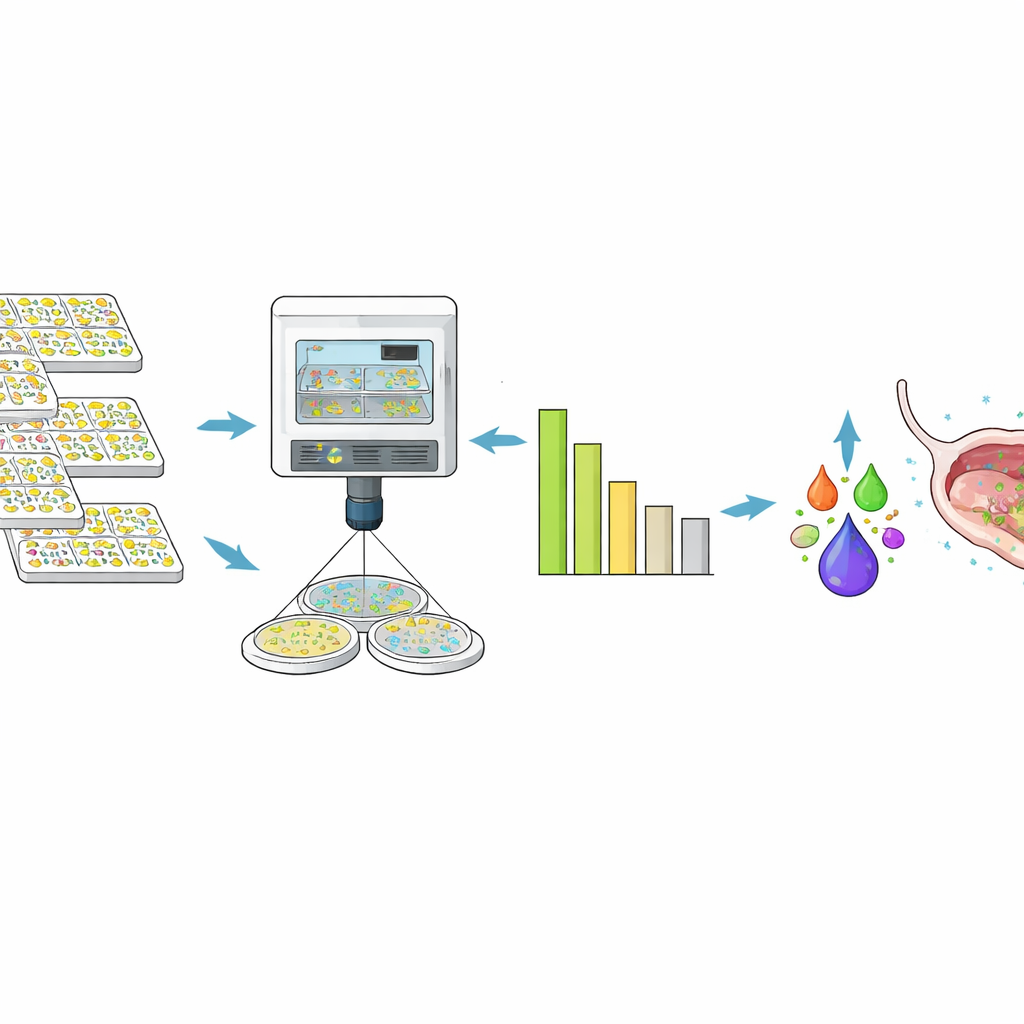
Von Millionen Tests zu einem starken Cocktail
Mithilfe dieser Hochdurchsatz-Assays und Vorhersagewerkzeuge reduzierten die Forscher Tausende von Möglichkeiten auf einen Sechs-Phagen-Cocktail, LBP-EC01. Unter pharmazeutischen Produktionsbedingungen hergestellt, zeigte dieser Cocktail im Labor Aktivität gegen 96,4 % der 356 Clinical-Panel-Stämme und verringerte die Bakterienzahlen in der Mehrheit der Fälle um mindestens den Faktor 100.000. Als das Team E. coli-Isolate aus dem ersten Teil einer laufenden Phase-2-Studie bei Frauen mit akuten HWIs testete, waren 97 % der einzigartigen Stämme empfindlich gegenüber dem Cocktail, und das Abtötungsmuster stimmte eng mit den Ergebnissen des vorab aufgebauten Panels überein. Wichtig: Während des beobachteten Zeitraums fanden sie keine Hinweise darauf, dass die Bakterien der Patientinnen genetische Resistenzen gegen die Phagen entwickelten.
Was das für künftige Behandlungen bedeutet
Kurz gesagt zeigt diese Arbeit, dass sorgfältig eingesetzte Automatisierung und Bildgebung die Unsicherheit in der Phagentherapie reduzieren können. Durch die Kombination realistischer Sammlungen patientenrelevanter Bakterien mit robotergestützten Tests und Computer Vision entwickelten die Forscher einen breit wirkenden Phagen-Cocktail, der gegen klinische Isolate aus der Praxis effektiv bleibt. Zwar sind größere Studien nötig, um klinische Vorteile zu bestätigen, doch bietet der Ansatz eine Blaupause zur Entwicklung fester, skalierbarer Phagenmedikamente zur Bekämpfung multiresistenter Infektionen und zur Verringerung der Abhängigkeit von klassischen Antibiotika.
Zitation: Penke, T.J.R., Hammack, A.T., McMillan, L.J. et al. High-throughput methods leveraging robotics and computer vision for the development of therapeutic phage cocktails. Nat Commun 17, 2192 (2026). https://doi.org/10.1038/s41467-026-68684-x
Schlüsselwörter: Phagentherapie, Harnwegsinfektion, Antibiotikaresistenz, Laborautomatisierung, Computer Vision