Clear Sky Science · de
Identifizierung antimikrobieller Peptide aus antiken Darmmikrobiomen
Alte Hinweise ausgraben, um moderne Keime zu bekämpfen
Während die Antibiotikaresistenz weltweit zunimmt, gehen Ärzten die Möglichkeiten aus, gefährliche Infektionen zu behandeln. Diese Studie wählt einen ungewöhnlichen Zugang zum Problem: Sie blickt nicht in Hightech-Chemielabore, sondern in die versteinerten Überreste menschlicher Fäkalien—antike Darm‑„Zeitkapseln“—um natürliche keimtötende Moleküle zu entdecken, die gegen heutige Bakterien noch wirken könnten.
Antike Mikroben als versteckte Hausapotheken
Lange vor der modernen Medizin war der menschliche Darm bereits ein Schlachtfeld, auf dem nützliche Mikroben und eindringende Krankheitserreger um Platz und Nahrung konkurrierten. Viele hilfreiche Darmbakterien produzieren antimikrobielle Peptide—kurze Proteinstücke, die Bakterienzellen Löcher zufügen oder sie anderweitig deaktivieren. Die moderne Forschung hat hauptsächlich in heutigen Mikrobiomen nach diesen keimtötenden Peptiden gesucht. Unsere gegenwärtigen Darmgemeinschaften haben sich jedoch zusammen mit dem Einsatz von Antibiotika und modernen Lebensweisen entwickelt, was schädlichen Bakterien viele Chancen gab, Resistenz zu entwickeln. Im Gegensatz dazu entstanden antike Darmgemeinschaften, die in getrockneten Fäkalien, sogenannten Koprolithen, erhalten sind, in einer Welt ohne verschreibungspflichtige Antibiotika. Das macht sie zu einer vielversprechenden Quelle „vergessener“ Abwehrmechanismen, denen moderne Krankheitserreger möglicherweise noch nicht ausweichen können.
Ein schlankes KI‑Werkzeug zum Lesen versteinerten Erbguts
Um diese antike Apotheke zu erforschen, bauten die Forschenden ein neues Computerwerkzeug namens AMPLiT (AMP Lightweight Identification Tool). Anstatt große Supercomputer zu benötigen, läuft AMPLiT effizient auf einem normalen Laptop und erreicht dennoch hohe Genauigkeit. Es durchsucht riesige DNA‑Datensätze aus Mikrobiomproben und markiert kurze Sequenzen, die wahrscheinlich antimikrobielle Peptide codieren. Das Team optimierte AMPLiTs Design so, dass es Millionen von Fragmenten aus beschädigter, jahrhundertealter DNA in wenigen Stunden verarbeiten konnte, wobei die Trainingszeit im Vergleich zu früheren Methoden um etwa 80 % reduziert wurde, während die Leistung beim Erkennen vielversprechender keimtötender Kandidaten nahe am Stand der Technik blieb.
Wiederbelebung von Keimtötern eines antiken Darmbewohners
Mithilfe von AMPLiT durchsuchten die Wissenschaftler das Darm‑DNA‑Material von sieben antiken Menschen, die vor 1.000–2.000 Jahren in Nordamerika lebten. Nach Entfernung von Umweltkontaminationen und Konzentration auf kurze, praktisch einsetzbare Peptidlängen sagte das Werkzeug Hunderttausende potenzieller antimikrobieller Sequenzen voraus. Eine strengere Filterreihe—Vorkommen in mehreren Individuen, chemische Eigenschaften und geringe vorausgesagte Toxizität—reduzierte diese Zahl auf 41 Kandidaten mit hoher Zuversicht, von denen 40 chemisch im Labor hergestellt werden konnten. Bei Tests gegen sowohl grampositive als auch gramnegative Bakterien (zwei große Gruppen, zu denen viele häufige Erreger gehören) bremsten oder stoppten 36 der 40 Peptide das Bakterienwachstum in relativ niedrigen Dosen—eine ungewöhnlich hohe Erfolgsquote für dieser Art Entdeckungsarbeit.
Der überraschende Star: ein schwindender Darmverbündeter
Ungefähr zwei Drittel der am stärksten aktiven Peptide stammten von einem einzigen Darmbakterium: Segatella copri, einem nahen Verwandten eines Mikrobenstamms, der früher unter Prevotella copri eingeordnet wurde. Diese Spezies war in antiken Darminhalten reichlich vorhanden und kommt noch heute bei Menschen mit traditionelleren, weniger industrialisierten Ernährungsweisen häufig vor, ist in vielen urbanen, westlich geprägten Populationen jedoch selten geworden. Durch die Verfolgung, wo die Peptidgene im Segatella‑Genom liegen, stellte das Team fest, dass die meisten eigentlich Fragmente größerer, alltäglicher „Housekeeping“‑Gene sind, die das Mikroben offenbar als Waffen umfunktioniert hat—ein effizienter evolutionärer Trick. Viele dieser antiken Peptide unterscheiden sich deutlich von denen in modernen Datenbanken, was darauf hindeutet, dass sie wirklich neue chemische Entwürfe darstellen und nicht nur kleine Variationen bekannter Antibiotika sind.
Für Wirte sicher, für Keime hart—und vielversprechend bei Wunden
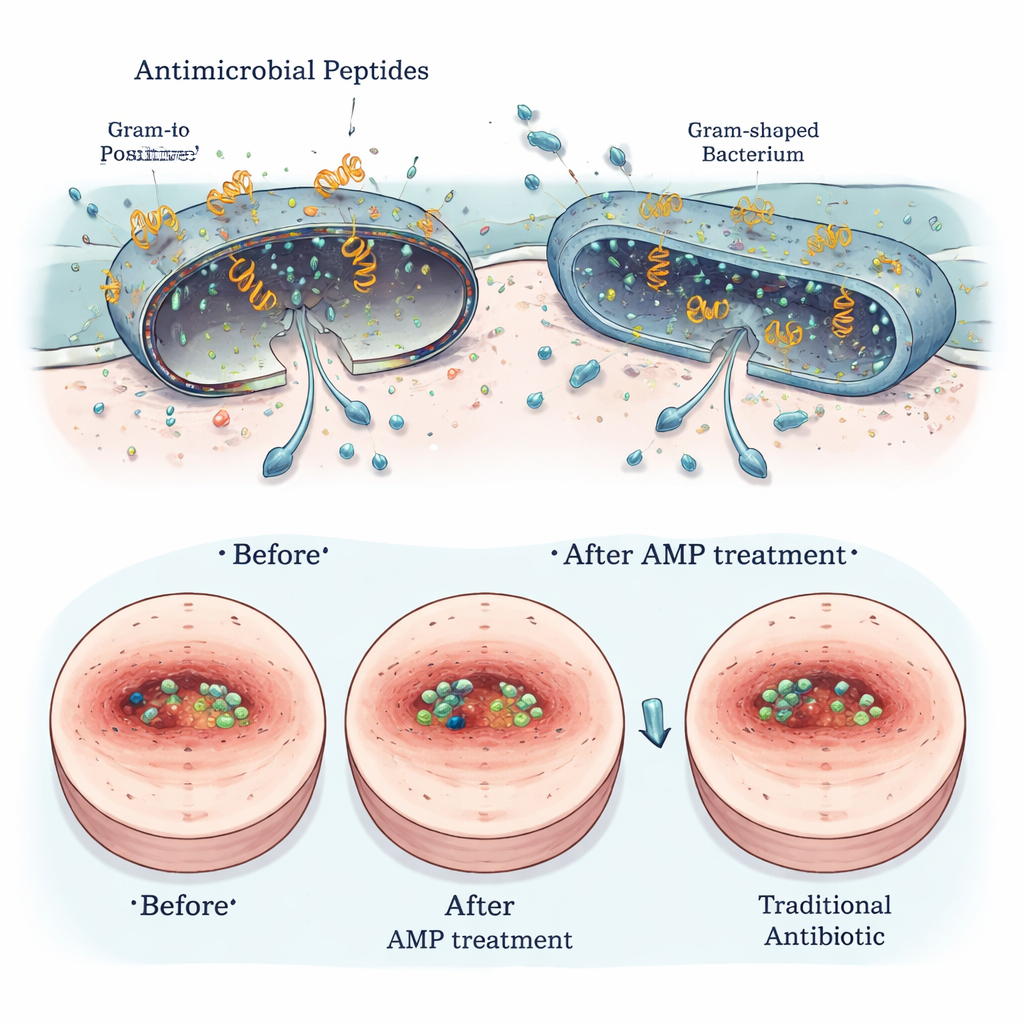
Mehrere der vielversprechendsten Segatella‑Peptide wurden auf Sicherheit und praktische Nützlichkeit geprüft. In Laborversuchen richteten sie wenig bis keinen Schaden an roten Blutkörperchen an und verursachten nur schwache, wenn überhaupt vorhandene Effekte auf menschliche darmähnliche Zellen. Hochauflösende Mikroskopie zeigte, dass die Peptide die äußeren Membranen schädlicher Bakterien physisch störten, während sie eukaryotische Zellen verschonten. In infizierten Wundmodellen bei Nagetieren reduzierten ausgewählte Peptide, auf die Haut aufgetragen, die Bakterienlast, beschleunigten den Wundverschluss und verringerten Entzündungszeichen, mit einer Wirkung, die mit etablierten Antibiotika wie Vancomycin und Polymyxin B vergleichbar war, insbesondere gegen grampositive Bakterien wie Staphylococcus aureus.
Was das für zukünftige Arzneien bedeutet
Für Nichtfachleute ist die Botschaft klar: Die Darmmikroben unserer Vorfahren könnten Blaupausen für neue Antibiotika enthalten, die gegen heutige schwer behandelbare Infektionen noch wirksam sind. Diese Studie zeigt, dass Wissenschaftler mit smarten, effizienten KI‑Werkzeugen wie AMPLiT antike DNA nach antimikrobiellen Peptiden durchkämmen können, die sowohl wirksam als auch relativ schonend für menschliche Zellen sind. Obwohl noch viele Schritte nötig sind, bevor eines dieser Moleküle als Medikament zugelassen werden kann, legt die Arbeit nahe, dass das Wiederbeleben „verlorener“ mikrobieller Partner wie Segatella copri—oder zumindest das Ausleihen ihrer molekularen Waffen—helfen könnte, unser schrumpfendes Arsenal gegen resistente Bakterien aufzufrischen.
Zitation: Chen, S., Yuan, Y., Wang, Y. et al. Identification of antimicrobial peptides from ancient gut microbiomes. Nat Commun 17, 1788 (2026). https://doi.org/10.1038/s41467-026-68495-0
Schlüsselwörter: antimikrobielle Peptide, antikes Mikrobiom, Segatella copri, Antibiotikaresistenz, metagenomisches Mining