Clear Sky Science · de
Das Genom von Camellia sinensis var. sinensis cv. Fuding Dabaicha enthüllt durch strukturelle Varianten angetriebene metabolische Innovation
Warum die Genetik der Teeblätter für Ihre Tasse wichtig ist
Jede Tasse Tee enthält ein chemisches Orchester aus Aromen und gesundheitsrelevanten Verbindungen, von beruhigenden Duftstoffen bis zu antioxidativ wirkenden Molekülen. Bislang verstanden Wissenschaftler jedoch nicht vollständig, wie die DNA der Teepflanze diese bemerkenswerte chemische Vielfalt entstehen lässt. Diese Studie entschlüsselt in beispielloser Detailtiefe das Genom einer klassischen chinesischen Teesorte namens Fuding Dabaicha und zeigt, wie großflächige DNA‑Unterschiede innerhalb einer einzelnen Pflanze Geschmack, Qualität und potenzielle gesundheitliche Wirkungen des getrunkenen Tees mitbestimmen.
Ein Blick unter die Haube der Teepflanze
Teepflanzen besitzen ungewöhnlich große und komplexe Genome, mit zwei elterlichen Kopien jedes Chromosoms, die stark voneinander abweichen können. Frühere Referenzgenome vermischten diese beiden Kopien zu einem einzigen „Konsensus“, wodurch viele wichtige Unterschiede verborgen blieben. In dieser Arbeit gingen die Forschenden weiter: Sie trennten und assemblten beide vollständigen Chromosomensätze – sogenannte Haplotypen – für Fuding Dabaicha. Dazu kombinierten sie hochgenaue lange DNA‑Reads, ultralange Nanopore‑Reads und Einzelzellsequenzierung von 107 einzelnen Spermienzellen der Teepflanze. Diese Kombination erlaubte es ihnen, nahezu lückenfreie Chromosomen zusammenzusetzen und die beiden elterlichen DNA‑Versionen mit sehr hoher Genauigkeit auseinanderzuhalten.

Versteckte strukturelle Veränderungen in der DNA
Mit beiden Haplotypen verglichen entdeckte das Team eine unerwartet große Menge an struktureller Variation – große Insertionen, Deletionen, Duplikationen und Inversionen von DNA, die weit über einfache Einzelbuchstabenmutationen hinausgehen. Etwa ein Viertel des Genoms unterschied sich in seiner Struktur zwischen den beiden Kopien, deutlich mehr als bei Vergleichen verschiedener Teesorten mit älteren Methoden festgestellt wurde. Viele dieser strukturellen Veränderungen entstanden durch die Aktivität von „springenden Genen“ bzw. transponierbaren Elementen, die sich kopieren und im Genom verschieben können. Zwei solcher Elemente, sogenannte Gypsy‑Retrotransposons und winzige DNA‑Elemente, bekannt als MITEs, spielten eine besondere Rolle bei der Umgestaltung der Chromosomen der Teepflanze in relativ kurzer evolutionärer Zeit.
Von der DNA‑Struktur zur ungleichmäßigen Genaktivität
Diese strukturellen Veränderungen sind nicht nur passive Narben im Genom – sie beeinflussen aktiv, wie Gene funktionieren. Die Forschenden zeigten, dass Tausende von Genen in der Nähe oder innerhalb dieser Umordnungen liegen. Als sie die Genaktivität in neun verschiedenen Teegeweben und in einer Nachkommenschaftsfamilie von Fuding Dabaicha maßen, fanden sie viele Gene, bei denen eine elterliche Kopie beständig aktiver war als die andere, ein Muster, das als allelspezifische Expression bezeichnet wird. Strukturelle Varianten in der Nähe von Genstartstellen neigten besonders dazu, die Expression zugunsten eines Haplotyps zu verschieben, wodurch eine elterliche Genkopie mehr „Lautstärke“ erhielt als die andere und funktionelle Ungleichgewichte entstehen konnten, die Pflanzeneigenschaften beeinflussen.
DNA‑Unterschiede mit Tee‑Metaboliten verknüpfen
Um das Genom mit dem zu verbinden, was letztlich in der Tasse landet, kombinierten die Forschenden ihr neues Genom mit groß angelegten chemischen Profilen von Tausenden Metaboliten in Teeblättern. Mithilfe von familienbasiertem Mapping und genomweiten Assoziationsanalysen über 215 diverse Teezugänge verbanden sie spezifische DNA‑Regionen mit der Variation von 2.837 Metaboliten. Ein auffälliges Beispiel betraf ein Gen namens CsDFRb, das zur Flavonoid‑Stoffwechselbahn gehört. In einem Haplotyp hatte sich ein großes Gypsy‑Element in die Promotorregion des Gens eingefügt und war stark methyliert, was die Genaktivität abschwächte. Das senkte die Expression von CsDFRb und führte über einen gemeinsamen chemischen Vorläufer zu erhöhten Mengen einer Verbindung namens p‑Coumaroylquinate in jungen Blättern. In anderen Regionen identifizierten sie Gene, die die Bildung von Chlorogensäuren und sulfatierten Metaboliten steuern, beide wichtig für Geschmack und mögliche gesundheitsbezogene Eigenschaften.
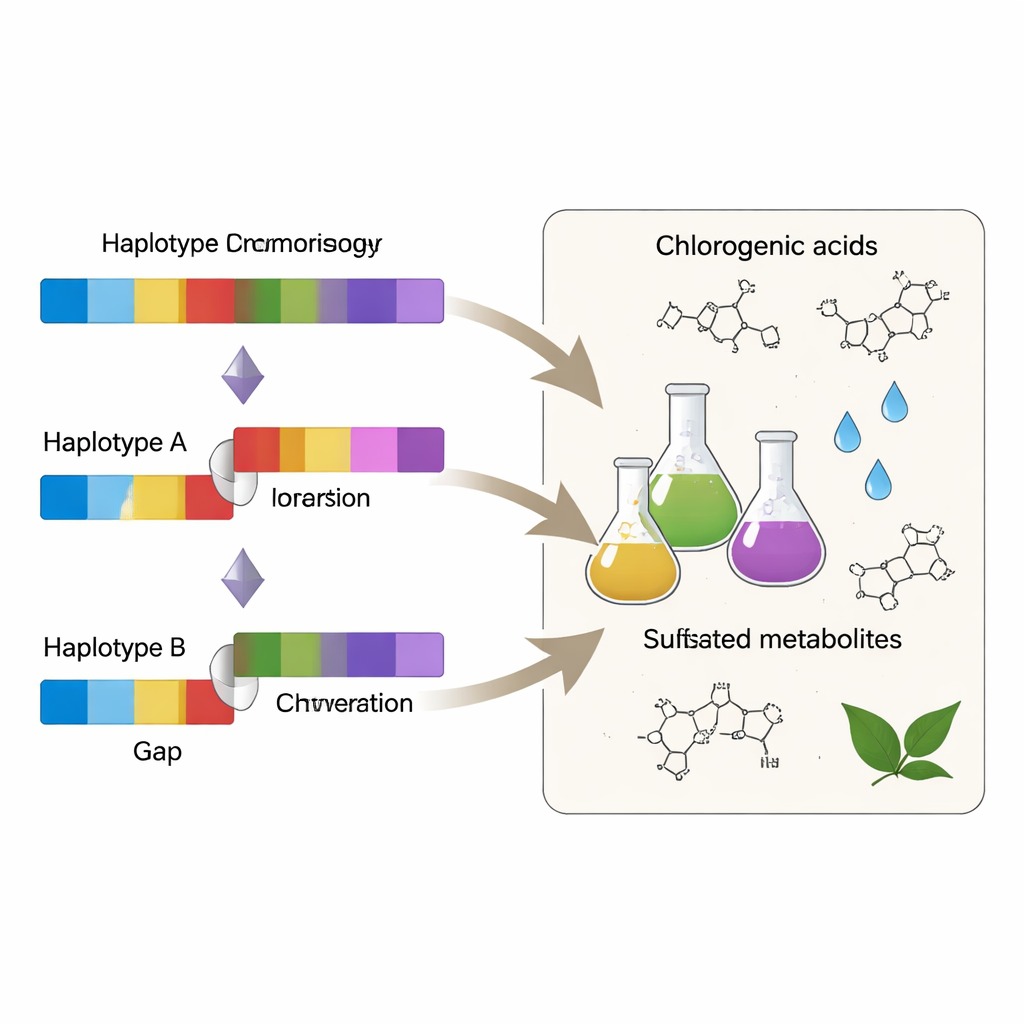
Eine bessere Genomkarte für besseren Tee
Indem sie zeigten, dass ein hochwertiges, haplotypaufgelöstes Genom weit mehr metabolitbezogene DNA‑Regionen offenbaren kann als ein älterer Referenzdatensatz, liefert diese Studie einen kraftvollen neuen Bauplan für die Teezüchtung. Für Nicht‑Spezialisten ist die Kernbotschaft: Großflächige DNA‑Umordnungen innerhalb einer einzelnen Teepflanze beeinflussen stark, welche nützlichen und aromatischen Verbindungen sich in ihren Blättern anreichern. Mit dieser detaillierten genetischen Karte können Züchter nun gezielter Pflanzenlinien auswählen oder kombinieren, um Geschmack, Aroma und gesundheitsrelevante Metaboliten zu steuern und so zukünftige Tees zu entwickeln, die sowohl schmackhafter als auch potenziell gesünder sind.
Zitation: Zhang, W., Jiang, X., Luo, S. et al. The Camellia sinensis var. sinensis cv. Fuding Dabaicha genome unveils structural variation-driven metabolic innovation. Nat Commun 17, 1754 (2026). https://doi.org/10.1038/s41467-026-68463-8
Schlüsselwörter: Genomik der Teepflanze, strukturelle Variation, Metabolit‑Diversität, haplotypaufgelöstes Genom, Teezüchtung