Clear Sky Science · de
Phosphorothioat-DNA-Modifikation durch BREX Typ‑4‑Systeme im menschlichen Darmmikrobiom
Verborgene chemische Feinabstimmungen in unseren Darmbakterien
Tief im menschlichen Darm tauschen Billionen von Bakterien ständig Gene aus, kämpfen gegen Viren und reagieren auf die Chemie unserer Nahrung. Diese Studie zeigt, dass viele dieser Mikroben stillschweigend das Rückgrat ihrer DNA umschreiben, indem sie Sauerstoffatome durch Schwefel ersetzen und damit eine spezielle Markierung namens Phosphorothioat erzeugen. Die Arbeit beschreibt eine neue Variante dieses Systems, die mit einem bakteriellen Abwehrbaukasten namens BREX Typ 4 verknüpft ist, und untersucht, wie weit verbreitet diese Schwefelmarken in Darmbakterien sind, die Gesundheit und Krankheit beeinflussen können.
Eine andere Art von DNA‑Marke
Die meisten Menschen haben schon von veränderten DNA‑Buchstaben — A, T, C und G — gehört, etwa durch kleine chemische Gruppen wie Methylierungen, die ein zentraler Teil der Epigenetik sind. Hier liegt der Fokus auf etwas weit radikalerem: Manche Bakterien ersetzen eines der Sauerstoffatome im DNA‑Rückgrat durch Schwefel. Diese Rückgratbearbeitung, bekannt als Phosphorothioatierung, verändert das Verhalten der DNA, ohne den genetischen Code zu ändern. Frühere Studien hatten zwei Hauptfamilien von Genen beschrieben, dnd und ssp, die solche Schwefelmarken in etwa einer von zehn bakteriellen und archäischen Arten anbringen. Diese Markierungen helfen Bakterien, ihre eigene DNA zu erkennen, sich gegen eindringende Viren (Phagen) zu verteidigen und möglicherweise auf oxidativen Stress und Entzündungen zu reagieren.
Durchsuchung Tausender Darm‑Genome
Um zu ermitteln, wie verbreitet schwefelmarkierte DNA in unserem Darm ist, durchsuchten die Forschenden 13.663 bakterielle Genome aus drei großen Sammlungen menschlicher Darmmikroben. Sie suchten nach genetischen Signaturen, die ausreichen, um Schwefelmarken zu erzeugen: Sets von dnd‑, ssp‑ oder einem neueren Kandidaten‑Gencluster namens brx, der Teil von BREX ist, einem bekannten Anti‑Phagen‑System. Etwa 6,3 % der Darm‑Genome trugen mindestens eines dieser Systeme, hauptsächlich in den häufigen Darmgruppen Bacteroidota, Bacillota und Pseudomonadota. Im Vergleich zu einem breiteren Katalog von Bakterien aus vielen Umgebungen zeigte der Darm eine deutliche Anreicherung der BREX Typ‑4‑Variante, was darauf hindeutet, dass diese schwefelbasierte Abwehr im Darmökosystem besonders begünstigt ist.
Ein neues schwefelbasiertes Abwehrsystem
Beim Betrachten der Genanordnung auf bakteriellen Chromosomen fiel dem Team auf, dass dnd‑ähnliche Gene zwischen BREX‑Abwehrgenen lagen, was darauf hindeutet, dass einige BREX‑Systeme direkt Schwefelmarken anbringen könnten. Sie konzentrierten sich auf eine Gruppe von vier Kerngenen, brxP, brxC, brxZ und brxL, und zeigten mittels Sequenzanalyse, dass BrxP und BrxC den schwefelverarbeitenden Proteinen aus ssp‑Systemen ähneln. Experimente im Darmbakterium Bacteroides salyersiae bestätigten den Verdacht: Als die Forschenden das brxC‑Gen löschten, verschwanden die schwefelmodifizierten DNA‑Marken; setzten sie brxC auf ein Plasmid zurück, kehrten die Schwefelmarken zurück. Sie transferierten außerdem Schlüssel‑BREX‑Gene in ein anderes Darmbakterium, das diese Systeme normalerweise nicht besitzt, und zeigten, dass es daraufhin dieselben schwefelgeprägten DNA‑Muster produzierte, was demonstriert, dass die BREX Typ‑4‑Maschinerie allein Phosphorothioat‑Marken erzeugen kann.
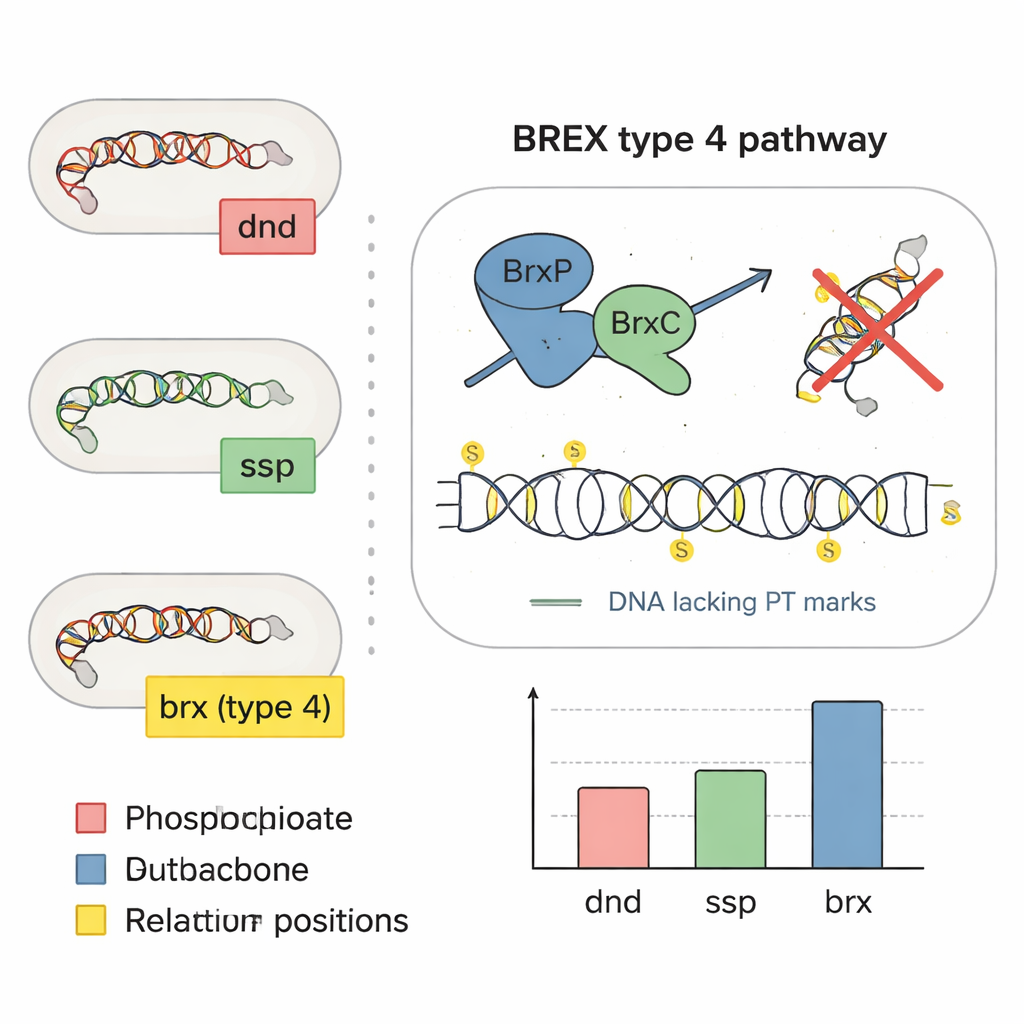
Kartierung, wo Schwefel im Genom landet
Schwefelmarken zu finden ist nur die halbe Geschichte; entscheidend für das Verständnis ihrer Funktion ist zu wissen, wo genau sie entlang der DNA erscheinen. Die Forschenden kombinierten empfindliche Massenspektrometrie mit einer maßgeschneiderten Sequenziermethode namens PT‑seq, die DNA selektiv an schwefelmodifizierten Stellen schneidet und dann die umliegende Sequenz liest. Über 226 isolierte Darmbakterienstämme hinweg identifizierten sie acht verschiedene schwefelhaltige Dinukleotid‑„Bausteine“ und ermittelten anhand repräsentativer Stämme vollständige kurze Sequenzmotive, an denen Schwefel bevorzugt landet. Interessanterweise produzierten Bakterien mit dnd‑, ssp‑ oder BREX‑Systemen unterschiedliche Sätze von Schwefelmustern, wie verschiedene Dialekte derselben chemischen Sprache. Die Markierungen waren nicht zufällig verteilt: Sie zeigten eine Anreicherung in ribosomalen RNA‑Genen und wurden generell an den Anfangs‑ und Endbereichen von proteinkodierenden Genen gemieden, was darauf hindeutet, dass Bakterien Schwefel möglicherweise von empfindlichen Kontrollregionen fernhalten.
Was das für unsere Gesundheit bedeutet
Für Nicht‑Spezialisten zeigen diese Befunde, dass Darmbakterien mehr tun, als nur von unserer Nahrung zu leben ‑ sie schreiben aktiv die Chemie ihrer eigenen DNA um, in Formen, die beeinflussen, wie sie gegen Viren kämpfen und auf die oft mit Entzündungen einhergehenden starken oxidierenden Bedingungen reagieren. Indem die Studie BREX Typ 4 als neues schwefelmarkierendes System identifiziert und zeigt, dass etwa einer von dreizehn Darmmikroben eine Form der Phosphorothioat‑Maschinerie trägt, legt sie die Grundlage dafür, zu erforschen, wie diese ungewöhnlichen DNA‑Marken die Stabilität des Mikrobioms, die Resistenz gegen Infektionen und möglicherweise den Verlauf von Krankheiten wie entzündlichen Darmerkrankungen beeinflussen. Langfristig könnte das Verständnis und vielleicht die gezielte Steuerung dieser schwefelbasierten epigenetischen Systeme neue Strategien bieten, um das Darmmikrobiom im Sinne der menschlichen Gesundheit zu modulieren.
Zitation: Yuan, Y., DeMott, M.S., Byrne, S.R. et al. Phosphorothioate DNA modification by BREX type 4 systems in the human gut microbiome. Nat Commun 17, 1717 (2026). https://doi.org/10.1038/s41467-026-68412-5
Schlüsselwörter: Darmmikrobiom, bakterielle Epigenetik, DNA‑Phosphorothioatierung, BREX‑Abwehrsystem, Bakteriophagen