Clear Sky Science · de
Biochemische Prinzipien der miRNA-Zielerkennung bei Fliegen
Winzige RNA-Botschaften, die Zellen von Fliegen steuern
In jeder Zelle der Fruchtfliege agieren winzige Moleküle, sogenannte microRNAs, wie Qualitätsprüfer: Sie entscheiden, welche genetischen Botschaften in Proteine umgesetzt und welche stillgelegt werden. Diese Studie stellt eine auf den ersten Blick einfache Frage: Wie erkennen diese microRNAs genau ihre Ziele in Fliegen? Indem die Autoren darauf eine Antwort geben, kommen sie dem Ziel näher, allein aus der Sequenz vorherzusagen, welche Gene während Entwicklung, Verhalten und Krankheit hoch- oder herunterreguliert werden.
Wie kleine RNAs Gene herunterfahren
MicroRNAs sind kurze RNA-Stücke von etwa 22 Bausteinen, die sich in Fruchtfliegen mit einem Protein namens Argonaute 1 (Ago1) zusammentun. Gemeinsam durchforsten sie viel längere messenger RNAs (mRNAs), die Anweisungen zur Proteinsynthese tragen. Findet eine microRNA eine teilweise passende Region auf einer mRNA, kann der Ago1-Komplex die mRNA entweder zerschneiden oder deren Translation in Protein blockieren und so die Genaktivität reduzieren. Bei Säugetieren haben Forscher die Erkennungsregeln sehr detailliert kartiert und eine überraschende Vielfalt an Bindungsmodi aufgedeckt. Im Gegensatz dazu waren die Regeln bei Fliegen weniger klar, obwohl microRNAs dort zentrale Prozesse wie Wachstum, Entwicklungszeitpunkt und den Schlaf-Wach-Rhythmus steuern.
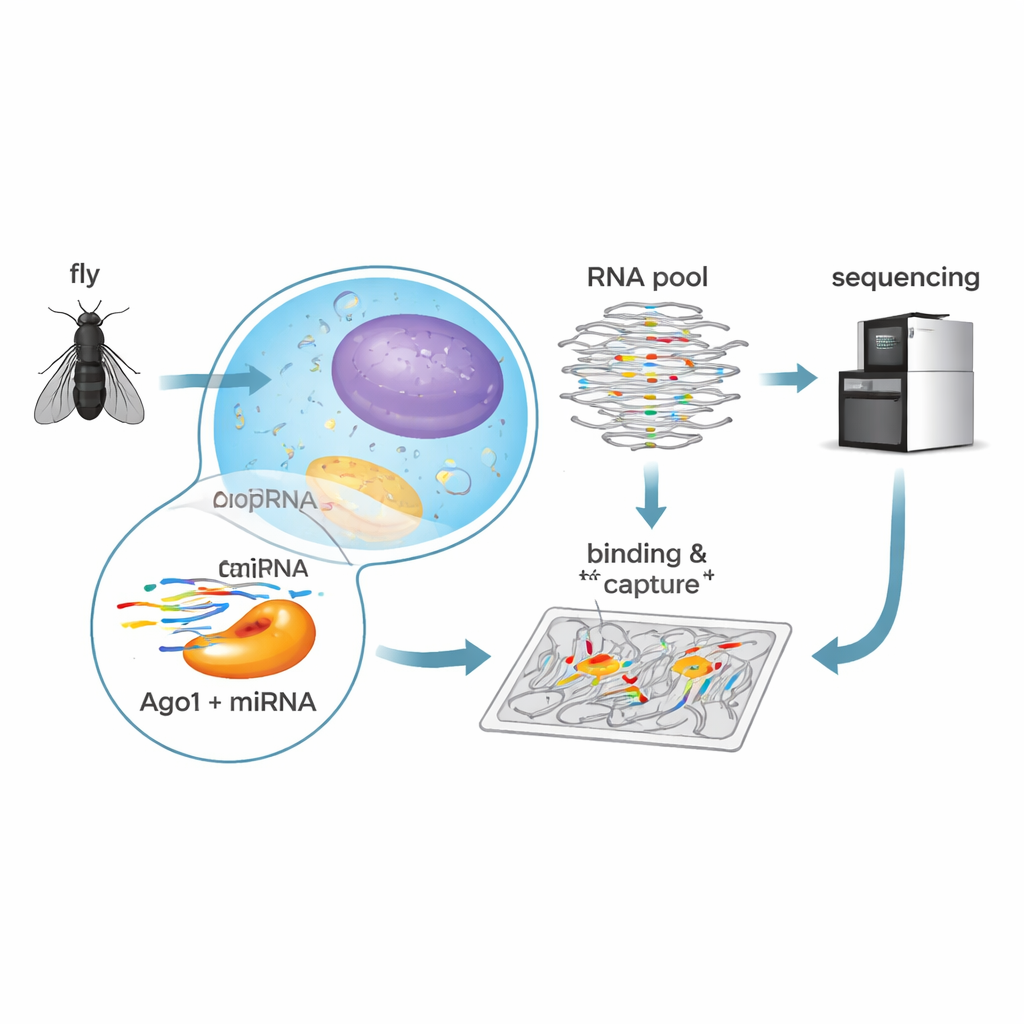
Ein Hochdurchsatz-Bindungstest
Um diese Regeln in Fruchtfliegen zu entschlüsseln, verwendeten die Forschenden eine biochemische Methode namens RNA Bind-n-Seq. Sie belegten gereinigtes Fliegen-Ago1 mit jeweils einer von fünf häufigen microRNAs — let-7, bantam, miR-184, miR-11 oder miR-124 — die jeweils bekannte Rollen in Entwicklung und Hirnfunktion haben. Anschließend mischten sie jeden Ago1–microRNA-Komplex mit einer riesigen Bibliothek synthetischer RNAs mit zufälligen Sequenzen. Nach einer Bindungsphase trennten sie gebundene von ungebundenen RNAs, sequenzierten die gebundenen Moleküle und nutzten statistische Modelle, um zu berechnen, wie stark jeder Sequenztyp erkannt wurde. Dieser Ansatz lieferte quantitative Bindungsstärken für Hunderte unterschiedlicher Zielmuster in einer einzigen Reihe von Experimenten.
Einfache Regeln mit einigen klugen Ausnahmen
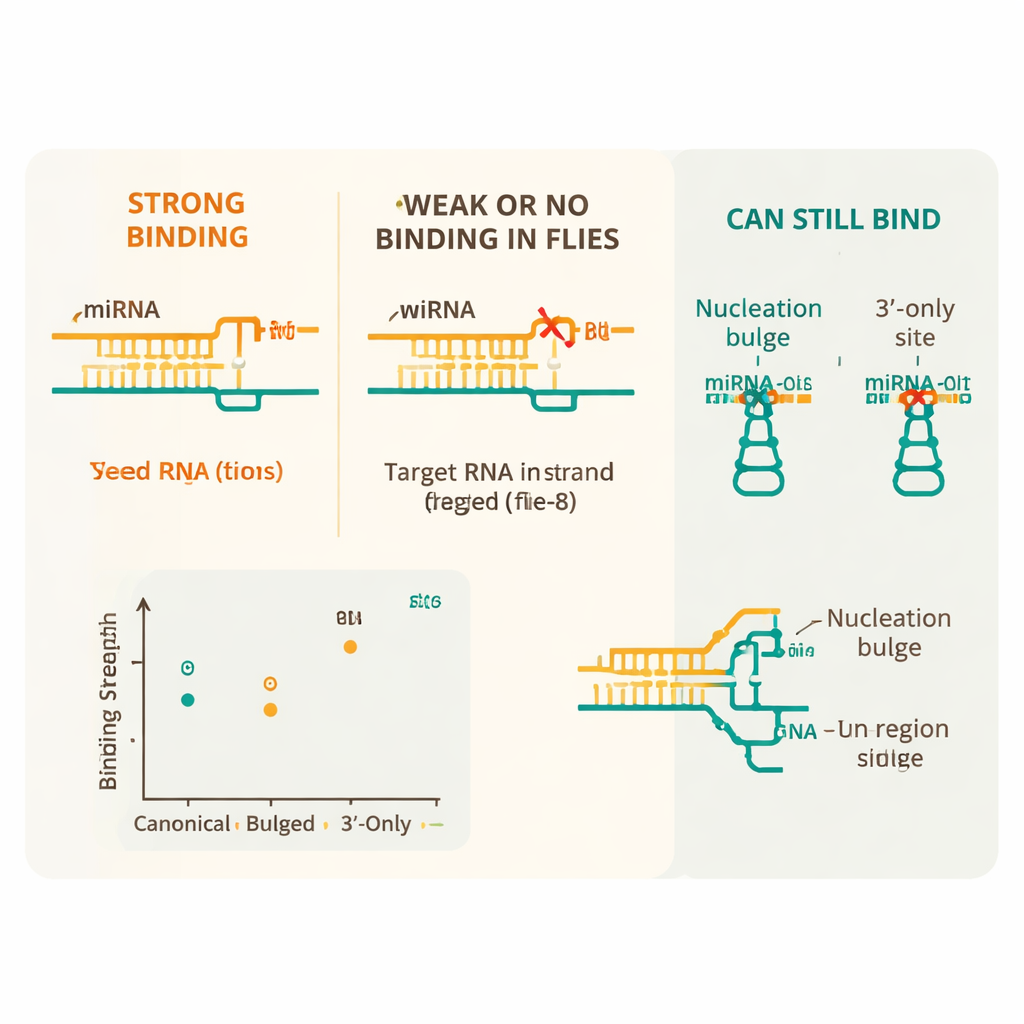
Die Ergebnisse zeigen, dass Fliegen-microRNAs einem strengeren Regelwerk folgen als ihre Säugetierpendants. Das wichtigste Merkmal ist eine „Seed“-Region — die Positionen 2 bis 8 der microRNA — die nahezu perfekt mit der mRNA paaren muss, damit starke Bindung entsteht. Kanonische Seed-angepasste Stellen, besonders solche mit acht passenden Basen und einer bestimmten benachbarten Nukleotidumgebung, wiesen die höchste Affinität auf. Hingegen reduzierte schon eine einzige falsche Wobble-Paarung (ein sogenanntes G:U-Paar) innerhalb dieses Seeds die Bindung deutlich, und zwei oder mehr solche Imperfektionen machten die Wechselwirkung ununterscheidbar vom Hintergrund. Fehlpaarungen in der Mitte des Seeds waren besonders schädlich, was betont, wie sensibel Ago1 dieses Kernsegment liest.
Versteckte Flexibilität jenseits der Kernpaarung
Trotz dieser Gesamtrigidität entdeckte die Studie mehrere wichtige Auswege, durch die einige unvollkommene Stellen trotzdem erkannt werden können. Zusätzliche Paarungen zwischen dem Schwanzende der microRNA und der mRNA konnten einen einzigen Fehler im Seed kompensieren und die starke Bindung wiederherstellen. Bestimmte spezielle Anordnungen, sogenannte Nukleations-Bulges — bei denen ein zusätzliches Nukleotid neben dem Seed herausragt — banden ebenfalls fast so gut wie Standardstellen. Das Team zeigte außerdem, dass Ago1 „3′-only“-Stellen binden kann, bei denen der Seed nicht beteiligt ist, aber das Ende der microRNA stark paart, und dass es effizient Ziele mit langen zentralen Matches zerschneiden kann. Schließlich stellte sich heraus, dass die umgebende Sequenz wichtig ist: Stellen, die von A- und U-reichen Regionen flankiert werden und daher eher unstrukturiert und zugänglich sind, wurden stärker gebunden als die gleichen Stellen in starreren Sequenzkontexten.
Warum diese Regeln für die Biologie der Fliege wichtig sind
In der Summe zeigen diese Befunde, dass Fliegen-microRNAs im Allgemeinen nahezu perfekte Übereinstimmung in ihrer Seed-Region verlangen, mit nur einer begrenzten Auswahl tolerierter Ausnahmen. Dieses einfachere und strengere Regelwerk steht im Gegensatz zur größeren Flexibilität bei Säugetieren. Indem die Arbeit harte Zahlen darüber liefert, wie stark verschiedene Zielmuster gebunden werden, schafft sie die Grundlage für nächste Generationen von Computertools, die genauer vorhersagen können, welche Fliegen-Gene von welchen microRNAs reguliert werden. Für Nicht-Spezialisten lautet die Schlussfolgerung: Die Genregulation bei Fliegen folgt, obwohl von winzigen RNAs geleitet, klaren biochemischen Prinzipien — Prinzipien, die nun genutzt werden können, um komplexe Merkmale wie Entwicklung, Verhalten und Krankheitsresistenz zu verstehen und letztlich zu beeinflussen.
Zitation: Vega-Badillo, J., Zamore, P.D. & Jouravleva, K. Biochemical principles of miRNA targeting in flies. Nat Commun 17, 1641 (2026). https://doi.org/10.1038/s41467-026-68360-0
Schlüsselwörter: microRNA, Drosophila, Argonaute, RNA-Bindung, Genregulation