Clear Sky Science · de
Genomische und physiologische Signaturen der Anpassung bei pathogenen Pilzen
Warum Pilze auf unserer Haut und im Boden wichtig sind
Pilze denkt man oft als Waldpilze oder Schimmel auf altem Brot, doch viele mikroskopische Pilze leben unaufgeregt im Boden, auf Pflanzen und sogar auf unserer Haut. Einige dieser harmlosen Arten können sich plötzlich in ernsthafte Gefahren verwandeln und lebensbedrohliche Infektionen bei Menschen mit geschwächtem Immunsystem auslösen. Diese Studie stellt eine auf den ersten Blick einfache Frage: Was ändert sich in diesen Pilzen, wenn sie vom Leben auf totem Pflanzenmaterial zum Eindringen in den menschlichen Körper übergehen?
Verwandtschaft nachvollziehen bei nützlichen und schädlichen Pilzen
Die Forschenden konzentrierten sich auf eine Gruppe von Hefen namens Trichosporonales, die sowohl Umweltarten umfasst, die sich von zerfallendem Material ernähren, als auch opportunistische Arten, die Menschen infizieren können. Durch den Vergleich der Genome von 45 Pilzstämmen bauten sie einen Stammbaum, der zeigt, wie diese Arten verwandt sind. Der Baum machte deutlich, dass menschliche Erreger über verschiedene Zweige verstreut sind und nicht in einer einzigen Linie gruppiert auftreten. Dieses Muster deutet darauf hin, dass die Fähigkeit, Menschen zu infizieren, mehrfach unabhängig entstanden ist und nicht nur einmalig und dann vererbt wurde.
Gleicher Werkzeugkasten, andere Nutzung
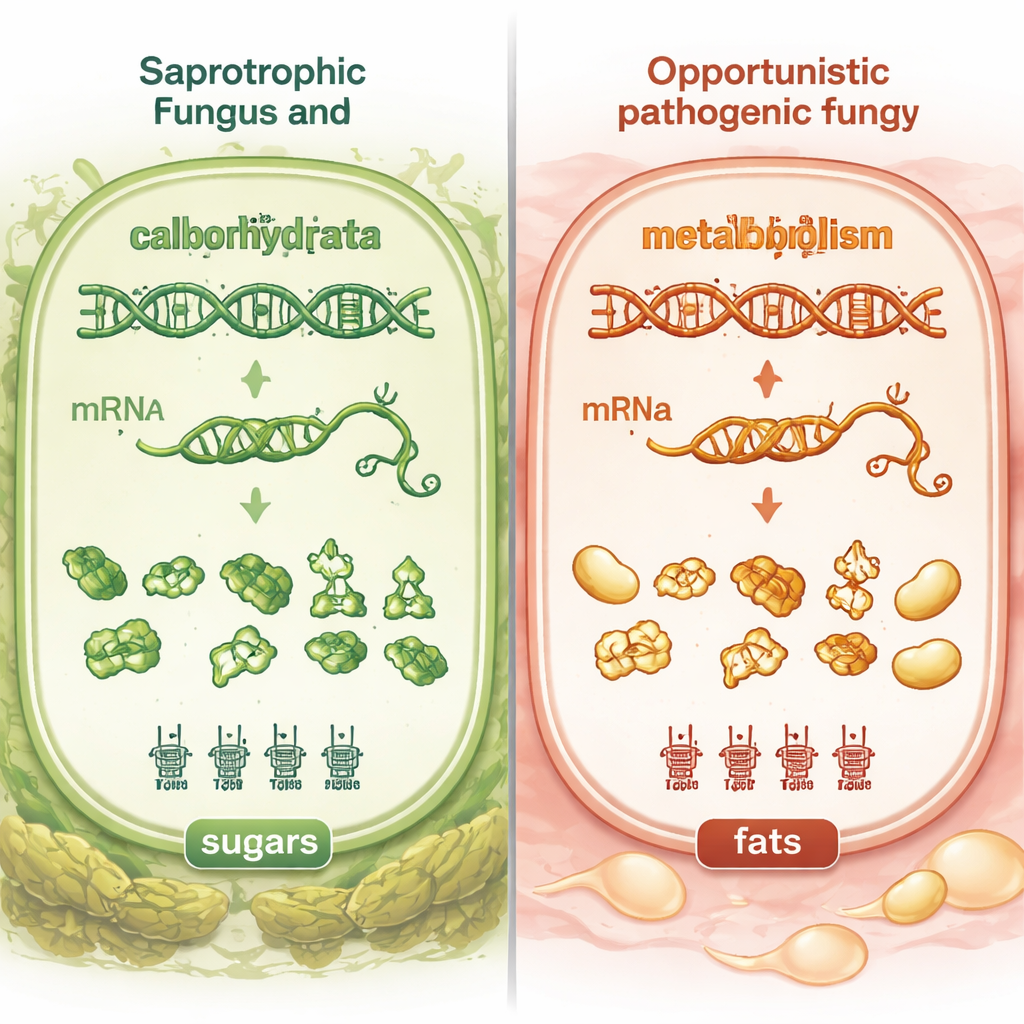
Eine naheliegende Vermutung ist, dass gefährliche Pilze spezielle Genpakete besitzen—wie zusätzliche Werkzeuge—die harmlose Pilze nicht haben. Um das zu prüfen, zählte das Team Gene, die am Abbau von Kohlenhydraten beteiligt sind (wichtig fürs Leben auf Pflanzenresten), und Gene, die mit dem Umgang von Fetten und Ölen zu tun haben (wichtig im Inneren von Tieren). Überraschenderweise fanden sie, dass Pathogene und Saprotrophe sehr ähnliche Zahlen dieser Gene sowie ähnliche Genomgrößen, repetitive DNA und sezernierte Enzyme besitzen. Mit anderen Worten: Allein das Vorhandensein bestimmter Gene trennt Pilze, die Menschen infizieren, nicht klar von solchen, die das nicht tun. Der entscheidende Unterschied scheint weniger darin zu liegen, welche Gene sie haben, sondern wie effizient sie diese nutzen können.
Die Proteinfabrik auf Geschwindigkeit trimmen
Um tiefer zu blicken, untersuchten die Autorinnen und Autoren den Prozess der Translation—den Schritt, bei dem Zellen genetische Informationen lesen und Proteine bauen. Die Translation hängt von Transfer‑RNAs (tRNAs) ab, kleinen Molekülen, die genetische „Codons“ mit Aminosäuren verknüpfen. Wenn die Codons eines Gens zu den häufigsten tRNAs passen, kann sein Protein schneller und effizienter hergestellt werden. Das Team maß, wie gut Codons in kohlenhydratbezogenen und lipidbezogenen Genen für die verfügbaren tRNAs jeder Art „optimiert“ sind. Sie fanden, dass saprotrophe Pilze tendenziell besser auf Kohlenhydratstoffwechsel abgestimmt waren, während opportunistische Pathogene eine relativ höhere Optimierung für Lipidstoffwechsel zeigten. Dieses Muster war so ausgeprägt, dass ein einfaches Entscheidungsbaum‑Modell meist vorhersagen konnte, ob eine Art Pathogen oder Saprotroph ist, allein anhand der relativen Optimierung von Lipid‑ gegenüber Kohlenhydratwegen.
Von genetischer Abstimmung zum Wachstum in der Praxis
Genomische Signaturen sind nur nützlich, wenn sie sich in der Praxis auswirken, also prüften die Forschenden, wie verschiedene Pilze im Labor wuchsen. Sie maßen das Wachstum in zuckerreichen Medien und in lipidreichen Medien und beobachteten außerdem, wie schnell sich die Pilze an neue Bedingungen anpassten. Während die Gesamtwachstumsraten nicht stark mit Codonoptimierung korrelierten, tat dies die Länge der Latenzphase—die Wartezeit, bevor das schnelle Wachstum begann. Pilze, deren Stoffwechselgene für eine bestimmte Nahrungsquelle optimierter kodiert waren, begannen auf diesem Substrat schneller zu wachsen. Das Team testete außerdem Wachstum bei höheren Temperaturen, einschließlich 33 °C und 37 °C, ähnlich der Körperwärme von Säugetieren. Viele bekannte Pathogene wuchsen gut bei diesen Temperaturen, aber einige vermeintlich „umweltbezogene“ Arten taten das ebenfalls, und manche Pathogene nicht, was zeigt, dass Hitzetoleranz wichtig, aber nicht der einzige Faktor für Pathogenität ist.
Versteckte Kandidaten für zukünftige Pilzbedrohungen
Ein auffälliges Ergebnis war, dass bestimmte Pilze, die derzeit als harmlose Saprotrophe klassifiziert sind, translationale Muster und Temperaturtoleranz zeigten, die bekannten opportunistischen Pathogenen ähneln. Besonders einige Apiotrichum‑ und Vanrija‑Arten erscheinen genetisch darauf vorbereitet, lipidreiche Umgebungen zu bewältigen und in Körpernähe zu wachsen, obwohl sie in klinischen Berichten noch nicht häufig vorkommen. Das legt nahe, dass die Grenze zwischen Umweltpilzen und potenziellen Pathogenen dünner ist als es scheint und dass einige stille Bewohner von Boden oder Laubstreu unter den richtigen Bedingungen zu künftigen Gesundheitsbedrohungen werden könnten.
Was das für die menschliche Gesundheit bedeutet
Für Nicht‑Spezialisten ist die Kernbotschaft, dass gefährliche Pilzeigenschaften möglicherweise nicht von exotischen „Virulenzgenen“ abhängen, sondern davon, wie effizient verbreitete Stoffwechselgene translatiert werden, wenn Pilze auf neue Umgebungen wie den menschlichen Körper treffen. Durch das Lesen subtiler Signale in Codon‑Nutzung und tRNA‑Zusammensetzung können Wissenschaftler beginnen, Umweltpilze zu identifizieren, die bereit sind, sich rasch an Wirte anzupassen. Solche genomischen und physiologischen Marker könnten Ärzten und Gesundheitsbehörden letztlich helfen, vorherzusagen, welche Arten mit hoher Wahrscheinlichkeit als nächste opportunistische Erreger auftreten, und so Überwachung und Vorsorge verbessern, bevor Ausbrüche stattfinden.
Zitation: Guerreiro, M.A., Yurkov, A., Nowrousian, M. et al. Genomic and physiological signatures of adaptation in pathogenic fungi. Nat Commun 17, 748 (2026). https://doi.org/10.1038/s41467-026-68330-6
Schlüsselwörter: pilzpathogene, Genomentwicklung, Codon‑Optimierung, opportunistische Infektionen, Wirtsanpassung