Clear Sky Science · de
Artübergreifende Entschlüsselung salzbezogener Gene durch genetische Analyse einer euryhalinen Mikroalge Chlorella sp
Warum eine winzige Grünalge für salzige Böden wichtig ist
Wachsende Bodensalinität verkleinert still und leise die weltweiten Ackerflächen und erschwert das Pflanzenwachstum. In dieser Studie wendeten sich die Forschenden einem unerwarteten Verbündeten zu: einer mikroskopisch kleinen Grünalge, Chlorella sp. MEM25, die sowohl in Süßwasser als auch in extrem salzigen Teichen gedeihen kann. Indem sie ihr vollständiges Genom entschlüsselten und verfolgten, wie Gene und Stoffwechselprodukte auf Salz reagieren, entdeckten die Wissenschaftlerinnen und Wissenschaftler ein Set „Salzgene“, das dieser Alge nicht nur das Überleben ermöglicht, sondern auch genutzt werden könnte, um salztolerantere Nutzpflanzen zu entwickeln.
Ein Überlebenskünstler zwischen Meer und Teich
MEM25 wurde in einem salzhaltigen Binnenpool auf der Insel Hainan (China) gefunden, dessen Wasser salziger ist als die meisten Meere und das das ganze Jahr über heiß bleibt. Bemerkenswerterweise wächst diese Mikroalge von null Salz bis hin zu mehr als dem Dreifachen der Meeresalinität, mit maximaler Wuchsleistung bei etwa der doppelten Salzstärke des Ozeans. Das Team stellte eine nahezu perfekte, chromosomenebene Kartierung ihrer DNA zusammen, die 16 Chromosomen mit klar markierten Zentren und Enden zeigte. Dieses Detaillierungsniveau erlaubte Vergleiche von MEM25 mit Dutzenden anderen Grünalgen und Landpflanzen und zeigte, wo sich diese Linie in der Evolutionsgeschichte von anderen verzweigt hat.

Ein evolutionärer Knotenpunkt für Leben in salzigem Wasser
Durch den Aufbau von Stammbäumen aus Hunderten gemeinsamer Gene von 38 Grünalgenarten sowie mehreren Pflanzen- und Bakterienoutgroups fanden die Forschenden heraus, dass MEM25 nahe einem der Aufspaltungspunkte zwischen Meer- und Süßwasser-Grünalgen sitzt. Molekulare Datierungen deuten darauf hin, dass es vor mehr als 600 Millionen Jahren entstanden ist und damit zu den älteren bekannten Chlorophyten-Linien gehört. Als das Team untersuchte, welche Genfamilien in salzigen gegenüber süßen Habitaten gehäuft auftreten, erwies sich MEM25 als ungewöhnlich: Es trägt viele der typischen „Meeresgene“ und zugleich eine überraschend große Anzahl von „Süßwassergenen“. Statistische Analysen zeigten, dass diese doppelte Identität MEM25 zur meeresbewohnenden Art macht, die den Süßwasseralgen am nächsten sitzt, und untermauern die Idee, dass sie eine evolutionäre Brücke zwischen beiden Umgebungen bildet.
Geteilte Werkzeuge und spezielle Tricks im Umgang mit Salz
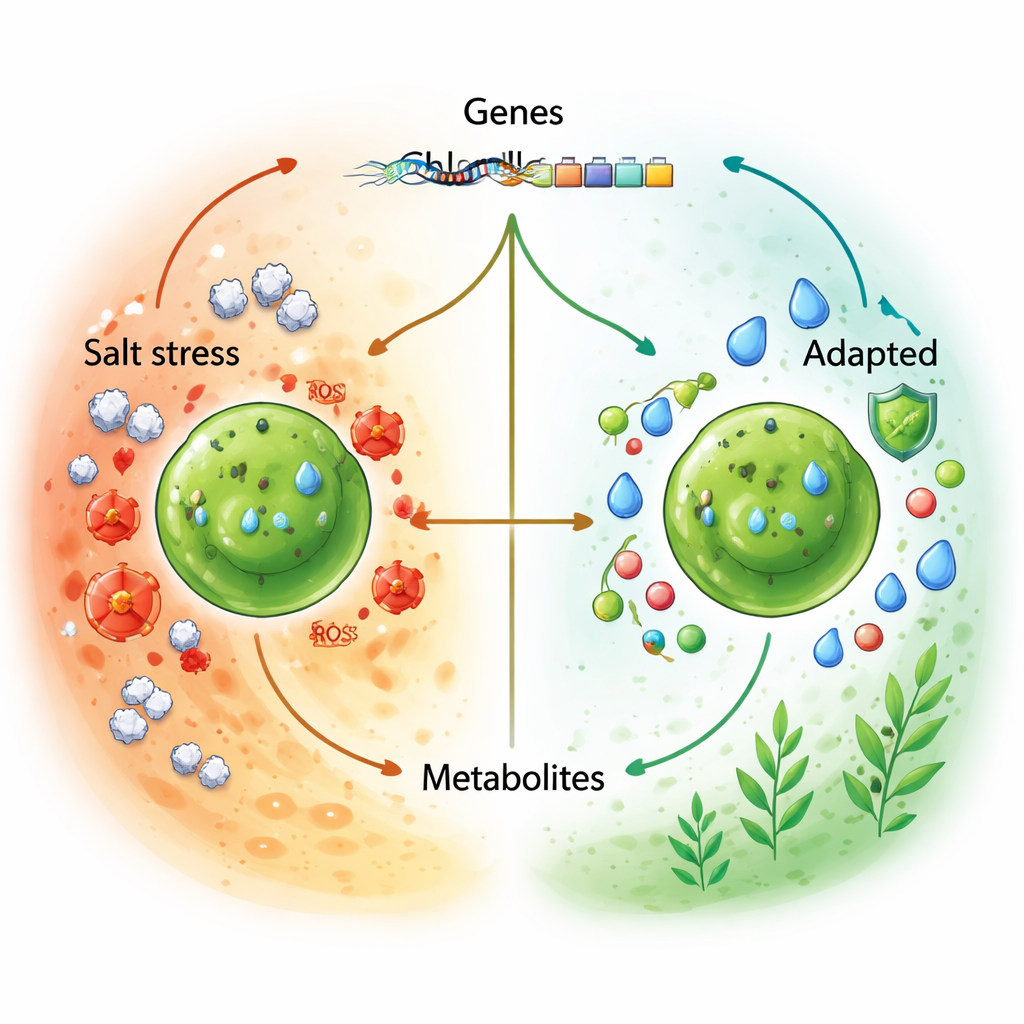
Um zu verstehen, wie MEM25 mit plötzlichen Salzveränderungen zurechtkommt, verglichen die Wissenschaftlerinnen und Wissenschaftler seine aktiven Gene und kleinen Moleküle mit denen eines nah verwandten Süßwasser-Chlorella-Stamms. Mithilfe von Netzwerk-Analysen gruppierten sie Tausende von Genen und Hunderte von Metaboliten in Module, die mit Salzgehalt und Arttyp korrelierten. Einige Module wurden zwischen Süß- und Salzwasserarten geteilt und weisen auf einen gemeinsamen Satz „ancestraler“ Werkzeuge hin: etwa Gene, die oxidativen Schaden managen, kleine Moleküle in und aus Zellen transportieren und klassische Schutzverbindungen wie Prolin, Zucker und bestimmte Lipide produzieren. Andere Module waren MEM25-exklusiv und nur unter Salzstress aktiv, was auf spezielle Strategien hindeutet, die bisher noch nicht beschrieben wurden.
Geliehene Gene und aktive Abwehrmechanismen
Genomweite Vergleiche zeigten, dass 89 Genfamilien in MEM25 gegenüber süßwasserverwandten Arten erweitert sind. Einige davon sind uralt und auch in Landpflanzen zu finden, darunter Gene, die bei der Entgiftung reaktiver Sauerstoffspezies helfen, das Zellvolumen anpassen und Proteine markieren, damit sie bei geänderten Bedingungen abgebaut werden. Die Mehrheit scheint jedoch MEM25-spezifisch zu sein. Ein auffälliges Beispiel kodiert ein Protein, das mit bakteriellen Enzymen verwandt ist, die vor osmotischem Stress schützen, was darauf hindeutet, dass diese Alge es möglicherweise von Bakterien erworben hat. Viele dieser erweiterten Gene wurden bei steigender Salzkonzentration aktiver, und die Alge steigerte gleichzeitig Metaboliten wie Prolin, ungesättigte Fettsäuren, Zucker und Vitamine. Zusammen deuten diese Veränderungen auf ein koordiniertes Abwehrsystem hin, das Zellmembranen stärkt, Wasser und Ionen ausgleicht und schädliche Nebenprodukte beseitigt, die unter Salzstress entstehen.
Von Labormutanten zu zukünftigen salztoleranten Nutzpflanzen
Um zu prüfen, ob die Kandidatengene tatsächlich die Salztoleranz beeinflussen, erzeugte das Team Zehntausende MEM25-Mutanten und nutzte genomweite Assoziationsmethoden, um DNA-Veränderungen mit Wachstum unter hohem Salz zu verknüpfen. Dabei traten mehrere Mitglieder einer Protein-Tagging-Genfamilie, bekannt als E3-Ligasen, besonders hervor. Die Forschenden bearbeiteten dann ausgewählte „salzempfindliche“ Gene in einer anderen Alge, die mäßige Salzgehalte bevorzugt; das Entfernen beliebiger sechs solcher Gene steigerte ihr Wachstum bei hohem Salz. Sie gingen einen Schritt weiter und entfernten Pflanzenversionen eines MEM25-Gens namens RMI1 in der Modellpflanze Arabidopsis. Pflanzen ohne RMI1 entwickelten unter salzigen Bedingungen längere Wurzeln, was zeigt, dass dieses Gen von Algen bis zu höheren Pflanzen eine bremsende Wirkung auf die Salztoleranz ausübt.
Was das für Leben in salzigen Welten bedeutet
Für Nichtfachleute lautet die Botschaft: MEM25 ist ein evolutionäres Versuchsfeld, in dem die Natur viele Wege ausgelotet hat, die Grenze zwischen Ozean und Süßwasser zu überqueren. Einige seiner Salzantwortgene sind alte Werkzeuge, die auch Landpflanzen gemeinsam haben, andere sind neue Erfindungen oder sogar von Bakterien übernommen. Da viele dieser Gene nachweislich beeinflussen, wie Organismen mit Salz umgehen, bilden sie eine praktische Auswahl an Zielgenen zur Verbesserung von Nutzpflanzen auf zunehmend versalzten Böden. Im Kern haben die Forschenden durch das Lesen und Experimentieren mit dem Genom dieser Alge damit begonnen, ihre Überlebensstrategien in Ansätze zu übersetzen, die helfen könnten, die künftige Nahrungsmittelproduktion in einem sich wandelnden Klima zu sichern.
Zitation: Wang, A., Gan, Q., Xin, Y. et al. Cross-species dissection of saline-related genes by genetically deciphering a euryhaline microalga Chlorella sp. Nat Commun 17, 1577 (2026). https://doi.org/10.1038/s41467-026-68287-6
Schlüsselwörter: Salztoleranz, Mikroalgen, Chlorella, Gene für Salzstress, Pflanzenverbesserung